Clear Sky Science · it
Un nuovo approccio integrato genetico e trascrittomico per studiare DUX4 e DUX4C
Geni al bordo dei nostri cromosomi
Alle estremità dei nostri cromosomi si trovano tratti di DNA altamente ripetuti che sono notoriamente difficili da studiare. Due geni nascosti in questo labirinto, chiamati DUX4 e DUX4C, sono stati collegati a una forma di distrofia muscolare e ad alcuni tumori, ma i loro ruoli precisi sono rimasti oscuri perché gli strumenti genetici standard faticano a distinguerli. Questo studio introduce nuovi modi per leggere e interpretare queste regioni confuse, rivelando come diverse varianti di DUX4 e DUX4C possano influenzare il rischio di malattia e il comportamento del sistema immunitario.
Districare due geni simili
DUX4 e DUX4C sono vicini tra loro vicino alla punta del cromosoma 4, circondati da dozzine di unità ripetute quasi identiche. Il sequenziamento a lettura corta, il cavallo di battaglia della genetica moderna, spesso non riesce a distinguere tra queste ripetizioni, tra DUX4 e DUX4C, o tra le loro numerose copie sparse nel genoma. Per superare questo limite, i ricercatori hanno combinato il sequenziamento a lettura lunga e a lettura corta per ricostruire le sequenze complete delle versioni più comuni, o aplotipi, di DUX4 e DUX4C. Hanno quindi costruito un genoma di riferimento personalizzato, chiamato D4Ref-T2T, che sostituisce il blocco ripetitivo confuso con copie chiaramente definite di ciascun aplotipo principale, permettendo ai dati di sequenziamento standard di essere mappati con maggiore precisione.
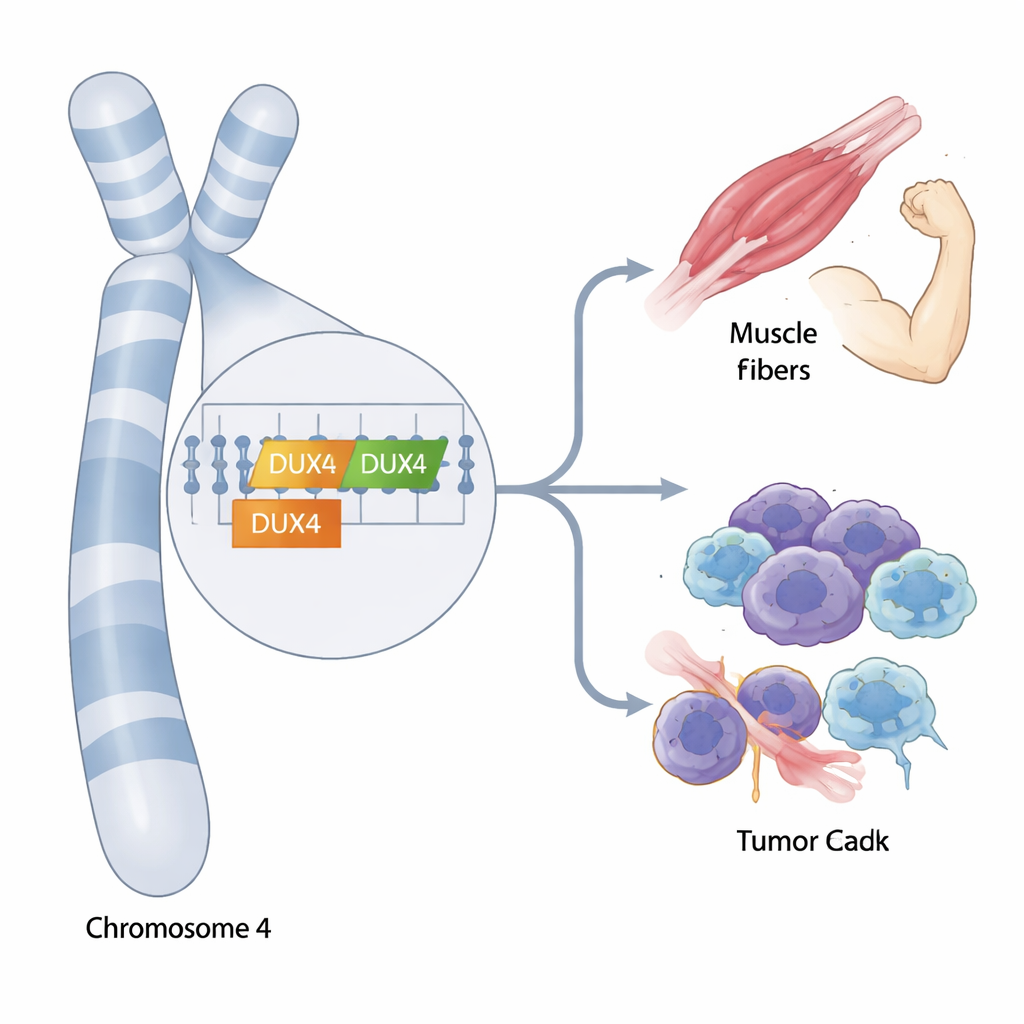
Varianti geniche comuni e chi le porta
Usando grandi dataset pubblici di popolazioni europee e giapponesi, il team ha identificato due principali aplotipi di DUX4C, che hanno denominato 4qα e 4qβ. Queste versioni differiscono per poche variazioni del DNA in una regione regolatoria vicino alla fine del gene, e sono entrambe presenti a frequenze simili in europei e giapponesi. Esaminando DUX4, hanno confermato che i genomi di riferimento esistenti rappresentano accuratamente solo alcune delle sue forme, e che un riferimento ampiamente utilizzato posiziona in modo errato parti dell'aplotipo di DUX4 associato alla malattia. Con il nuovo riferimento D4Ref-T2T, sono riusciti a genotipizzare entrambi i geni in modo più affidabile e hanno scoperto che la versione DUX4C-4qα tende a viaggiare insieme a una particolare variante di DUX4, chiamata 4qB, mostrando un forte legame genetico tra i due loci.
Nuovi messaggi da DUX4C
Oltre al DNA, gli scienziati hanno esplorato come DUX4C venga trascritto in RNA nelle cellule viventi. Usando il sequenziamento RNA a lettura lunga in linee cellulari immunitarie umane stimolate con interferone, hanno ricostruito trascritti di DUX4C a lunghezza intera e scoperto due isoforme di RNA precedentemente non caratterizzate con regioni di inizio e fine ben definite. Queste isoforme codificano una proteina che condivide gli stessi domini di legame al DNA di DUX4 ma è priva della sua classica coda attivatrice. Invece, la coda di DUX4C è intrinsecamente disordinata e ricca di brevi motivi di sequenza che spesso fungono da siti di ancoraggio flessibili per altre proteine e molecole di segnalazione, suggerendo che DUX4C potrebbe agire come un centro regolatorio piuttosto che come un semplice interruttore on/off dei geni.
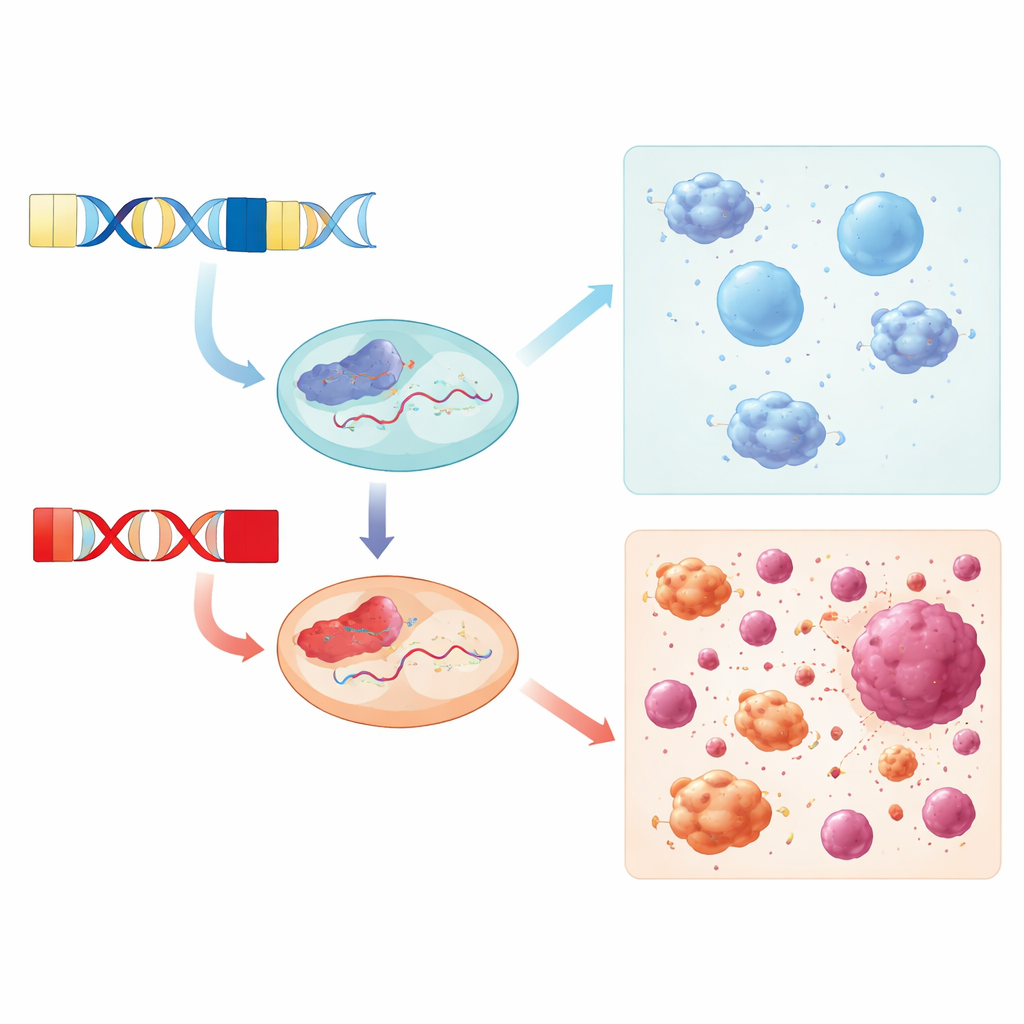
Dove e quando i geni si attivano
Il team si è quindi chiesto quando DUX4 e DUX4C sono effettivamente espressi nei tessuti umani. Rianalizzando dati RNA provenienti da tumori mammari, biopsie muscolari di pazienti con distrofia muscolare facioscapolomerale (FSHD) e linee cellulari immunitarie stimolate con interferone, hanno trovato schemi distinti. Sia DUX4 sia DUX4C risultavano elevati nei tumori mammari rispetto al tessuto mammario normale, mentre solo DUX4 era costantemente aumentato nel muscolo FSHD. DUX4C era per lo più silente nei campioni FSHD, sebbene alcuni familiari non affetti mostrassero livelli modesti, suggerendo che potrebbe essere meno dannoso per il muscolo rispetto a DUX4 o addirittura giocare un ruolo protettivo o riparativo. Nelle linee cellulari immunitarie, nessuno dei due geni veniva fortemente indotto semplicemente dal trattamento con interferone.
Indizi di un ruolo nel dirigere il sistema immunitario
Infine, i ricercatori si sono concentrati su un piccolo insieme di linee cellulari immunitarie che differivano sia negli aplotipi di DUX4C e DUX4 sia nell'espressione di DUX4C. Le cellule portatrici della combinazione DUX4C-4qα / DUX4-4qB e che esprimevano attivamente DUX4C mostravano un aumento dell'attività di geni coinvolti nel movimento delle cellule immunitarie, come la chemiotassi dei leucociti e dei linfociti. Questo, insieme ai motivi di segnalazione trovati nella coda della proteina DUX4C, suggerisce che DUX4C potrebbe contribuire a guidare la migrazione o l'attivazione delle cellule immunitarie in particolari contesti genetici, influenzando potenzialmente il modo in cui i tumori e i tessuti infiammati sono sorvegliati dal sistema immunitario.
Perché questo lavoro è importante
Costruendo mappe genetiche e trascrittomiche su misura per DUX4 e DUX4C, questo studio fornisce strumenti per vedere con chiarezza in uno degli angoli più ripetitivi e soggetti a errori del genoma umano. I risultati mostrano che diverse versioni di questi geni sono strettamente collegate e possono agire in opposizione: DUX4 come noto promotore di danno muscolare e di attenuazione immunitaria, e DUX4C come possibile modulatore della segnalazione immunitaria e del movimento cellulare. Queste intuizioni aprono la strada a una migliore diagnosi genetica della FSHD, a un'interpretazione più accurata dei dati di sequenziamento nei tumori e a ricerche future su come leggere differenze sottili alle punte dei cromosomi possano spostare l'equilibrio tra danno tissutale, riparazione e difesa immunitaria.
Citazione: Zhuang, Z., Ueda, M.T., Yamaguchi, K. et al. A new integrated genetic and transcriptomic approach for investigating DUX4 and DUX4C. J Hum Genet 71, 373–381 (2026). https://doi.org/10.1038/s10038-025-01450-x
Parole chiave: DUX4, DUX4C, distrofia muscolare facioscapolomerale, cancro al seno, chemiotassi immunitaria