Clear Sky Science · fr
Une nouvelle approche intégrée génétique et transcriptomique pour l’étude de DUX4 et DUX4C
Des gènes au bord de nos chromosomes
Aux extrémités de nos chromosomes se trouvent des étendues d’ADN fortement répétées, notoirement difficiles à étudier. Deux gènes nichés dans ce dédale, nommés DUX4 et DUX4C, ont été associés à une forme de dystrophie musculaire et à plusieurs cancers, mais leurs rôles précis sont restés obscurs parce que les outils génétiques standards peinent à les distinguer. Cette étude introduit de nouvelles méthodes pour lire et interpréter ces régions confuses, révélant comment différentes versions de DUX4 et DUX4C peuvent influencer le risque de maladie et le comportement immunitaire.
Démêler deux gènes quasiment identiques
DUX4 et DUX4C sont situés à proximité, près de l’extrémité du chromosome 4, entourés de dizaines d’unités répétées presque identiques. Le séquençage court, pilier de la génétique moderne, ne parvient souvent pas à distinguer ces répétitions, ni DUX4 de DUX4C, ni leurs nombreux homologues dispersés dans le génome. Pour surmonter cet obstacle, les chercheurs ont combiné séquençage longue lecture et courte lecture afin de reconstruire les séquences complètes des haplotypes les plus courants de DUX4 et DUX4C. Ils ont ensuite construit un génome de référence personnalisé, nommé D4Ref-T2T, qui remplace le bloc répétitif déroutant par des copies clairement définies de chaque haplotype majeur, permettant aux données de séquençage standard d’être cartographiées avec plus de précision.
Variants courants des gènes et leur répartition
En utilisant de larges jeux de données publics provenant de populations européennes et japonaises, l’équipe a identifié deux principaux haplotypes de DUX4C, qu’ils ont nommés 4qα et 4qβ. Ces versions diffèrent par quelques changements d’ADN dans une région régulatrice proche de la fin du gène, et les deux sont présentes à des fréquences similaires chez les Européens et les Japonais. Lorsqu’ils ont examiné DUX4, ils ont confirmé que les génomes de référence existants représentent fidèlement seulement certaines de ses formes, et qu’une référence largement utilisée place de manière incorrecte des parties de l’haplotype de DUX4 associé à la maladie. Grâce à leur nouveau référentiel D4Ref-T2T, ils ont pu génotyper les deux gènes de façon plus fiable et ont découvert que la version DUX4C-4qα a tendance à être co-transmise avec une variante particulière de DUX4, appelée 4qB, révélant un fort lien génétique entre les deux loci.
Nouveaux transcrits de DUX4C
Au-delà de l’ADN lui-même, les scientifiques ont exploré comment DUX4C est transcrit en ARN dans des cellules vivantes. En utilisant le séquençage long des ARN dans des lignées de cellules immunitaires humaines stimulées par l’interféron, ils ont reconstruit des transcrits DUX4C en pleine longueur et découvert deux isoformes d’ARN jusqu’ici non caractérisées, avec des régions de début et de fin bien définies. Ces isoformes encodent une protéine qui partage les mêmes domaines de liaison à l’ADN que DUX4 mais qui a perdu sa queue d’activation classique. À la place, la queue de DUX4C est intrinsèquement désordonnée et riche en courts motifs de séquence qui servent souvent de sites d’amarrage flexibles pour d’autres protéines et molécules de signalisation, suggérant que DUX4C pourrait agir comme un centre régulateur plutôt que comme un simple interrupteur marche/arrêt des gènes.
Où et quand les gènes s’activent
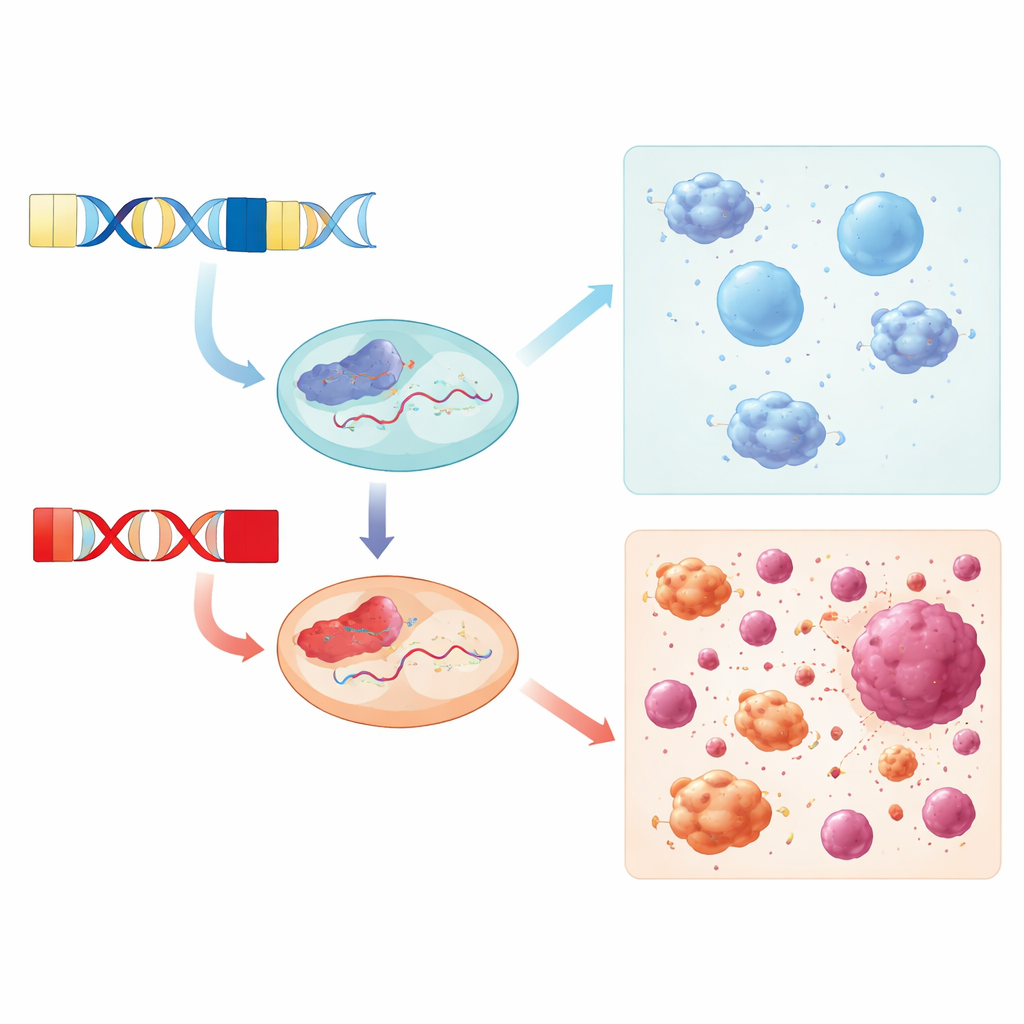
L’équipe s’est ensuite intéressée au moment et aux tissus où DUX4 et DUX4C sont réellement exprimés chez l’humain. En réanalysant des données d’ARN provenant de tumeurs mammaires, de biopsies musculaires de patients atteints de dystrophie musculaire facioscapulohumérale (FSHD) et de lignées cellulaires immunitaires stimulées par l’interféron, ils ont mis en évidence des profils distincts. DUX4 et DUX4C étaient tous deux élevés dans les tumeurs mammaires comparées au tissu mammaire normal, tandis que seul DUX4 était systématiquement augmenté dans le muscle FSHD. DUX4C était majoritairement silencieux dans les échantillons FSHD, bien que quelques membres non affectés de familles aient montré des niveaux modestes, ce qui suggère qu’il pourrait être moins délétère pour le muscle que DUX4 ou qu’il pourrait même jouer un rôle protecteur ou lié à la réparation. Dans les lignées cellulaires immunitaires, aucun des deux gènes n’a été fortement induit par une simple stimulation par l’interféron.
Indices d’un rôle dirigeant pour le système immunitaire
Enfin, les chercheurs se sont concentrés sur un petit ensemble de lignées cellulaires immunitaires qui différaient à la fois par leurs haplotypes DUX4C et DUX4 et par l’expression de DUX4C. Les cellules portant la combinaison DUX4C-4qα / DUX4-4qB et exprimant activement DUX4C présentaient une activité accrue des gènes impliqués dans le mouvement des cellules immunitaires, tels que la chimiotaxie des leucocytes et des lymphocytes. Cela, combiné aux motifs de signalisation trouvés dans la queue protéique de DUX4C, suggère que DUX4C pourrait contribuer à guider la migration ou l’activation des cellules immunitaires dans certains contextes génétiques, influençant potentiellement la façon dont les tumeurs et les tissus enflammés sont surveillés par le système immunitaire.
Pourquoi ce travail est important
En construisant des cartes génétiques et transcriptomiques sur mesure pour DUX4 et DUX4C, cette étude fournit des outils permettant d’éclairer l’un des recoins les plus répétitifs et sujets aux erreurs du génome humain. Les résultats montrent que différentes versions de ces gènes sont étroitement liées et peuvent agir en opposition : DUX4 en tant que moteur connu de lésions musculaires et d’atténuation immunitaire, et DUX4C en tant que modulateur possible du signalement immunitaire et du mouvement cellulaire. Ces découvertes ouvrent la voie à un meilleur diagnostic génétique de la FSHD, à une interprétation plus précise des données de séquençage en cancérologie et à des travaux futurs sur la façon dont de subtiles différences aux extrémités chromosomiques peuvent faire pencher la balance entre dommage tissulaire, réparation et défense immunitaire.
Citation: Zhuang, Z., Ueda, M.T., Yamaguchi, K. et al. A new integrated genetic and transcriptomic approach for investigating DUX4 and DUX4C. J Hum Genet 71, 373–381 (2026). https://doi.org/10.1038/s10038-025-01450-x
Mots-clés: DUX4, DUX4C, dystrophie musculaire facioscapulohumérale, cancer du sein, chimiotaxie immunitaire