Clear Sky Science · zh
基于分子与相互作用网络洞见的Aphanomyces属(卵菌)宿主偏好与专化研究
水中与土壤中的隐形攻击者
世界上许多作物、鱼类和淡水甲壳类正被一些外观类似真菌但实际上与藻类更为亲缘的微观生物悄然威胁。在这些生物中,属Aphanomyces因引起诸如小龙虾灾难性疫病以及豌豆、豆类和其他作物的严重根腐病等毁灭性疾病而尤为突出。本研究提出了一个简单却至关重要的问题:这些生物究竟偏好哪些宿主,它们的专化程度有多窄?研究者通过将现代DNA工具与网络分析相结合,绘制出跨植物与动物的感染图谱,揭示了隐藏的多样性及宿主利用上的明显分化。
用DNA追踪隐藏的多样性
为了弄清Aphanomyces有多少种类,研究人员首先建立了一个详尽的基因目录。他们收集了261条DNA序列(来自一个标准标记区),这些序列代表已知的Aphanomyces物种及其近缘种,外加许多未命名的菌株。研究者采用了若干互补的算法来判断遗传相似性中自然出现的“断点”,这些断点很可能对应独立的物种。大多数方法一致识别出34个候选物种:其中20个对应已描述的名称,14个可能是新发现的种。在某些情况下,长期被视为单一物种的分类单元(例如Aphanomyces stellatus)实际上分化为三条不同的遗传谱系,这提示显微镜下未被识别的隐蔽物种存在。
植物与动物侵染者的家系图
接着,团队重建了这些生物的系统树。所得的进化画像显示出三大类群。第一类包含主要生活在水中的物种,常感染淡水动物如小龙虾与鱼类。第二类以生活在湿润土壤并侵袭植物根部的物种为主,包括若干臭名昭著的农作物病原体。第三类包含与植物和潮湿土壤相关的近缘属。总体而言,这些模式说明Aphanomyces的演化史受到水生与根际生活方式转换的强烈影响,并经历了多次宿主偏好的收窄。一些近缘种在Aphanomyces分支内的位置也表明,目前的属界定可能需要修订。
重建感染网络
仅靠遗传学无法完全揭示这些生物在自然界中的行为,因此作者转向文献资料。他们汇编了来自百余年研究的1,221条记录,每条记录都记载了在某一宿主或基质上发现的类似Aphanomyces的生物,从小龙虾鳃与鱼鳞到作物根系与湖泊沉积物。将这些资料视为一个网络,研究者在病原物种与宿主科或环境基质之间建立了连线。随后他们量化了网络的连接密度、模块化程度,以及每个病原物种相对于随机期望的专化程度。
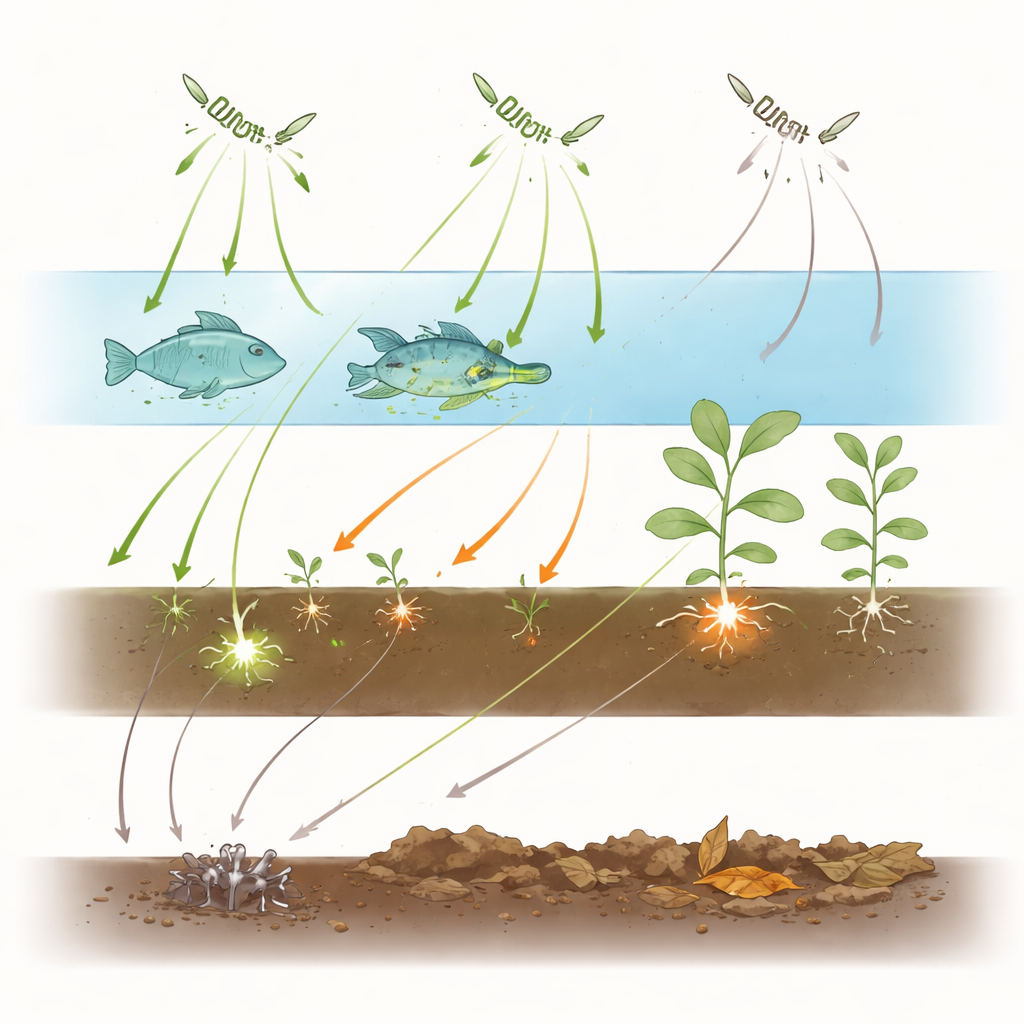
强烈的偏好与紧密的簇群
感染网络表现出稀疏且高度簇化的特征,这类模式典型地反映了如寄生者与其宿主之间的亲密关系。网络并非形成一个高度互联的整体,而是分解为对应广泛生态位的模块:一个以湿土中的植物病原体为主,另一个由淡水小龙虾及相关甲壳动物的寄生物占据,还有一个以鱼类为中心,另一个围绕软壳龟宿主。当作者为每个物种计算专化得分时,生活在水或土壤中的广泛生态型得分较低,而经典的致病体例如寄生豆科植物的Aphanomyces euteiches、危害甜菜的A. cochlioides以及侵染小龙虾和鱼类的A. astaci和A. invadans得分都很高,表明它们对特定宿主群体有着狭窄的专注。
对粮食与生态系统的重要性
对于非专业读者来说,关键的信息是这些类真菌生物并非模糊的机会主义威胁——它们往往对特定宿主和栖息地有明确而敏锐的适应性。研究揭示了许多可能的新物种,并表明危害鱼类、小龙虾和农作物的危险病原体存在于一个更大且高度结构化的、以专化谱系为主的网络之中。更加清晰的“谁感染谁”图景,可帮助科学家预测当某一Aphanomyces物种进入新区域时哪些宿主可能面临风险,改进水产养殖和农业的预警系统,并为未来研究这些微观攻击者如何进化以利用其植物和动物目标提供指导。
引用: Casabella-Herrero, G., Martín-Torrijos, L., Pérez-Ortega, S. et al. Host preference and specialization in the genus Aphanomyces (Oomycetes) from molecular and interaction network insights. Sci Rep 16, 14262 (2026). https://doi.org/10.1038/s41598-026-44513-5
关键词: Aphanomyces, 卵菌病原体, 宿主专化, 植物与鱼类疾病, 相互作用网络