Clear Sky Science · fr
Préférence d’hôte et spécialisation dans le genre Aphanomyces (Oomycètes) : apports de la génétique et des réseaux d’interaction
Attaquants invisibles dans l’eau et le sol
De nombreuses cultures, poissons et crustacés d’eau douce sont silencieusement menacés par des organismes microscopiques qui ressemblent à des champignons mais sont en réalité plus proches des algues. Parmi eux, le genre Aphanomyces se distingue en provoquant des maladies dévastatrices comme la peste du crayfish et d’importantes pourritures des racines chez les pois, les haricots et d’autres cultures. Cette étude pose une question simple mais essentielle : quels hôtes ces organismes préfèrent-ils vraiment, et à quel point sont-ils spécialisés ? En combinant des outils d’ADN modernes et l’analyse de réseaux, les auteurs cartographient qui infecte qui parmi les plantes et les animaux, révélant une diversité cachée et des divisions nettes dans l’utilisation des hôtes.
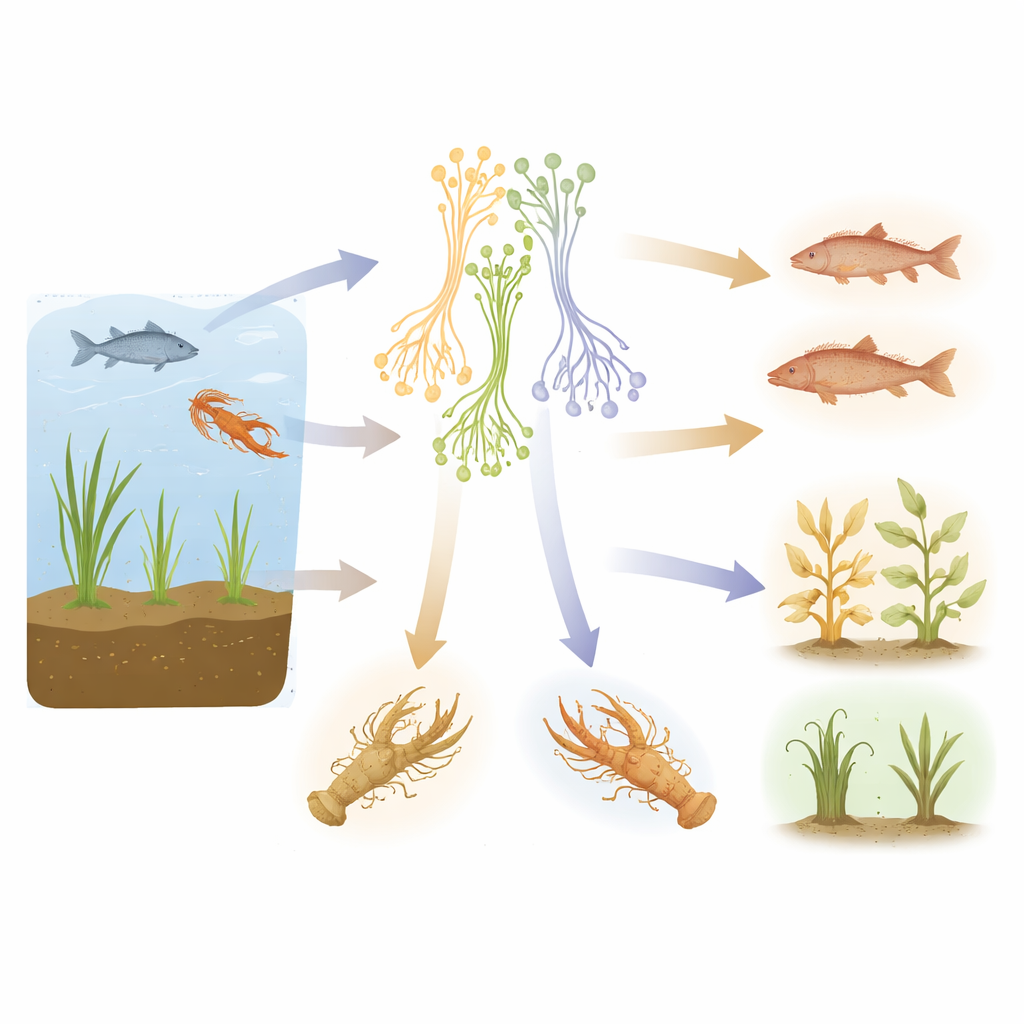
Repérer la diversité cachée grâce à l’ADN
Pour estimer le nombre de types distincts d’Aphanomyces, les chercheurs ont d’abord constitué un vaste catalogue génétique. Ils ont rassemblé 261 séquences d’ADN (d’une région marqueur standard) représentant des espèces connues d’Aphanomyces et de ses proches parents, ainsi que de nombreuses souches non nommées. En utilisant plusieurs algorithmes complémentaires, ils ont cherché où se produisent des « ruptures » naturelles dans la similarité génétique correspondant probablement à des espèces séparées. La plupart des méthodes ont convergé vers 34 espèces candidates : 20 correspondant à des noms déjà décrits et 14 représentant de potentielles nouveautés. Dans certains cas, ce qui était longtemps considéré comme une seule espèce, comme Aphanomyces stellatus, s’est en fait résolu en trois lignées génétiques distinctes, laissant entrevoir des espèces cryptiques restées inaperçues au microscope.
Arbre familial des envahisseurs végétaux et animaux
Ensuite, l’équipe a reconstruit un arbre phylogénétique pour ces organismes. Le portrait évolutif obtenu montre trois grands groupes. Un groupe inclut des espèces vivant principalement dans l’eau et infectant souvent des animaux d’eau douce comme les crayfishs et les poissons. Un second groupe est dominé par des espèces vivant dans les sols humides et attaquant les racines des plantes, y compris plusieurs agents pathogènes agricoles notoires. Un troisième groupe contient des genres apparentés également associés aux plantes et aux sols humides. Ensemble, ces schémas indiquent que l’histoire d’Aphanomyces a été fortement marquée par des basculements entre la vie en eau et la vie autour des racines des plantes, et par des resserrements répétés des préférences d’hôtes. La position de certains proches parents au sein des branches d’Aphanomyces suggère aussi que les limites actuelles du genre pourraient devoir être révisées.
Reconstituer un réseau d’infections
La génétique seule ne peut pas révéler le comportement de ces organismes dans la nature, aussi les auteurs se sont tournés vers la littérature. Ils ont compilé 1 221 observations issues de plus d’un siècle d’études, chacune documentant un organisme de type Aphanomyces trouvé sur un hôte ou un substrat donné, des branchies de crayfish et de la peau de poisson aux racines de cultures et aux sédiments lacustres. Traité comme un réseau, cela a permis de tracer des liens entre les espèces pathogènes d’un côté et les familles d’hôtes ou les substrats environnementaux de l’autre. Les auteurs ont ensuite quantifié la densité de connexions du réseau, son découpage en grappes, et le degré de spécialisation apparent de chaque pathogène par rapport à une attente aléatoire.
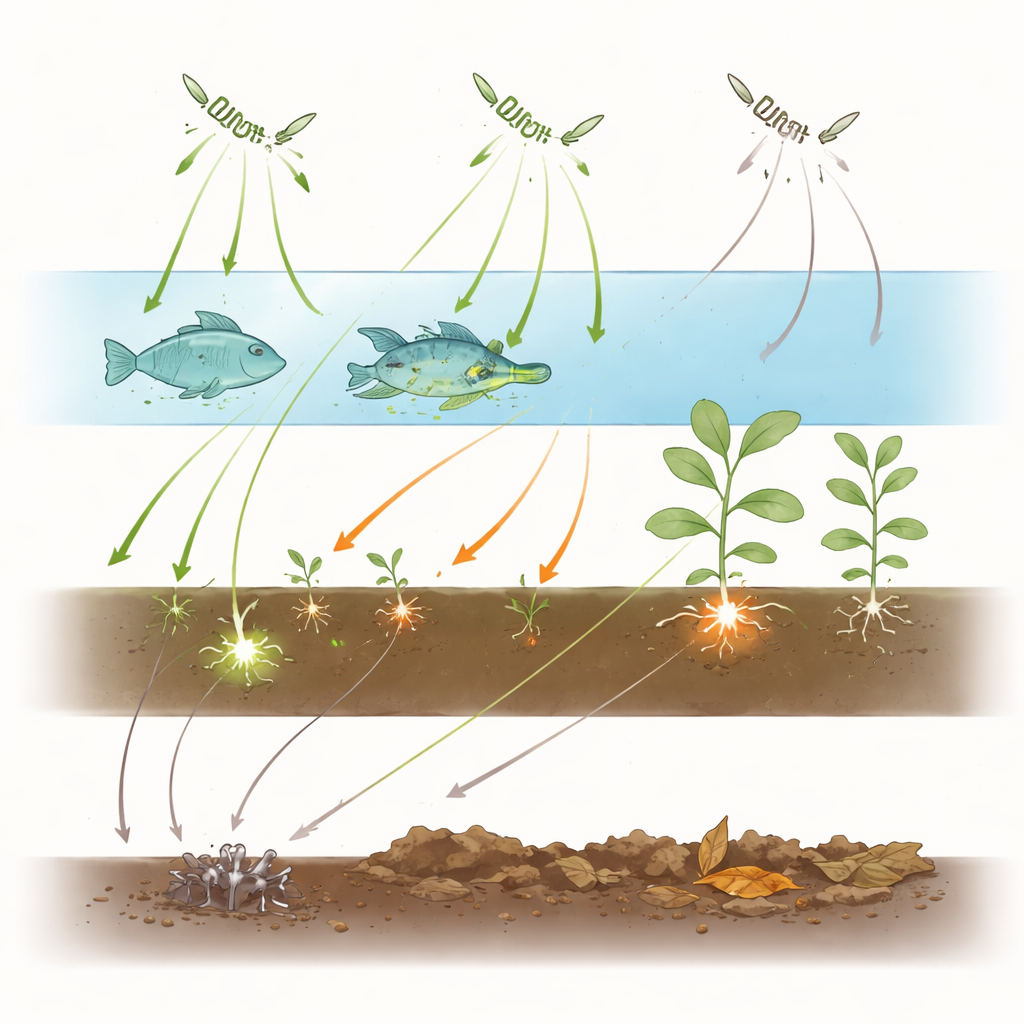
Préférences marquées et grappes serrées
Le réseau d’infection s’est révélé peu dense et fortement compartimenté, des schémas typiques de relations étroites et intimes comme celles entre parasites et hôtes. Plutôt que de former un seul réseau très interconnecté, il se scinde en modules correspondant à de larges niches écologiques : un module dominé par des pathogènes de plantes dans les sols humides, un autre par des parasites de crayfishs d’eau douce et de crustacés apparentés, un module séparé centré sur les poissons, et un autre autour d’un hôte tortue à carapace molle. Lorsque les auteurs ont calculé un indice de spécialisation pour chaque espèce, les formes généralistes et libres dans l’eau ou le sol ont obtenu des scores faibles, tandis que des agents de maladies classiques comme Aphanomyces euteiches chez les légumineuses, A. cochlioides chez la betterave sucrière, et A. astaci et A. invadans chez les crayfishs et les poissons ont obtenu des scores très élevés, indiquant une focalisation étroite sur des groupes d’hôtes particuliers.
Pourquoi cela compte pour l’alimentation et les écosystèmes
Pour les non-spécialistes, le message clé est que ces organismes proches des champignons ne sont pas des menaces vagues et opportunistes : ils sont souvent finement adaptés à des hôtes et des habitats spécifiques. L’étude révèle de nombreuses espèces probablement nouvelles et montre que des pathogènes dangereux pour les poissons, les crayfishs et les cultures s’insèrent dans un réseau plus large, très structuré et majoritairement composé de lignées spécialisées. Cette vision plus précise de qui infecte qui peut aider les scientifiques à prédire quels hôtes pourraient être à risque lorsqu’une espèce d’Aphanomyces arrive dans une nouvelle région, à améliorer les systèmes d’alerte précoce pour l’aquaculture et l’agriculture, et à orienter les travaux futurs sur la manière dont ces attaquants microscopiques évoluent pour exploiter leurs cibles végétales et animales.
Citation: Casabella-Herrero, G., Martín-Torrijos, L., Pérez-Ortega, S. et al. Host preference and specialization in the genus Aphanomyces (Oomycetes) from molecular and interaction network insights. Sci Rep 16, 14262 (2026). https://doi.org/10.1038/s41598-026-44513-5
Mots-clés: Aphanomyces, pathogènes oomycètes, spécialisation des hôtes, maladies des plantes et des poissons, réseaux d’interaction