Clear Sky Science · de
Wirtpräferenz und Spezialisierung in der Gattung Aphanomyces (Oomyceten) aus molekularen und Interaktionsnetzwerk-Einsichten
Unsichtbare Angreifer in Wasser und Boden
Viele der weltweiten Nutzpflanzen, Fische und Süßwasser-Krebstiere sind still bedroht durch mikroskopisch kleine Organismen, die pilzähnlich aussehen, aber näher mit Algen verwandt sind. Unter ihnen sticht die Gattung Aphanomyces hervor, weil sie verheerende Krankheiten wie die Flusskrebspest und schwere Wurzelfäulen bei Erbsen, Bohnen und anderen Feldfrüchten verursacht. Die Studie stellt eine einfache, aber entscheidende Frage: Welche Wirte bevorzugen diese Organismen tatsächlich, und wie eng spezialisiert sind sie? Durch die Kombination moderner DNA‑Methoden mit Netzwerk‑Analysen kartieren die Autorinnen und Autoren, wer wen über Pflanzen und Tiere hinweg infiziert, und offenbaren dabei verborgene Vielfalt und deutliche Trennlinien in der Wirtsnutzung.
Verborgene Vielfalt mit DNA verfolgen
Um zu klären, wie viele verschiedene Typen von Aphanomyces es gibt, erstellten die Forschenden zunächst einen umfangreichen genetischen Katalog. Sie sammelten 261 DNA‑Sequenzen (aus einem Standardmarker), die bekannte Arten von Aphanomyces und seinen nahen Verwandten sowie viele unbenannte Stämme repräsentieren. Mit mehreren komplementären Algorithmen suchten sie nach natürlichen „Brüchen“ in der genetischen Ähnlichkeit, die wahrscheinlich separaten Arten entsprechen. Die meisten Methoden kamen auf 34 Kandidatenarten: 20 entsprachen bereits beschriebenen Namen und 14 stellten mögliche Neuentdeckungen dar. In einigen Fällen löste sich eine lange Zeit als einzelne Art behandelte Einheit, etwa Aphanomyces stellatus, in drei verschiedene genetische Linien auf, was auf kryptische Arten hinweist, die unter dem Mikroskop unbemerkt geblieben waren.
Stammbaum von Pflanzen- und Tierinvasoren
Als Nächstes rekonstruierten die Forschenden einen Stammbaum für diese Organismen. Das resultierende evolutionäre Porträt zeigte drei große Gruppen. Eine Gruppe umfasst Arten, die überwiegend im Wasser leben und häufig Süßwasser‑Tiere wie Krebse und Fische infizieren. Eine zweite Gruppe wird von Arten dominiert, die in nassen Böden vorkommen und Pflanzenwurzeln angreifen, darunter mehrere berüchtigte Feldschädlinge. Eine dritte Gruppe enthält verwandte Gattungen, die ebenfalls mit Pflanzen und feuchten Böden verbunden sind. Zusammengenommen deuten diese Muster darauf hin, dass die Geschichte von Aphanomyces stark von Verschiebungen zwischen Leben im Wasser und Leben an Pflanzenwurzeln geprägt wurde und von wiederholter Verengung der Wirtpräferenzen. Die Stellung einiger naher Verwandter innerhalb der Aphanomyces-Zweige lässt zudem vermuten, dass die derzeitigen Gattungsgrenzen überdacht werden sollten.
Ein Infektionsnetz rekonstruieren
Genetische Daten allein können nicht zeigen, wie sich diese Organismen in der Natur verhalten, daher werteten die Autorinnen und Autoren die Fachliteratur aus. Sie kompilierten 1.221 Einträge aus mehr als einem Jahrhundert Studien, von denen jeder ein bestimmtes Aphanomyces-ähnliches Vorkommen auf einem bestimmten Wirt oder Substrat dokumentiert — von Kiemen von Flusskrebsen und Fischhaut bis hin zu Pflanzenwurzeln und Seesedimenten. Behandelt als Netzwerk zogen sie Verbindungen zwischen Pathogenarten auf der einen Seite und Wirtsfamilien oder Umweltsubstraten auf der anderen. Anschließend quantifizierten sie, wie dicht das Netzwerk verknüpft ist, wie stark es in getrennte Cluster zerfällt und wie spezialisiert jede Pathogenart im Vergleich zu einer zufälligen Erwartung erscheint.
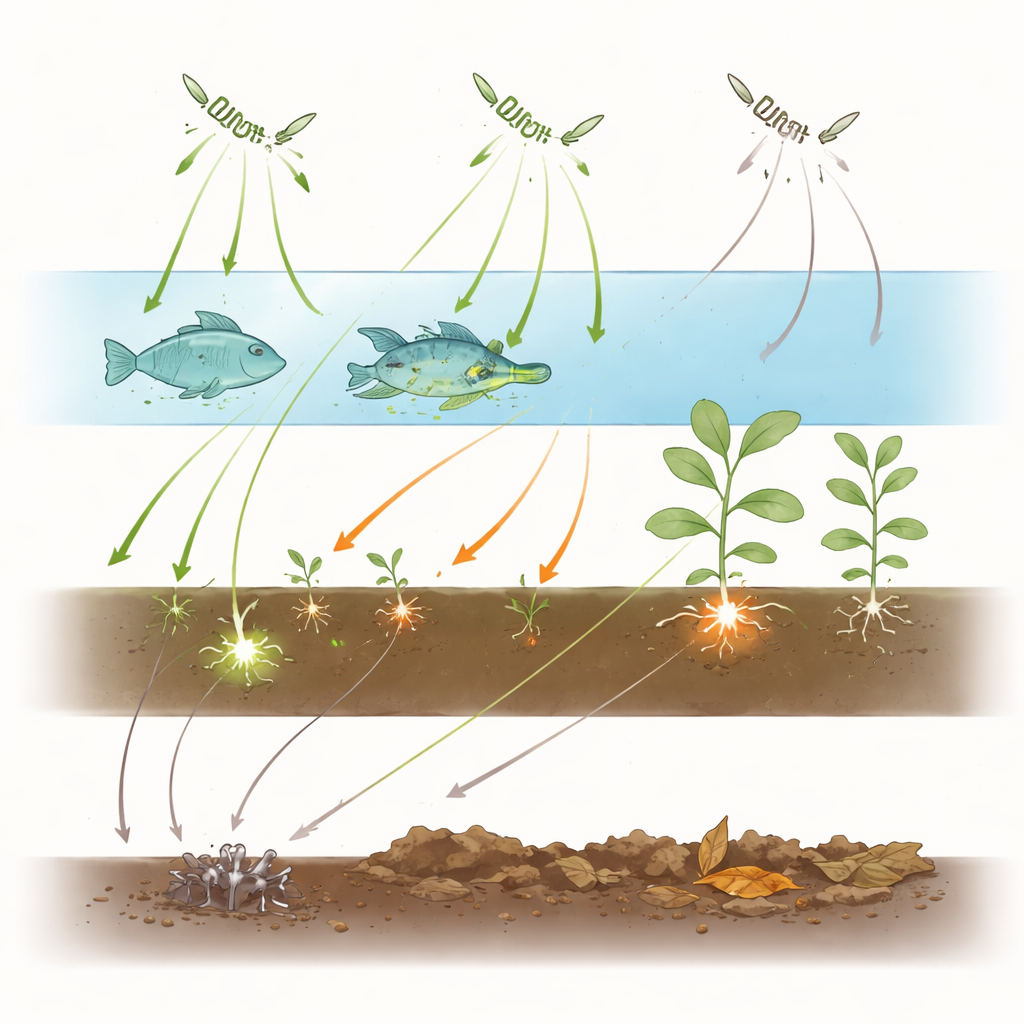
Starke Präferenzen und enge Cluster
Das Infektionsnetz erwies sich als dünn verknüpft und stark gegliedert — Muster, die typisch sind für enge, intime Beziehungen wie die zwischen Parasiten und ihren Wirten. Anstatt ein einziges, stark vernetztes Netz zu bilden, zerfällt das Netzwerk in Module, die breiten ökologischen Nischen entsprechen: eines dominiert von Pflanzenpathogenen in nassen Böden, ein anderes von Parasiten von Süßwasser‑Flusskrebsen und verwandten Krebstieren, ein eigenes Modul rund um Fische und ein weiteres um einen Weichschildkröten‑Wirt. Bei der Berechnung eines Spezialisierungswerts für jede Art erzielten generalistische, freilebende Formen im Wasser oder Boden niedrige Werte, während klassische Krankheitserreger wie Aphanomyces euteiches bei Leguminosen, A. cochlioides bei Zuckerrüben sowie A. astaci und A. invadans bei Krebsen und Fischen sehr hohe Werte erreichten — ein Hinweis auf eine enge Ausrichtung auf bestimmte Wirtgruppen.
Warum das für Ernährung und Ökosysteme wichtig ist
Für Nicht‑Spezialisten lautet die Kernbotschaft: Diese pilzähnlichen Organismen sind keine vagen, opportunistischen Bedrohungen — sie sind häufig sehr genau auf bestimmte Wirte und Habitate eingestellt. Die Studie deckt viele vermutlich neue Arten auf und zeigt, dass gefährliche Erreger von Fischen, Krebsen und Nutzpflanzen in einem größeren, stark strukturierten Netzwerk überwiegend spezialisierter Linien eingebettet sind. Dieses detailliertere Bild davon, wer wen infiziert, kann Forschenden helfen vorherzusagen, welche Wirte gefährdet sein könnten, wenn sich eine Aphanomyces-Art in eine neue Region ausbreitet, Frühwarnsysteme für Aquakultur und Landwirtschaft verbessern und künftige Arbeiten darüber leiten, wie diese mikroskopischen Angreifer sich entwickeln, um ihre Pflanzen‑ und Tierziele auszunutzen.
Zitation: Casabella-Herrero, G., Martín-Torrijos, L., Pérez-Ortega, S. et al. Host preference and specialization in the genus Aphanomyces (Oomycetes) from molecular and interaction network insights. Sci Rep 16, 14262 (2026). https://doi.org/10.1038/s41598-026-44513-5
Schlüsselwörter: Aphanomyces, Oomyceten-Erreger, Wirtspezialisierung, Pflanzen- und Fischkrankheiten, Interaktionsnetzwerke