Clear Sky Science · sv
Högkvalitativa genommonteringar av två stammar av Prototheca wickerhamii
Varför denna lilla alg betyder något för vår hälsa
De flesta av oss tänker på alger som ofarligt grönt skräp på dammar, drivna av solljus. Men några algsläktingar har förlorat sitt gröna pigment och förvandlats till dolda mikrober som kan infektera människor och djur. En sådan gärningsman, Prototheca wickerhamii, orsakar sällsynta men långdragna infektioner i hud, mjukdelar och ibland djupare organ. Läkare får ofta problem med den delvis därför att dess grundläggande biologi fortfarande är dåligt kartlagd. Denna studie levererar högkvalitativa ritningar av DNA från två kliniska stammar av denna mikroorganism, vilket ger forskare en detaljerad reservdelslista som kan hjälpa förklara hur den överlever i kroppen och hur vi bättre kan diagnosticera och behandla de infektioner den orsakar. 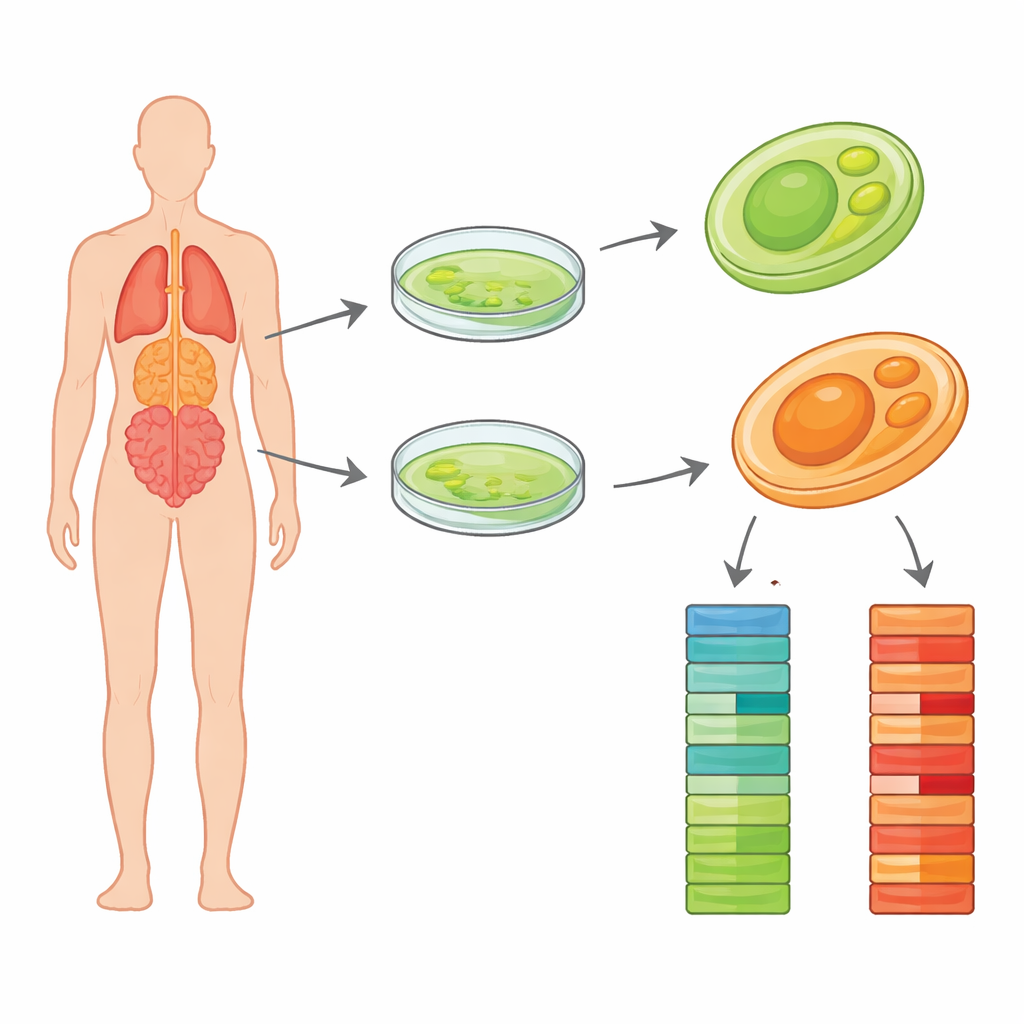
En färglös släkting som gömmer sig i fullt dagsljus
Prototheca wickerhamii tillhör en lite känd grupp av ”färg lösa” mikroalger som inte längre utför fotosyntes. Istället för att leva på solljus som sina gröna släktingar, lever de i fuktiga miljöer och ibland inne i varmblodiga värdar. Under de senaste två decennierna har rapporterade infektioner orsakade av dessa organismer ökat, särskilt hos personer med nedsatt immunförsvar och hos sällskapsdjur. Den verkliga bördan är sannolikt underskattad, eftersom Prototheca kan missas eller felidentifieras i rutinprov. Tidigare arbete avkodat DNA:t hos en referensstam och antydde att organismen bär många gener som liknar kända virulensfaktorer hos sjukdomsframkallande svampar, vilket tyder på att dess genom formats för att frodas i människokroppen.
Insamling och läsning av mikroben DNA
I den nya studien fokuserade forskarna på två kliniska stammar, kallade Pw26 och PwS1, isolerade från patienter i olika kinesiska städer. De odlade först rena kolonier på standardodlingssubstrat och bekräftade att inga andra mikrober förorenade kulturerna. Teamet extraherade sedan högkvalitativt DNA och använde en modern långläsningsmetod kallad PacBio HiFi-sekvensering. Till skillnad från äldre tekniker som klyver DNA i mycket korta fragment, sträcker sig HiFi-läsningar över tiotusentals baspar åt gången med hög noggrannhet. Det gör det enklare att rekonstruera hela kromosomer med få luckor. Forskarna genererade mer än en och en halv miljard baser sekvensdata för Pw26 och över åttahundra miljoner för PwS1, vilket gav djup täckning av båda genomen.
Bygga kompletta genom och hitta upprepade mönster
Med specialiserad monteringsmjukvara syddes de långa DNA-läsningarna ihop till kontinuerliga sträckor som representerar organismens kromosomer. De slutliga genomstorlekarna var ungefär 17,8 miljoner respektive 17,4 miljoner baser för Pw26 och PwS1 — liknande, men något större än den tidigare studerade stammen. Var och en monterades i endast 14 till 17 bitar, och statistiska kontroller visade att de flesta förväntade kärn gener fanns med, ett tecken på fullständighet. Teamet sökte därefter efter upprepade DNA-element, som kan forma hur genom utvecklas. Dessa repetitioner utgjorde ungefär 6 procent av Pw26 och 4 procent av PwS1, dominerade av en klass kallad long terminal repeats som ofta ses i växt- och alggenom. Subtila skillnader i mängd och typ av repetitioner mellan de två stammarna kan spegla hur varje stam anpassat sig till olika miljöer eller värdar.
Vad generna säger om hur mikroben lever
Efter att ha maskerat upprepningar förutsåg forskarna protein‑kodande gener med en kombination av tre tillvägagångssätt: datorbaserade modeller tränade på genstruktur, jämförelse med kända proteiner från besläktade alger och Prototheca‑stammar, och justering mot tidigare insamlade RNA‑data. Detta gav ungefär 6 400 gener i varje genom. De annoterade sedan dessa gener med två välkända kataloger över genfunktion. Den ena, kallad Gene Ontology, grupperar gener efter vilka uppgifter de utför i cellen, medan KEGG-databasen kopplar dem till metaboliska vägar. Båda stammarna hade många gener involverade i energiproduktion, nedbrytning och uppbyggnad av näringsämnen samt reglering av cellulära processer. PwS1 visade extra tonvikt på lipidrelaterade vägar och signalering, vilket ekar tidigare fynd som kopplat denna stams ovanliga slemliknande utseende och lägre toxicitet till förändringar i dess yta och metabolism. 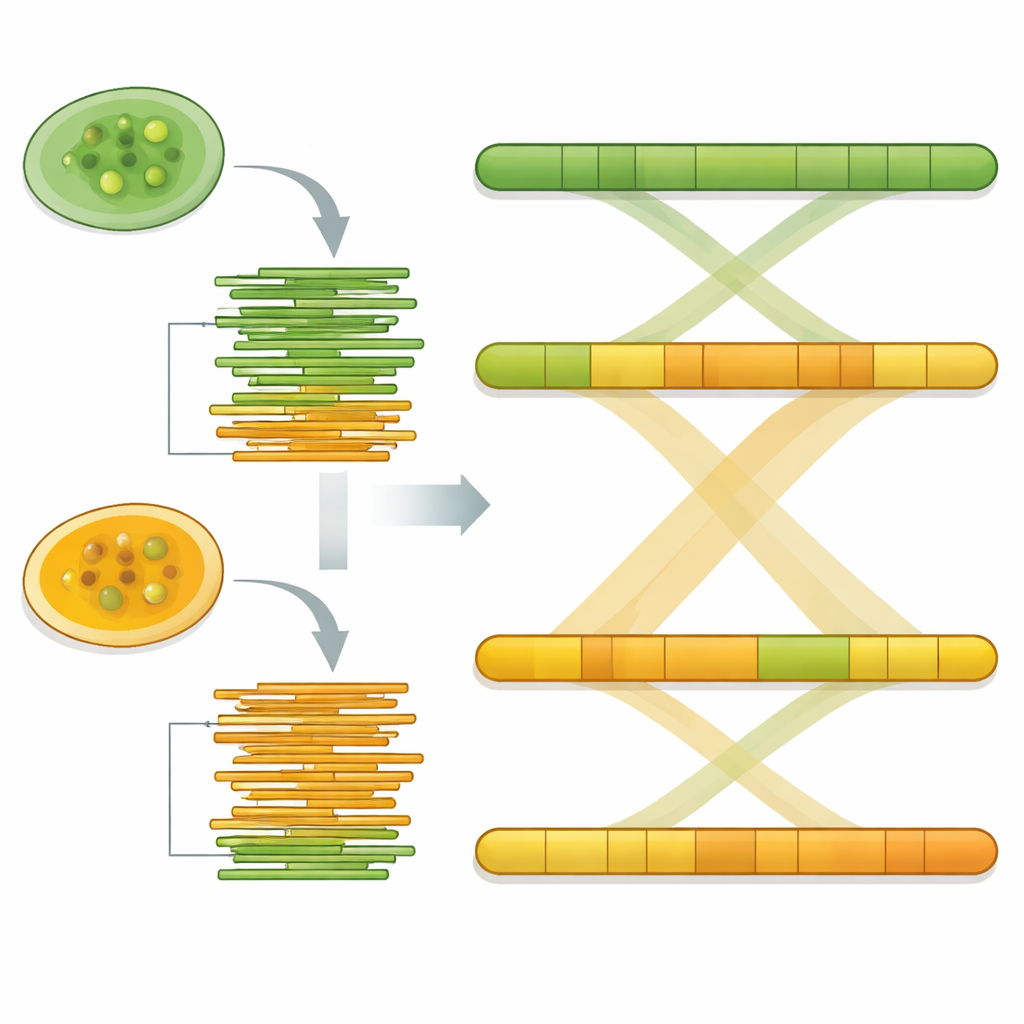
Kontroll av noggrannhet och jämförelse av de två stammarna
För att säkerställa att deras rekonstruktioner var pålitliga remappade teamet de ursprungliga långläsningarna mot varje monterat genom. Över 93 procent av läsningarna matchade tillbaka med jämn täckning, och fördelningen av baser visade inga tecken på kontaminering. En annan kvalitetskontroll, kallad BUSCO, bekräftade att mer än 86 procent av en standarduppsättning konserverade alggener fanns närvarande och intakta i båda stammarna. Slutligen, när de två genomen linjerades upp med verktyg för helgenomsjämförelse, matchade deras DNA‑segment nästan ett‑till‑ett, vilket indikerar en mycket hög grad av likhet och stärker idén att monteringar korrekt fångar de underliggande kromosomerna.
Vad detta betyder för framtida diagnostik och behandling
För icke‑specialister är huvudbudskapet att vi nu har detaljerade, pålitliga DNA‑kartor för två sjukdomsframkallande stammar av Prototheca wickerhamii. Dessa kartor botar inte infektioner i sig, men de utgör grunden för skarpare frågor: vilka gener tillåter mikroben att undkomma immunförsvaret, vilka vägar kan riktas med befintliga läkemedel, och hur varierar olika stammar i virulens och läkemedelssvar? Eftersom data har gjorts offentligt tillgängliga kan laboratorier över hela världen använda dem för att utforma bättre diagnostiska tester, spåra utbrott ur ett One Health‑perspektiv som länkar mänsklig och djurhälsa, och så småningom informera mer precisa behandlingsstrategier för denna ovanliga men utmanande patogen.
Citering: Fang, L., Guo, J., Ning, Q. et al. High-Quality Genome Assemblies of Two Prototheca wickerhamii Strains. Sci Data 13, 633 (2026). https://doi.org/10.1038/s41597-026-06916-x
Nyckelord: Prototheca wickerhamii, genommontering, opportunistisk infektion, långläsningsekvensering, patogenomik