Clear Sky Science · pt
Montagens de Genoma de Alta Qualidade de Duas Cepas de Prototheca wickerhamii
Por que essa minúscula alga importa para nossa saúde
A maioria de nós pensa em algas como aquela camada verde inofensiva sobre lagoas, movida pela luz do sol. Mas alguns parentes das algas perderam seu pigmento verde e se transformaram em agentes furtivos que podem infectar pessoas e animais. Um desses culpados, Prototheca wickerhamii, causa infecções raras, porém persistentes, de pele, tecidos moles e, ocasionalmente, órgãos mais profundos. Os médicos têm dificuldades com esse microrganismo em parte porque sua biologia básica ainda é pouco compreendida. Este estudo fornece projetos de alta qualidade do DNA de duas cepas clínicas desse micro-organismo, oferecendo aos pesquisadores uma lista detalhada de componentes que pode ajudar a explicar como ele sobrevive no organismo e como poderíamos diagnosticar e tratar melhor as infecções que causa. 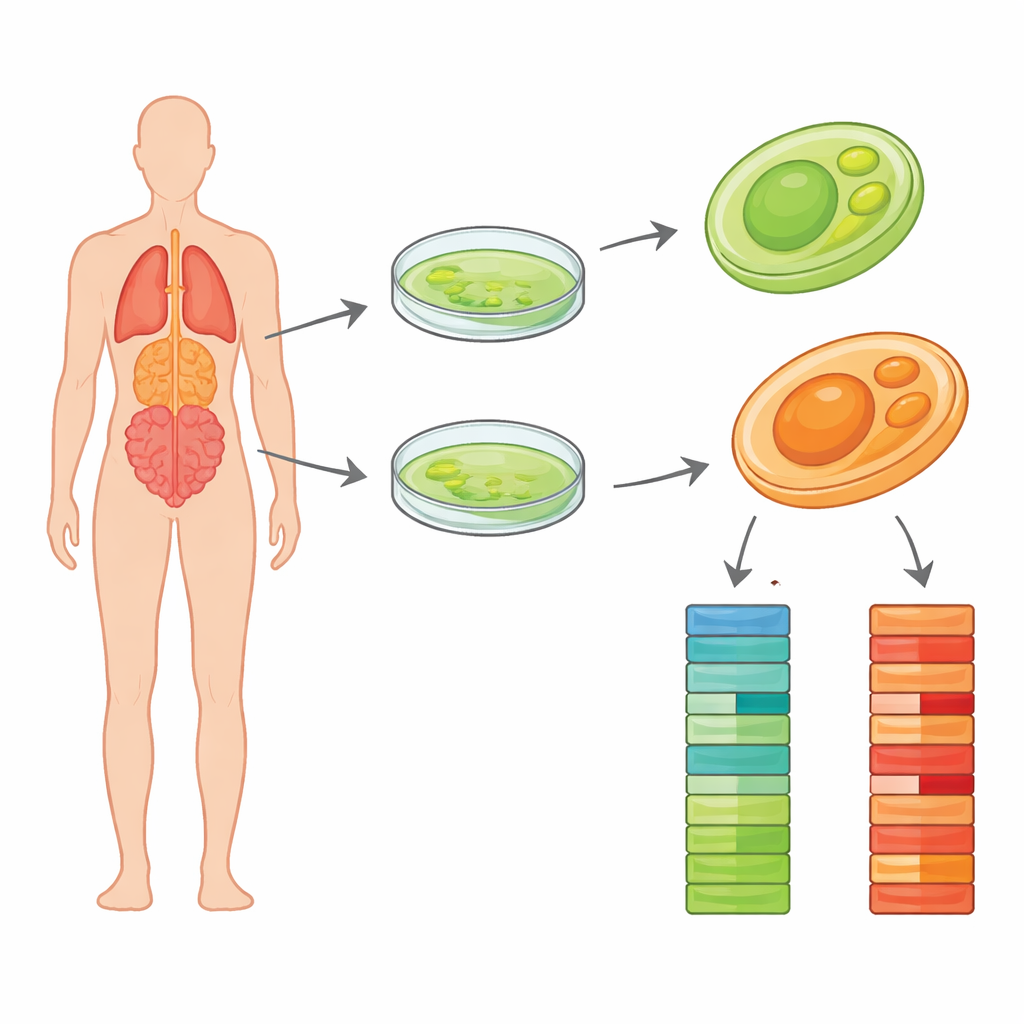
Um parente incolor escondido à vista de todos
Prototheca wickerhamii pertence a um grupo pouco conhecido de microalgas “incolores” que não realizam mais fotossíntese. Em vez de viverem à custa da luz solar como seus parentes verdes, elas se mantêm em ambientes úmidos e, às vezes, dentro de hospedeiros de sangue quente. Nas últimas duas décadas, as infecções relatadas causadas por esses organismos aumentaram, especialmente em pessoas com o sistema imunológico enfraquecido e em animais de companhia. Ainda assim, a carga real provavelmente é subestimada, porque Prototheca pode passar despercebida ou ser identificada incorretamente em testes laboratoriais de rotina. Trabalhos anteriores decodificaram o DNA de uma cepa de referência e sugeriram que o organismo carrega muitos genes semelhantes a fatores de virulência conhecidos em fungos patogênicos, o que indica que seu genoma pode ter sido moldado para prosperar no corpo humano.
Coletando e lendo o DNA do microrganismo
No novo estudo, os cientistas concentraram-se em duas cepas clínicas, chamadas Pw26 e PwS1, isoladas de pacientes em diferentes cidades chinesas. Primeiro cultivaram colônias puras em meios de cultura padrão e confirmaram que nenhuma outra micro-organismo contaminava os cultivos. A equipe então extraiu DNA de alta qualidade e usou um método moderno de leitura longa chamado sequenciamento PacBio HiFi. Ao contrário de técnicas mais antigas que fragmentam o DNA em pedaços muito curtos, as leituras HiFi cobrem dezenas de milhares de bases de uma só vez com alta precisão. Isso facilita reconstruir cromossomos inteiros com poucas lacunas. Os pesquisadores geraram mais de um bilhão e meio de bases de sequência para Pw26 e mais de oitocentas milhões para PwS1, fornecendo cobertura profunda de ambos os genomas.
Construindo genomas completos e encontrando padrões repetidos
Usando softwares especializados de montagem, as leituras longas de DNA foram costuradas em trechos contínuos que representam os cromossomos do organismo. Os tamanhos finais dos genomas foram cerca de 17,8 milhões e 17,4 milhões de bases para Pw26 e PwS1 — semelhantes a, mas ligeiramente maiores que, a cepa estudada anteriormente. Cada um foi montado em apenas 14 a 17 fragmentos, e verificações estatísticas mostraram que a maioria dos genes centrais esperados estava presente, um sinal de completude. A equipe então procurou por elementos de DNA repetidos, que podem influenciar a evolução dos genomas. Esses repetidos constituíram aproximadamente 6% de Pw26 e 4% de PwS1, dominados por uma classe chamada repetições terminais longas (long terminal repeats), frequentemente vistas em genomas de plantas e algas. Diferenças sutis na quantidade e no tipo de repetições entre as duas cepas podem refletir como cada uma se adaptou a ambientes ou hospedeiros diferentes.
O que os genes dizem sobre o modo de vida do microrganismo
Após mascarar as repetições, os pesquisadores previram genes codificadores de proteínas usando uma combinação de três abordagens: modelos computacionais treinados na estrutura gênica, comparação com proteínas conhecidas de algas relacionadas e cepas de Prototheca, e alinhamento de dados de RNA coletados anteriormente. Isso resultou em cerca de 6.400 genes em cada genoma. Eles então anotaram esses genes usando dois catálogos amplamente usados de função gênica. Um, chamado Gene Ontology, agrupa genes pelos tipos de tarefas que desempenham na célula, enquanto o banco de dados KEGG os mapeia para vias metabólicas. Ambas as cepas apresentaram muitos genes envolvidos na produção de energia, na degradação e síntese de nutrientes e na regulação de processos celulares. PwS1 mostrou ênfase adicional em vias relacionadas a lipídios e sinalização, ecoando descobertas anteriores que ligaram a aparência mucosa incomum dessa cepa e sua menor toxicidade a mudanças em sua superfície e metabolismo. 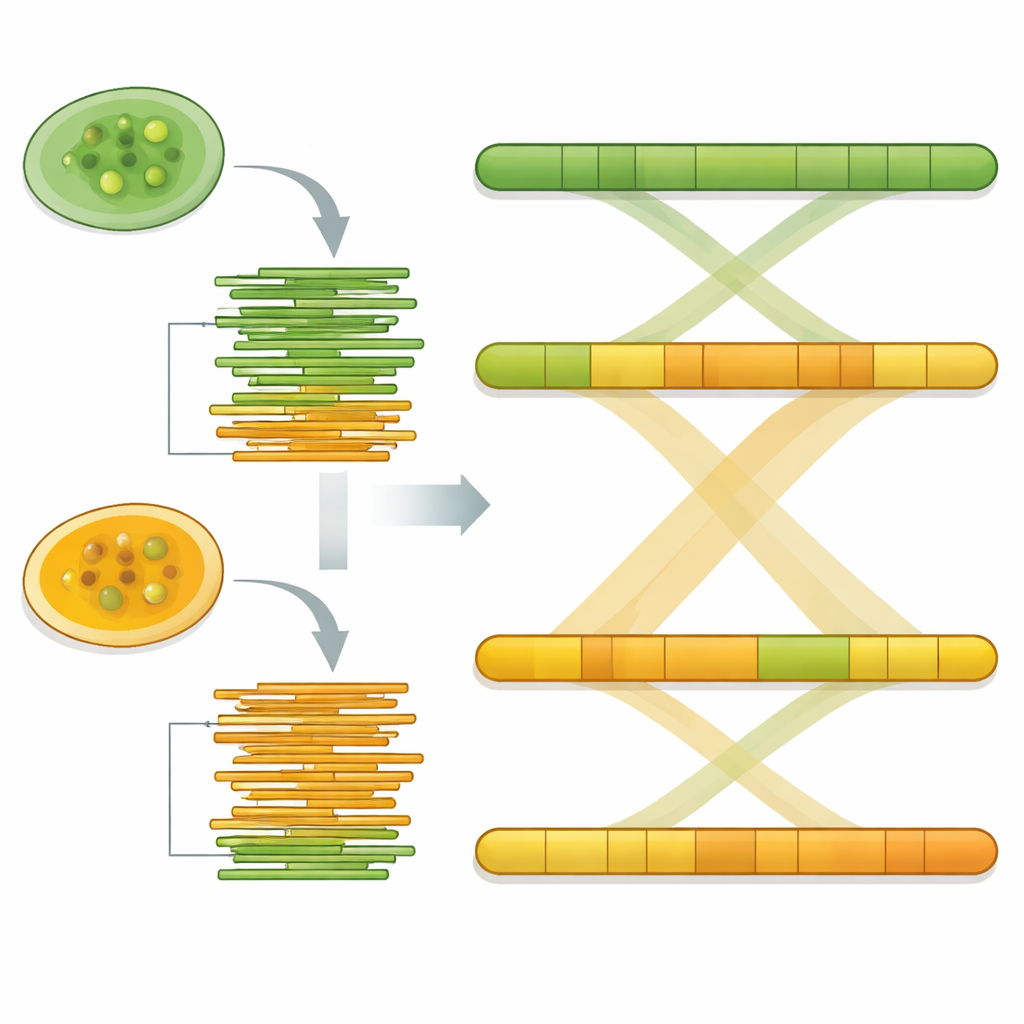
Verificando a precisão e comparando as duas cepas
Para garantir que suas reconstruções fossem confiáveis, a equipe remapeou as leituras longas originais em cada genoma montado. Mais de 93% das leituras corresponderam de volta com cobertura uniforme, e o padrão de composição de bases não mostrou sinais de contaminação. Outra verificação de qualidade, chamada BUSCO, confirmou que mais de 86% de um conjunto padrão de genes conservados de algas estavam presentes e intactos em ambas as cepas. Finalmente, quando os dois genomas foram alinhados usando ferramentas de comparação de genoma inteiro, seus segmentos de DNA corresponderam quase um a um, indicando um grau muito alto de semelhança e apoiando a ideia de que as montagens capturam com precisão os cromossomos subjacentes.
O que isso significa para diagnóstico e tratamento futuros
Para não especialistas, a mensagem principal é que agora dispomos de mapas de DNA detalhados e confiáveis de duas cepas patogênicas de Prototheca wickerhamii. Esses mapas por si só não curam infecções, mas fornecem a base para formular perguntas mais precisas: quais genes permitem que o microrganismo evada o sistema imunológico, quais vias poderiam ser alvo de medicamentos existentes e como diferentes cepas variam em virulência e resposta a fármacos? Como os dados foram tornados publicamente disponíveis, laboratórios em todo o mundo podem usá-los para desenhar melhores testes diagnósticos, rastrear surtos sob uma perspectiva One Health que liga a saúde humana e animal, e, eventualmente, informar estratégias de tratamento mais precisas para esse patógeno incomum, porém desafiador.
Citação: Fang, L., Guo, J., Ning, Q. et al. High-Quality Genome Assemblies of Two Prototheca wickerhamii Strains. Sci Data 13, 633 (2026). https://doi.org/10.1038/s41597-026-06916-x
Palavras-chave: Prototheca wickerhamii, montagem de genoma, infecção oportunista, sequenciamento de leitura longa, genômica de patógenos