Clear Sky Science · it
Assemblaggi genomici di alta qualità di due ceppi di Prototheca wickerhamii
Perché questa piccola alga conta per la nostra salute
La maggior parte di noi pensa alle alghe come a innocui aggregati verdi sui laghetti, alimentati dalla luce solare. Ma alcuni parenti delle alghe hanno perso il loro pigmento verde e si sono trasformati in agenti furtivi in grado di infettare persone e animali. Uno di questi colpevoli, Prototheca wickerhamii, provoca infezioni rare ma tenaci della pelle, dei tessuti molli e, occasionalmente, di organi più profondi. I medici fanno fatica a gestirlo anche perché la sua biologia di base è ancora poco compresa. Questo studio fornisce progetti del DNA ad alta qualità di due ceppi clinici di questo microrganismo, offrendo ai ricercatori un elenco dettagliato delle componenti che può aiutare a spiegare come sopravvive nell’organismo e come potremmo migliorare la diagnosi e il trattamento delle infezioni che causa. 
Un cugino incolore nascosto in piena vista
Prototheca wickerhamii appartiene a un gruppo poco noto di microalghe “incolori” che non svolgono più la fotosintesi. Invece di vivere alla luce del sole come i loro parenti verdi, si mantengono in ambienti umidi e talvolta all’interno di ospiti endotermici. Negli ultimi due decenni le infezioni causate da questi organismi sono aumentate, soprattutto in persone con sistemi immunitari indeboliti e negli animali da compagnia. Tuttavia, il carico reale è probabilmente sottostimato, perché Prototheca può essere trascurata o identificata erroneamente nei test di laboratorio di routine. Lavori precedenti hanno decodificato il DNA di un ceppo di riferimento e suggerito che l’organismo possiede molti geni simili a fattori di virulenza noti nei funghi patogeni, insinuando che il suo genoma si sia modellato per prosperare nell’organismo umano.
Raccolta e lettura del DNA del microbo
Nel nuovo studio, gli scienziati si sono concentrati su due ceppi clinici, denominati Pw26 e PwS1, isolati da pazienti in diverse città cinesi. Hanno prima coltivato colonie pure su terreni di laboratorio standard e confermato l’assenza di altri microrganismi nelle colture. Il team ha quindi estratto DNA di alta qualità e ha utilizzato un metodo moderno a letture lunghe chiamato sequenziamento PacBio HiFi. Diversamente dalle tecniche più vecchie che tagliano il DNA in frammenti molto corti, le letture HiFi coprono decine di migliaia di basi alla volta con alta accuratezza. Questo rende più semplice ricostruire cromosomi interi con pochi gap. I ricercatori hanno generato più di un miliardo e mezzo di basi di sequenza per Pw26 e oltre ottocento milioni per PwS1, fornendo una copertura profonda di entrambi i genomi.
Costruire genomi completi e trovare schemi ripetuti
Usando software di assemblaggio specializzato, le lunghe letture di DNA sono state cucite in tratti continui che rappresentano i cromosomi dell’organismo. Le dimensioni finali dei genomi sono state di circa 17,8 milioni e 17,4 milioni di basi per Pw26 e PwS1—simili a, ma leggermente maggiori rispetto, al ceppo precedentemente studiato. Ciascuno è stato assemblato in appena 14-17 frammenti, e controlli statistici hanno mostrato che la maggior parte dei geni core attesi era presente, segnale di completezza. Il team ha poi cercato elementi ripetuti di DNA, che possono influenzare l’evoluzione dei genomi. Queste ripetizioni costituivano circa il 6% di Pw26 e il 4% di PwS1, dominate da una classe chiamata long terminal repeat spesso osservata nei genomi di piante e alghe. Differenze sottili nella quantità e nel tipo di ripetizioni tra i due ceppi possono riflettere come ciascuno si sia adattato a ambienti o ospiti diversi.
Cosa dicono i geni sullo stile di vita del microbo
Dopo aver mascherato le ripetizioni, i ricercatori hanno predetto i geni codificanti proteine usando una combinazione di tre approcci: modelli computazionali addestrati sulla struttura dei geni, confronto con proteine note di alghe correlate e ceppi di Prototheca, e allineamento di dati di RNA raccolti in precedenza. Questo ha portato a circa 6.400 geni in ciascun genoma. Hanno quindi annotato questi geni utilizzando due cataloghi ampiamente usati di funzione genica. Uno, chiamato Gene Ontology, raggruppa i geni per i tipi di compiti che svolgono nella cellula, mentre il database KEGG li mappa in vie metaboliche. Entrambi i ceppi presentavano numerosi geni coinvolti nella produzione di energia, nella degradazione e sintesi di nutrienti e nella regolazione dei processi cellulari. PwS1 mostrava un’enfasi aggiuntiva su vie correlate ai lipidi e alla segnalazione, riecheggiando risultati precedenti che collegavano l’aspetto mucoso insolito di questo ceppo e la sua minore tossicità a cambiamenti nella superficie e nel metabolismo. 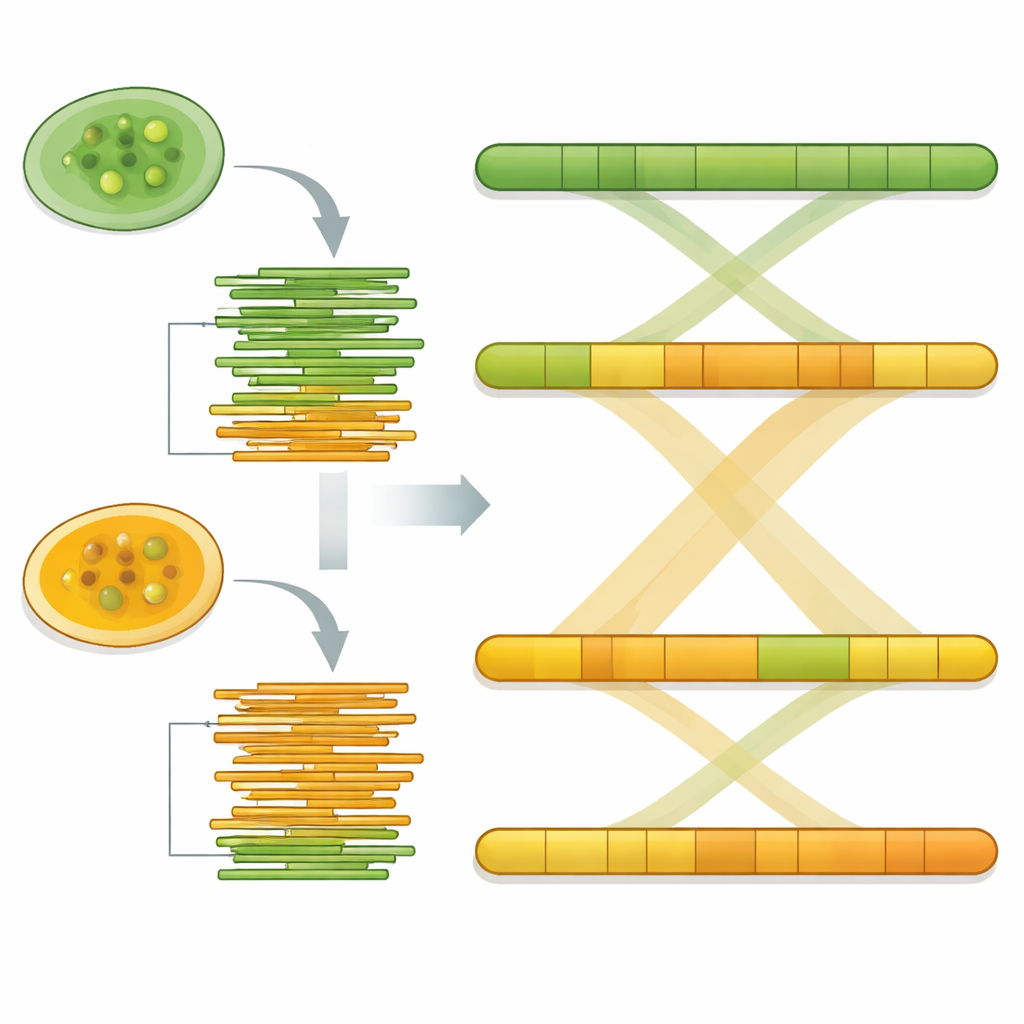
Verifica dell’accuratezza e confronto tra i due ceppi
Per garantire che le loro ricostruzioni fossero affidabili, il team ha rimappato le letture lunghe originali su ciascun genoma assemblato. Oltre il 93% delle letture si è ricongiunto con copertura uniforme, e il profilo della composizione delle basi non ha mostrato segni di contaminazione. Un altro controllo di qualità, chiamato BUSCO, ha confermato che oltre l’86% di un set standard di geni algali conservati era presente e integro in entrambi i ceppi. Infine, quando i due genomi sono stati allineati usando strumenti di confronto a livello di intero genoma, i loro segmenti di DNA combaciavano quasi uno a uno, indicando un grado molto elevato di somiglianza e supportando l’idea che gli assemblaggi rappresentino accuratamente i cromosomi sottostanti.
Cosa significa per diagnosi e trattamento futuri
Per i non specialisti, il messaggio principale è che ora disponiamo di mappe del DNA dettagliate e affidabili per due ceppi patogeni di Prototheca wickerhamii. Queste mappe non curano da sole le infezioni, ma forniscono la base per porre domande più precise: quali geni permettono al microbo di eludere il sistema immunitario, quali vie potrebbero essere bersagliate da farmaci esistenti e come variano i diversi ceppi in virulenza e risposta ai farmaci? Poiché i dati sono stati resi pubblicamente disponibili, laboratori di tutto il mondo possono usarli per progettare test diagnostici migliori, tracciare focolai seguendo una prospettiva One Health che collega salute umana e animale, e infine informare strategie di trattamento più mirate per questo patogeno poco comune ma impegnativo.
Citazione: Fang, L., Guo, J., Ning, Q. et al. High-Quality Genome Assemblies of Two Prototheca wickerhamii Strains. Sci Data 13, 633 (2026). https://doi.org/10.1038/s41597-026-06916-x
Parole chiave: Prototheca wickerhamii, assemblaggio genomico, infezione opportunistica, sequenziamento a letture lunghe, genomica dei patogeni