Clear Sky Science · pt
Um conjunto de dados multimodal para a biodiversidade de insetos com imagens e DNA no nível da armadilha e do indivíduo
Por que insetos minúsculos e big data importam
Em todo o mundo, as populações de insetos estão mudando rapidamente, com alguns grupos em declínio antes mesmo que os cientistas tenham tempo de descrevê‑los. Métodos tradicionais de triagem, nomenclatura e contagem dependem do tempo escasso de especialistas e de trabalho meticuloso ao microscópio. Este artigo apresenta um novo tipo de recurso que reúne fotografias detalhadas e informações de DNA para dezenas de milhares de pequenas criaturas capturadas em armadilhas de campo reais. Ao emparelhar biologia com visão computacional moderna, os autores pretendem acelerar a forma como medimos e monitoramos a vida de insetos em um planeta em mudança.
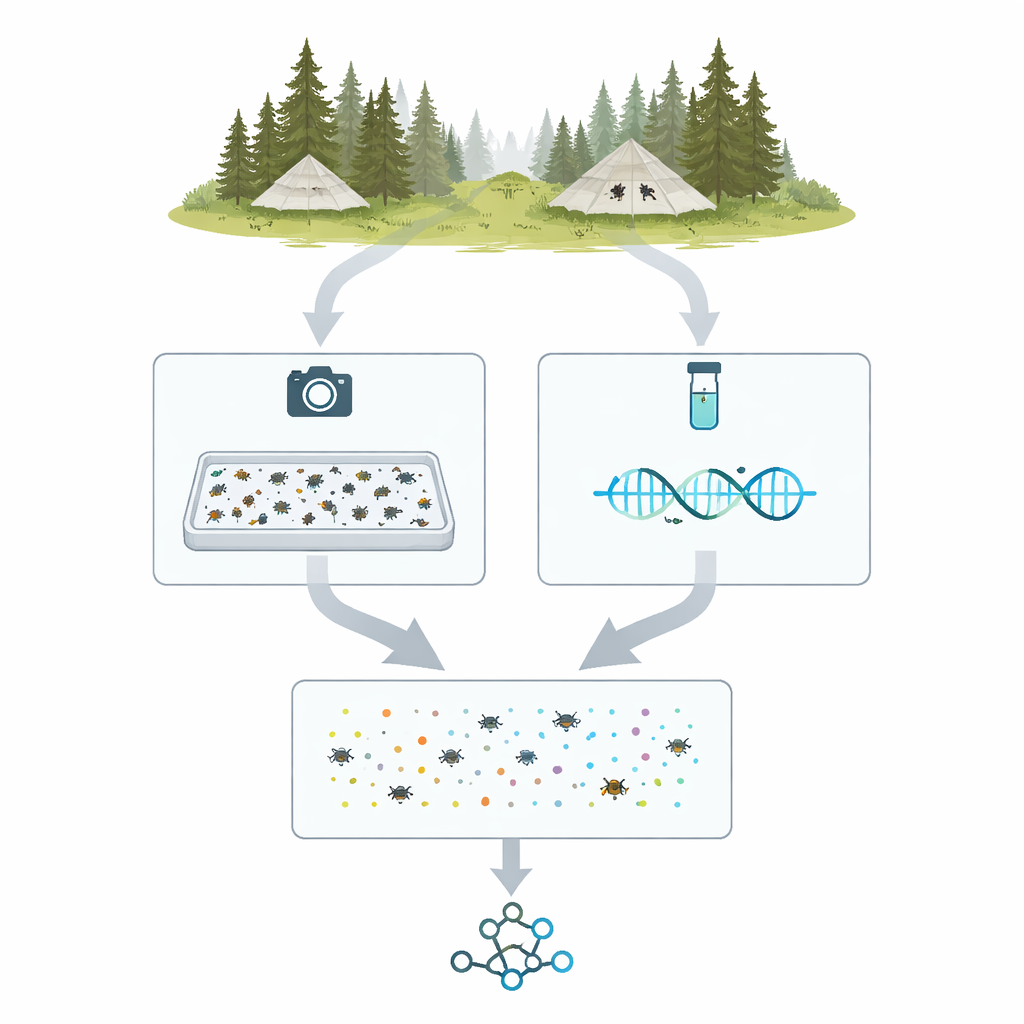
De tendas de campo a espécimes digitais
O projeto, chamado MassID45, começa nas florestas e áreas úmidas do norte da Suécia e da Finlândia, onde armadilhas Malaise em forma de tenda direcionam insetos voadores para frascos de coleta. Ao longo da temporada de 2021, 45 amostras semanais de 19 locais foram escolhidas para análise aprofundada. No laboratório, cada coleta mista foi pesada, processada com cuidado para liberar DNA e despejada em uma bandeja rasa com uma fina camada de álcool. Os insetos foram espalhados e fotografados de cima com uma câmera de alta resolução sob iluminação cuidadosamente controlada, criando uma única "imagem de amostra" na qual milhares de indivíduos aparecem como formas do tamanho de um alfinete.
Ver os mesmos insetos de duas maneiras
Após a captura das imagens de amostra, a equipe dividiu as amostras em insetos individuais para trabalho mais detalhado. Cada espécime foi colocado em seu próprio poço minúsculo ou montado em alfinete e fotografado em close. Ao mesmo tempo, um trecho curto e padronizado de DNA — frequentemente chamado de código de barras — foi sequenciado para cada inseto usando máquinas modernas de sequenciamento de alto rendimento. Isso produziu mais de 35.000 sequências individuais de código de barras. Comparar essas sequências com grandes bancos de referência permitiu aos pesquisadores agrupar a maioria dos espécimes em grupos bem conhecidos, como moscas, besouros e famílias de mariposas, fornecendo uma lista ancorada em DNA dos tipos de artrópodes presentes em cada amostra de armadilha.
Ensinando computadores a encontrar criaturas minúsculas
Para tornar as fotos da bandeja úteis para automação, os autores precisaram ensinar os computadores onde cada inseto está e a qual grupo amplo pertence. Eles usaram um processo de anotação em duas etapas. Primeiro, um algoritmo delineou de forma aproximada cada objeto escuro na imagem da bandeja; em seguida, anotadores humanos refinaram esses contornos usando uma ferramenta web assistida por IA, garantindo que cada inseto — frequentemente com apenas algumas pixels de largura — recebesse sua própria máscara limpa. Em segundo lugar, um especialista examinou cada inseto mascarado e o atribuiu ao nível taxonômico mais preciso possível a partir da fotografia, guiado por uma lista personalizada de grupos esperados derivada dos códigos de barras de DNA correspondentes. Essa estratégia concentrou o esforço dos especialistas no reconhecimento em vez do desenho tedioso, e resultou em mais de 17.000 artrópodes nas imagens de amostra sendo vinculados a nomes de grupos robustos.
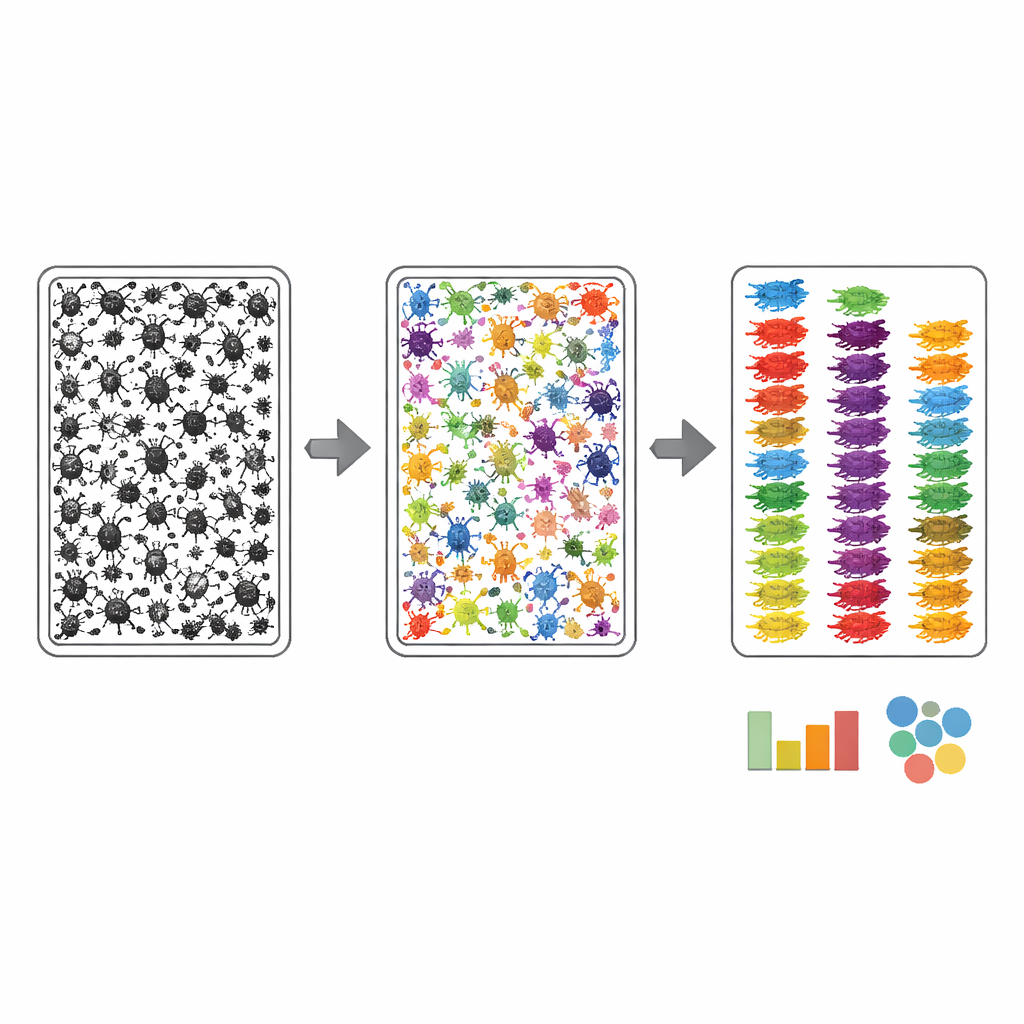
O quão bem o sistema funciona?
A equipe então tratou o MassID45 como um teste de estresse para a visão computacional moderna. As imagens de amostra foram divididas em blocos sobrepostos para que insetos minúsculos permanecessem nítidos o suficiente para análise, e diversos modelos de segmentação de imagem de ponta foram avaliados. Sistemas gerais "zero‑shot", que nunca tinham visto esses dados antes, tiveram dificuldades: tendiam a perder os menores insetos e a confundi‑los com fragmentos de detritos. Em contraste, modelos que foram reentreinados nas imagens cuidadosamente rotuladas do MassID45 foram muito melhores em localizar e delinear indivíduos, especialmente grupos comuns como moscas e vespas. Ainda assim, os menores colêmbolos e outras formas pálidas e pontilhadas muitas vezes permaneceram difíceis de distinguir do material de fundo, destacando um limite visual inerente.
O que isso significa para acompanhar a vida na Terra
MassID45 não é um único novo algoritmo, mas um rico conjunto de referência que outros pesquisadores podem baixar e expandir. Ao unir fotos de nível de bandeja, imagens de espécimes individuais, sequências de DNA e rótulos de grupo fornecidos por especialistas a partir de amostras de campo reais, ele oferece um campo de treino realista para que computadores aprendam a contar e caracterizar enxames de pequenos artrópodes. Embora as imagens raramente permitam identificação a nível de espécie, elas capturam de forma confiável grupos mais amplos, o que frequentemente é suficiente para revelar mudanças nas comunidades de insetos ao longo do tempo e do espaço. Na prática, isso significa que programas de monitoramento futuros poderão combinar fotografia simples de armadilhas com amostragem de DNA e aprendizado de máquina para oferecer visões mais rápidas, detalhadas e escaláveis da biodiversidade de insetos do que seria possível apenas por especialistas humanos.
Citação: Orsholm, J., Quinto, J., Autto, H. et al. A multi-modal dataset for insect biodiversity with imagery and DNA at the trap and individual level. Sci Data 13, 630 (2026). https://doi.org/10.1038/s41597-026-07251-x
Palavras-chave: biodiversidade de insetos, codificação de DNA, visão computacional, monitoramento ecológico, conjunto de dados de aprendizado de máquina