Clear Sky Science · es
Un conjunto de datos multimodal sobre la biodiversidad de insectos con imágenes y ADN a nivel de trampa e individual
Por qué importan los insectos diminutos y los grandes volúmenes de datos
En todo el mundo, las poblaciones de insectos están cambiando con rapidez, y algunos grupos disminuyen antes incluso de que los científicos tengan oportunidad de describirlos. Los métodos tradicionales de clasificar, nombrar y contar insectos dependen del tiempo escaso de expertos y del trabajo meticuloso con microscopios. Este artículo presenta un nuevo tipo de recurso que reúne fotografías detalladas e información de ADN de decenas de miles de diminutas criaturas capturadas en trampas de campo reales. Al combinar biología con visión por ordenador moderna, los autores pretenden acelerar la medición y el seguimiento de la vida de los insectos en un planeta cambiante.
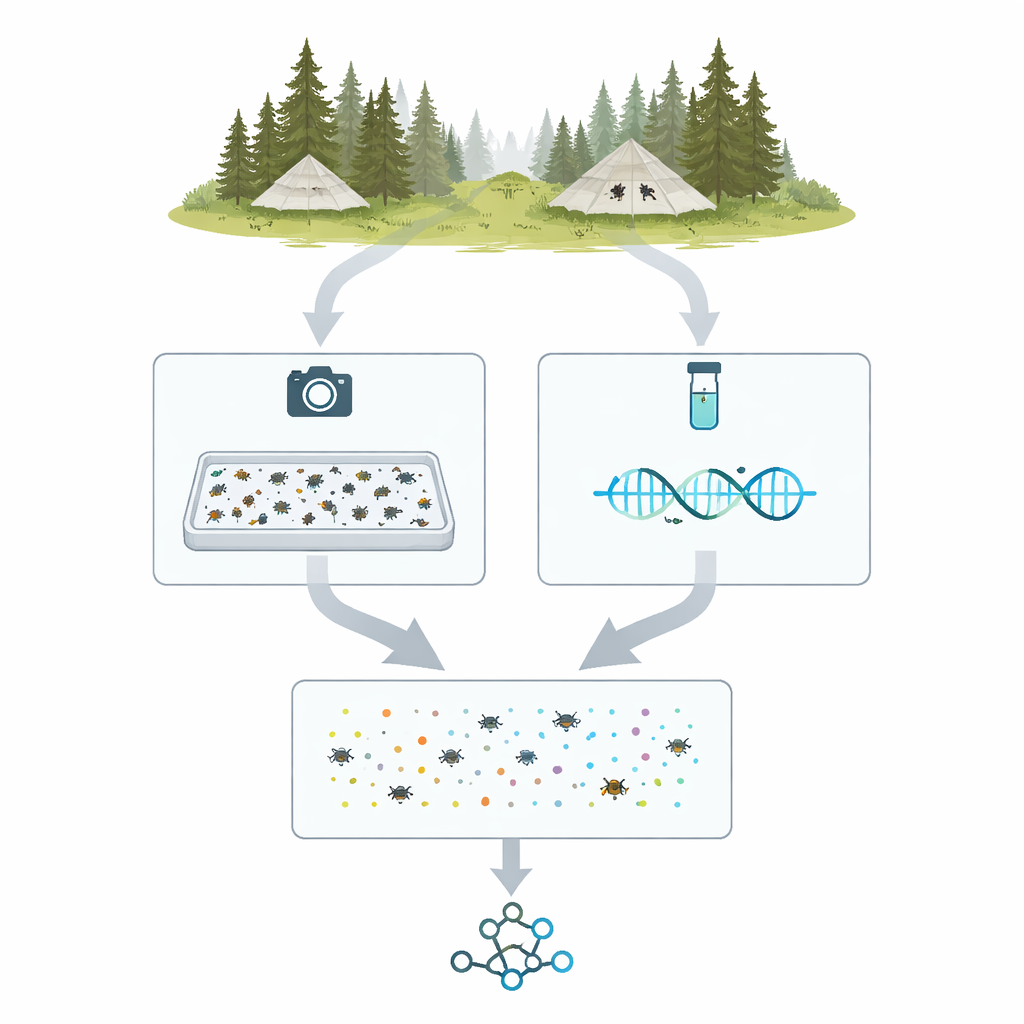
De las tiendas de campaña de campo a los especímenes digitales
El proyecto, llamado MassID45, comienza en los bosques y humedales del norte de Suecia y Finlandia, donde trampas Malaise en forma de tienda canalizan insectos voladores hacia botellas colectoras. Durante la temporada de 2021, se eligieron 45 muestras semanales de 19 ubicaciones para un análisis profundo. En el laboratorio, cada captura mixta se pesó, se procesó con cuidado para liberar ADN y se vertió en una bandeja poco profunda con una fina capa de alcohol. Los insectos se distribuyeron y fotografiaron desde arriba con una cámara de alta resolución bajo iluminación cuidadosamente controlada, creando una única "imagen de bandeja" en la que miles de individuos aparecen como formas del tamaño de una alfiler.
Ver los mismos insectos de dos maneras
Tras tomar las imágenes de las bandejas, el equipo dividió las muestras en insectos individuales para un trabajo más detallado. Cada espécimen se colocó en su propio pozo diminuto o se montó en alfiler y se fotografió en primer plano. Al mismo tiempo, se leyó una secuencia corta y estandarizada de ADN —a menudo llamada código de barras— para cada insecto usando máquinas modernas de secuenciación de alto rendimiento. Esto produjo más de 35.000 secuencias individuales de código de barras. Comparar esas secuencias con grandes bases de referencia permitió a los investigadores asignar la mayoría de los especímenes a grupos bien conocidos, como dípteros, coleópteros y familias de lepidópteros, proporcionando una lista anclada en ADN de qué tipos de artrópodos estuvieron presentes en cada muestra de trampa.
Enseñar a las máquinas a encontrar criaturas diminutas
Para que las fotos de las bandejas fueran útiles para la automatización, los autores tuvieron que enseñar a las máquinas dónde está cada insecto y a qué grupo amplio pertenece. Usaron un proceso de anotación en dos pasos. Primero, un algoritmo delineó de forma aproximada cada objeto oscuro en la imagen de la bandeja; luego, anotadores humanos refinaron esos contornos usando una herramienta web asistida por IA, asegurando que cada insecto —a menudo de apenas unos píxeles de ancho— recibiera su propia máscara limpia. En segundo lugar, un experto examinó cada insecto enmascarado y lo asignó al nivel taxonómico más fino que podía distinguir en la fotografía, guiado por una lista personalizada de grupos esperados derivada de los códigos de barras coincidentes. Esta estrategia concentró el esfuerzo de los expertos en el reconocimiento más que en el trazado tedioso, y resultó en que más de 17.000 artrópodos en las imágenes de bandeja quedaran vinculados a nombres de grupos sólidos.
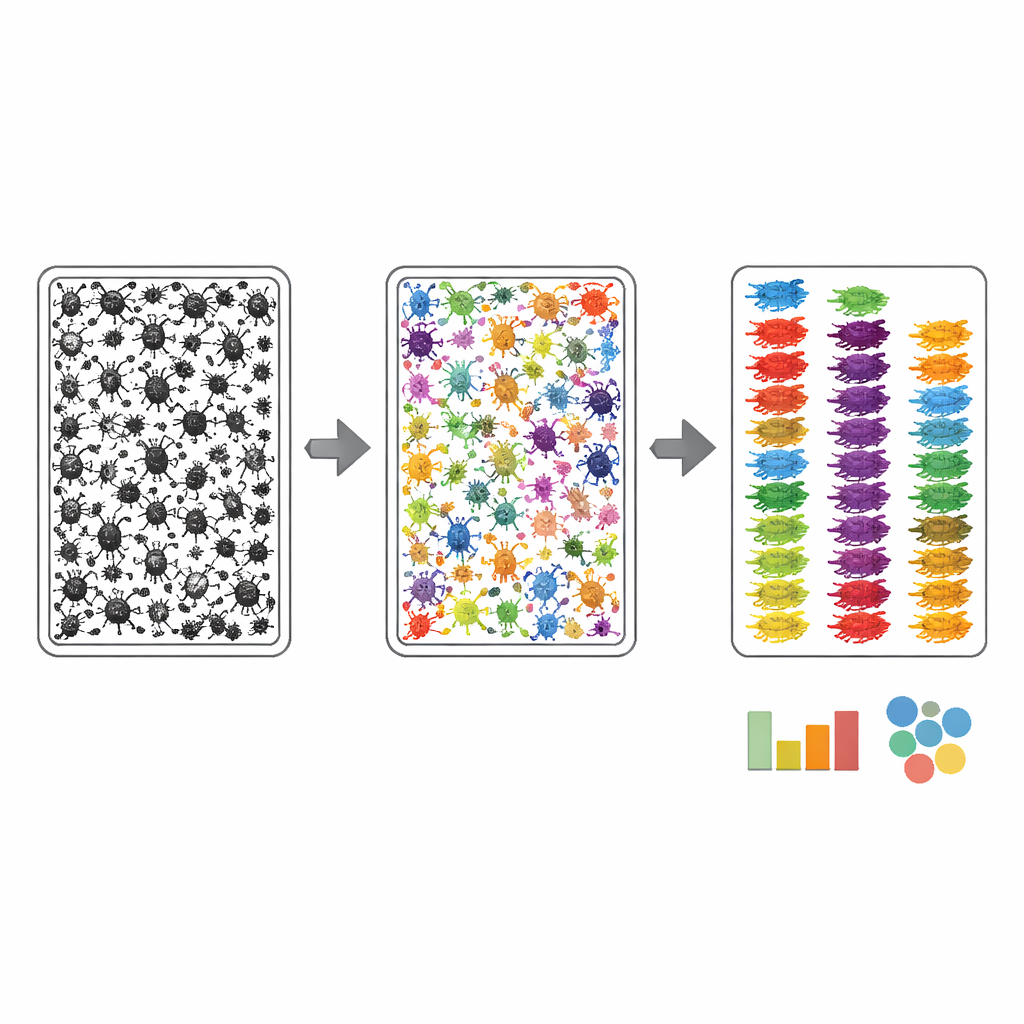
¿Qué tan bien funciona el sistema?
El equipo trató MassID45 como una prueba de esfuerzo para la visión por ordenador moderna. Las imágenes de las bandejas se dividieron en mosaicos superpuestos para que los insectos diminutos permanecieran lo bastante nítidos para el análisis, y se evaluaron varios modelos de segmentación de imagen de última generación. Los sistemas generales "zero-shot", que nunca habían visto estos datos antes, tuvieron dificultades: tendían a pasar por alto los insectos más pequeños y a confundirlos con restos. En contraste, los modelos reentrenados con las imágenes cuidadosamente etiquetadas de MassID45 funcionaron mucho mejor a la hora de encontrar y delinear individuos, especialmente grupos comunes como moscas y avispas. Aun así, los colémbolos más diminutos y otras formas pálidas y moteadas con frecuencia seguían siendo difíciles de distinguir del material de fondo, lo que subraya un límite visual inherente.
Qué significa esto para el seguimiento de la vida en la Tierra
MassID45 no es un único algoritmo nuevo, sino un rico conjunto de referencia que otros investigadores pueden descargar y ampliar. Al vincular fotografías a nivel de bandeja, imágenes de especímenes individuales, secuencias de ADN y etiquetas de grupo por expertos procedentes de muestras de campo reales, ofrece un terreno de entrenamiento realista para que las máquinas aprendan a contar y caracterizar enjambres de pequeños artrópodos. Si bien las imágenes rara vez permiten la identificación a nivel de especie, capturan de forma fiable grupos más amplios, que a menudo son suficientes para revelar cambios en las comunidades de insectos a lo largo del tiempo y el espacio. En la práctica, esto significa que los futuros programas de seguimiento podrían combinar la fotografía simple de trampas con muestreo de ADN y aprendizaje automático para ofrecer vistas más rápidas, más detalladas y más escalables de la biodiversidad de insectos que las que podrían lograr únicamente los expertos humanos.
Cita: Orsholm, J., Quinto, J., Autto, H. et al. A multi-modal dataset for insect biodiversity with imagery and DNA at the trap and individual level. Sci Data 13, 630 (2026). https://doi.org/10.1038/s41597-026-07251-x
Palabras clave: biodiversidad de insectos, codificación por ADN, visión por ordenador, monitoreo ecológico, conjunto de datos de aprendizaje automático