Clear Sky Science · it
Un set di dati multimodale per la biodiversità degli insetti con immagini e DNA a livello di trappola e di individuo
Perché i piccoli insetti e i big data sono importanti
In tutto il mondo le popolazioni di insetti stanno cambiando rapidamente, con alcuni gruppi in declino prima ancora che gli scienziati abbiano avuto il tempo di descriverli. I metodi tradizionali di ordinamento, denominazione e conteggio degli insetti dipendono dal tempo limitato degli esperti e dal lavoro meticoloso al microscopio. Questo articolo presenta un nuovo tipo di risorsa che mette insieme fotografie dettagliate e informazioni sul DNA per decine di migliaia di piccole creature catturate in trappole sul campo. Accoppiando la biologia con la moderna visione artificiale, gli autori mirano ad accelerare il modo in cui misuriamo e monitoriamo la vita degli insetti in un pianeta in cambiamento.
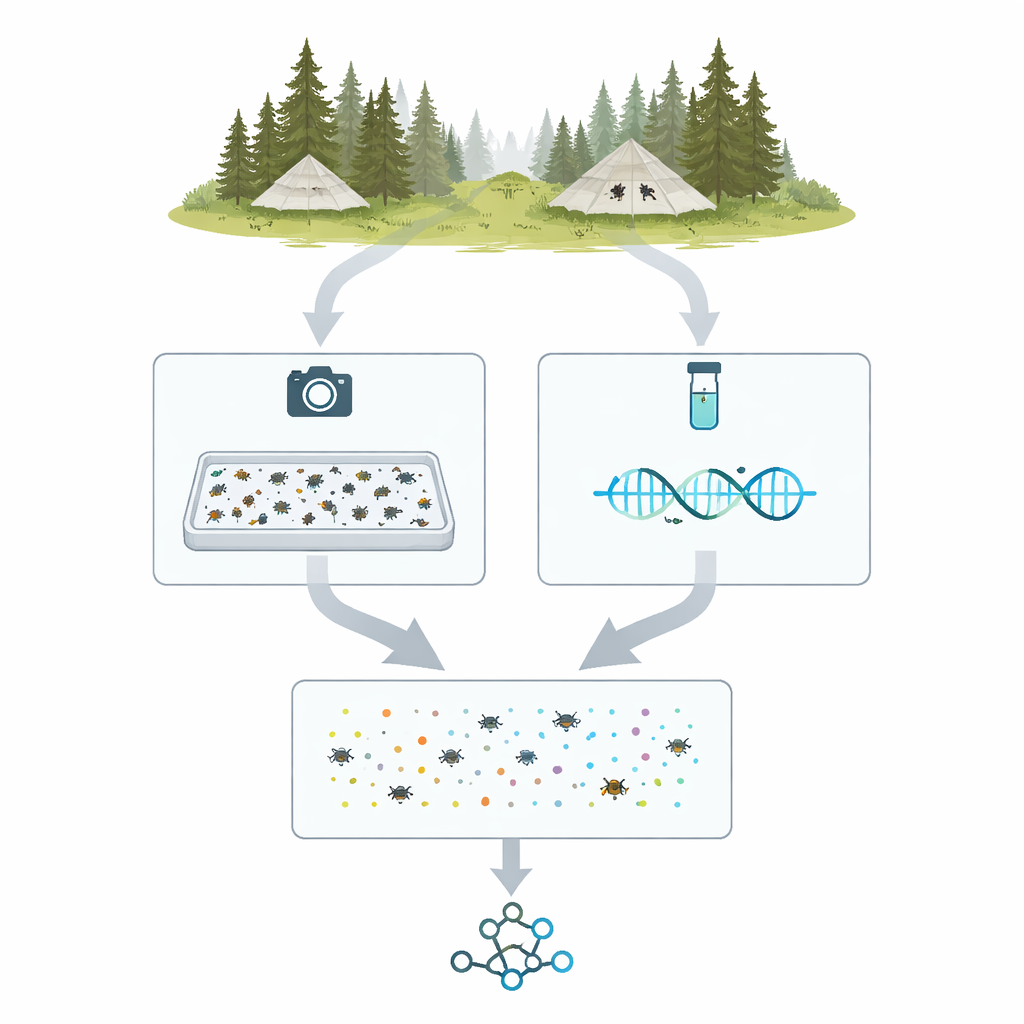
Dalle tende da campo agli esemplari digitali
Il progetto, chiamato MassID45, parte dalle foreste settentrionali e dalle zone umide di Svezia e Finlandia, dove speciali trappole tipo Malaise a forma di tenda convogliano insetti volanti in bottiglie collezionatrici. Nella stagione 2021, 45 campioni settimanali provenienti da 19 località sono stati scelti per un’analisi approfondita. In laboratorio, ogni cattura mista è stata pesata, lavorata con delicatezza per rilasciare il DNA e versata in una vaschetta poco profonda con uno strato sottile di alcool. Gli insetti sono stati distribuiti e fotografati dall’alto con una fotocamera ad alta risoluzione sotto illuminazione attentamente controllata, creando una singola “immagine di massa” in cui migliaia di individui compaiono come sagome piccolissime.
Vedere gli stessi insetti in due modi
Dopo aver scattato le immagini di massa, il team ha separato i campioni in insetti individuali per lavori più dettagliati. Ogni esemplare è stato collocato nella propria minuscola cavità o appuntato e fotografato in primo piano. Allo stesso tempo, per ogni insetto è stato letto un breve tratto standardizzato di DNA—spesso chiamato codice a barre—utilizzando moderne macchine di sequenziamento ad alto rendimento. Ciò ha prodotto oltre 35.000 sequenze di codice a barre individuali. Il confronto di queste sequenze con grandi database di riferimento ha permesso ai ricercatori di collocare la maggior parte degli esemplari in gruppi ben noti, come mosche, coleotteri e falene, fornendo un elenco ancorato al DNA dei tipi di artropodi presenti in ciascun campione di trappola.
Insegnare ai computer a trovare creature minuscole
Per rendere utili le foto delle vaschette per l’automazione, gli autori hanno dovuto insegnare ai computer dove si trova ogni insetto e a quale gruppo ampio appartiene. Hanno utilizzato un processo di annotazione in due fasi. Prima, un algoritmo ha tracciato approssimativamente ogni oggetto scuro nell’immagine della vaschetta; poi annotatori umani hanno perfezionato questi contorni usando uno strumento web assistito dall’IA, assicurandosi che ogni insetto—spesso largo solo poche decine di pixel—ricevesse la propria maschera pulita. Secondo, un esperto ha esaminato ogni insetto mascherato e lo ha assegnato al livello tassonomico più dettagliato visibile dalla fotografia, guidato da una lista personalizzata di gruppi attesi derivata dai codici a barre corrispondenti. Questa strategia ha concentrato lo sforzo degli esperti sul riconoscimento piuttosto che sul disegno laborioso, risultando nel collegamento di oltre 17.000 artropodi nelle immagini di massa a nomi di gruppo solidi.
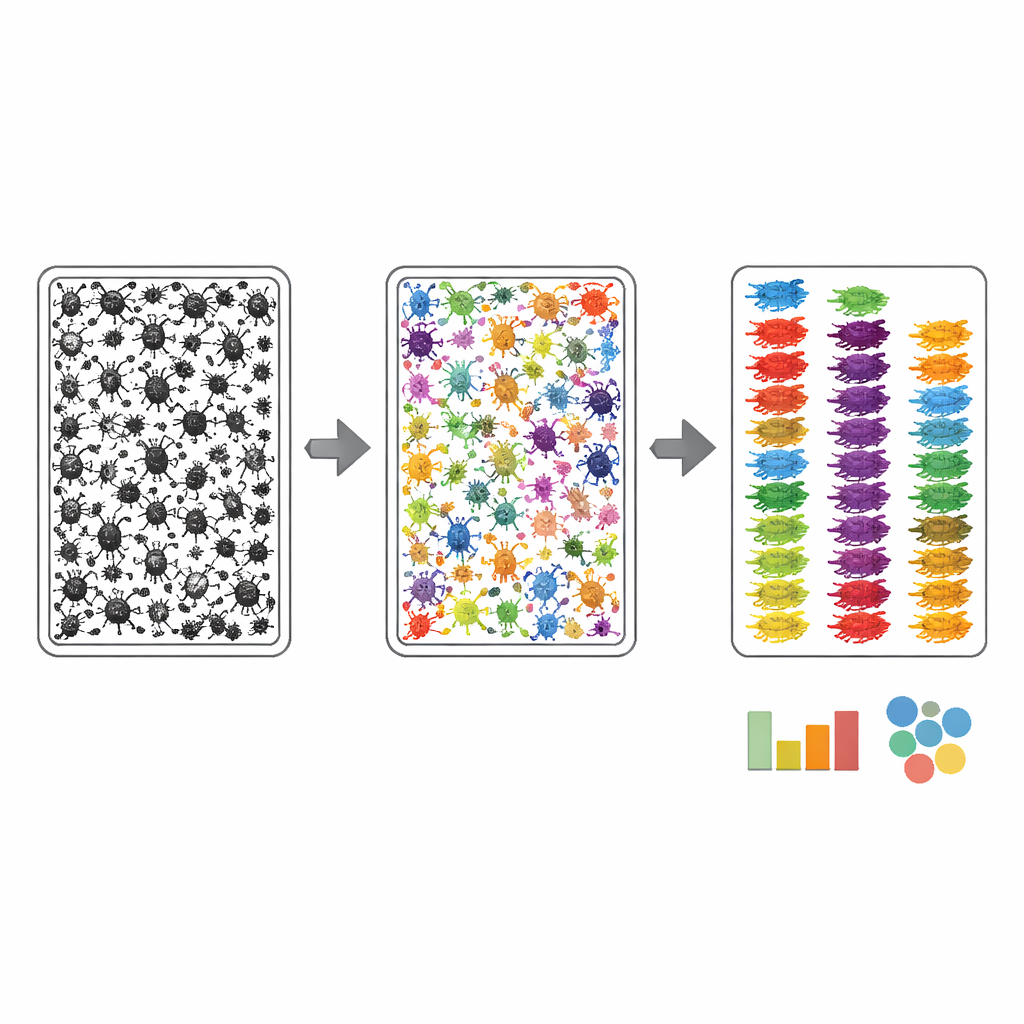
Quanto bene funziona il sistema?
Il team ha quindi considerato MassID45 come un test di stress per la visione artificiale moderna. Le immagini di massa sono state suddivise in tessere sovrapposte in modo che i minuscoli insetti rimanessero abbastanza nitidi per l’analisi, e sono stati valutati diversi modelli di segmentazione d’immagine all’avanguardia. I sistemi generali “zero‑shot”, che non avevano mai visto questi dati prima, hanno faticato: tendevano a perdere gli insetti più piccoli e a confonderli con frammenti di detriti. Al contrario, i modelli riaddestrati sulle immagini accuratamente etichettate di MassID45 hanno fatto molto meglio nel trovare e delineare gli individui, specialmente per i gruppi comuni come mosche e vespe. Tuttavia, i più piccoli collemboli e altre forme chiare e puntiformi sono spesso rimasti difficili da distinguere dal materiale di sfondo, evidenziando un limite visivo intrinseco.
Che cosa significa per il monitoraggio della vita sulla Terra
MassID45 non è un singolo nuovo algoritmo ma un ricco dataset di riferimento che altri ricercatori possono scaricare e su cui costruire. Collegando foto a livello di vaschetta, immagini di esemplari individuali, sequenze di DNA e etichette di gruppo fornite dagli esperti su campioni di campo reali, offre un terreno di addestramento realistico per i computer che devono imparare a contare e caratterizzare sciami di piccoli artropodi. Sebbene le immagini raramente consentano l’identificazione a livello di specie, catturano in modo affidabile gruppi più ampi, che spesso sono sufficienti per rivelare spostamenti nelle comunità di insetti nel tempo e nello spazio. In pratica, ciò significa che i futuri programmi di monitoraggio potrebbero combinare la fotografia semplice delle trappole con campionamenti di DNA e machine learning per fornire vedute della biodiversità degli insetti più rapide, dettagliate e scalabili di quanto sarebbe possibile per soli esperti umani.
Citazione: Orsholm, J., Quinto, J., Autto, H. et al. A multi-modal dataset for insect biodiversity with imagery and DNA at the trap and individual level. Sci Data 13, 630 (2026). https://doi.org/10.1038/s41597-026-07251-x
Parole chiave: biodiversità degli insetti, codifica a barre del DNA, visione artificiale, monitoraggio ecologico, dataset per machine learning