Clear Sky Science · pl
Zunifikowane ramy oparte na EfficientSwinB do rozpoznawania roślin leczniczych i klasyfikacji zasobów genowych krokusa
Dlaczego inteligentniejsze rozpoznawanie roślin ma znaczenie
Od ziół kuchennych po tradycyjne środki lecznicze — wiele roślin wspierających nasze zdrowie wygląda zaskakująco podobnie. Rozróżnianie ich gołym okiem wymaga lat treningu, a pomyłki mogą wpływać na jakość leków, decyzje rolnicze i działania na rzecz ochrony bioróżnorodności. W tym badaniu przedstawiono nowe ramy sztucznej inteligencji (AI), które potrafią rozpoznawać rośliny lecznicze na zwykłych zdjęciach, a nawet rozróżniać bardzo blisko spokrewnione odmiany krokusa na podstawie liści. Przyspieszając i zwiększając niezawodność identyfikacji roślin, praca ta wskazuje drogę do praktycznych narzędzi dla farmaceutów, rolników i konserwatorów przyrody.
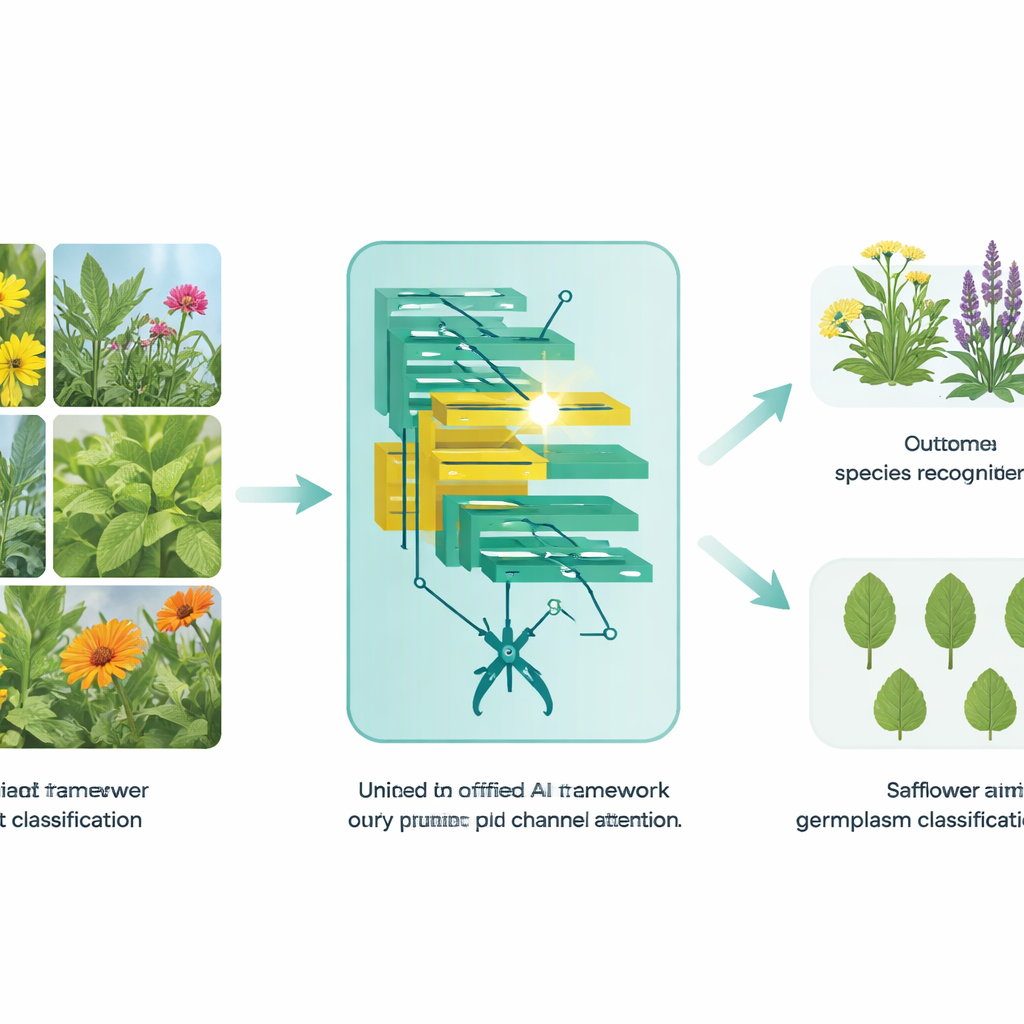
Od zdjęć liści do wiarygodnych odpowiedzi
Autorzy skupiają się na jednej z najtrudniejszych wersji rozpoznawania roślin: pracy bezpośrednio na obrazach liści. Zdjęcia terenowe roślin leczniczych zawierają bałagan w postaci gleby, cieni i innych roślin, a wiele gatunków ma niemal identyczne kształty i unerwienie. Tradycyjne metody widzenia komputerowego wymagały dużych, starannie przygotowanych zestawów danych i nadal miały problemy z taką zmiennością. W tej pracy badacze opierają się na nowoczesnej rodzinie modeli AI zwanych vision transformerami, które traktują obraz jako zbiór małych fragmentów i uczą się zależności między nimi. Celem jest zaprojektowanie jednego ramienia, które poradzi sobie zarówno z szerokim rozpoznawaniem gatunków w terenie, jak i z drobnymi rozróżnieniami między odmianami upraw w warunkach laboratoryjnych.
Bardziej zwinne i celne oko dla roślin leczniczych
Do ogólnego rozpoznawania roślin leczniczych zespół proponuje model nazwany EfficientSwinB-SE. Opiera się on na Swin Transformerze, popularnym vision transformerze analizującym pokrywające się okna obrazu, dzięki czemu uchwycone zostają zarówno lokalne detale, jak i większa scena. Pierwszą poprawą jest etap przycinania: model automatycznie usuwa najmniej użyteczne połączenia w swojej wstępnej warstwie przetwarzania obrazu, odchudzając obliczenia wewnętrzne bez zmiany ogólnej struktury. Drugą poprawą jest blok squeeze-and-excitation, który uczy model nadawać większą wagę niektórym kanałom wizualnym kosztem innych, podobnie jak botanik zwracający szczególną uwagę na unerwienie czy fakturę krawędzi, ignorując rozpraszające piksele tła.
Zbliżenie na różnice w rodzinie krokusa
Rozpoznawanie odmian w obrębie jednej uprawy jest jeszcze trudniejsze niż odróżnianie różnych gatunków, ponieważ różnice wizualne mogą być niezwykle subtelne. Aby temu sprostać, autorzy rozszerzają swoje ramy o drugi model nazwany OLSF-EfficientSwinB-SE, dopasowany do zasobów genowych krokusa — linii genetycznych wykorzystywanych w hodowli. W warunkach laboratoryjnych najpierw wzmacniają obrazy liści za pomocą procesu „Optimal Leaf Structure Feature”, który uwydatnia kierunki unerwienia i drobną teksturę. Te wzmocnione obrazy są następnie wprowadzane do tej samej przyciętej i uważnej architektury transformera. To połączenie pomaga AI skupić się na malutkich, lecz biologicznie istotnych wskazówkach strukturalnych, które odróżniają jedną linię krokusa od drugiej, wspierając precyzyjniejsze prace hodowlane i zarządzanie zasobami genowymi.
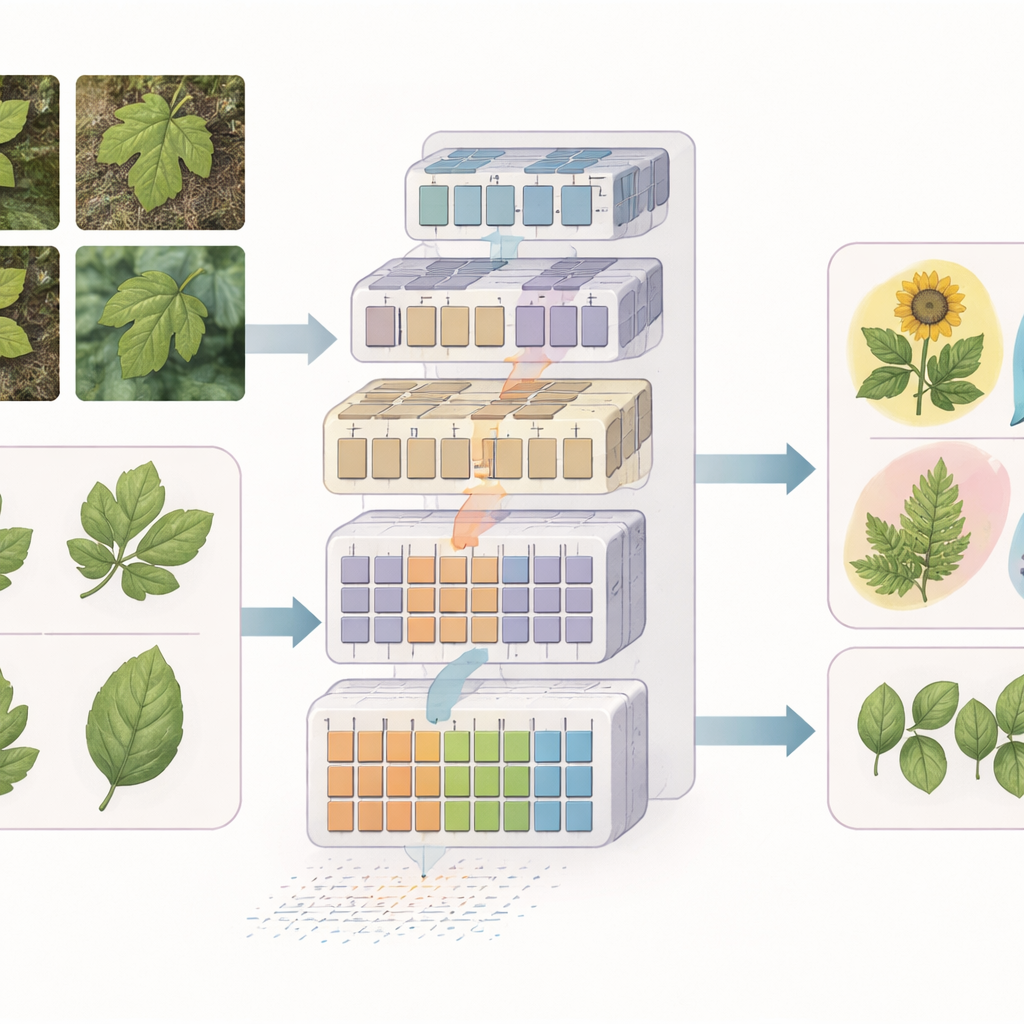
Testy nowego systemu
Badacze ocenili swoje modele na trzech publicznych zestawach danych: indyjskich roślinach leczniczych fotografowanych w ogrodach, indonezyjskich roślinach leczniczych pozyskanych z różnych źródeł internetowych oraz zbiorze krokusa zawierającym kilkadziesiąt odmian fotografowanych w kontrolowanych warunkach laboratoryjnych. W każdym przypadku EfficientSwinB-SE przewyższał znane modele głębokiego uczenia, w tym klasyczne sieci konwolucyjne i inne transformery. Osiągnął około 99,75% dokładności na zestawie indyjskim i 97,70% na indonezyjskim, nawet przy różnym oświetleniu i zanieczyszczonym tle. W zadaniu drobnego rozróżniania odmian krokusa wariant OLSF-EfficientSwinB-SE osiągnął około 91,63% dokładności, przewyższając wcześniejsze podejście oparte na transformerze zaprojektowane specjalnie dla tej uprawy.
Co to oznacza dla praktycznego wykorzystania roślin
Mówiąc prościej, badanie pokazuje, że możliwe jest zbudowanie jednego, wydajnego „oka” AI, które potrafi zarówno rozpoznawać szeroki wachlarz roślin leczniczych w terenie, jak i niezawodnie rozdzielać niemal identyczne liście w laboratorium. Poprzez usunięcie zbędnych obliczeń i nauczenie modelu podkreślania najbardziej informacyjnych cech wizualnych, autorzy stworzyli narzędzia dokładne, odporne i praktyczne do pracy w czasie zbliżonym do rzeczywistego. Takie systemy mogłyby zasilać aplikacje mobilne do identyfikacji ziół, automatyczne katalogowanie zasobów genowych oraz inteligentne platformy rolnicze śledzące uprawy po liściach. W miarę rozszerzania tych koncepcji na więcej gatunków i środowisk mogą one pomóc połączyć tradycyjną wiedzę o roślinach z nowoczesnym, opartym na danych rolnictwem.
Cytowanie: Khuat, P.T., Thien Van, H. A unified EfficientSwinB-based framework for medicinal plant recognition and safflower germplasm classification. Sci Rep 16, 11791 (2026). https://doi.org/10.1038/s41598-026-42449-4
Słowa kluczowe: rozpoznawanie roślin leczniczych, głębokie uczenie, vision transformer, zasoby genowe krokusa, identyfikacja roślin