Clear Sky Science · nl
Een verenigd EfficientSwinB-gebaseerd raamwerk voor herkenning van medicinale planten en classificatie van saffloer-germplasma
Waarom slimmer planten identificeren ertoe doet
Van keukenkruiden tot traditionele remedies: veel planten die onze gezondheid ondersteunen lijken verrassend op elkaar. Ze visueel onderscheiden vergt jaren training, en fouten kunnen de kwaliteit van geneesmiddelen, landbouwbeslissingen en inspanningen om biodiversiteit te beschermen beïnvloeden. Deze studie introduceert een nieuw kunstmatig-intelligentieraamwerk dat medicinale planten kan herkennen op gewone foto’s en zelfs nauw verwante saffloer-variëteiten kan onderscheiden aan de hand van hun bladeren. Door plantenidentificatie sneller en betrouwbaarder te maken, wijst het werk op praktische hulpmiddelen voor apothekers, boeren en natuurbeschermers.
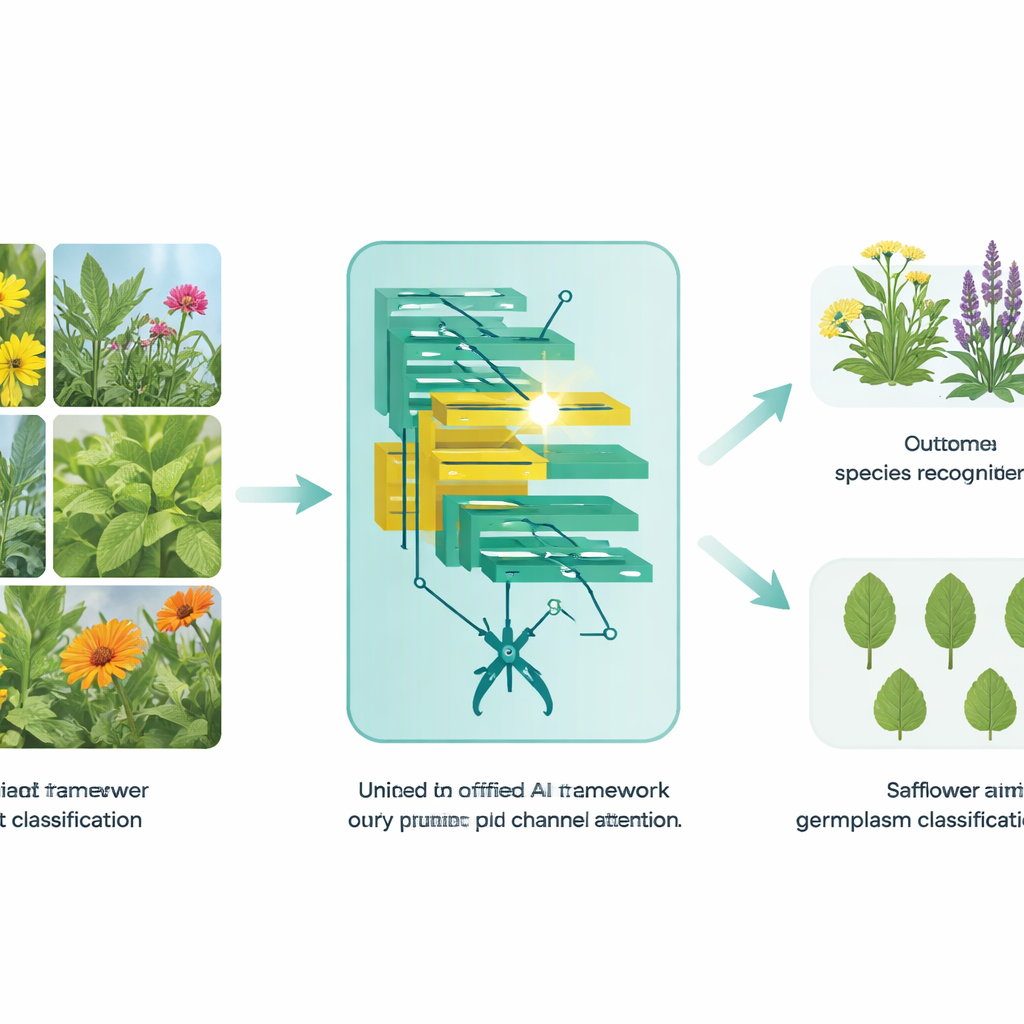
Van bladfoto’s naar betrouwbare antwoorden
De auteurs richten zich op een van de moeilijkste varianten van plantenherkenning: direct werken met bladbeelden. Buitenfoto’s van medicinale planten zijn vaak rommelig door aarde, schaduwen en andere planten, terwijl veel soorten bijna identieke vormen en nerfpatronen delen. Traditionele computer vision-methoden hadden grote, zorgvuldig samengestelde datasets nodig en hadden nog steeds moeite met zulke variatie. Hier bouwen de onderzoekers voort op een moderne familie van AI-modellen genaamd vision transformers, die een afbeelding behandelen als een verzameling kleine patches en leren hoe die stukjes zich tot elkaar verhouden. Hun doel is het ontwerpen van één enkel raamwerk dat zowel brede soortherkenning in het veld als fijne onderscheidingen tussen gewasvariëteiten in het laboratorium aankan.
Een slanker, scherper oog voor medicinale planten
Voor algemene herkenning van medicinale planten stelt het team een model voor dat EfficientSwinB-SE heet. Het vertrekt van de Swin Transformer, een populaire vision transformer die naar overlappende vensters van een afbeelding kijkt om zowel lokale details als de grotere scène vast te leggen. De eerste verbetering is een pruning-stap: het model verwijdert automatisch de minst nuttige verbindingen in zijn vroege beeldverwerkingslaag, waardoor de interne berekeningen worden versmald zonder de algehele structuur te veranderen. De tweede verbetering is een squeeze-and-excitation-blok, dat het model leert sommige visuele kanalen zwaarder te wegen dan andere — vergelijkbaar met een botanicus die extra let op nerfstructuur of randtextuur en storende achtergrondpixels negeert.
Inzoomen op verschillen binnen de saffloerfamilie
Het herkennen van variëteiten binnen één gewas is nog moeilijker dan het onderscheiden van verschillende soorten, omdat de visuele verschillen uiterst subtiel kunnen zijn. Om dit aan te pakken, breiden de auteurs hun raamwerk uit naar een tweede model genaamd OLSF-EfficientSwinB-SE, afgestemd op saffloer-germplasma — de genetische lijnen die in veredeling worden gebruikt. In een laboratoriumopstelling verbeteren ze eerst bladbeelden met een "Optimal Leaf Structure Feature"-proces dat nerfrichtingen en fijne textuur benadrukt. Deze verbeterde beelden worden vervolgens gevoed aan dezelfde geprunde en aandachtige transformer-backbone. Deze combinatie helpt de AI zich te richten op kleine maar biologisch betekenisvolle structurele aanwijzingen die de ene saffloer-lijn van de andere onderscheiden, wat preciezere veredeling en beheer van genetische hulpbronnen ondersteunt.
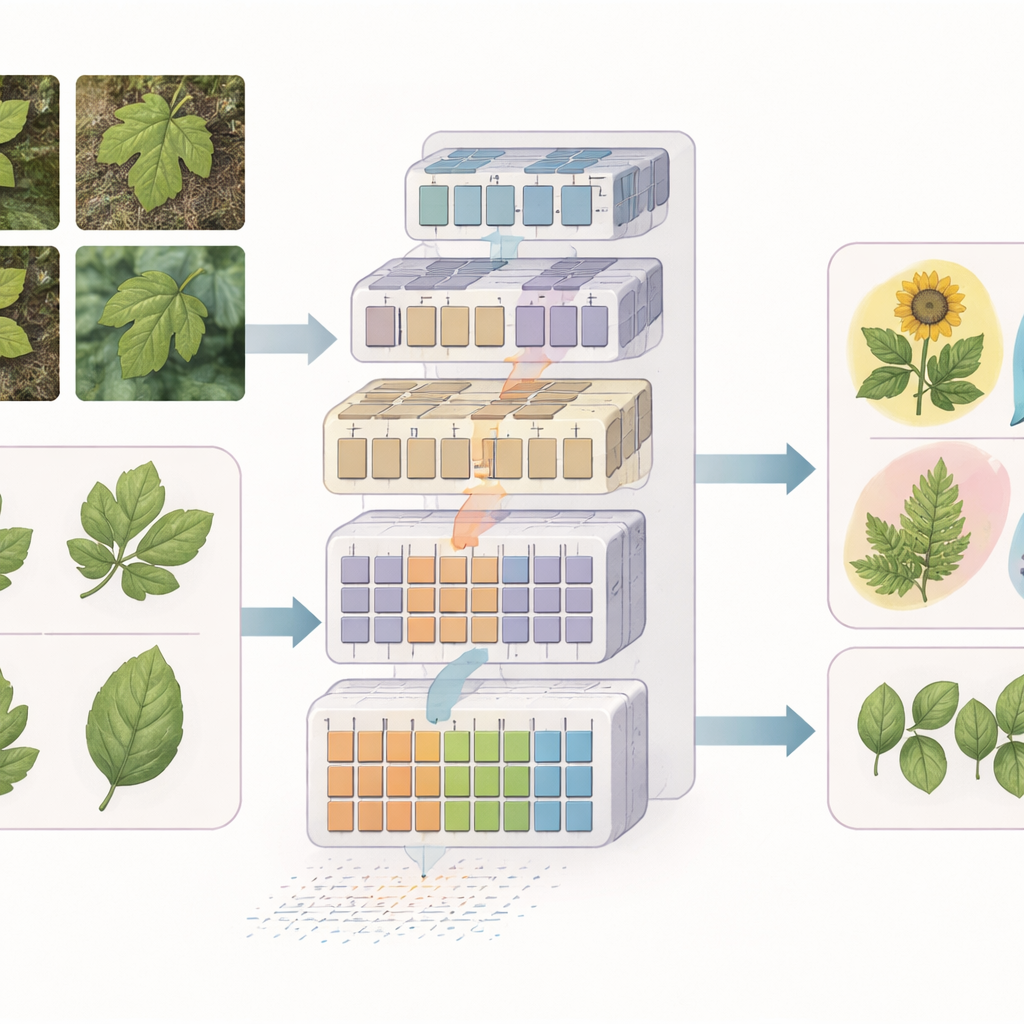
Het nieuwe raamwerk op de proef stellen
De onderzoekers evalueren hun modellen op drie openbare datasets: Indiase medicinale planten gefotografeerd in tuinen, Indonesische medicinale planten verzameld van diverse online bronnen, en een saffloer-dataset met tientallen variëteiten gefotografeerd onder gecontroleerde laboratoriumomstandigheden. Over de hele linie presteert EfficientSwinB-SE beter dan bekende deep learning-modellen, inclusief klassieke convolutionele netwerken en andere transformers. Het bereikt ongeveer 99,75% nauwkeurigheid op de Indiase dataset en 97,70% op de Indonesische dataset, zelfs bij gevarieerde belichting en rommelige achtergronden. Voor de fijnmazige saffloer-taak behaalt de OLSF-EfficientSwinB-SE-variant rond de 91,63% nauwkeurigheid en overtreft daarmee een eerdere transformer-gebaseerde aanpak die specifiek voor dit gewas was ontworpen.
Wat dit betekent voor praktisch plantgebruik
In praktische termen laat de studie zien dat het mogelijk is één efficiënt AI-“oog” te bouwen dat zowel een breed scala aan medicinale planten in het veld kan herkennen als vrijwel identieke bladeren in het laboratorium betrouwbaar kan sorteren. Door onnodige berekeningen weg te snijden en het model te leren de meest informatieve visuele aanwijzingen te benadrukken, creëren de auteurs tools die nauwkeurig, robuust en praktisch genoeg zijn voor bijna real-time gebruik. Dergelijke systemen kunnen de basis vormen voor smartphone-apps voor kruidherkenning, geautomatiseerde catalogisering van genetische hulpbronnen en intelligente landbouwplatforms die gewassen via hun bladeren volgen. Als dezelfde ideeën worden uitgebreid naar meer soorten en omgevingen, kunnen ze helpen traditionele plantenkennis en moderne datagedreven landbouw met elkaar te verbinden.
Bronvermelding: Khuat, P.T., Thien Van, H. A unified EfficientSwinB-based framework for medicinal plant recognition and safflower germplasm classification. Sci Rep 16, 11791 (2026). https://doi.org/10.1038/s41598-026-42449-4
Trefwoorden: herkenning van medicinale planten, deep learning, vision transformer, saffloer-germplasma, plantidentificatie