Clear Sky Science · nl
Chromosoom-schaal genoomassemblage van Wu’s rotsagama (Laudakia wui) uit laaggelegen habitats
Een hagedis in een dampige rivierkloof
Langs de diepe valleien van de Yarlung Zangbo-rivier in zuidoostelijk Xizang, China, leeft een rotsbewonende hagedis die bekendstaat als Wu’s rotsagama op zonbeschenen kliffen in een hete, vochtige regenwoudklimaat. Deze studie bouwt een gedetailleerd genetisch blauwdruk van een populatie die op ongebruikelijk lage hoogte leeft, waar temperatuur en vochtigheid meer lijken op tropische jungle dan op hoge berghellingen. Door het DNA van deze hagedis op geheel-chromosomaal niveau te ontcijferen, bieden de onderzoekers een venster in hoe reptielen zich aanpassen aan zeer verschillende omgevingen langs een steile bergkloof en leveren ze een krachtig nieuw hulpmiddel voor het behoud van een soort die nergens anders op aarde voorkomt.

Leven op hete rotsen
Wu’s rotsagama is een middelgrote hagedis met een plat, rotsaanliggend lichaam en een lange, stevige staart. Hij leeft uitsluitend in het stroomgebied van de Yarlung Zangbo-rivier en aangrenzende valleien en komt voor van ongeveer 550 meter tot meer dan 2.300 meter boven zeeniveau. Op lagere locaties zoals het district Mêdog wordt het klimaat bepaald door warme, vochtige lucht van de Indische Oceaan: de temperaturen blijven hoog, de neerslag is overvloedig en dichte moessonbossen bedekken de valleiwanden. Op hogere locaties zijn de omstandigheden koeler en droger. Deze scherpe verschuivingen over korte afstanden maken Wu’s rotsagama tot een uitstekend natuurlijk voorbeeld om te bestuderen hoe dieren zich aanpassen aan verschillende combinaties van hitte en vochtigheid, en hoe die aanpassingen in hun DNA zijn vastgelegd.
Het genoom lezen als een kaart
Om een nauwkeurig beeld te bouwen van het genetische profiel van de laaggelegen populatie verzamelde het team een gezonde volwassen vrouw uit Mêdog en extraheerde DNA uit meerdere weefsels. Ze gebruikten vervolgens een combinatie van state-of-the-art sequentiemethoden. De ene technologie leverde veel lange, zeer nauwkeurige DNA-stukken op, die bijzonder nuttig zijn om grote delen van het genoom aan elkaar te rijgen. Een andere leverde enorme hoeveelheden kortere fragmenten, handig om de nauwkeurigheid te controleren en de totale genoomgrootte te schatten. Een derde techniek, Hi-C genoemd, legde vast hoe DNA-stukken naast elkaar liggen in de celkern, wat de wetenschappers hielp lange DNA-stroken tot volledige chromosomen te rangschikken—vergelijkbaar met het gebruiken van de vouwen van een verfrommelde kaart om de oorspronkelijke indeling te herstellen.
Van fragmenten naar volledige chromosomen
Door al deze gegevens zorgvuldig samen te stellen en te kruiscontroleren produceerden de onderzoekers een genoom van ongeveer 1,77 miljard DNA-“letters”, georganiseerd in 18 chromosomen. Zes daarvan zijn grote, zogenaamde macrochromosomen, en twaalf zijn kleinere microchromosomen. Geautomatiseerde computertools scanden vervolgens dit DNA-landschap om stroken te identificeren die als genen fungeren, en voorspelden in totaal 19.725 eiwitcoderende genen. De meeste van deze genen konden aan bekende functies worden gekoppeld door ze te matchen met grote openbare databanken, en standaard kwaliteitscontroles toonden aan dat de assemblage het overgrote deel van belangrijke gewervelde-genen vastlegt met zeer weinig hiaten of fouten. Herhaalde DNA-segmenten zoals transposabele elementen werden ook gecatalogiseerd, waaruit bleek dat ze ongeveer twee vijfde van het genoom uitmaken.
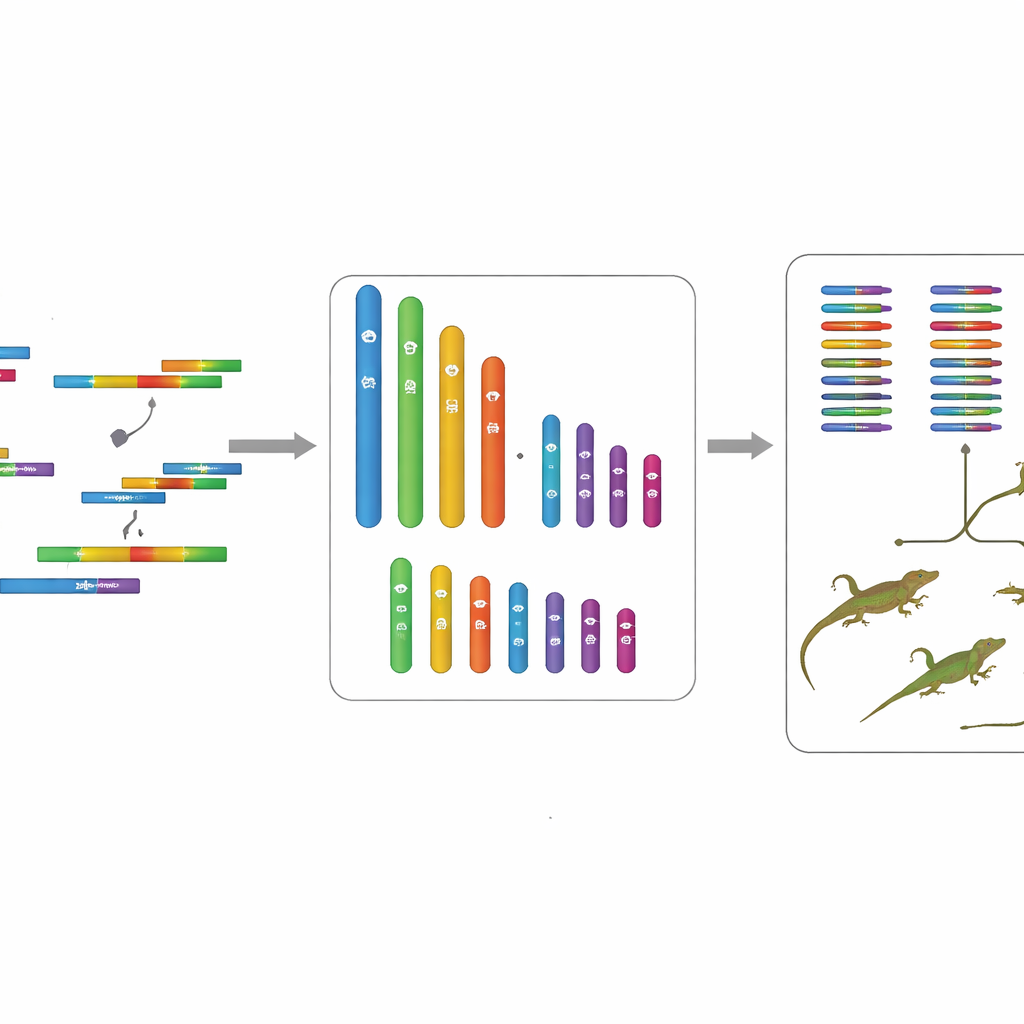
Bergburen, genetische neven
Aangezien een eerdere studie al het genoom van een hooggelegen populatie van Wu’s rotsagama had ontcijferd, kon het team de twee vergelijken. De grootste chromosomen kwamen netjes overeen tussen de laag- en hooggelegen genomen, wat suggereert dat de algemene structuur van de genetische “boekenplanken” van de soort vrij stabiel is. De kleinere chromosomen vertoonden daarentegen meer verschillen, wat erop wijst dat zij hotspots voor verandering kunnen zijn terwijl de soort zich aan verschillende hoogtes aanpast. Door beide populaties ook te vergelijken met verschillende verwante hagedissoorten schatten de onderzoekers dat de hoog- en laaggelegen lijnages ongeveer 4,8 miljoen jaar geleden zijn gesplitst, waardoor ruim de tijd is geweest voor subtiele genetische verschillen om zich op te bouwen als reactie op hun verschillende klimaten.
Waarom dit genoom er toe doet
Het nieuwe chromosoom-schaal genoom voor de laaggelegen Wu’s rotsagama is geen medische doorbraak of nieuw snufje, maar een zorgvuldig samengesteld referentiewerk. Het geeft wetenschappers een gedetailleerd, betrouwbaar kader om te achterhalen welke genen en DNA-veranderingen reptielen helpen omgaan met intense hitte en vochtigheid in tropische valleien, in tegenstelling tot koelere, drogere hellingen hogerop. Even belangrijk biedt het natuurbeheerders een moleculair dossier van een unieke populatie die in een ecologisch cruciaal rivierbekken leeft, waardoor beter onderbouwde inspanningen mogelijk worden om zowel de hagedis als het rijke web van leven dat zijn steile, dampige habitat deelt te beschermen.
Bronvermelding: Tan, S., Wang, Y., Chen, Y. et al. A chromosome-scale genome assembly of Wu’s rock agama (Laudakia wui) from low-altitude habitats. Sci Data 13, 501 (2026). https://doi.org/10.1038/s41597-026-06845-9
Trefwoorden: genoomassemblage, hagedisaanpassing, tropische bergta vendalen, chromosoomevolutie, biodiversiteitsbehoud