Clear Sky Science · it
Una sequenza del genoma a scala cromosomica dell’agama di Wu (Laudakia wui) da habitat a bassa quota
Una lucertola in una valle fluviale umida
Lungo le profonde valli del fiume Yarlung Zangbo nel sud-est del Xizang, Cina, un’agama che vive sulle rocce, nota come agama di Wu, abita le scogliere assolate in un clima di foresta pluviale caldo e umido. Questo studio costruisce una dettagliata mappa genetica di una popolazione che vive a un’altitudine insolitamente bassa, dove temperatura e umidità assomigliano più a quelle delle giungle tropicali che ai pendii montani elevati. Decodificando il DNA di questa lucertola a livello cromosomico, i ricercatori aprono una finestra su come i rettili si adattano a ambienti molto diversi lungo una ripida valle montana e forniscono un nuovo strumento potente per conservare una specie che non si trova in nessun altro luogo sulla Terra.

Vita su rocce roventi
L’agama di Wu è una lucertola di taglia media con corpo appiattito che aderisce alle rocce e una coda lunga e robusta. Vive solo nel bacino del fiume Yarlung Zangbo e nelle valli vicine, estendendosi da circa 550 metri fino a oltre 2.300 metri sul livello del mare. Nei siti più bassi, come la contea di Mêdog, il clima è plasmato dall’aria calda e umida proveniente dall’Oceano Indiano: le temperature rimangono elevate, le precipitazioni sono abbondanti e pareti vallive ricoperte da foresta monsonica sono comuni. Nei siti più alti le condizioni sono più fresche e più secche. Questi bruschi cambiamenti su brevi distanze rendono l’agama di Wu un eccellente esempio naturale per studiare come gli animali si adattano a diverse combinazioni di calore e umidità e come tali adattamenti siano scritti nel loro DNA.
Leggere il genoma come una mappa
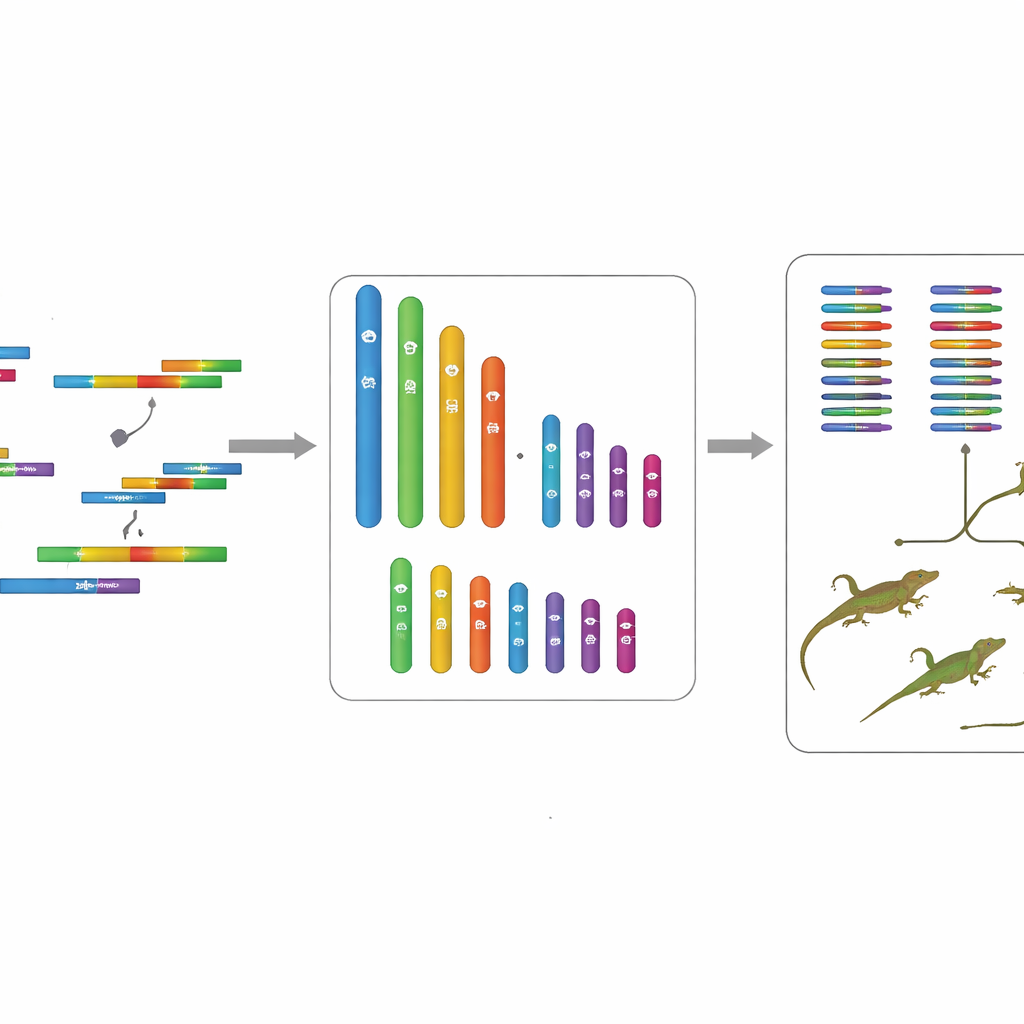
Per costruire un quadro preciso della composizione genetica della popolazione a bassa quota, il gruppo ha raccolto una femmina adulta in buona salute a Mêdog ed estratto il DNA da diversi tessuti. Hanno poi usato una combinazione di metodi di sequenziamento all’avanguardia. Una tecnologia ha prodotto molte sequenze di DNA lunghe e altamente accurate, particolarmente utili per cucire insieme grandi porzioni del genoma. Un’altra ha generato un enorme numero di frammenti più corti, utili per verificare l’accuratezza e stimare la dimensione complessiva del genoma. Una terza tecnica, chiamata Hi-C, ha catturato come i segmenti di DNA si dispongono l’uno vicino all’altro nel nucleo cellulare, aiutando gli scienziati ad ordinare le lunghe sequenze di DNA in cromosomi completi—proprio come usare le pieghe di una mappa spiegazzata per ricostruirne il layout originale.
Da frammenti a cromosomi completi
Assemblando e controllando accuratamente tutti questi dati, i ricercatori hanno prodotto un genoma di circa 1,77 miliardi di “lettere” di DNA, organizzato in 18 cromosomi. Sei di questi sono grandi, i cosiddetti macrocromosomi, e dodici sono più piccoli, i microcromosomi. Strumenti informatici automatici hanno quindi scandagliato questo paesaggio di DNA per identificare regioni che funzionano da geni, prevedendo in totale 19.725 geni codificanti proteine. La maggior parte di questi geni è stata collegata a funzioni note mediante il confronto con grandi banche dati pubbliche, e controlli di qualità standard hanno mostrato che l’assemblaggio cattura la gran parte dei geni vertebrati importanti con pochissime lacune o errori. Sono stati inoltre catalogati segmenti ripetuti di DNA, come elementi genetici mobili, rivelando che costituiscono circa due quinti del genoma.
Vicini di montagna, cugini genetici
Poiché uno studio precedente aveva già decodificato il genoma di una popolazione di agama di Wu ad alta quota, il team ha potuto confrontare i due. I cromosomi più grandi si sono allineati nettamente tra i genomi a bassa e ad alta quota, suggerendo che la struttura complessiva degli “scaffali” genetici della specie è piuttosto stabile. Al contrario, i cromosomi più piccoli hanno mostrato maggiori differenze, lasciando intendere che possano essere punti caldi per il cambiamento mentre la specie si adatta a diverse altitudini. Confrontando inoltre entrambe le popolazioni con diverse specie di lucertole imparentate, i ricercatori hanno stimato che le linee ad alta e bassa quota si sono separate circa 4,8 milioni di anni fa, lasciando ampio tempo perché si accumulassero sottili differenze genetiche in risposta ai loro climi distinti.
Perché questo genoma è importante
Il nuovo genoma a scala cromosomica per l’agama di Wu a bassa quota non è una scoperta medica né un nuovo gadget, ma un’opera di riferimento accuratamente realizzata. Fornisce agli scienziati un quadro dettagliato e affidabile per individuare quali geni e quali cambiamenti nel DNA aiutano i rettili ad affrontare calore intenso e umidità nelle valli tropicali, rispetto ai pendii più freschi e secchi in quota. Altrettanto importante, offre ai pianificatori della conservazione un registro molecolare di una popolazione unica che vive in un bacino fluviale ecologicamente critico, sostenendo sforzi più informati per proteggere sia la lucertola sia la ricca rete di vita che condivide il suo habitat ripido e umido.
Citazione: Tan, S., Wang, Y., Chen, Y. et al. A chromosome-scale genome assembly of Wu’s rock agama (Laudakia wui) from low-altitude habitats. Sci Data 13, 501 (2026). https://doi.org/10.1038/s41597-026-06845-9
Parole chiave: assemblaggio del genoma, adattamento delle lucertole, valli montane tropicali, evoluzione dei cromosomi, conservazione della biodiversità