Clear Sky Science · de
Eine genombasierte Chromosomen-Assembly der Wus Felsenagame (Laudakia wui) aus Tieflandhabitaten
Eine Eidechse im schwülen Flusstal
Entlang der tiefen Täler des Yarlung-Zangbo-Flusses im Südosten Xizangs, China, lebt auf sonnenbeschienenen Felsen eine eidechsenbewohnende Art, die als Wus Felsenagame bekannt ist, in einem heißen, feuchten Regenwaldklima. Diese Studie erstellt einen detaillierten genetischen Bauplan einer Population, die ungewöhnlich niedrig lebt, wo Temperatur und Feuchtigkeit eher tropischen Dschungeln als hohen Berghängen gleichen. Durch das Entschlüsseln der DNA dieser Eidechse auf Chromosomenebene öffnen die Forschenden ein Fenster dafür, wie Reptilien sich entlang eines steilen Bergtals an sehr unterschiedliche Umgebungen anpassen, und liefern ein leistungsfähiges neues Werkzeug zum Schutz einer nur an diesem Ort vorkommenden Art.

Leben auf heißen Felsen
Wus Felsenagame ist eine mittelgroße Eidechse mit flachem, felsanliegendem Körper und langem, kräftigem Schwanz. Sie kommt ausschließlich im Einzugsgebiet des Yarlung-Zangbo-Flusses und in benachbarten Tälern vor und reicht in der Verbreitung von etwa 550 bis über 2.300 Meter über dem Meeresspiegel. An tieferen Standorten wie dem Kreis Mêdog wird das Klima vom warmen, feuchten Luftstrom aus dem Indischen Ozean geprägt: Die Temperaturen bleiben hoch, Niederschläge sind reichlich und dichte Monsunwälder bedecken die Talwände. In höheren Lagen sind die Bedingungen kühler und trockener. Diese scharfen Veränderungen über kurze Distanzen machen Wus Felsenagame zu einem hervorragenden natürlichen Modell, um zu untersuchen, wie Tiere auf unterschiedliche Kombinationen von Hitze und Feuchtigkeit reagieren und wie diese Anpassungen im Erbgut festgehalten sind.
Das Genom wie eine Karte lesen
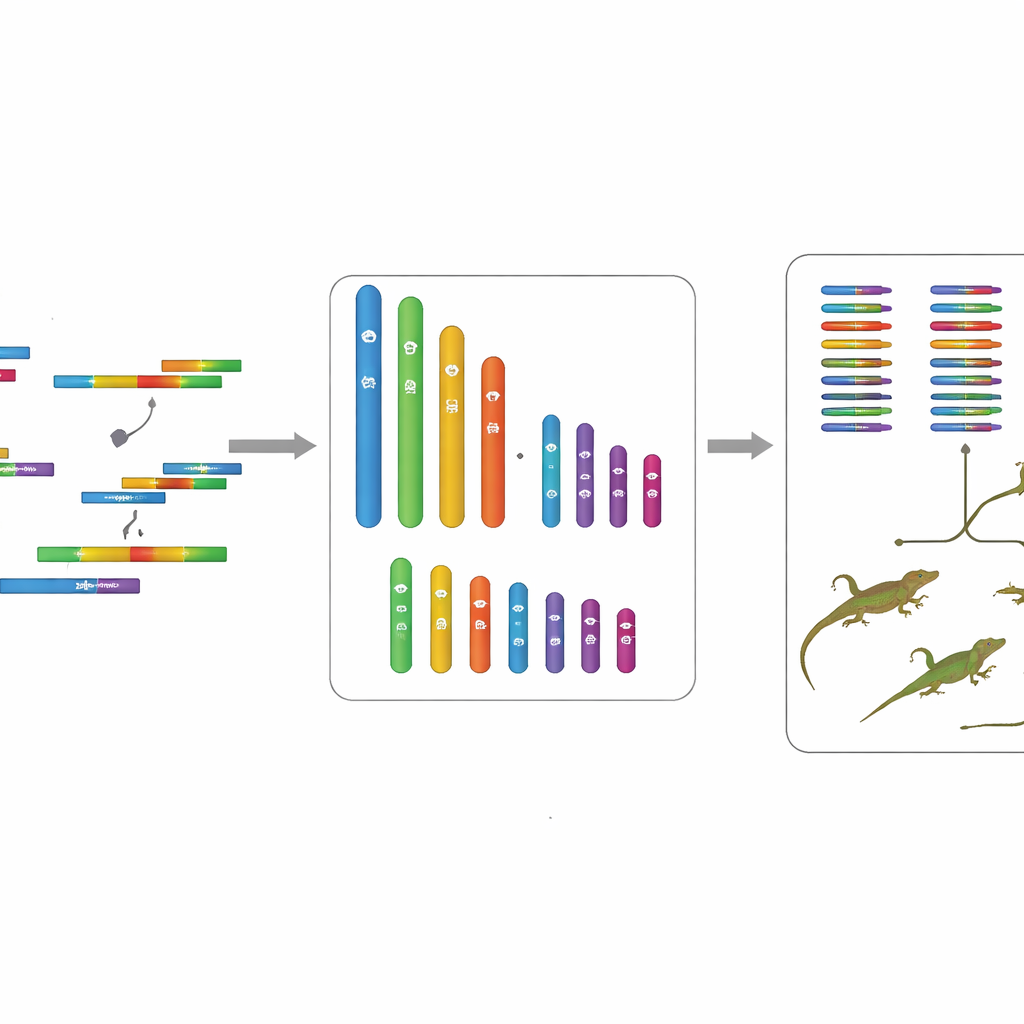
Um ein präzises Bild der genetischen Zusammensetzung der Tieflandpopulation zu erstellen, sammelte das Team eine gesunde adulten weiblichen Individuum aus Mêdog und isolierte DNA aus mehreren Geweben. Anschließend nutzten sie eine Kombination moderner Sequenzierverfahren. Eine Technologie lieferte viele lange, sehr genaue DNA-Abschnitte, die besonders nützlich sind, um große Genomteile zusammenzunähen. Eine andere erzeugte enorme Mengen kürzerer Fragmente, hilfreich zur Überprüfung der Genauigkeit und zur Abschätzung der Gesamtgenomgröße. Eine dritte Technik, Hi-C genannt, erfasste, wie DNA-Abschnitte im Zellkern nebeneinanderliegen, und half den Wissenschaftlern dabei, lange DNA-Stränge zu vollständigen Chromosomen anzuordnen – ähnlich wie man die Falten einer zerknitterten Karte nutzt, um ihr ursprüngliches Layout wiederherzustellen.
Von Fragmenten zu vollständigen Chromosomen
Durch sorgfältiges Zusammenfügen und Abgleichen all dieser Daten erzeugten die Forschenden ein Genom von etwa 1,77 Milliarden DNA-„Buchstaben“, organisiert auf 18 Chromosomen. Sechs davon sind große sogenannte Makrochromosomen, zwölf sind kleinere Mikrochromosomen. Automatisierte Computerwerkzeuge durchsuchten anschließend diese DNA-Landschaft, um Bereiche zu identifizieren, die als Gene fungieren, und sagten insgesamt 19.725 proteinkodierende Gene voraus. Die meisten dieser Gene konnten durch Abgleich mit großen öffentlichen Datenbanken bekannten Funktionen zugeordnet werden, und gängige Qualitätskontrollen zeigten, dass die Assembly den weitaus größten Teil wichtiger Wirbeltiergene mit nur sehr wenigen Lücken oder Fehlern erfasst. Wiederholte DNA-Abschnitte wie springende genetische Elemente wurden ebenfalls katalogisiert und machen schätzungsweise rund zwei Fünftel des Genoms aus.
Bergnachbarn, genetische Cousins
Da eine frühere Studie bereits das Genom einer hochalpinen Population von Wus Felsenagame entschlüsselt hatte, konnte das Team beide vergleichen. Die größten Chromosomen stimmten zwischen den Tiefland- und Hochlandgenomen gut überein, was darauf hindeutet, dass die Gesamtstruktur der genetischen „Bücherregale“ der Art relativ stabil ist. Im Gegensatz dazu zeigten die kleineren Chromosomen mehr Unterschiede, was vermuten lässt, dass sie mögliche Hotspots für Veränderungen sind, während die Art sich an verschiedene Höhenlagen anpasst. Durch den Vergleich beider Populationen mit mehreren verwandten Eidechsenarten schätzten die Forschenden, dass sich die Hochland- und Tieflandlinien vor etwa 4,8 Millionen Jahren getrennt haben, was reichlich Zeit ließ, damit sich feine genetische Unterschiede als Reaktion auf ihre unterschiedlichen Klimata herausbilden konnten.
Warum dieses Genom wichtig ist
Das neue Chromosomen-unterstützte Genom der Tieflandpopulation von Wus Felsenagame ist weder ein medizinischer Durchbruch noch ein neues Gadget, sondern ein sorgfältig erarbeitetes Referenzwerk. Es bietet Forschenden ein detailliertes, verlässliches Gerüst, um zu entschlüsseln, welche Gene und DNA-Veränderungen Reptilien helfen, mit intensiver Hitze und Feuchte in tropischen Tälern umzugehen, im Gegensatz zu kühleren, trockeneren Hängen weiter oben. Ebenso wichtig ist, dass es Naturschutzplanern eine molekulare Dokumentation einer einzigartigen Population in einem ökologisch kritischen Flussbecken liefert und damit fundierte Maßnahmen unterstützt, sowohl die Eidechse als auch das reiche Gefüge des Lebens zu schützen, das ihr steiles, schwüles Habitat teilt.
Zitation: Tan, S., Wang, Y., Chen, Y. et al. A chromosome-scale genome assembly of Wu’s rock agama (Laudakia wui) from low-altitude habitats. Sci Data 13, 501 (2026). https://doi.org/10.1038/s41597-026-06845-9
Schlüsselwörter: Genom-Assembly, Eidechsenanpassung, tropische Bergtäler, Chromosomenentwicklung, Artenschutz und Biodiversität