Clear Sky Science · it
UTR-DynaPro: un modello multimodale CNN–transformer per decodificare i meccanismi regolatori della 5′UTR
Come la parte anteriore dell'RNA plasma la vita e la medicina
Le istruzioni per costruire le proteine nelle nostre cellule sono scritte in filamenti di RNA messaggero, ma non ogni porzione di quel filamento viene tradotta in proteina. Un tratto all'inizio, chiamato regione non tradotta 5′ (5′UTR), funziona più come una manopola di controllo che come un progetto dettagliato. Piccole variazioni lì possono modificare drasticamente la quantità di proteina prodotta, influenzando tutto, da quanto efficacemente funziona un vaccino a se una terapia genica fornisce una quantità sufficiente di una proteina terapeutica. Questo articolo presenta un nuovo modello di intelligenza artificiale, UTR-DynaPro, progettato per leggere e interpretare quella manopola di controllo con maggiore precisione rispetto ai metodi precedenti.
La zona di controllo silenziosa prima del codice
Prima che inizi la parte codificante di una mRNA, la 5′UTR aiuta a decidere quanto efficientemente verrà prodotta la proteina. La sua sequenza e la sua struttura influenzano se le macchine cellulari che sintetizzano le proteine, i ribosomi, riescono ad agganciarsi, scorrere lungo il filamento e avviare il lavoro senza intoppi. Caratteristiche come la lunghezza della regione, l'equilibrio delle basi A, U, G e C e la presenza di piccoli segnali di inizio a monte possono accelerare o rallentare il processo. Questi effetti sono rilevanti in contesti pratici: nei vaccini a mRNA, per esempio, una 5′UTR ben ottimizzata può significare una risposta immunitaria più forte con dosi minori; nelle malattie genetiche, una variazione disturbante in questa regione può ridurre drasticamente la produzione proteica anche quando il codice genico principale è intatto.
Perché gli strumenti predittivi tradizionali non bastano
I ricercatori si sono rivolti al deep learning per prevedere come si comporterà una data 5′UTR, con l'obiettivo di progettare sequenze che producano la quantità di proteina desiderata. I modelli precedenti, tuttavia, tendono a concentrarsi o su pattern molto brevi e locali o su relazioni ampie e a lungo raggio, ma non su entrambi contemporaneamente. Alcuni fanno fatica ad adattarsi quando cambiano le condizioni sperimentali fra tipi cellulari o protocolli di laboratorio diversi, e molti ignorano informazioni laterali importanti come l'energia di ripiegamento dell'RNA o la lunghezza della regione codificante. Di conseguenza, la loro accuratezza si è assestata, limitando la nostra capacità di progettare sistematicamente 5′UTR per vaccini, terapie geniche e produzione industriale di proteine.
Un lettore a due percorsi per i segnali dell'RNA
UTR-DynaPro colma queste lacune combinando due modalità complementari di lettura della 5′UTR. Un percorso, basato su reti convoluzionali, è sintonizzato per individuare pattern brevi e locali—analoghi a “parole” ricorrenti nell'RNA che funzionano come interruttori on–off. L'altro percorso, costruito con strati transformer, eccelle nel cogliere interazioni a lunga distanza, come il modo in cui parti distanti del filamento si ripiegano insieme o si coordinano con la regione codificante che segue. Una “porta” dinamica decide poi, posizione per posizione lungo l'RNA, quanto peso assegnare alle informazioni locali rispetto a quelle globali. Inoltre, il modello integra segnali aggiuntivi, inclusa la tendenza dell'RNA al ripiegamento, la lunghezza del segmento codificante e la presenza di eventuali piccoli frame di lettura a monte. Insieme, questi ingredienti consentono a UTR-DynaPro di costruire un ritratto ricco di come una 5′UTR è probabile che regoli la produzione proteica.
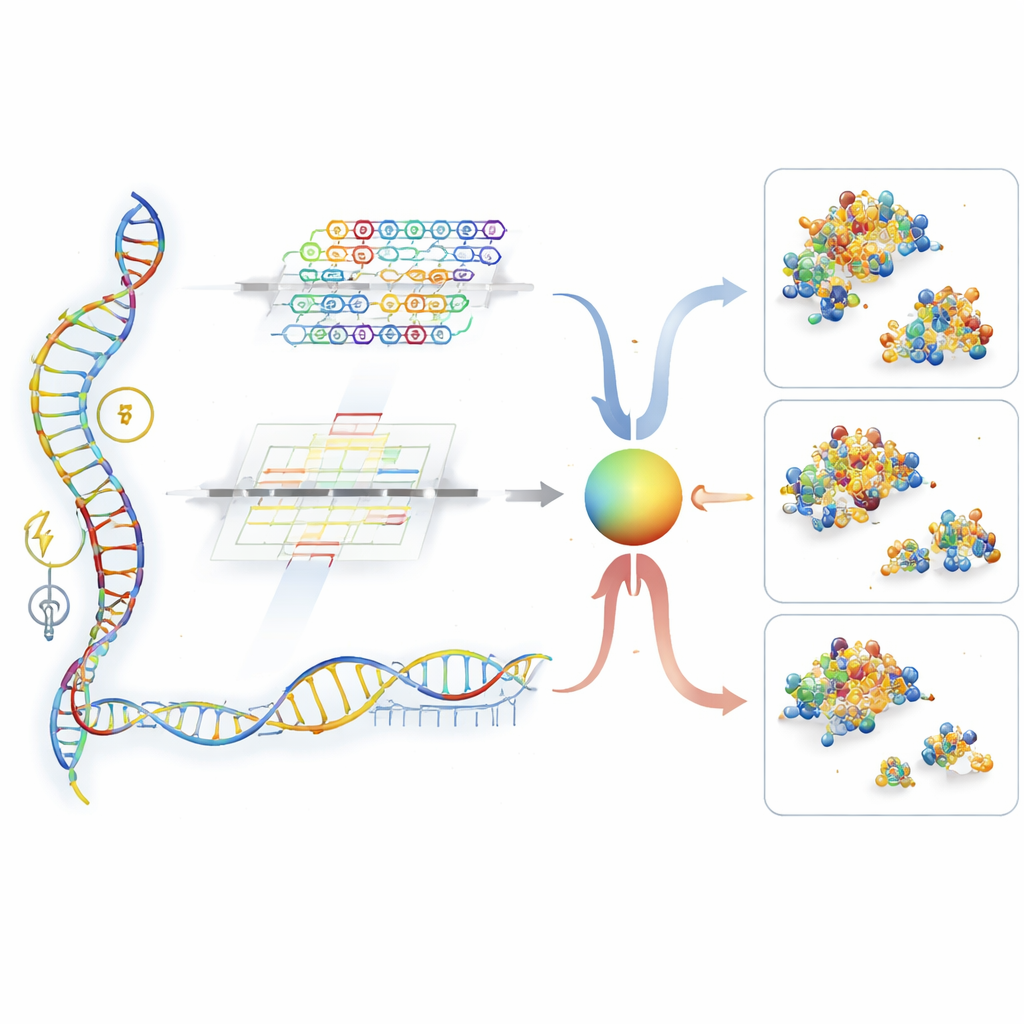
Mettere il modello alla prova
Gli autori hanno addestrato e valutato UTR-DynaPro su dataset ampi e diversificati: 5′UTR sintetiche e naturali provenienti da esseri umani e altre specie, e misurazioni ottenute in diversi tipi cellulari e tessuti umani. Si sono concentrati su tre esiti correlati: carico medio di ribosomi (quanti ribosomi si accumulano su un mRNA in media), efficienza di traduzione (quanta proteina viene prodotta per singola molecola di RNA) e livello di espressione complessivo. In tutti questi compiti, il nuovo modello ha superato costantemente diverse delle metodiche di riferimento, talvolta riducendo l'errore predittivo di quasi il dieci percento. Test di “ablazione” accurati—rimuovendo o semplificando parti dell'architettura—hanno mostrato che ogni componente principale, dal design a doppio percorso ai sotto-moduli mixture-of-experts e agli input sulle condizioni sperimentali, migliorava misurabilmente le prestazioni. La visualizzazione della porta di fusione ha inoltre rivelato che il modello sposta la sua dipendenza tra indizi locali e globali lungo la sequenza e tra tipi cellulari, rispecchiando la logica biologica complessa che gli scienziati si attendono in questa regione.
Da previsioni migliori a progettazioni migliori
Per i non specialisti, il messaggio chiave è che questo lavoro offre un modo più potente e flessibile di leggere le istruzioni di controllo sottili all'inizio di un mRNA. Prevedendo con maggiore accuratezza come una modifica della 5′UTR influenzerà la produzione proteica, UTR-DynaPro può guidare la progettazione di sequenze sintetiche che aumentino o modulino la produzione per esigenze specifiche—vaccini più efficaci, terapie geniche più sicure o enzimi industriali migliori. Allo stesso tempo, la sua architettura interpretabile aiuta i ricercatori a scoprire pattern regolatori noti e precedentemente nascosti. In termini pratici, questo modello ci avvicina al considerare la 5′UTR come una manopola programmabile per l'espressione genica che può essere regolata con fiducia anziché con tentativi ed errori.
Citazione: Shen, H., Liu, S., Guo, F. et al. UTR-DynaPro: a CNN–transformer multimodal language model for decoding 5′UTR regulatory mechanisms. Sci Rep 16, 10779 (2026). https://doi.org/10.1038/s41598-026-42175-x
Parole chiave: regolazione della 5′UTR, traduzione dell'mRNA, deep learning per la biologia, controllo dell'espressione genica, progettazione di vaccini a mRNA