Clear Sky Science · it
Un’assemblaggio genomico telomero‑a‑telomero di Castanopsis orthacantha (Fagaceae)
Un albero che tiene insieme la foresta
In alto, sulle montagne sempreverdi del sud‑ovest della Cina, cresce un albero robusto il cui legno costruisce case, i cui frutti nutrono le persone e le cui radici aiutano a tenere saldi interi versanti. Questo albero, Castanopsis orthacantha, è un pilastro silenzioso della vita locale e delle foreste che attenuano le piene, immagazzinano carbonio e ospitano innumerevoli altre specie. Lo studio qui descritto fornisce qualcosa di invisibile ma potente per questa specie chiave: una lettura quasi completa, da un estremo all’altro, del suo progetto genetico, aprendo nuove strade per comprendere e proteggere queste foreste in un mondo che si sta riscaldando.

Perché questo albero di montagna è importante
Castanopsis orthacantha appartiene alla famiglia delle faggiole‑querce ed è particolarmente abbondante nelle foreste sempreverdi subtropicali dell’altopiano dello Yunnan. Prospera tra i 1.700 e i 2.500 metri sul livello del mare, dove i ripidi pendii e il clima variabile rendono cruciale la stabilità delle foreste. Il suo legno denso e resistente alla putrefazione è apprezzato per l’edilizia e i mobili, e i suoi frutti da sempre aiutano le comunità locali a superare i periodi di scarsità. Dal punto di vista ecologico è una specie «fondamentale»: dove prospera, i suoli restano al loro posto, l’acqua scorre più dolcemente e molte altre piante e animali possono fiorire intorno a essa.
Leggere l’intero progetto genetico dell’albero
Il gruppo di ricerca si è prefissato di assemblare il genoma dell’albero da un estremo all’altro di ciascun cromosoma — un livello di completezza che fino a poco tempo fa era possibile solo per poche specie. Hanno raccolto foglie fresche, fiori e germogli da un albero maturo sul monte Maxiong nello Yunnan. Da questi tessuti hanno estratto sia il DNA, che porta le istruzioni genetiche a lungo termine, sia l’RNA, che riflette quali geni sono attivi in diverse parti della pianta. Queste molecole sono diventate la materia prima per una serie di tecniche avanzate di sequenziamento e mappatura.
Molti punti di vista sullo stesso genoma
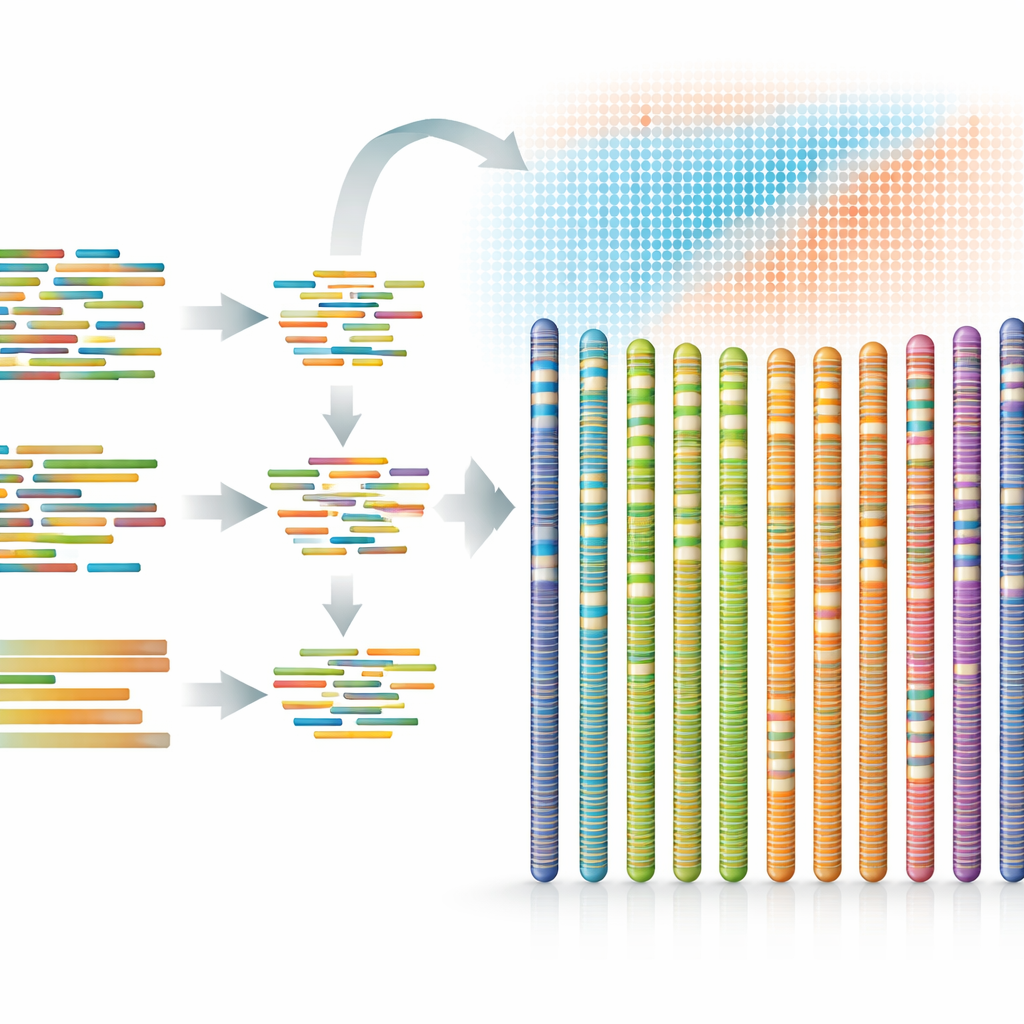
Invece di affidarsi a una sola tecnologia, gli scienziati ne hanno combinate diverse, ognuna con i propri punti di forza. Piccoli frammenti di DNA altamente accurati sono stati prodotti da una piattaforma per fornire una visione pulita e dettagliata. Un’altra piattaforma ha generato letture lunghe ad alta fedeltà capaci di collegare tratti ripetuti o difficili del DNA. Una terza ha fornito frammenti ultra‑lunghi che attraversano regioni particolarmente contorte. Infine, una tecnica che misura come i pezzi di DNA si trovano l’uno rispetto all’altro all’interno dei cromosomi reali ha aiutato il team a ordinare e orientare i frammenti assemblati lungo 12 “pseudomolecole” corrispondenti alla lunghezza dei cromosomi. Questa strategia stratificata ha prodotto un genoma di circa 893 milioni di basi, con quasi tutto assegnato ordinatamente ai cromosomi e con un’unica piccola lacuna rimanente.
Cosa contiene questo genoma
Una volta definito l’impalcatura genetica, i ricercatori hanno proceduto a etichettarne i contenuti. Hanno scoperto che quasi tre quinti del genoma sono costituiti da elementi ripetuti, sequenze mobili o duplicate che riempiono gran parte del DNA vegetale e spesso confondono i metodi di sequenziamento più datati. Su questo sfondo hanno identificato 35.978 geni codificanti proteine, ciascuno potenzialmente istruttivo per costruire una parte dell’organismo o dei suoi sistemi di risposta. Confrontando questi geni con quelli di specie affini e con grandi banche dati pubbliche, hanno potuto assegnare ruoli probabili a quasi tutti e localizzarne la posizione lungo i cromosomi. Hanno inoltre catalogato migliaia di piccole molecole di RNA che contribuiscono a regolare finemente come e quando i geni vengono attivati.
Un nuovo kit per il futuro delle foreste
Per garantire che questo genoma possa essere considerato un riferimento affidabile, il team ha verificato quanto bene le letture di DNA originali si riallineassero all’assemblaggio e quanti geni vegetali ampiamente conservati contenesse; l’assemblaggio ha superato questi test con ottimi risultati. Per gli scienziati, questo significa una base affidabile per studiare tutto, dalla storia evolutiva dell’albero a come affronta freddo, siccità o parassiti. Per i pianificatori della conservazione e i gestori forestali, crea uno strumento potente per monitorare la diversità genetica, guidare i rimboschimenti e selezionare alberi più adatti ai climi futuri. In sostanza, lo studio trasforma un tempo misterioso albero di montagna in un alleato ben mappato geneticamente negli sforzi per mantenere sane e resilienti le foreste subtropicali della Cina.
Citazione: Yin, S., Wang, H., Chu, H. et al. A telomere-to-telomere genome assembly of Castanopsis orthacantha (Fagaceae). Sci Data 13, 450 (2026). https://doi.org/10.1038/s41597-026-06787-2
Parole chiave: genomica forestale, alberi subtropicali, assemblaggio del genoma, resilienza degli ecosistemi, genetica della conservazione