Clear Sky Science · es
Ensamblaje del genoma de extremo a extremo de Castanopsis orthacantha (Fagaceae)
Un árbol que mantiene unido al bosque
En lo alto de las montañas perennifolias del suroeste de China crece un árbol robusto cuya madera construye viviendas, cuyos frutos alimentan a la gente y cuyas raíces ayudan a sostener laderas enteras. Este árbol, Castanopsis orthacantha, es un pilar silencioso de la vida local y de los bosques que atenúan las inundaciones, almacenan carbono y albergan a innumerables otras especies. El estudio descrito aquí ofrece algo invisible pero potente para este taxón clave: una lectura casi completa, de extremo a extremo, de su plano genético, que abre nuevas vías para comprender y proteger estos bosques en un mundo que se calienta.

Por qué importa este árbol de montaña
Castanopsis orthacantha forma parte de la familia de las hayas y las encinas y es especialmente abundante en los bosques subtropicales perennifolios de la meseta de Yunnan. Prospera entre 1.700 y 2.500 metros sobre el nivel del mar, donde las pendientes pronunciadas y el clima variable hacen que los bosques estables sean fundamentales. Su madera densa y resistente a la pudrición es apreciada para la construcción y el mueble, y sus frutos han ayudado durante mucho tiempo a las comunidades locales a superar años de escasez. Ecológicamente, es una especie «fundacional»: donde prospera, el suelo se mantiene en su lugar, el agua discurre con más suavidad y muchas otras plantas y animales pueden florecer a su alrededor.
Leer el plano genético completo del árbol
El equipo de investigación se propuso ensamblar el genoma del árbol de un extremo al otro de cada cromosoma —un nivel de completitud que hasta hace poco solo era posible para unas pocas especies. Recogieron hojas frescas, flores y brotes jóvenes de un árbol adulto en la montaña Maxiong, en Yunnan. De estos tejidos extrajeron tanto ADN, que porta las instrucciones genéticas a largo plazo, como ARN, que refleja qué genes están activos en distintas partes de la planta. Estas moléculas se convirtieron en la materia prima para una serie de técnicas avanzadas de secuenciación y cartografiado.
Muchas lentes sobre el mismo genoma
En lugar de confiar en una sola tecnología, los científicos combinaron varias, cada una con sus fortalezas. Una plataforma generó fragmentos cortos y muy precisos de ADN para ofrecer una visión limpia y detallada. Otra produjo lecturas largas de alta fidelidad que pudieron cubrir tramos de ADN repetitivo o difíciles. Una tercera proporcionó fragmentos ultralargos que atravesaron regiones especialmente enredadas. Finalmente, una técnica que mide cómo se sitúan las piezas de ADN unas respecto a otras dentro de cromosomas reales ayudó al equipo a ordenar y orientar los fragmentos ensamblados a lo largo de 12 «seudomoléculas» de longitud cromosómica. Esta estrategia en capas produjo un genoma de aproximadamente 893 millones de letras de ADN, con casi todo asignado a cromosomas y solo una pequeña brecha residual.
Qué vive dentro de este genoma
Una vez asentado el andamiaje genético, los investigadores procedieron a etiquetar su contenido. Encontraron que casi tres quintas partes del genoma están compuestas por elementos repetidos, esas secuencias móviles o duplicadas que llenan gran parte del ADN vegetal y que con frecuencia confunden los métodos de secuenciación más antiguos. Sobre este fondo identificaron 35.978 genes codificadores de proteínas, cada uno una instrucción potencial para construir alguna parte del cuerpo del árbol o de su sistema de respuesta. Comparando estos genes con los de especies emparentadas y con grandes bases de datos públicas, pudieron asignarles funciones probables a casi todos y mapear su ubicación a lo largo de los cromosomas. También catalogaron miles de moléculas de ARN más pequeñas que ayudan a afinar cómo y cuándo se activan los genes.
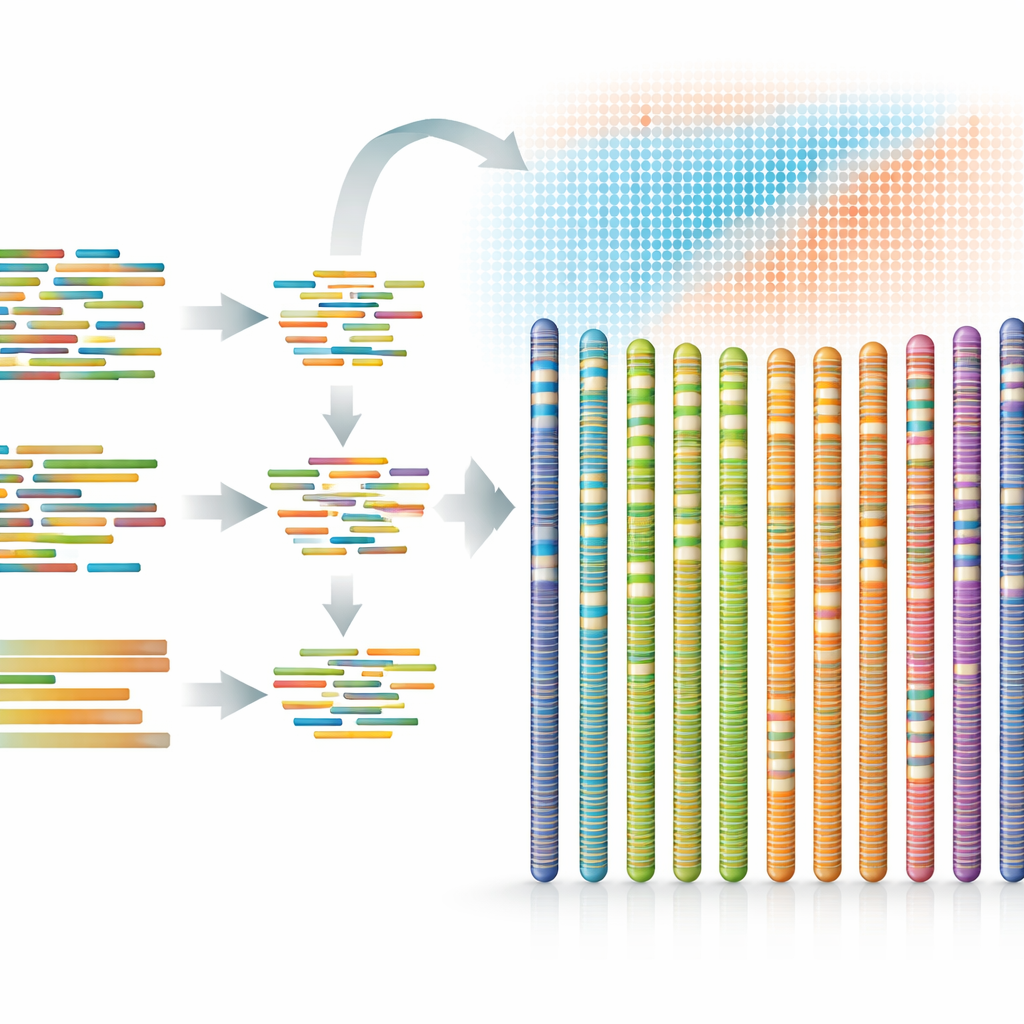
Un nuevo conjunto de herramientas para el futuro de los bosques
Para asegurar que este genoma pueda utilizarse como referencia fiable, el equipo comprobó cómo se realineaban las lecturas de ADN originales contra él y cuántos genes vegetales ampliamente conservados contenía; el ensamblaje superó estas pruebas con creces. Para los científicos, esto significa una base fiable para estudiar desde la historia evolutiva del árbol hasta cómo afronta el frío, la sequía o las plagas. Para los planificadores de conservación y los gestores forestales, crea un potente conjunto de herramientas para seguir la diversidad genética, guiar las plantaciones de restauración y seleccionar árboles más adecuados para climas futuros. En esencia, el estudio convierte a un árbol de montaña antes misterioso en un aliado genéticamente bien cartografiado en los esfuerzos por mantener saludables y resilientes los bosques subtropicales de China.
Cita: Yin, S., Wang, H., Chu, H. et al. A telomere-to-telomere genome assembly of Castanopsis orthacantha (Fagaceae). Sci Data 13, 450 (2026). https://doi.org/10.1038/s41597-026-06787-2
Palabras clave: genómica forestal, árboles subtropicales, ensamblaje del genoma, resiliencia del ecosistema, genética de la conservación