Clear Sky Science · de
Eine Telomer‑zu‑Telomer‑Genomassemblierung von Castanopsis orthacantha (Fagaceae)
Ein Baum, der einen Wald zusammenhält
Hoch in den immergrünen Bergen Südwestchinas wächst ein kräftiger Baum, dessen Holz Häuser baut, dessen Nüsse Menschen ernähren und dessen Wurzeln ganze Hänge stabilisieren helfen. Dieser Baum, Castanopsis orthacantha, ist eine stille Stütze des lokalen Lebens und der Wälder, die Überschwemmungen abmildern, Kohlenstoff speichern und zahllosen anderen Arten Schutz bieten. Die hier beschriebene Studie liefert etwas Unsichtbares, aber Mächtiges für diesen Schlüsselbaum: eine nahezu vollständige, von einem Chromosomenende zum anderen reichende Entschlüsselung seines genetischen Bauplans und eröffnet neue Wege, diese Wälder in einer sich erwärmenden Welt zu verstehen und zu schützen.

Warum dieser Bergbaum wichtig ist
Castanopsis orthacantha gehört zur Buchsbaum‑ und Eichenfamilie und ist besonders häufig in den subtropischen Immergrünwäldern des Yunnan‑Plateaus. Er gedeiht in 1.700 bis 2.500 Metern Höhe, wo steile Hänge und wechselhaftes Wetter stabile Wälder unverzichtbar machen. Sein dichtes, fäulnisresistentes Holz wird für Bau und Möbel geschätzt, und seine Nüsse haben lokalen Gemeinschaften seit langem geholfen, Engpässe zu überstehen. Ökologisch ist er eine „Fundamentalspezies“: Wo er gut wächst, bleiben Böden an ihrem Platz, Wasser fließt behutsamer, und viele andere Pflanzen und Tiere können dort gedeihen.
Den gesamten genetischen Bauplan des Baums lesen
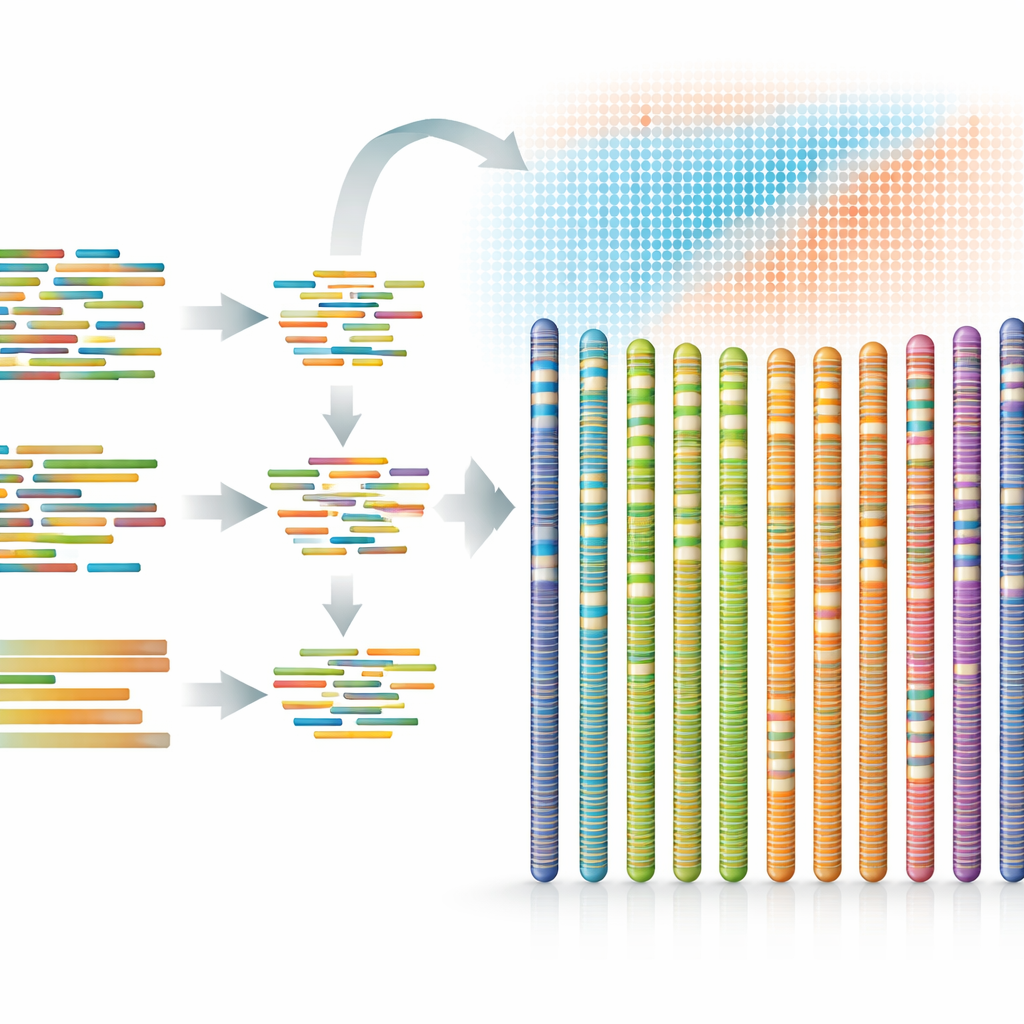
Das Forschungsteam hatte sich vorgenommen, das Genom des Baums von einem Ende jedes Chromosoms zum anderen zusammenzusetzen — eine Vollständigkeit, die bis vor kurzem nur für wenige Arten möglich war. Sie sammelten frische Blätter, Blüten und junge Triebe von einem ausgewachsenen Baum am Maxiong‑Berg in Yunnan. Aus diesen Geweben gewannen sie sowohl DNA, die die langfristigen genetischen Anweisungen trägt, als auch RNA, die aufzeichnet, welche Gene in verschiedenen Teilen der Pflanze aktiv sind. Diese Moleküle wurden zur Rohware für eine Reihe fortgeschrittener Sequenzier‑ und Kartierungsmethoden.
Viele Blickwinkel auf dasselbe Genom
Anstatt sich auf eine einzelne Technologie zu verlassen, kombinierten die Wissenschaftler mehrere, jeweils mit eigenen Stärken. Kurze, hochpräzise DNA‑Fragmente wurden auf einer Plattform erzeugt, um ein sauberes, detailliertes Bild zu liefern. Eine andere Plattform erzeugte lange, hochzuverlässige Reads, die Strecken mit Wiederholungen oder schwierigen Sequenzen überbrücken konnten. Eine dritte lieferte ultra‑lange Fragmente, die besonders verknotete Bereiche durchliefen. Schließlich half eine Technik, die misst, wie DNA‑Stücke innerhalb realer Chromosomen nebeneinanderliegen, dem Team dabei, die zusammengebauten Fragmente entlang von 12 chromosomenlangen „Pseudomolekülen“ anzuordnen und zu orientieren. Diese gestapelte Strategie produzierte ein Genom von etwa 893 Millionen DNA‑Basen, wobei nahezu der gesamte Anteil sauber den Chromosomen zugewiesen ist und nur eine einzige kleine Lücke verbleibt.
Was in diesem Genom steckt
Sobald das genetische Gerüst stand, gingen die Forschenden daran, seinen Inhalt zu beschriften. Sie fanden, dass fast drei Fünftel des Genoms aus repetitiven Elementen bestehen — den springenden oder duplizierten Sequenzen, die viel Pflanzen‑DNA füllen und ältere Sequenziermethoden oft verwirren. Auf diesem Hintergrund identifizierten sie 35.978 proteinkodierende Gene, jedes eine potenzielle Anweisung zum Aufbau eines Teils des Baumes oder zu seiner Reaktionsmechanik. Durch den Vergleich dieser Gene mit denen verwandter Arten und mit großen öffentlichen Datenbanken konnten sie nahezu allen wahrscheinliche Funktionen zuweisen und ihre Lage entlang der Chromosomen kartieren. Außerdem katalogisierten sie Tausende kleinerer RNA‑Moleküle, die dabei helfen, fein zu steuern, wie und wann Gene ein‑ oder ausgeschaltet werden.
Ein neues Werkzeugset für die Zukunft der Wälder
Damit dieses Genom als Referenz verlässlich ist, prüfte das Team, wie gut die ursprünglichen DNA‑Reads wieder darauf ausgerichtet werden konnten und wie viele breit konservierte Pflanzen‑Gene es enthielt; die Assemblierung bestand diese Tests mit Bravour. Für Wissenschaftler bedeutet das eine verlässliche Grundlage, um alles zu untersuchen — von der Evolutionsgeschichte des Baums bis hin zu seiner Reaktion auf Kälte, Dürre oder Schädlinge. Für Naturschützer und Forstmanager schafft es ein mächtiges Instrumentarium, um genetische Vielfalt zu verfolgen, Aufforstungsmaßnahmen zu leiten und Bäume auszuwählen, die besser an zukünftige Klimata angepasst sind. Im Kern macht die Studie aus einem einst rätselhaften Bergbaum einen genetisch gut kartierten Verbündeten in den Bemühungen, Chinas subtropische Wälder gesund und widerstandsfähig zu erhalten.
Zitation: Yin, S., Wang, H., Chu, H. et al. A telomere-to-telomere genome assembly of Castanopsis orthacantha (Fagaceae). Sci Data 13, 450 (2026). https://doi.org/10.1038/s41597-026-06787-2
Schlüsselwörter: Waldgenomik, subtropische Bäume, Genomassemblierung, Ökosystemresilienz, Erhaltungsgenietik