Clear Sky Science · it
Tracciare l’attività ligando-target spaziale con Renoir
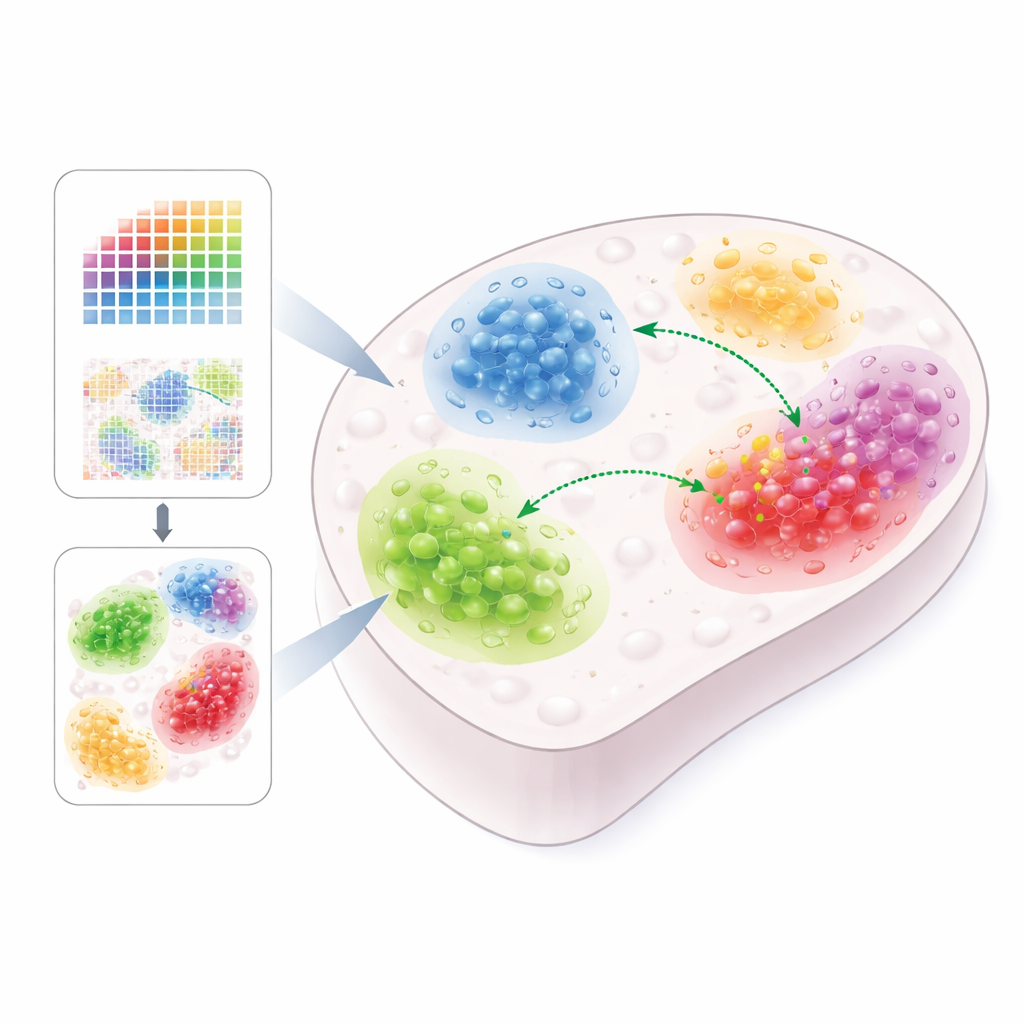
Come le cellule comunicano nei loro quartieri
I nostri corpi sono composti da innumerevoli cellule che costantemente "parlano" tra loro per mantenere i tessuti sani, costruire organi e, in alcuni casi, alimentare malattie come il cancro. Questo articolo presenta Renoir, un metodo computazionale che legge mappe su larga scala dell’attività genica per determinare dove e come avvengono queste conversazioni cellulari nei tessuti reali. Combinando la genomica spaziale moderna e l’analisi single-cell, Renoir aiuta i ricercatori a vedere non solo chi parla con chi, ma anche dove nel tessuto queste conversazioni sono più intense e quali effetti producono.
Segnali, messaggeri e conversazioni cellulari
Le cellule comunicano usando piccoli messaggeri proteici detti ligandi, rilasciati da una cellula e percepiti dalle cellule vicine tramite recettori sulla loro superficie. Quando un ligando si lega al suo recettore, può attivare una cascata di geni “target” all’interno della cellula ricevente, modificandone il comportamento. Molti strumenti esistenti cercano di inferire queste interazioni dai dati di espressione genica, ma spesso trascurano la posizione fisica delle cellule. Poiché molti segnali agiscono solo su brevi distanze, perdere questo contesto spaziale può portare a risultati fuorvianti — mostrando comunicazioni apparenti tra tipi cellulari che in realtà sono lontani nel tessuto.
Che cosa rende Renoir diverso
Renoir è progettato specificamente per reintegrare lo spazio nel quadro analitico. Accetta sia dataset spaziali a risoluzione single-cell sia una combinazione di dati spaziali a risoluzione inferiore e dati single-cell classici dallo stesso tessuto. Utilizzando elenchi curati di ligandi e dei loro potenziali geni target, Renoir calcola un “punteggio di attività di vicinato” per ogni coppia ligando–target in ciascuna posizione del tessuto. Questo punteggio fonde diverse informazioni: quali tipi cellulari sono presenti nelle vicinanze, quanto esprimono il ligando e il gene target, se le cellule riceventi esprimono effettivamente il recettore giusto e quanto strettamente ligando e target tendono a variare insieme tra i tipi cellulari. Il risultato è una mappa spaziale che mette in evidenza dove particolari relazioni di segnalazione sono probabilmente attive.
Trovare quartieri nascosti in tessuti sani e malati
Una volta calcolati i punteggi di vicinato, Renoir può raggruppare le posizioni in “domini di comunicazione” — aree del tessuto che condividono pattern simili di segnalazione. Applicato a dati del cervello di topo, questi domini si sono allineati con regioni cerebrali note e hanno rivelato comunicazioni specifiche di regione tra astrociti e diversi tipi di neuroni. Nel carcinoma mammario triplo negativo, Renoir ha scoperto nicchie tumorali distinte in cui cellule tumorali, cellule immunitarie e cellule del tessuto connettivo scambiano segnali legati alla crescita, all’invasione e alla soppressione immunitaria. Nel fegato fetale umano in sviluppo, ha identificato una nicchia in cui gli epatociti e macrofagi specializzati interagiscono tramite una molecola chiamata plasminogeno, suggerendo un ruolo nella crescita e nel rimodellamento epatico.
Mettere alla prova Renoir rispetto ad altri metodi
Gli autori hanno testato rigorosamente Renoir creando dataset semi-sintetici in cui i veri pattern di segnalazione erano noti a priori. Hanno confrontato Renoir con diversi strumenti di punta che inferiscono la comunicazione cellulare a partire da dati spaziali. In tessuti come intestino, cervello e carcinoma mammario, Renoir ha distinto con maggiore precisione le posizioni con vera attività ligando–target da quelle senza, ed è stato meno propenso a segnalare interazioni false in luoghi privi dei recettori corretti. Anche quando i dati sono stati resi più rumorosi — riducendo la profondità di sequenziamento o mescolando alcune etichette cellulari — le prestazioni di Renoir sono rimaste stabili. In una regione ben studiata del cervello umano, i domini di comunicazione inferiti dal metodo corrispondevano meglio ai livelli tissutali definiti da esperti rispetto agli approcci concorrenti.
Dalle mappe della comunicazione a indizi terapeutici
Renoir non è solo uno strumento di mappatura; può anche classificare quali ligandi sono più influenti in ciascun dominio e riassumere l’attività di interi percorsi di segnalazione. Nel carcinoma epatico, questo ha evidenziato circuiti di segnalazione “onco-fetali” in cui cellule associate al tumore riutilizzano programmi di sviluppo osservati nel fegato fetale. Renoir ha previsto che ligandi come l’interleuchina-6 provenienti da questa nicchia potrebbero riprogrammare le cellule epatiche vicine di tipo staminale; esperimenti di laboratorio hanno confermato che l’interleuchina-6 spinge le cellule del cancro del fegato verso uno stato più simile a quello staminale. Nel complesso, lo studio mostra come combinare la genomica spaziale con calcoli intelligenti possa trasformare mappe geniche statiche in ritratti dinamici del dialogo cellulare, offrendo nuovi punti di ingresso per terapie mirate a interrompere conversazioni dannose preservando quelle salutari.
Citazione: Rao, N., Kumar, T., Kazemi, D. et al. Charting spatial ligand-target activity using Renoir. Nat Commun 17, 3983 (2026). https://doi.org/10.1038/s41467-026-72388-7
Parole chiave: trascrittomica spaziale, comunicazione cellulare, segnalazione dei ligandi, microambiente tumorale, biologia computazionale
Scopri di più sul sito web del gruppo di ricerca: https://sites.google.com/view/cosmiclab-iitk/home