Clear Sky Science · de
Räumliche Ligand‑Ziel‑Aktivität mit Renoir kartieren
Wie Zellen in ihrer Nachbarschaft sprechen
Unser Körper besteht aus unzähligen Zellen, die ständig miteinander "sprechen", um Gewebe gesund zu erhalten, Organe aufzubauen und in manchen Fällen Krankheiten wie Krebs voranzutreiben. Dieses Papier stellt Renoir vor, eine rechnerische Methode, die groß angelegte Karten der Genaktivität ausliest, um herauszufinden, wo und wie dieser zelluläre Austausch im echten Gewebe stattfindet. Durch die Kombination moderner Einzelzell‑ und räumlicher Genomik hilft Renoir Forschern nicht nur zu sehen, wer mit wem kommuniziert, sondern auch, wo im Gewebe diese Gespräche am stärksten sind und welche Folgen sie haben.
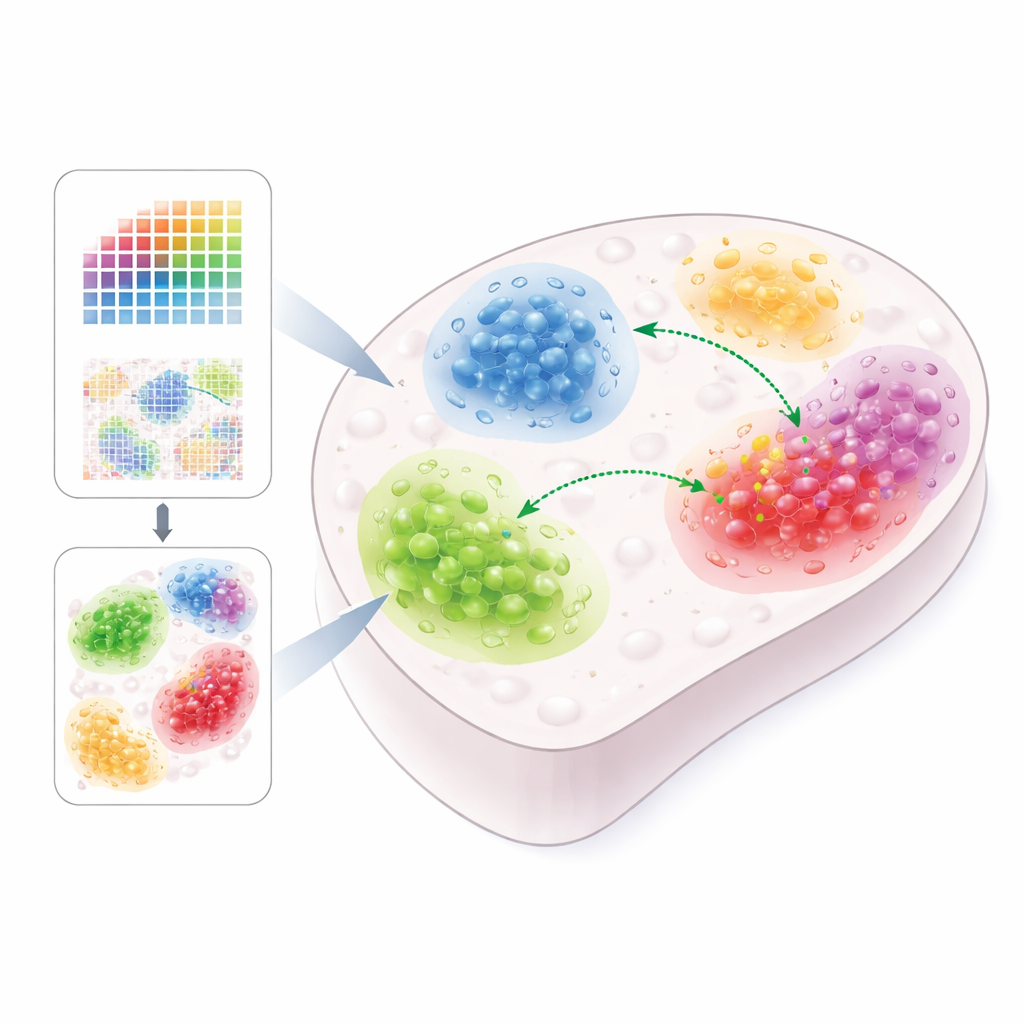
Signale, Botenstoffe und zelluläre Gespräche
Zellen kommunizieren über kleine Proteinbotenstoffe, sogenannte Liganden, die von einer Zelle freigesetzt und von benachbarten Zellen über Rezeptoren an deren Oberfläche wahrgenommen werden. Wenn ein Ligand an seinen Rezeptor bindet, kann er eine Kaskade von "Ziel"‑Genen in der empfangenden Zelle einschalten und damit deren Verhalten verändern. Viele bestehende Werkzeuge versuchen, diese Interaktionen aus Genaktivitätsdaten abzuleiten, vernachlässigen dabei aber oft die physische Lage der Zellen. Da viele Signale nur über kurze Distanzen wirken, kann das Fehlen dieses räumlichen Kontexts zu irreführenden Ergebnissen führen — etwa indem angebliche Kommunikation zwischen Zelltypen angezeigt wird, die im Gewebe tatsächlich weit auseinander liegen.
Was Renoir unterscheidet
Renoir wurde speziell entwickelt, um den Raum wieder in das Bild zu bringen. Es verarbeitet entweder räumliche Datensätze mit Einzelzellauflösung oder eine Kombination aus räumlichen Daten mit niedrigerer Auflösung und klassischen Einzelzelldaten aus demselben Gewebe. Mithilfe kuratierter Listen von Liganden und ihren potenziellen Zielgenen berechnet Renoir für jedes Ligand‑Ziel‑Paar an jedem Ort im Gewebe einen "Nachbarschaftsaktivitätswert". Dieser Wert vereint mehrere Informationsbestandteile: welche Zelltypen in der Nähe vorkommen, wie stark sie den Liganden und das Zielgen exprimieren, ob die Empfängerzellen tatsächlich den passenden Rezeptor exprimieren, und wie stark Ligand und Ziel typischerweise gemeinsam über Zelltypen variieren. Das Ergebnis ist eine räumliche Karte, die hervorhebt, wo bestimmte Signalbeziehungen wahrscheinlich aktiv sind.
Verborgene Nachbarschaften in gesunden und erkrankten Geweben finden
Sobald die Nachbarschaftswerte berechnet sind, kann Renoir Orte in "Kommunikationsdomänen" gruppieren — Gewebeflächen, die ähnliche Muster der Signalgebung teilen. Angewandt auf Mausgehirndaten stimmten diese Domänen mit bekannten Gehirnregionen überein und zeigten regionsspezifische Kommunikation zwischen Astrozyten und verschiedenen Neuronentypen. Beim triple-negativen Brustkrebs entdeckte Renoir unterschiedliche Tumornischen, in denen Krebszellen, Immunzellen und Bindegewebe Zellsignale austauschen, die mit Wachstum, Invasion und Immunsuppression verbunden sind. Im sich entwickelnden menschlichen fetalen Lebergewebe identifizierte es eine Nische, in der Leberzellen (Hepatozyten) und spezialisierte Makrophagen über ein Molekül namens Plasminogen interagieren, was auf eine Rolle bei Leberwachstum und Umgestaltung hinweist.
Renoir im Vergleich zu anderen Methoden testen
Die Autoren testeten Renoir rigoros, indem sie semi‑synthetische Datensätze erstellten, in denen die wahren Signalgebungsmuster im Voraus bekannt waren. Sie verglichen Renoir mit mehreren führenden Werkzeugen, die Zell‑zu‑Zell‑Kommunikation aus räumlichen Daten ableiten. In Geweben wie Darm, Gehirn und Brustkrebs unterschied Renoir genauer Orte mit echter Ligand‑Ziel‑Aktivität von solchen ohne und meldete seltener falsche Interaktionen an Orten, denen die passenden Rezeptoren fehlten. Selbst wenn die Daten verrauschter gemacht wurden — durch geringere Sequenziertiefe oder durch Vertauschen einiger Zelllabels — blieb Renoirs Leistung stabil. In einer gut untersuchten Region des menschlichen Gehirns stimmten die vom Verfahren abgeleiteten Kommunikationsdomänen besser mit fachkundig definierten Gewebeschichten überein als die konkurrierenden Ansätze.
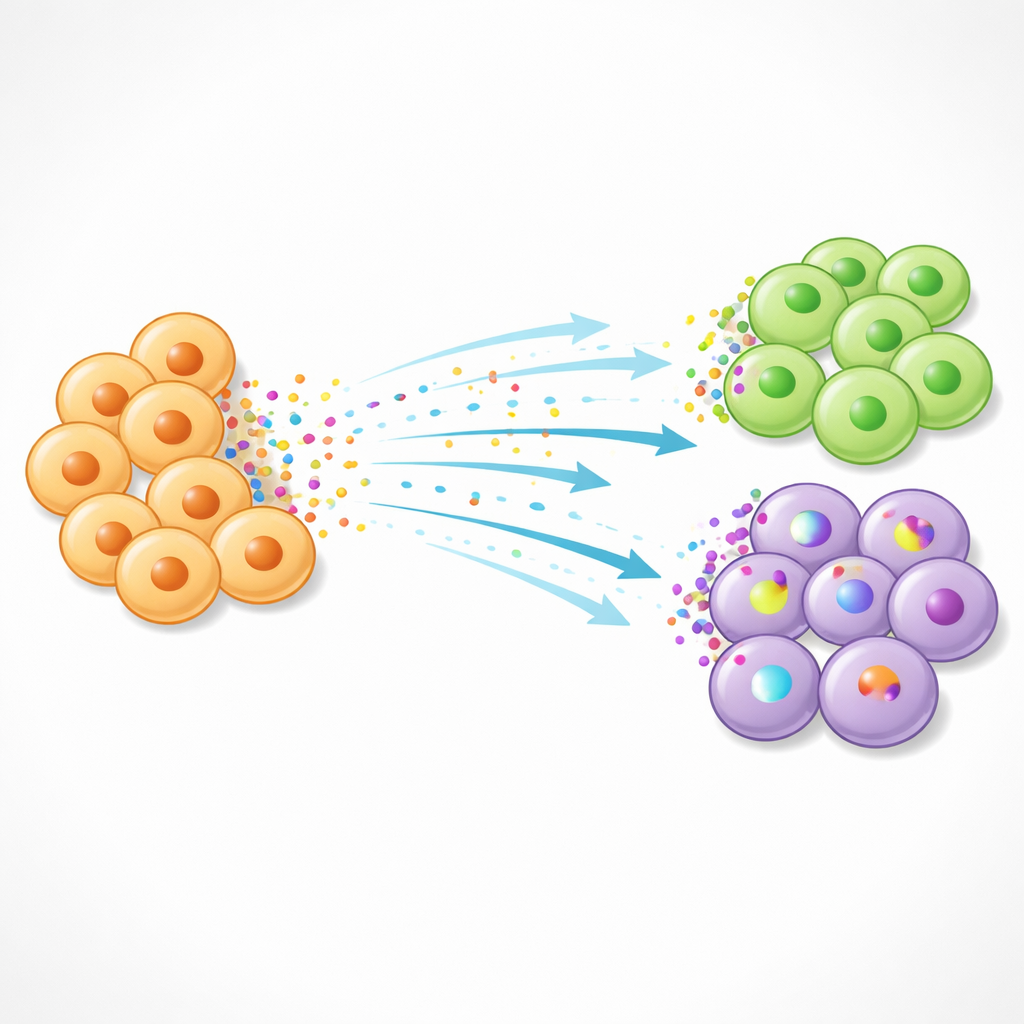
Von Kommunikationskarten zu therapeutischen Hinweisen
Renoir ist nicht nur ein Kartierungswerkzeug; es kann auch Liganden danach priorisieren, welche in jeder Domäne am einflussreichsten sind, und die Aktivität ganzer Signalwege zusammenfassen. Beim Leberkrebs hob dies "onko‑fötale" Signalwege hervor, in denen tumornah zugeordnete Zellen entwicklungsbezogene Programme aus der fetalen Leber wiederverwenden. Renoir sagte voraus, dass Liganden wie Interleukin‑6 aus dieser Nische nahegelegene, stammzellähnliche Leberzellen umprogrammieren könnten; Laborversuche bestätigten, dass Interleukin‑6 Leberkrebszellen in einen stärker stammzellähnlichen Zustand treibt. Insgesamt zeigt die Studie, wie die Kombination aus räumlicher Genomik und intelligenter Berechnung statische Genkarten in dynamische Porträts zellulärer Dialoge verwandeln kann und neue Ansatzpunkte für Therapien bietet, die schädliche Gespräche stören, gesunde aber bewahren wollen.
Zitation: Rao, N., Kumar, T., Kazemi, D. et al. Charting spatial ligand-target activity using Renoir. Nat Commun 17, 3983 (2026). https://doi.org/10.1038/s41467-026-72388-7
Schlüsselwörter: räumliche Transkriptomik, Zellkommunikation, Ligand‑Signalgebung, Tumormikroumgebung, computationale Biologie
Mehr auf der Website der Forschungsgruppe: https://sites.google.com/view/cosmiclab-iitk/home