Clear Sky Science · it
Struttura e dinamica del complesso PARP1-HPF1 su DNA lesionato suggeriscono un meccanismo per l’ADP-ribosilazione acuta e localizzata
Come le cellule rilevano piccole rotture nel loro DNA
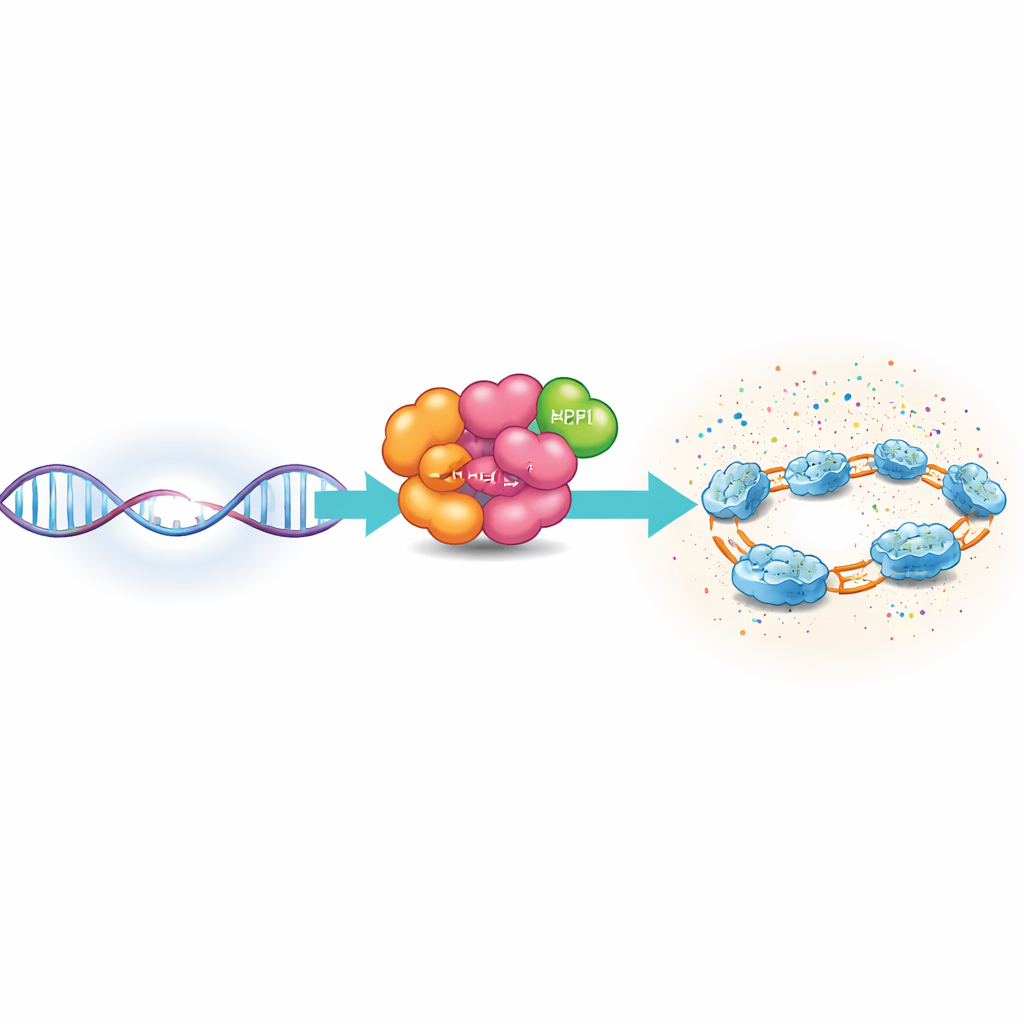
Ogni cellula del tuo corpo è continuamente sottoposta a eventi che provocano incisioni o rotture del DNA. Se queste lesioni non vengono rilevate e riparate rapidamente, possono portare a mutazioni e, in ultima analisi, al cancro. Questo studio rivela come uno dei primi soccorritori cellulari, una proteina chiamata PARP1 che agisce insieme alla sua partner HPF1, riconosca una piccola interruzione nel DNA e quindi decori rapidamente le proteine vicine con marcatori chimici. Questi segnali funzionano come un faro luminoso, richiamando e organizzando la squadra di riparazione proprio dove è necessario.
Un primo soccorritore molecolare in azione
PARP1 è una proteina guardiana presente in grande quantità che scandaglia il DNA alla ricerca di danni. Quando incontra una singola incisione su un filamento – un taglio su uno solo dei due filamenti del DNA – PARP1 si ancora alla lesione usando diverse regioni specializzate che afferrano il DNA. Una volta attivata, PARP1 utilizza una molecola di carburante cellulare, il NAD+, per costruire catene di ADP-ribosio su se stessa e sulle proteine vicine, in particolare sulle istoni, che aiutano a compattare il DNA nella cromatina. Queste modifiche allentano temporaneamente la struttura cromatinica locale e attirano fattori di riparazione, creando una zona di riparazione molto focalizzata intorno al sito danneggiato.
Osservare la macchina completa sul DNA rotto
Finora, la maggior parte degli istantanee strutturali di PARP1 mostrava solo porzioni della proteina, lasciando aperta la domanda su come la molecola a lunghezza intera si assemblasse su una rottura del DNA insieme ai suoi partner. Gli autori hanno utilizzato la crio-microscopia elettronica a singola particella, una tecnica che visualizza molecole congelate a dettaglio quasi atomico, per vedere PARP1 a lunghezza intera legato a un frammento di DNA incisionato insieme a HPF1 e a un frammento di un altro partner chiamato Timeless. Hanno combinato queste immagini con esperimenti di fluorescenza a singola molecola e misure di scattering in soluzione per capire non solo la struttura, ma anche il movimento di questo complesso in azione.
Piegare il DNA e organizzare l’impalcatura
Le immagini rivelano che diverse regioni di PARP1 serrano l’incisione e piegano bruscamente il DNA di circa 75 gradi. Tre segmenti a dito di zinco e un dominio WGR formano un’impalcatura sciolta ma coordinata che ancora PARP1 direttamente alla rottura. Una regione adiacente chiamata dominio elicale si unisce a questo assemblaggio, contribuendo a stabilizzare lo stato legato al DNA. Insieme, questi elementi creano un’ancora rigida nel sito del danno, mentre altre parti di PARP1 – in particolare un dominio BRCT più interno – restano flessibili e spesso invisibili nelle immagini, indicando che si muovono liberamente anche quando il nucleo legante il DNA è bloccato in posizione.
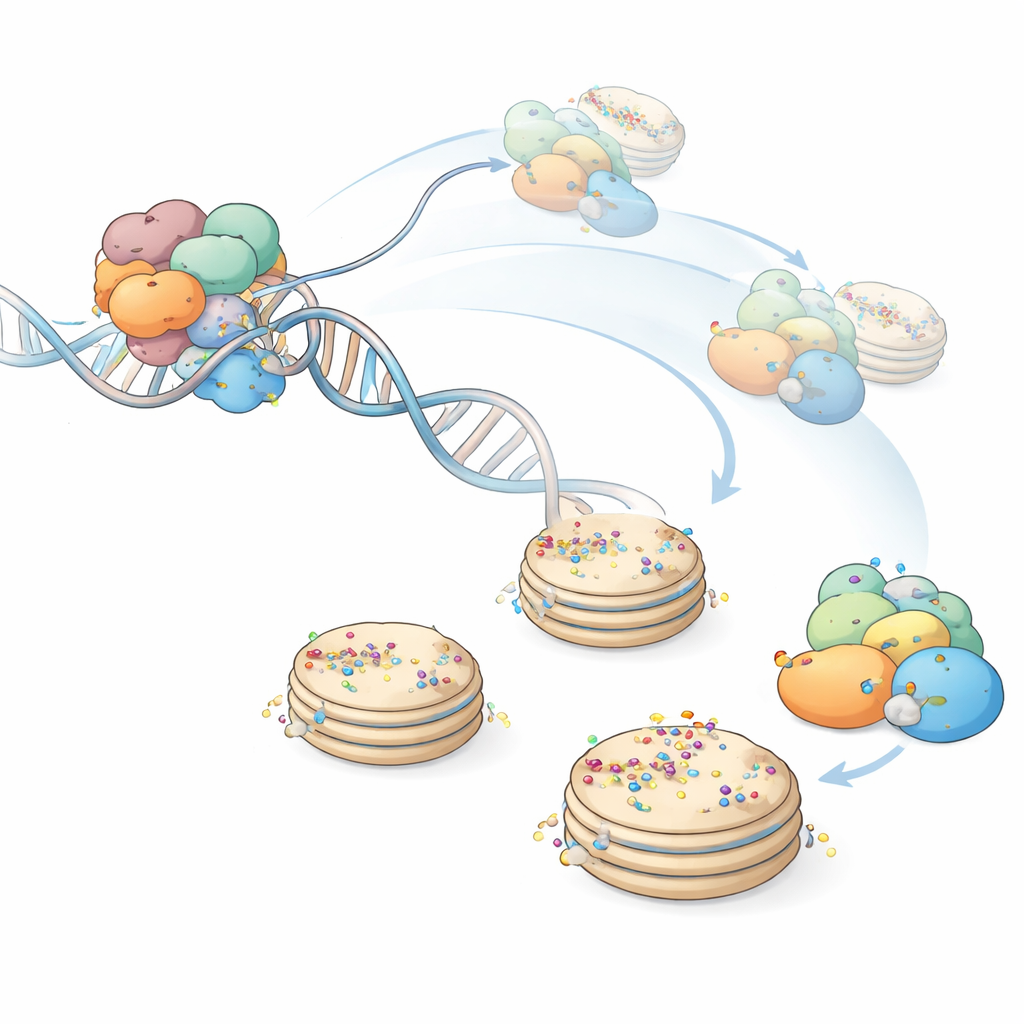
Un braccio catalitico con un guinzaglio flessibile
La scoperta più sorprendente riguarda la regione catalitica di PARP1, la parte che costruisce effettivamente le catene di ADP-ribosio. Nelle precedenti strutture cristalline, questo blocco catalitico stava aderente al dominio elicale in uno stato “spento” che bloccava l’accesso al NAD+. Nelle nuove viste crio-EM, una volta che PARP1 è completamente organizzata sul DNA inciso, questo blocco catalitico si stacca in gran parte dal vicino elicale e diventa altamente mobile, rimanendo collegato solo da connettori flessibili. HPF1 si lega direttamente a questa regione catalitica mobile, rimodellando il sito attivo in modo che i residui di serina sugli istoni diventino bersagli preferenziali. Le misure di fluorescenza a singola molecola confermano che il legame di un composto che imita il NAD+ stabilizza PARP1 sul DNA e riduce le fluttuazioni nella piegatura del DNA, coerente con un braccio catalitico attivato ma dinamicamente assicurato.
Un flare chimico locale ma potente
Combinando imaging strutturale, dinamiche a singola molecola e scattering in soluzione, gli autori propongono un modello in cui il legame a un’incisione del DNA organizza la metà N-terminale di PARP1 in una pinza rigida mentre libera la regione catalitica all’estremità opposta per oscillare su un “guinzaglio.” Questo braccio catalitico mobile ma costantemente attivo, in collaborazione con HPF1, può etichettare rapidamente PARP1 e gli istoni vicini con catene di ADP-ribosio entro un raggio limitato attorno alla rottura. Il risultato è un’esplosione di segnalazione acuta ma altamente localizzata che rimodella la cromatina e recluta i fattori di riparazione esattamente dove servono, aiutando le cellule a mantenere la stabilità del genoma minimizzando al contempo interruzioni inutili altrove nel nucleo.
Citazione: Sverzhinsky, A., Xue, H., Langelier, MF. et al. PARP1-HPF1 structure and dynamics on nicked DNA suggest a mechanism for acute and localized ADP-ribosylation. Nat Commun 17, 2825 (2026). https://doi.org/10.1038/s41467-026-69375-3
Parole chiave: Riparazione del DNA, PARP1, ADP-ribosilazione, crio-EM, cromatina