Clear Sky Science · fr
La structure et la dynamique PARP1-HPF1 sur ADN nické suggèrent un mécanisme d’ADP-ribosylation aiguë et localisée
Comment les cellules détectent de minuscules cassures dans leur ADN
Chaque cellule de votre corps est constamment exposée à des événements qui éraflent ou rompent son ADN. Si ces lésions ne sont pas détectées et réparées rapidement, elles peuvent provoquer des mutations et, au bout du compte, un cancer. Cette étude révèle comment l’un des premiers intervenants clés de la cellule, une protéine appelée PARP1, en coopération avec sa partenaire HPF1, reconnaît une petite coupure dans l’ADN puis marque rapidement les protéines voisines par des étiquettes chimiques. Ces marques agissent comme une puissante balise lumineuse, attirant et organisant l’équipe de réparation exactement là où elle est nécessaire.
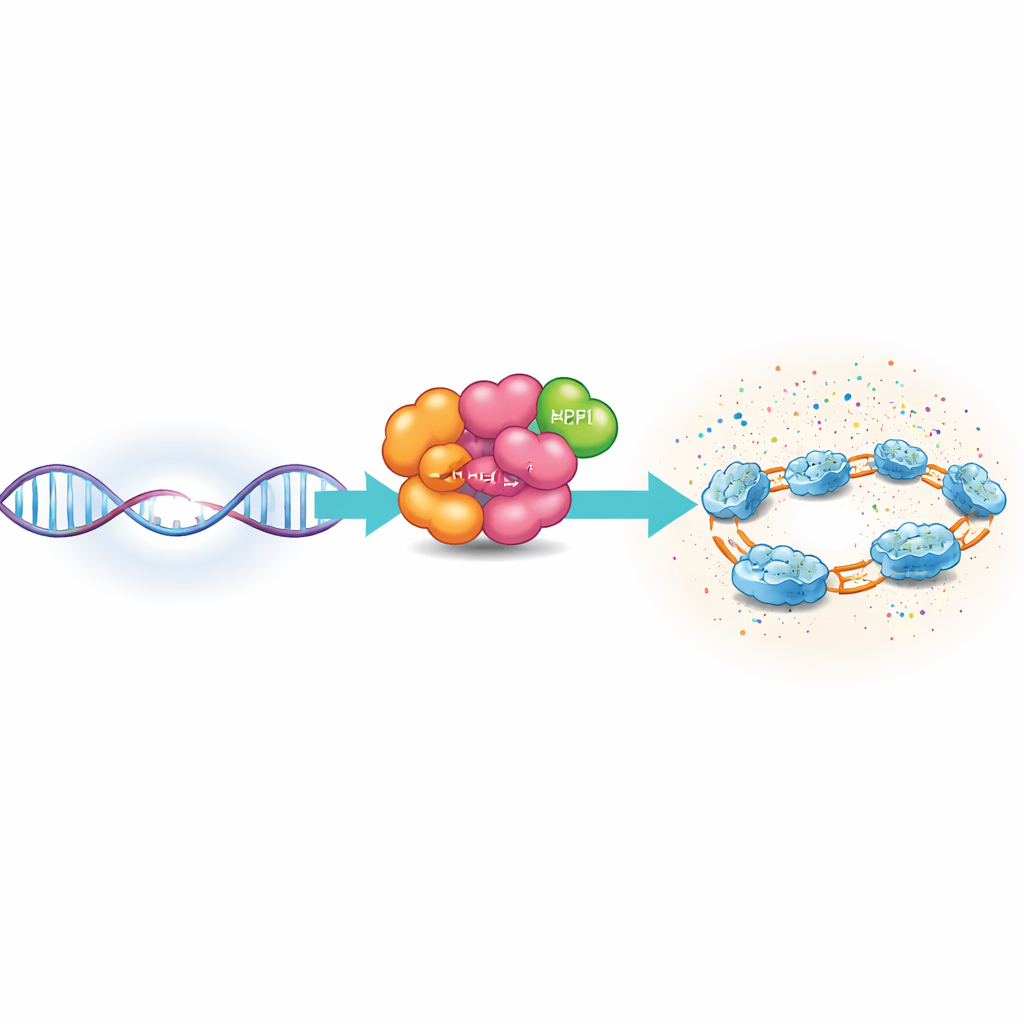
Un premier intervenant moléculaire en action
PARP1 est une protéine gardienne abondante qui scrute l’ADN à la recherche de dommages. Lorsqu’elle rencontre une coupure simple-brin – une incision dans une seule des deux brins d’ADN – PARP1 se fixe sur la brèche à l’aide de plusieurs régions spécialisées qui agrippent l’ADN. Une fois activée, PARP1 utilise une molécule énergétique cellulaire, le NAD+, pour construire des chaînes d’ADP-ribose sur elle-même et sur des protéines voisines, en particulier les histones, qui contribuent à empaqueter l’ADN en chromatine. Ces modifications relâchent temporairement la structure locale de la chromatine et attirent des facteurs de réparation, créant une zone de réparation très focalisée autour du site endommagé.
Voir la machine complète sur l’ADN rompu
Jusqu’à présent, la plupart des instantanés structuraux de PARP1 ne montraient que des portions de la protéine, laissant ouverte la question de savoir comment la molécule en pleine longueur s’assemble sur une brèche d’ADN avec ses partenaires. Les auteurs ont utilisé la cryo‑microscopie électronique en particules isolées, une technique qui image des molécules vitrifiées à un détail quasi-atomique, pour visualiser PARP1 en pleine longueur lié à un fragment d’ADN nické, accompagné de HPF1 et d’un fragment d’un autre partenaire appelé Timeless. Ils ont combiné ces vues avec des expériences de fluorescence sur molécule unique et des mesures de diffusion en solution pour comprendre non seulement la structure, mais aussi le mouvement de ce complexe en action.
Courber l’ADN et organiser l’échafaudage
Les images révèlent que plusieurs régions de PARP1 se referment autour de la brèche et plient nettement l’ADN d’environ 75 degrés. Trois segments en doigt de zinc et un domaine WGR forment un échafaudage lâche mais coordonné qui ancre PARP1 directement au niveau de la coupure. Une région adjacente appelée domaine hélicoïdal rejoint cet assemblage, contribuant à stabiliser l’état lié à l’ADN. Ensemble, ces éléments créent une ancre rigide au site de dommage, tandis que d’autres parties de PARP1 – notamment un domaine BRCT plus central – restent flexibles et souvent invisibles dans les images, ce qui indique qu’elles bougent librement même lorsque le noyau de liaison à l’ADN est verrouillé.
Un bras catalytique au bout d’une laisse flexible
La découverte la plus frappante concerne la région catalytique de PARP1, la partie qui construit effectivement les chaînes d’ADP-ribose. Dans des structures cristallines antérieures, ce bloc catalytique était appuyé contre le domaine hélicoïdal dans un état « éteint » bloquant l’accès au NAD+. Dans les nouvelles vues cryo-EM, une fois que PARP1 est complètement organisé sur l’ADN nické, ce bloc catalytique se détache largement de son voisin hélicoïdal et devient très mobile, restant connecté uniquement par des liaisons flexibles. HPF1 se lie directement à cette région catalytique mobile, remodelant son site actif de sorte que les résidus sérine des histones deviennent des cibles privilégiées. Des mesures de fluorescence sur molécule unique confirment que la liaison d’un composé mimant le NAD+ stabilise PARP1 sur l’ADN et réduit les fluctuations de courbure de l’ADN, en accord avec un bras catalytique activé mais dynamiquement retenu.
Une lueur chimique locale mais puissante
En combinant imagerie structurale, dynamique sur molécule unique et diffusion en solution, les auteurs proposent un modèle selon lequel la liaison à une brèche d’ADN organise la moitié N‑terminale de PARP1 en une pince rigide tout en libérant la région catalytique à l’autre extrémité pour qu’elle oscille sur une « laisse ». Ce bras catalytique mobile mais constamment actif, en partenariat avec HPF1, peut rapidement marquer PARP1 lui‑même et les histones proches par des chaînes d’ADP-ribose dans un rayon limité autour de la brèche. Le résultat est une poussée de signalisation aiguë mais très localisée qui remodèle la chromatine et recrute les facteurs de réparation précisément là où ils sont nécessaires, aidant les cellules à préserver la stabilité du génome tout en minimisant les perturbations inutiles ailleurs dans le noyau.
Citation: Sverzhinsky, A., Xue, H., Langelier, MF. et al. PARP1-HPF1 structure and dynamics on nicked DNA suggest a mechanism for acute and localized ADP-ribosylation. Nat Commun 17, 2825 (2026). https://doi.org/10.1038/s41467-026-69375-3
Mots-clés: Réparation de l’ADN, PARP1, ADP-ribosylation, cryo-EM, chromatine