Clear Sky Science · fr
Transmission de clones de Salmonella entre différentes espèces animales dans une région d’élevage équin et bovin au Japon
Pourquoi les microbes qui sautent d’un animal d’élevage à un autre comptent
Les intoxications alimentaires dues à Salmonella sont un problème mondial qui peut commencer bien avant que les aliments n’atteignent nos cuisines. Elles prennent souvent naissance dans les exploitations agricoles, où les mêmes microbes peuvent circuler discrètement entre différentes espèces animales puis entrer dans la chaîne alimentaire humaine. Cette étude examine de près une région active d’élevage de chevaux et de bovins dans le nord du Japon pour comprendre comment un type particulièrement performant de Salmonella se propage entre les espèces, et s’il s’agit d’un problème local, d’une vague d’infection mondiale, ou des deux.
Un germe robuste qui aime de nombreux hôtes
Les chercheurs se sont concentrés sur une forme de Salmonella, dite « sequence type 34 » (ST34), qui est aujourd’hui l’une des causes les plus courantes de diarrhée chez l’homme et chez les animaux dans le monde. Contrairement à certaines souches spécialisées sur un seul hôte, ST34 infecte librement de nombreux mammifères et oiseaux. Elle porte souvent plusieurs gènes conférant une résistance à des antibiotiques importants et une tolérance aux métaux comme le cuivre ou le zinc — des traits qui favorisent sa survie sur les exploitations modernes. Le Japon a connu des vagues répétées de différentes souches de Salmonella au cours des quarante dernières années, et ST34 est devenue la souche dominante chez les bovins depuis les années 2010.
Retracer les infections entre exploitations et au fil des années
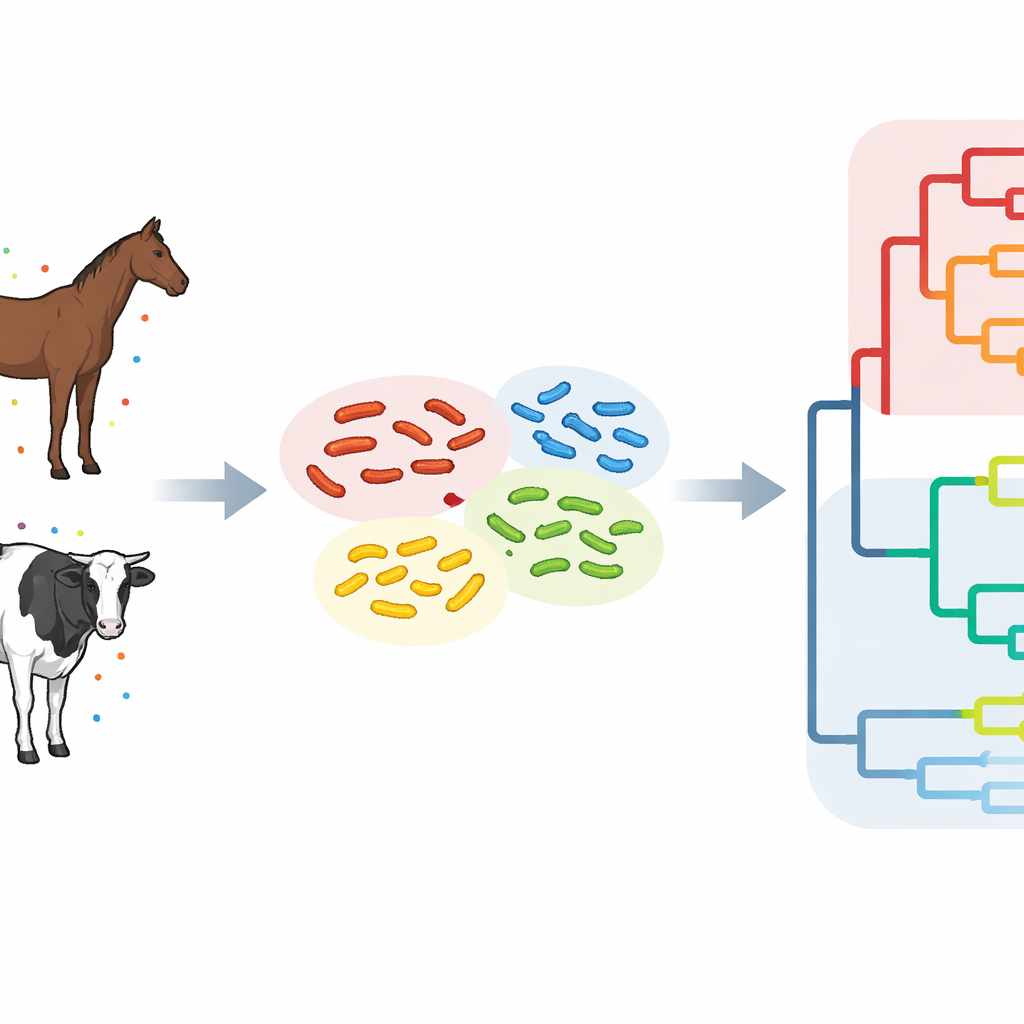
Pour comprendre le comportement de ST34 là où chevaux et bovins cohabitent, l’équipe a analysé 42 isolats de Salmonella prélevés sur des animaux dans un district d’Hokkaidô entre 1981 et 2023. Grâce au séquençage du génome complet, ils ont lu presque l’intégralité du code ADN de chaque isolat bactérien et comparé de petites différences, appelées substitutions nucléotidiques simples, dans leur génome central. Les souches qui différaient de moins de 25 de ces changements ont été regroupées en cinq « clusters » étroitement liés, indiquant qu’elles s’étaient séparées d’un ancêtre commun relativement récemment. Dans la plupart des clusters, des bactéries presque identiques ont été trouvées chez des chevaux et des bovins sur des exploitations différentes, parfois séparées de plusieurs années et de dizaines de kilomètres, ce qui suggère fortement une transmission interespèces et entre exploitations.
Épidémies locales au sein d’un arbre généalogique mondial
Les scientifiques ont ensuite replacé les souches d’Hokkaidô dans un contexte mondial en les comparant à près de 500 génomes ST34 issus de 28 pays. Cette analyse plus large a révélé trois branches principales, ou clades, de l’arbre généalogique de Salmonella. Deux branches consistaient principalement en souches ayant circulé au Japon et ont été qualifiées de lignées épidémiques japonaises, tandis que la troisième branche contenait un mélange de souches d’Europe, d’Asie, des Amériques, d’Afrique et d’Océanie et a été considérée comme la lignée mondiale. Trois des clusters d’Hokkaidô s’inscrivaient clairement dans une lignée épidémique japonaise, montrant que les infections locales chez chevaux et bovins faisaient partie d’un problème national plus large et de longue date. Un autre cluster s’est retrouvé associé à des souches d’Asie de l’Est comme la Chine et la Corée du Sud, et un autre encore montrait des liens génétiques avec des souches européennes, laissant entrevoir des introductions répétées depuis l’étranger.
Voies de circulation cachées et hausse de la résistance aux médicaments
En estimant quand différentes branches se sont séparées les unes des autres, l’équipe a conclu que la lignée principale ST34 du Japon s’était détachée de la lignée mondiale à la fin des années 1990 ou au début des années 2000, puis s’était adaptée aux animaux destinés à l’alimentation au sein du pays. Parallèlement, au moins une sous-lignée d’Asie de l’Est portant des gènes supplémentaires de résistance aux médicaments semble être entrée au Japon séparément. Si les itinéraires exacts restent flous, les schémas suggèrent que les mouvements d’animaux, des aliments contaminés, des véhicules ou même des animaux sauvages tels que les oiseaux et les ratons laveurs pourraient transporter ces bactéries entre exploitations et espèces. Presque toutes les souches portaient un ensemble de gènes de résistance de base aux antibiotiques courants, et certaines portaient des gènes additionnels susceptibles de rendre le traitement plus difficile si ces bactéries atteignent l’homme.
Ce que cela signifie pour les exploitations et la sécurité alimentaire
Pour un lecteur général, le message clé est que les microbes dangereux ne respectent ni les frontières d’espèce ni les clôtures des exploitations. Dans ce district japonais, les mêmes clones de Salmonella ont été trouvés chez les chevaux et les bovins et peuvent être reliés génétiquement à des vagues d’infection nationales et internationales plus larges. L’étude montre qu’un suivi précis par ADN peut révéler la manière discrète dont ces bactéries circulent entre animaux, régions et frontières. Pour réduire le risque d’intoxication alimentaire et de maladies animales, les programmes de lutte ne peuvent pas se concentrer sur une seule espèce ni sur un seul pays : ils doivent surveiller les sauts interespèces, limiter la propagation des souches résistantes aux médicaments et considérer les exploitations, la faune et le commerce mondial comme les éléments d’un même système connecté.
Citation: Arai, N., Niwa, H., Uchida-Fujii, E. et al. Transmission of Salmonella clones between different animal species in a horse and cattle breeding region in Japan. Sci Rep 16, 12412 (2026). https://doi.org/10.1038/s41598-026-39311-y
Mots-clés: Salmonella, transmission interespèces, résistance aux antibiotiques, élevage, séquençage du génome