Clear Sky Science · de
Übertragung von Salmonella-Klonen zwischen verschiedenen Tierarten in einer Pferde- und Rinderzüchterregion in Japan
Warum Keime, die zwischen Stalltieren springen, wichtig sind
Lebensmittelvergiftungen durch Salmonella sind ein globales Problem, das oft lange bevor Lebensmittel in unseren Küchen landen seinen Ausgang nimmt. Häufig beginnt es auf Höfen, wo sich dieselben Keime still zwischen verschiedenen Tierarten bewegen und dann in die menschliche Nahrungskette gelangen können. Diese Studie untersucht eingehend eine dicht besiedelte Pferde- und Rinderzuchtregion im Norden Japans, um zu klären, wie sich ein besonders erfolgreicher Salmonella‑Typ zwischen Arten ausbreitet und ob er Teil eines lokalen Problems, einer globalen Infektionswelle oder beidem ist.
Ein widerstandsfähiger Keim mit vielen Wirten
Die Forschenden konzentrierten sich auf eine Form von Salmonella, bezeichnet als Sequenztyp 34 (ST34), die heute weltweit zu den häufigsten Ursachen von Durchfällen bei Menschen und Tieren gehört. Anders als manche Salmonella‑Stämme, die einen bestimmten Wirt bevorzugen, infiziert ST34 viele Säugetiere und Vögel. Häufig trägt er mehrere Gene, die ihn gegen wichtige Antibiotika resistent machen, sowie Gene, die Toleranz gegenüber Metallen wie Kupfer oder Zink vermitteln – Eigenschaften, die ihm auf modernen Betrieben das Überleben erleichtern. Japan hat in den letzten vier Jahrzehnten wiederholt Wellen unterschiedlicher Salmonella‑Stämme erlebt, und seit den 2010er‑Jahren ist ST34 beim Rind dominierend geworden.
Infektionsspuren über Betriebe und Jahre hinweg
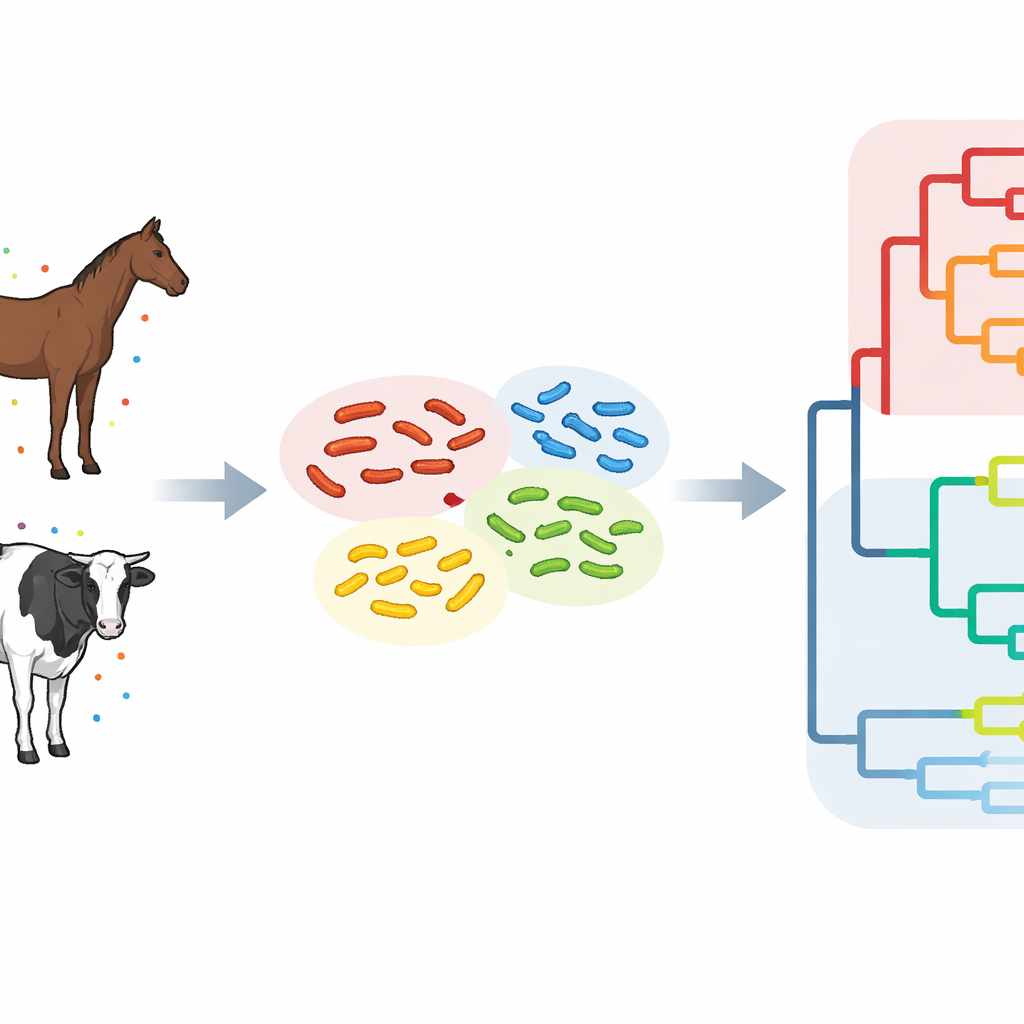
Um zu verstehen, wie sich ST34 dort verhält, wo Pferde und Rinder nebeneinander gehalten werden, analysierte das Team 42 Salmonella‑Proben, die zwischen 1981 und 2023 in einem Distrikt von Hokkaido von Tieren entnommen wurden. Mittels vollständiger Genomsequenzierung lasen sie nahezu den gesamten DNA‑Code jeder bakteriellen Isolats und verglichen winzige Unterschiede, sogenannte Einzelnukleotid‑Varianten, im Kerngenom. Stämme, die sich um weniger als 25 solcher Veränderungen unterschieden, wurden zu fünf eng verwandten „Clustern“ zusammengefasst, was darauf hindeutet, dass sie sich erst vor relativ kurzer Zeit von einem gemeinsamen Vorfahren getrennt hatten. In den meisten Clustern wurden nahezu identische Bakterien sowohl bei Pferden als auch bei Rindern auf verschiedenen Höfen gefunden, teils Jahre auseinander und über Dutzende Kilometer verteilt, was stark auf artübergreifende und zwischenbetrieblich Übertragungen hinweist.
Lokale Ausbrüche innerhalb eines globalen Stammbaums
Die Wissenschaftler ordneten die Hokkaido‑Stämme in einen globalen Kontext ein, indem sie sie mit knapp 500 ST34‑Genomen aus 28 Ländern verglichen. Diese breitere Analyse ergab drei Hauptäste, oder Kladen, im Salmonella‑Familienstammbaum. Zwei Äste bestanden überwiegend aus Stämmen, die in Japan zirkulierten und als japanische epidemische Linien bezeichnet wurden, während der dritte Ast eine Mischung aus Stämmen aus Europa, Asien, Amerika, Afrika und Ozeanien enthielt und als globale Linie galt. Drei der Hokkaido‑Cluster lagen klar innerhalb einer japanischen epidemischen Linie, was zeigt, dass lokale Pferde‑ und Rinderinfektionen Teil eines größeren, längerdauernden nationalen Problems sind. Ein weiteres Cluster gruppierte sich mit Stämmen aus ostasiatischen Ländern wie China und Südkorea, und ein anderes wies genetische Verbindungen zu europäischen Stämmen auf, was auf wiederholte Einschleppungen aus dem Ausland hindeutet.
Verborgene Wege und zunehmende Arzneimittelresistenz
Durch die Schätzung, wann sich verschiedene Äste voneinander abgespalten haben, kamen die Forschenden zu dem Schluss, dass sich Japans Hauptlinie von ST34 in den späten 1990er‑ oder frühen 2000er‑Jahren von der globalen Linie trennte und sich dann innerhalb des Landes an Nutztiere anpasste. Gleichzeitig scheint mindestens eine ostasiatische Unterlinie, die zusätzliche Resistenzgene trägt, separat nach Japan eingedrungen zu sein. Obwohl die genauen Wege unklar bleiben, deuten die Muster darauf hin, dass Tierbewegungen, kontaminiertes Futter, Fahrzeuge oder auch Wildtiere wie Vögel und Waschbären diese Bakterien zwischen Höfen und Arten verschleppen könnten. Fast alle Stämme trugen einen Kernsatz an Resistenzgenen gegen gängige Antibiotika, und einige besaßen zusätzliche Gene, die eine Behandlung erschweren könnten, falls diese Bakterien Menschen erreichen.
Was das für Betriebe und Lebensmittelsicherheit bedeutet
Für eine allgemeine Leserschaft lautet die Kernaussage: Gefährliche Keime kennen weder Artgrenzen noch Hoftore. In diesem japanischen Distrikt wurden dieselben Salmonella‑Klonen bei Pferden und Rindern gefunden, die zudem genetisch mit größeren nationalen und internationalen Infektionswellen verknüpft werden können. Die Studie zeigt, dass sorgfältiges DNA‑Monitoring offenlegt, wie unbemerkt diese Bakterien über Tierarten, Regionen und Grenzen hinweg wandern. Um das Risiko von Lebensmittelvergiftungen und Tierkrankheiten zu verringern, dürfen Seuchenbekämpfungsprogramme sich nicht auf eine einzige Tierart oder ein einziges Land beschränken: Sie müssen artübergreifende Sprünge beobachten, die Verbreitung multiresistenter Stämme begrenzen und Betriebe, Wildtiere sowie den globalen Handel als Teile eines verbundenen Systems betrachten.
Zitation: Arai, N., Niwa, H., Uchida-Fujii, E. et al. Transmission of Salmonella clones between different animal species in a horse and cattle breeding region in Japan. Sci Rep 16, 12412 (2026). https://doi.org/10.1038/s41598-026-39311-y
Schlüsselwörter: Salmonella, Artübergreifende Übertragung, Antibiotikaresistenz, Nutztierhaltung, Genomsequenzierung