Clear Sky Science · fr
Identification informatique d’épitope conservés de la protéine d’enveloppe du virus de la dengue pour la conception de vaccins et une plateforme immunodiagnostique
Pourquoi cette recherche est importante
La dengue est une maladie transmise par les moustiques qui menace aujourd’hui près de la moitié de la population mondiale. Pourtant, les médecins ne disposent toujours pas d’un vaccin qui protège en toute sécurité contre les quatre variantes du virus ni de tests sanguins capables d’identifier de manière fiable quelle variante provoque une infection. Cette étude utilise des outils informatiques avancés pour analyser le virus en détail, à la recherche de petits fragments susceptibles de constituer la base d’un vaccin plus sûr et plus large ainsi que de tests diagnostiques plus précis.
Quatre virus semblables, un gros problème
Le virus de la dengue existe sous quatre formes étroitement apparentées, ou sérotypes, chacune pouvant provoquer des symptômes allant d’une fièvre bénigne à une maladie potentiellement mortelle. Une infection par un sérotype protège uniquement contre ce sérotype et peut même aggraver la maladie si l’on est ensuite infecté par un autre sérotype. Les vaccins actuels peinent à déclencher une protection forte et équilibrée contre les quatre sérotypes à la fois, sans provoquer de réaction immune délétère. Par ailleurs, les tests sanguins courants peuvent confondre la dengue avec des virus apparentés comme le Zika, rendant difficile le suivi précis des épidémies.
Zoom sur la coque virale
Les chercheuses et chercheurs se sont concentrés sur la protéine d’enveloppe du virus, un composant majeur de la couche externe que le système immunitaire « voit » en premier. Ils ont recueilli des milliers de séquences de la protéine d’enveloppe provenant des quatre sérotypes et les ont alignées pour repérer des régions soit très conservées (similaires entre tous les types), soit clairement distinctes d’un type à l’autre. L’objectif était double : les régions conservées pourraient servir d’ossature à un vaccin universel, tandis que les régions uniques pourraient faire office d’empreintes pour des tests distinguant les sérotypes.
Trouver des cibles prometteuses avec des ordinateurs
À l’aide d’un ensemble d’outils d’immunoinformatique, l’équipe a prédit quels courts segments de la protéine d’enveloppe sont susceptibles d’être reconnus par les cellules T et B — les cellules immunitaires qui coordonnent et exécutent les attaques. Ils ont évalué chaque segment candidat en fonction de son potentiel à déclencher une réponse immunitaire, de sa ressemblance avec des protéines humaines (ce qui pourrait provoquer de l’auto-immunité), et de son risque d’être toxique ou allergène. Plusieurs segments se sont distingués comme à la fois sûrs et fortement visibles par le système immunitaire, y compris un ensemble partagé par tous les sérotypes qui pourrait soutenir un vaccin « tétravalent » contre la dengue, ainsi que d’autres ensembles spécifiques aux sérotypes 2, 3 ou 4, idéaux pour des tests diagnostiques très spécifiques.
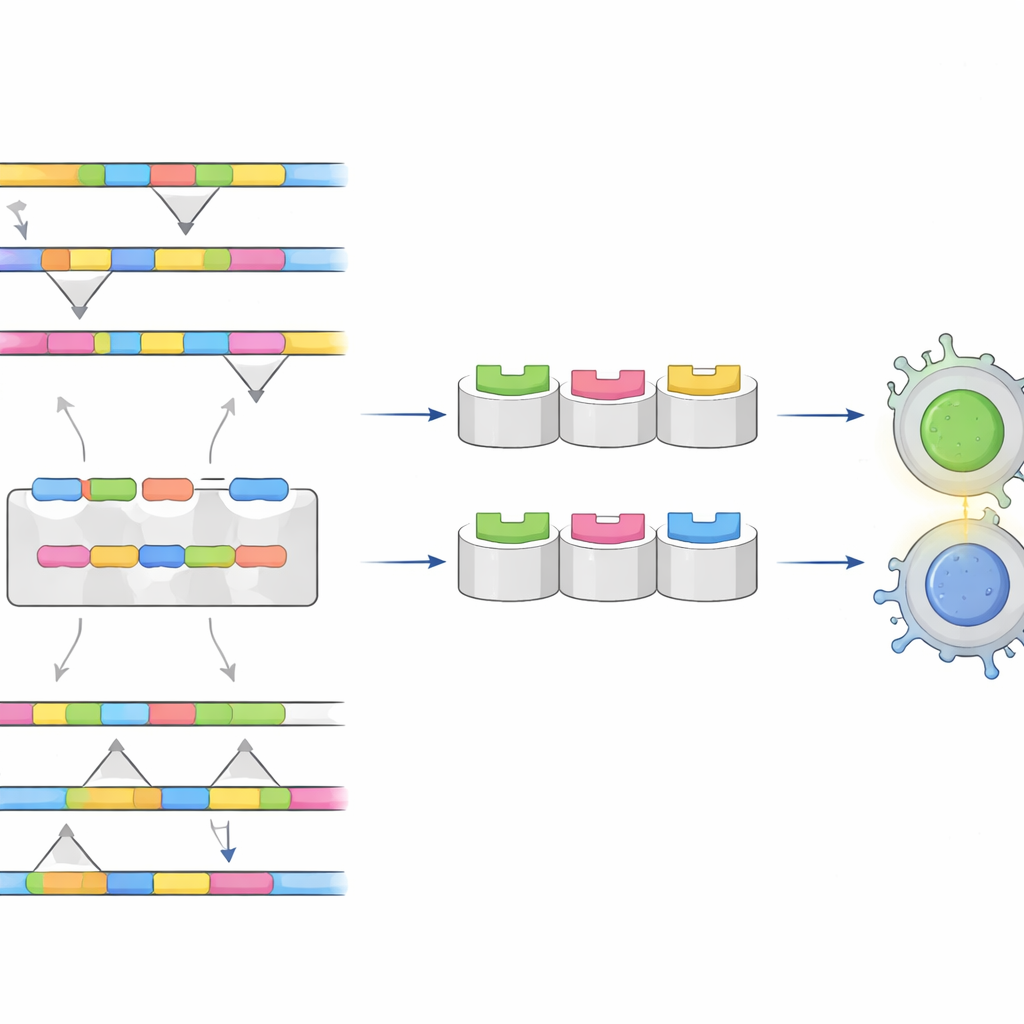
Tester l’ajustement en 3D
Pour aller au-delà des seuls motifs de séquence, les chercheurs ont construit des modèles tridimensionnels montrant comment ces segments viraux s’insèreraient dans les molécules immunitaires humaines qui les présentent aux cellules T. Ils ont utilisé le docking moléculaire pour simuler l’ajustement physique entre le peptide et le récepteur immunitaire, et l’analyse des modes normaux pour sonder la stabilité de ces complexes lorsqu’ils se fléchissent et bougent. Certaines paires peptide–récepteur ont formé des liaisons particulièrement serrées et stables, suggérant qu’elles pourraient alerter de manière fiable les cellules T chez de nombreuses personnes à travers le monde. Une analyse de population, basée sur la fréquence des variantes de récepteurs immunitaires dans différentes régions, a indiqué que le meilleur ensemble de candidats pourrait, en théorie, couvrir environ les deux tiers de la population mondiale, avec une couverture particulièrement forte en Asie de l’Est, en Europe et dans les Amériques.
Ce que cela signifie pour les outils futurs
Concrètement, ce travail fournit une liste soigneusement filtrée de « morceaux » viraux qui paraissent particulièrement prometteurs pour les vaccins de nouvelle génération contre la dengue et pour les tests sanguins. Les segments conservés pourraient aider à construire un vaccin unique efficace contre les quatre types de dengue, tandis que les segments uniques pourraient permettre aux médecins d’identifier précisément quel type provoque la maladie d’un patient. Bien que ces prédictions doivent encore être validées en laboratoire et en études cliniques, l’étude montre comment l’analyse informatisée peut accélérer et affiner considérablement la recherche de cibles vaccinales et diagnostiques contre une maladie tropicale en forte expansion.
Citation: da Silva, M.K., Fulco, U.L., Alqahtani, T. et al. Computational identification of conserved dengue virus envelope protein epitopes for vaccine design and immunodiagnostic platform. Sci Rep 16, 14167 (2026). https://doi.org/10.1038/s41598-026-37744-z
Mots-clés: vaccin contre la dengue, cartographie d’épitope, protéine d’enveloppe, immunoinformatique, diagnostics spécifiques de sérotype