Clear Sky Science · es
Identificación computacional de epítopos conservados de la proteína de la envoltura del virus del dengue para el diseño de vacunas y plataformas inmunodiagnósticas
Por qué importa esta investigación
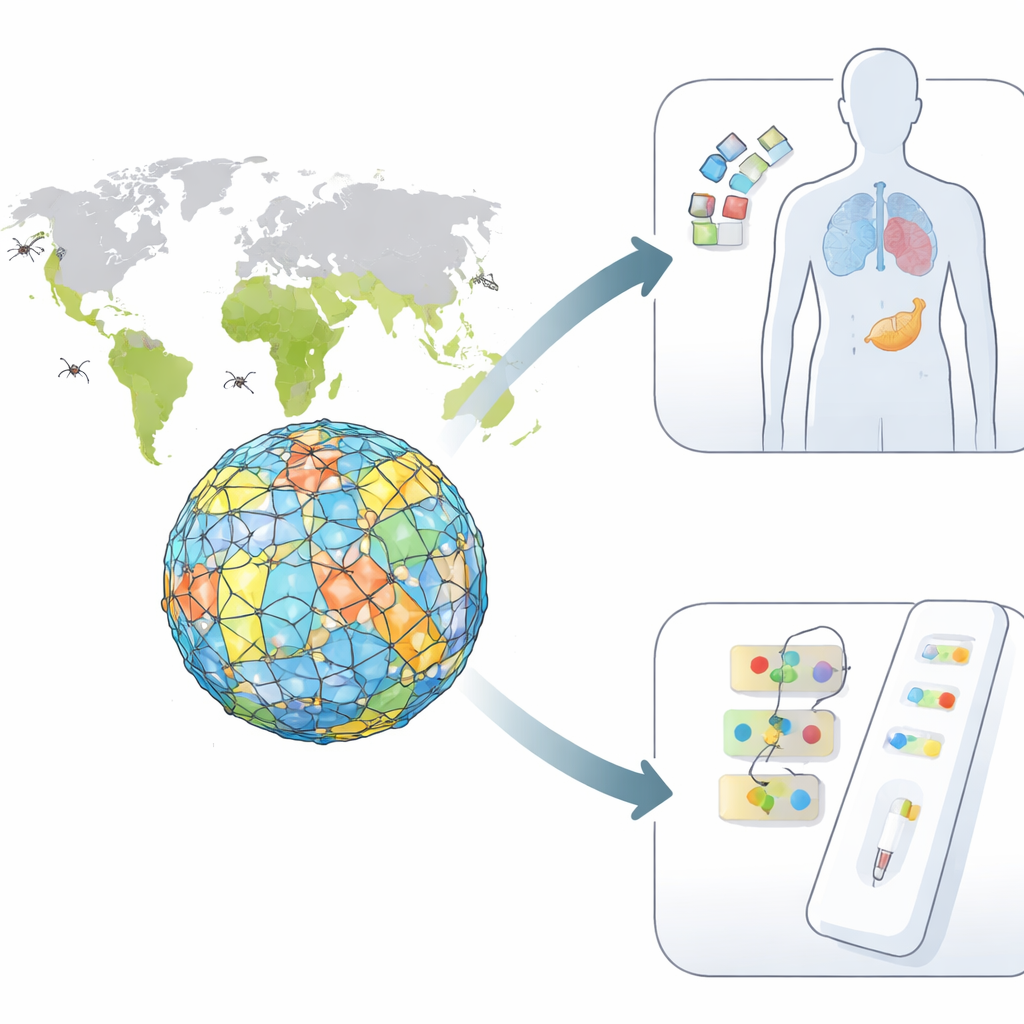
La fiebre del dengue es una enfermedad transmitida por mosquitos que hoy amenaza a casi la mitad de la población mundial. Aun así, los médicos carecen de una vacuna que proteja de forma segura contra las cuatro variantes del virus y de pruebas de sangre que puedan indicar con fiabilidad qué variante está causando una infección. Este estudio utiliza herramientas informáticas avanzadas para explorar el virus en detalle, buscando fragmentos pequeños que podrían servir como base para una vacuna más segura y amplia y para pruebas diagnósticas más precisas.
Cuatro virus similares, un gran problema
El virus del dengue existe en cuatro formas estrechamente relacionadas, o serotipos, cada una capaz de causar desde una fiebre leve hasta una enfermedad potencialmente mortal. La infección por un serotipo solo protege frente a ese serotipo y puede incluso agravar la enfermedad si posteriormente se contrae otro serotipo. Las vacunas actuales tienen dificultades porque deben inducir una protección fuerte y equilibrada contra los cuatro a la vez, sin provocar una reacción inmune perjudicial. Además, las pruebas de laboratorio actuales pueden confundir el dengue con virus relacionados como el Zika, lo que dificulta el seguimiento preciso de los brotes.
Acercándose al recubrimiento viral
Los investigadores se centraron en la proteína de la envoltura del virus, un componente principal de la capa externa que el sistema inmunitario “ve” primero. Reunieron miles de secuencias de la proteína de la envoltura de los cuatro serotipos y las alinearon para encontrar regiones que fueran altamente conservadas (similares entre todos los tipos) o claramente diferentes entre serotipos. El objetivo era doble: las regiones conservadas podrían servir como la base de una vacuna universal, mientras que las regiones únicas podrían funcionar como huellas distintivas para pruebas que diferencien los serotipos.
Encontrar dianas prometedoras con ordenadores
Empleando un conjunto de herramientas de inmunoinformática, el equipo predijo qué tramos cortos de la proteína de la envoltura son probables de ser reconocidos por las células T y B del organismo—las células blancas que coordinan y ejecutan las respuestas inmunitarias. Evaluaron cada segmento candidato según la intensidad con que podría desencadenar una respuesta inmune, si se parece a alguna proteína humana (lo que podría causar autoinmunidad) y si probablemente sea tóxico o alergénico. Varios segmentos destacaron por ser tanto seguros como altamente visibles al sistema inmune, incluidos un conjunto compartido por todos los serotipos que podría sustentar una vacuna «tetravalente» contra el dengue y otros conjuntos exclusivos de los serotipos 2, 3 o 4, ideales para pruebas diagnósticas muy específicas.
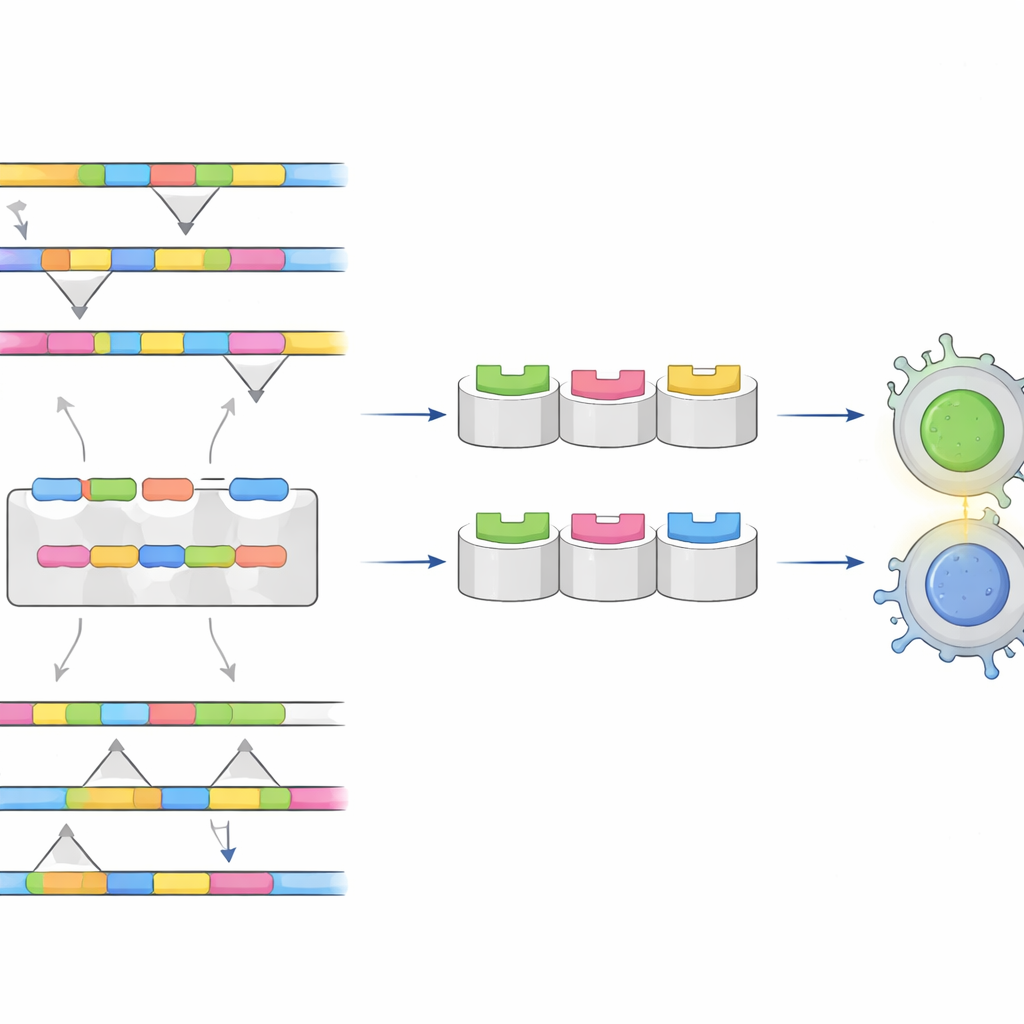
Probar el encaje en 3D
Para ir más allá de los patrones de secuencia, los investigadores construyeron modelos tridimensionales de cómo estos fragmentos virales se insertarían en las moléculas inmunitarias humanas que los presentan a las células T. Utilizaron acoplamiento molecular para simular el ajuste físico entre el péptido y el receptor inmune, y análisis de modos normales para sondear la estabilidad de esos complejos mientras se flexionan y se mueven. Algunas parejas péptido–receptor formaron uniones especialmente firmes y estables, lo que sugiere que podrían alertar de forma fiable a las células T en muchas personas alrededor del mundo. Un análisis poblacional, basado en la frecuencia de variantes de receptores inmunitarios en distintas regiones, indicó que el mejor conjunto de candidatos podría, en teoría, cubrir alrededor de dos tercios de la población mundial, con cobertura particularmente fuerte en Asia oriental, Europa y las Américas.
Qué significa esto para herramientas futuras
En términos sencillos, este trabajo ofrece una lista cuidadosamente filtrada de «piezas» virales que parecen especialmente prometedoras para vacunas y pruebas de sangre de próxima generación contra el dengue. Los fragmentos conservados podrían ayudar a construir una vacuna única eficaz frente a los cuatro tipos de dengue, mientras que los fragmentos únicos permitirían a los médicos identificar exactamente qué tipo está causando la enfermedad de un paciente. Aunque estas predicciones aún deben probarse en laboratorio y en estudios clínicos, el estudio demuestra cómo el análisis impulsado por ordenadores puede acelerar y afinar considerablemente la búsqueda de dianas para vacunas y diagnósticos frente a una enfermedad tropical de rápida expansión.
Cita: da Silva, M.K., Fulco, U.L., Alqahtani, T. et al. Computational identification of conserved dengue virus envelope protein epitopes for vaccine design and immunodiagnostic platform. Sci Rep 16, 14167 (2026). https://doi.org/10.1038/s41598-026-37744-z
Palabras clave: vacuna contra el dengue, mapeo de epítopos, proteína de la envoltura, inmunoinformática, diagnósticos específicos por serotipo