Clear Sky Science · de
OncoRisk: ein hochmoderner Webserver zur Verbindung onkogener Datenbanken und pan-krebs Kohorten mit der translationalen Onkologie
DNA-Daten in klare Krebsantworten übersetzen
Die Krebsbehandlung basiert zunehmend darauf, die DNA eines Tumors zu lesen, doch die Flut genetischer Daten kann selbst Expertinnen und Experten überfordern. Verschiedene Datenbanken speichern Teile des Puzzles, große Patientenkohorten enthalten realweltliche Muster, und Kliniken müssen all dies in Entscheidungen zu Medikamenten und Prognose überführen. Dieser Beitrag stellt OncoRisk vor, eine kostenlose Webplattform, die darauf ausgelegt ist, diese verstreuten Ressourcen zusammenzuführen, damit Ärztinnen, Ärzte und Forschende schneller von rohen DNA-Daten zu praktischen Erkenntnissen für Krebspatienten gelangen.
Warum die Interpretation von Krebs-DNA so schwierig ist
Jeder Tumor trägt eine einzigartige Mischung aus DNA-Veränderungen. Einige Alterationen treiben das Krebswachstum aktiv voran, andere beeinflussen, wie gut ein Medikament wirkt, und viele sind schlicht harmlose Hintergrundrauschen. Bestehende Experten-Datenbanken wie ClinVar, CIViC und OncoKB erfassen jeweils Teile dieses Wissens, während massive Projekte wie The Cancer Genome Atlas und das AACR Project GENIE Hunderttausende von Patientinnen und Patienten profilieren. Diese Ressourcen sind jedoch verstreut, verwenden unterschiedliche Formate und erfordern oft Programmierkenntnisse oder manuelles Abgleichen über viele Websites hinweg. Diese Fragmentierung verlangsamt Forschung und klinische Entscheidungsfindung, besonders wenn der Tumor einer einzelnen Person tausende DNA-Veränderungen enthalten kann, die überprüft werden müssen.
Eine Webzentrale für Wissen über Krebsvarianten
OncoRisk wurde als einheitliche Zentrale für diese komplexe Landschaft entwickelt. Die Plattform integriert mehr als zehn onkologische Wissensbasen und sieben große pan-krebs Kohorten in einer einzigen Weboberfläche. Nutzerinnen und Nutzer können nach einem Gen, einer spezifischen Mutation, einer Krebsart oder einer Therapie suchen und sofort sehen, wie diese miteinander verknüpft sind. Eine „Schnellsuche“-Funktion unterstützt flexible Abfragen mit gebräuchlichen Gennamen, technischen Mutationskodes oder allgemeinen Krankheitsbegriffen. Für tiefere Einblicke zeigt eine interaktive Netzwerkansicht, wie ein Medikament, eine Mutation und eine Krebsart durch geteilte Evidenz verbunden sind, während ein „Stammbaum“ der Krebserkrankungen jede Erkrankung in breitere Gewebe- und Subtyp-Beziehungen einordnet.
Von einer einzelnen Mutation zu 3D-Strukturen und realen Patientinnen und Patienten
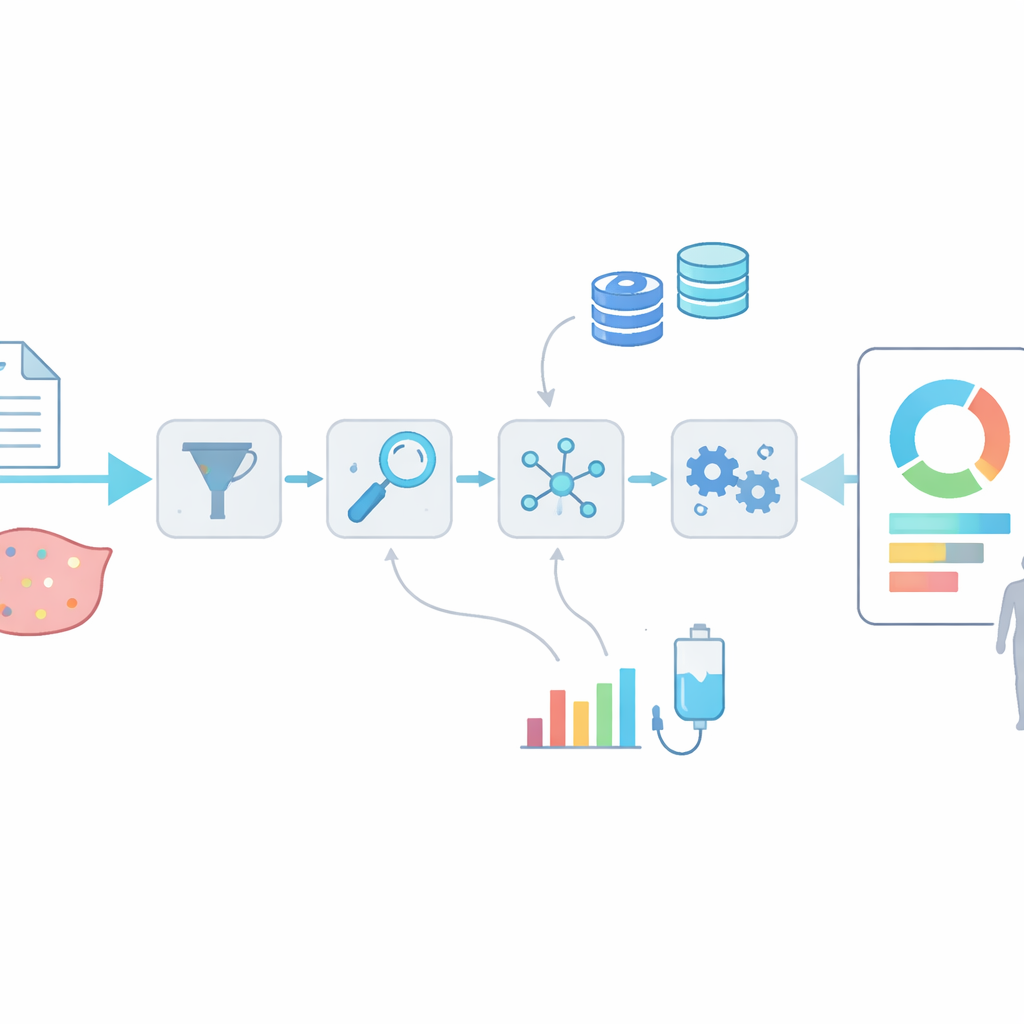
Für jede DNA-Veränderung kann OncoRisk eine ausführliche, variantenzentrierte Seite zusammenstellen. Im Hintergrund laufen etablierte Annotationswerkzeuge, anschließend werden Klassifizierungen darüber herangezogen, wie schädlich eine Mutation ist, welche Medikamente sie beeinflussen könnte und ob relevante klinische Studien existieren. Das System ordnet die Mutation in Krebs-Stammbäume ein und kann 3D-Proteinstrukturen anzeigen, die zeigen, wo ein Medikament und ein mutiertes Protein sich physisch im Inneren der Zelle treffen — oder eben nicht. Gleichzeitig prüft OncoRisk große Patientenkohorten, um zu berichten, wie häufig die Mutation über Krebsarten hinweg vorkommt und wie stark sie in einer gegebenen Tumorprobe auftritt. Diese Kombination aus strukturellen Ansichten, klinischer Evidenz und Realwelt-Häufigkeitsdaten hilft Nutzerinnen und Nutzern einzuschätzen, welche Mutationen wahrscheinlich am wichtigsten sind.
Automatisierte Berichte für einzelne Patientinnen und Patienten sowie ganze Kohorten
Über einzelne Varianten hinaus bietet OncoRisk eine semi-automatisierte Pipeline, die eine komplette Tumor-DNA-Datei in einen menschenlesbaren Bericht verwandelt. Nutzerinnen und Nutzer laden eine standardisierte Variantendatei hoch; das System filtert dann qualitativ hochwertige Veränderungen, annotiert sie und zieht unterstützende Evidenz aus mehreren Datenbanken heran. Anschließend gruppiert es Mutationen in Tiers basierend darauf, wie stark und handlungsrelevant die Evidenz ist, und erzeugt ein strukturiertes PDF sowie eine exportierbare Datendatei, die potenzielle Wirkstoffziele und klinische Studienoptionen hervorheben. In Tests an sechs realen Tumorproben identifizierte das System schnell bekannte krebstreibende Mutationen und Therapien, selbst wenn diese ursprünglich in anderen Krebsarten beschrieben wurden. Ein Begleitmodul namens server-maftools ermöglicht Forschenden, Hunderte oder Tausende von Proben gleichzeitig zu laden, Mutationsmuster zu visualisieren, Krebs-Subtypen zu vergleichen und bestimmte DNA-Veränderungen mit Überleben oder Tumorstadium zu verknüpfen.
Was das für Krebsversorgung und Forschung bedeutet
OncoRisk ist kein eigenständiges diagnostisches Gerät und ersetzt weder Expertenrichtlinien noch medizinisches Urteil. Vielmehr fungiert es als leistungsfähiger Assistent, der verstreute Evidenz sammelt, konsistent organisiert und die Verknüpfungen zwischen DNA-Veränderungen, Krebsarten, Medikamenten und Ergebnissen deutlich sichtbarer macht. Indem kuratiertes Expertenwissen mit realweltlichen Patientendaten vereint wird, zielt die Plattform darauf ab, den Weg vom Sequenzieren eines Tumors bis zur Benennung der relevantesten Fragen, Studien und Behandlungsoptionen zu verkürzen. Für Patientinnen und Patienten könnte das schnellere, klarere Erklärungen dessen bedeuten, was die Tumor-DNA aussagt; für Forschende bietet es eine einzige, flexible Umgebung, um mutationale Landschaften zu erkunden und neue Ideen über zahlreiche Kohorten hinweg zu testen.
Zitation: Song, X., Green, E., Liao, X. et al. OncoRisk: a state-of-the-art web server for bridging the oncogenic databases and pan-cancer cohorts to the translational oncology. Commun Biol 9, 519 (2026). https://doi.org/10.1038/s42003-026-10005-5
Schlüsselwörter: präzisionsonkologie, Krebsgenomik, Variantenauslegung, Bioinformatik-Plattform, pan-krebs Kohorten