Clear Sky Science · sv
Genetiskt modifierade Streptomyces viridosporus ATCC 14672-stammar för upptäckt av nya moenomyciner
Varför detta arbete är viktigt
Antibiotikaresistensen ökar så snabbt att många tidigare rutinartade infektioner blir svåra att behandla. Den här studien undersöker hur man kan finjustera ett kraftfullt men ofullkomligt antibiotikum, moenomycin, genom att omkonstruera jordbakterien som tillverkar det. Genom att ändra bakteriens gener framställer forskarna nya varianter av moenomycin som i förlängningen kan leda till bättre läkemedel för att bekämpa svårbehandlade, sjukhusförvärvade infektioner.
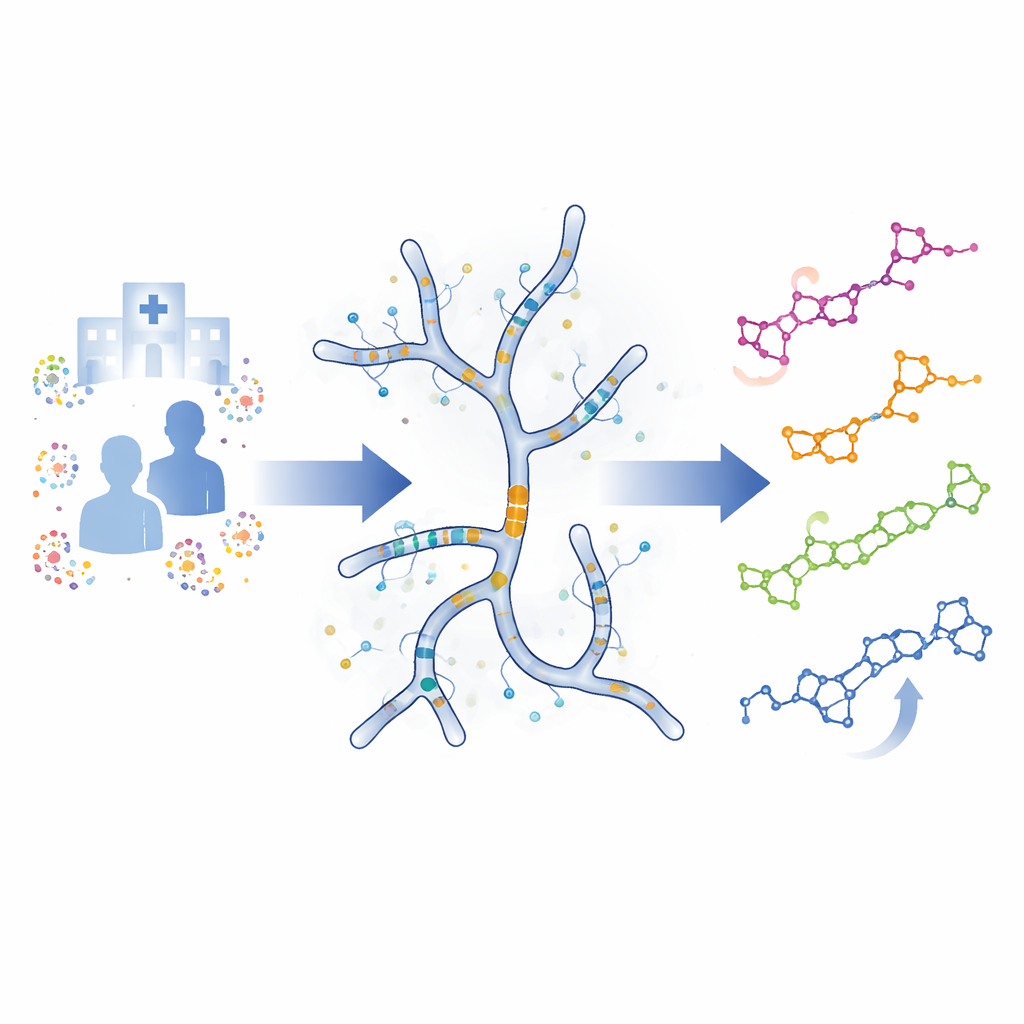
Ett kraftfullt men problematiskt antibiotikum
Moenomycin är en naturlig förening som produceras av bakterien Streptomyces viridosporus. Den blockerar ett avgörande steg i uppbyggnaden av bakteriens cellvägg och är det enda kända läkemedlet som träffar detta mål direkt vid extremt låga doser. Det har använts säkert i djur i årtionden utan utbredd resistens, vilket gör det mycket lockande som utgångspunkt för nya läkemedel för människor. Moenomycin har emellertid två stora nackdelar i kroppen: det tas inte upp vid oral administrering och det dröjer kvar länge i blodomloppet. Båda problemen är kopplade till dess ovanligt långa fettlösliga ”svans” bestående av 25 kolatomer.
Omarbetning av den bakteriella fabriken
Teamet fokuserade på generna som bygger denna svans i Streptomyces viridosporus-stam ATCC 14672, den mest studerade producenten av moenomycin. Två gener, kallade moeO5 och moeN5, utför tidiga steg som fäster och sedan förlänger lipid-svansen. Forskarnas använde moderna genetiska verktyg för att ta bort varje gen separat och skapade därigenom två nya bakteriestammar. En mutant, benämnd dO5, förlorade helt förmågan att tillverka några moenomyciner. Den andra, kallad M12, producerade fortfarande närbesläktade föreningar men med en kortare 15-kolatoms svans istället för den ursprungliga 25-kolatomsvarianten.
Att göra mutanter till upptäcktsverktyg
dO5-stammen, som inte kan starta byggandet av svansen själv, blev en ren testplatta för att prova utbytesgener från andra mikrober. När forskarna införde liknande gener från två andra antibiotikaproducerande bakterier återkom moenomycinproduktionen, vilket visar att dessa enzymer kan ersätta det saknade steget. Men en mer avlägsen släkting från en insektassocierad bakterie återställde inte aktiviteten, vilket antyder att den kan verka på andra utgångsmaterial eller ha en annan struktur. Datorbaserade strukturmodeller och evolutionära analyser stödde denna idé och grupperade detta enzym i en separat familj. Tillsammans visar dessa experiment att dO5 kan användas som en levande sensor för att avgöra om nya enzymer från genomdatabaser kan initiera moenomycinliknande kemi.
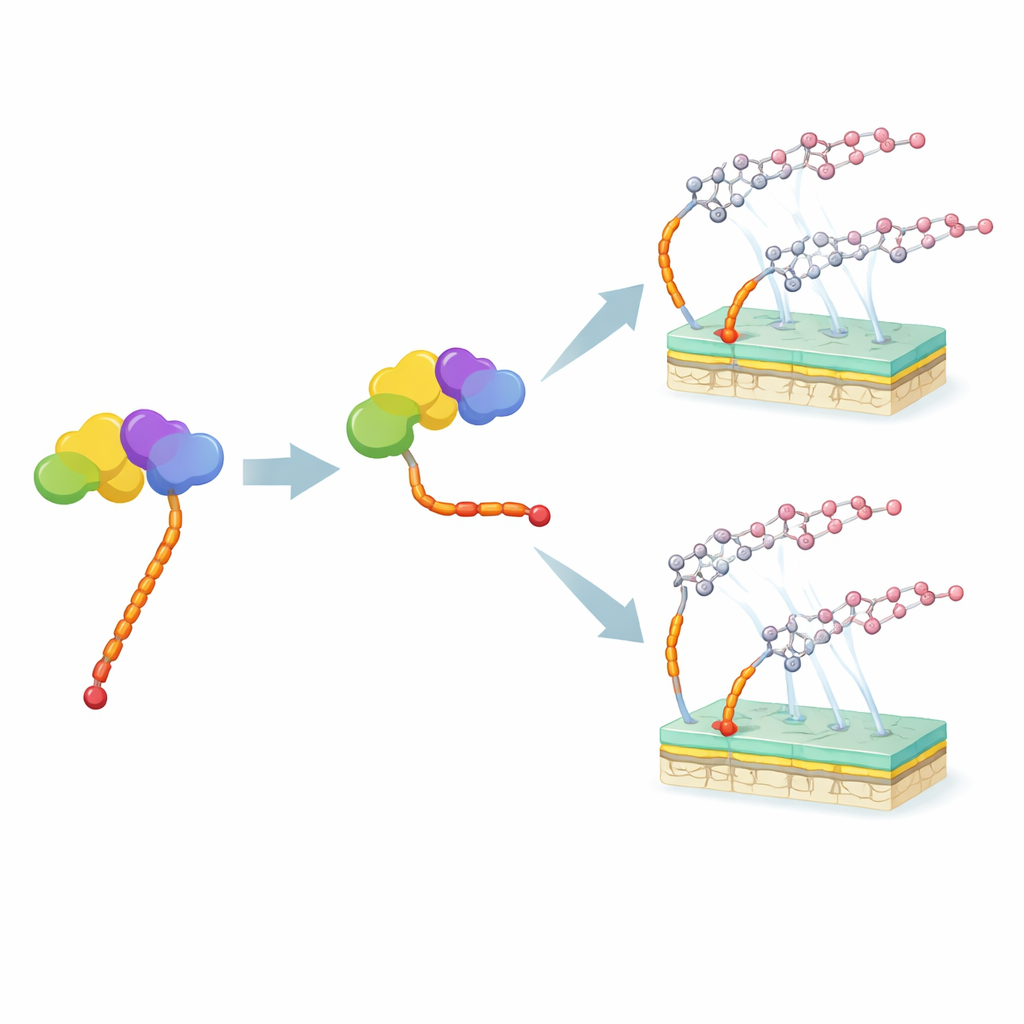
Nya molekyler med kortare svansar
M12-stammen, som saknar genen moeN5, gav en annan fördel: den ackumulerade naturligt nya moenomycinvarianter med kortare svans. Med avancerad masspektrometri identifierade forskarna två sådana föreningar, nära besläktade med kända medlemmar av moenomycinfamiljen men med en 15-kolatoms svans. De renade dessa molekyler och jämförde deras förmåga att stoppa tillväxten av patogenen Staphylococcus aureus med den ursprungliga moenomycinens. Versionerna med kortare svans var mycket mindre potenta—upp till hundra gånger svagare—även om vissa andra egenskaper på sockerdelen av molekylen delvis kunde återställa aktiviteten.
Vad detta betyder för framtida antibiotika
Detta arbete visar att en enkel förkortning av moenomycins svans, även om den är lockande för att förbättra läkemedlets farmakokinetiska egenskaper, kommer till ett högt pris i antibakteriell styrka. Samtidigt levererar studien två värdefulla genetiska verktyg: en stam som kan hysa och testa svansbyggande gener från många källor, och en annan som pålitligt producerar nya molekyler med kortare svans för detaljerad studie. Tillsammans bildar dessa konstruerade bakterier en plattform för att utforska ett brett spektrum av moenomycinliknande föreningar. Med tiden kan detta tillvägagångssätt hjälpa kemister och mikrobiologer att balansera potens med säkrare, mer hanterbara läkemedegenskaper och föra moenomycininspirerade antibiotika närmare klinisk användning.
Citering: Ostash, B., Makitrynskyy, R., Fedchyshyn, M. et al. Genetically engineered Streptomyces viridosporus ATCC 14672 strains for the discovery of novel moenomycins. Sci Rep 16, 12851 (2026). https://doi.org/10.1038/s41598-026-43988-6
Nyckelord: antibiotikaresistens, moenomycin, Streptomyces, genteknik, naturliga produkter