Clear Sky Science · fr
Souche de Streptomyces viridosporus ATCC 14672 génétiquement modifiée pour la découverte de nouveaux moénomycines
Pourquoi ce travail est important
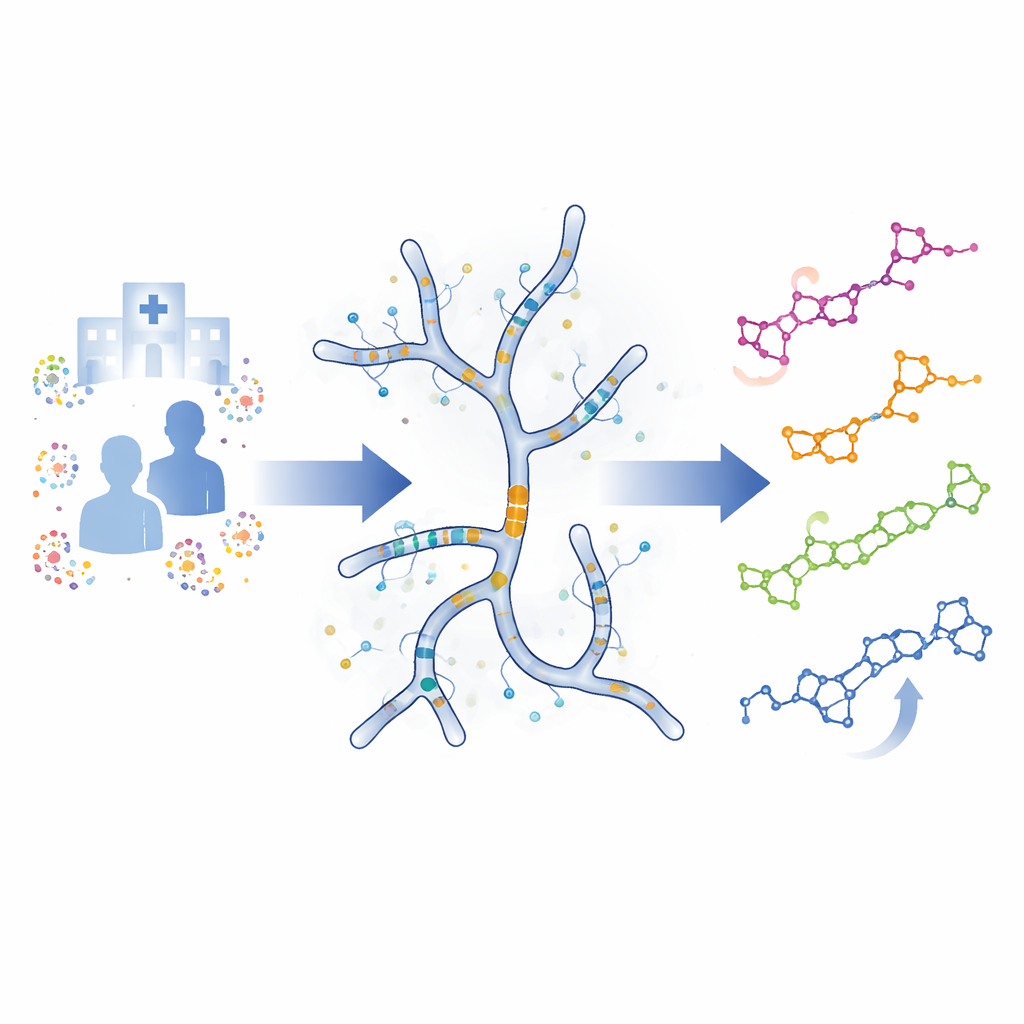
La résistance aux antibiotiques augmente si rapidement que de nombreuses infections autrefois banales deviennent difficiles à traiter. L’étude présentée ici explore comment modifier un antibiotique puissant mais imparfait, la moénomycine, en réingénierant la bactérie du sol qui la produit. En changeant les gènes de la bactérie, les chercheurs créent de nouvelles variantes de moénomycine qui pourraient, à terme, conduire à de meilleurs médicaments pour combattre les infections nosocomiales persistantes.
Un antibiotique puissant mais problématique
La moénomycine est un composé naturel produit par la bactérie Streptomyces viridosporus. Elle bloque une étape clé de la construction de la paroi bactérienne et est le seul médicament connu qui cible directement cette étape à des doses extrêmement faibles. Elle a été utilisée en toute sécurité chez les animaux pendant des décennies sans apparition massive de résistance, ce qui en fait un point de départ attractif pour de nouveaux médicaments humains. Cependant, la moénomycine présente deux inconvénients majeurs dans notre organisme : elle n’est pas absorbée par voie orale et elle persiste longtemps dans le sang. Ces deux problèmes sont liés à sa « queue » anormalement longue et hydrophobe composée de 25 atomes de carbone.
Redessiner l’usine bactérienne
L’équipe s’est concentrée sur les gènes qui construisent cette queue dans Streptomyces viridosporus souche ATCC 14672, le producteur de moénomycine le mieux étudié. Deux gènes, appelés moeO5 et moeN5, réalisent les premières étapes qui attachent puis allongent la chaîne lipidique. Les chercheurs ont utilisé des outils génétiques modernes pour supprimer chaque gène séparément, créant ainsi deux nouvelles souches bactériennes. Un mutant, nommé dO5, a totalement perdu la capacité de fabriquer des moénomycines. L’autre, appelé M12, produisait encore des composés apparentés mais avec une queue plus courte de 15 carbones au lieu des 25 d’origine.
Transformer les mutants en outils de découverte
La souche dO5, qui ne peut pas démarrer la construction de la queue par elle‑même, est devenue un terrain d’essai propre pour tester des gènes de remplacement venant d’autres microbes. Lorsque les scientifiques ont introduit des gènes similaires issus de deux autres bactéries productrices d’antibiotiques, la production de moénomycine a repris, montrant que ces enzymes peuvent suppléer l’étape manquante. Mais un parent plus éloigné issu d’une bactérie associée aux insectes n’a pas restauré l’activité, suggérant qu’il agit sur des précurseurs différents ou qu’il a une forme différente. Des modèles structuraux informatiques et des analyses évolutives ont confirmé cette idée en regroupant cette enzyme dans une famille distincte. Ensemble, ces expériences montrent que dO5 peut servir de capteur vivant pour déterminer si de nouvelles enzymes issues de bases de données génomiques sont capables d’initier une chimie de type moénomycine.
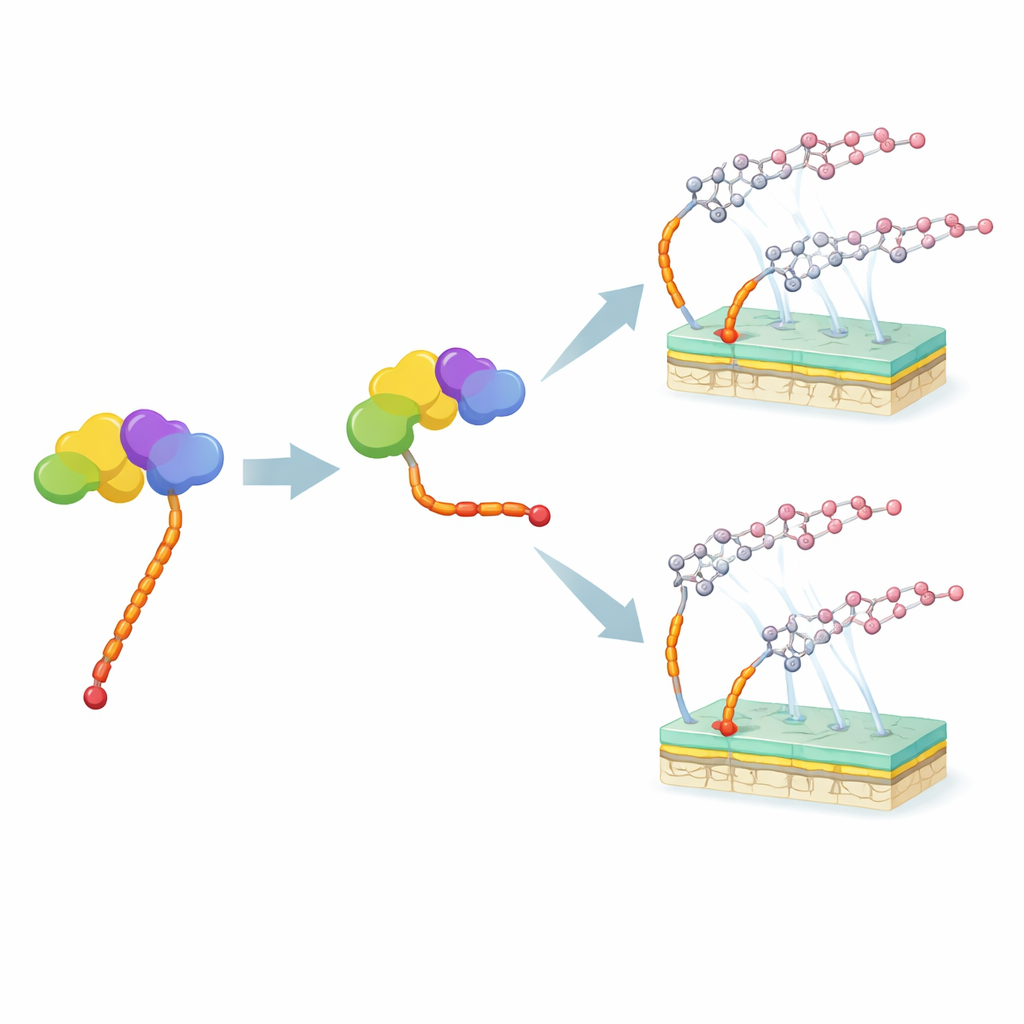
Nouvelles molécules à queues raccourcies
La souche M12, dépourvue du gène moeN5, offrait un autre avantage : elle accumulait naturellement de nouvelles variantes de moénomycine avec une queue plus courte. Grâce à la spectrométrie de masse avancée, les chercheurs ont identifié deux de ces composés, proches des membres connus de la famille des moénomycines mais portant la chaîne à 15 carbones. Ils ont purifié ces molécules et comparé leur capacité à inhiber la croissance du pathogène Staphylococcus aureus à celle de la moénomycine originale. Les versions à queue plus courte étaient beaucoup moins puissantes — jusqu’à cent fois moins actives — bien que certaines caractéristiques de la partie sucre de la molécule puissent en restaurer partiellement l’activité.
Ce que cela implique pour les antibiotiques futurs
Ce travail montre que le simple raccourcissement de la queue de la moénomycine, certes attractif pour améliorer le comportement pharmacologique, entraîne un coût élevé en termes d’activité antibactérienne. En parallèle, l’étude fournit deux outils génétiques précieux : une souche capable d’accueillir et de tester des gènes de construction de queue issus de nombreuses sources, et une autre qui produit de façon fiable de nouvelles molécules à queue raccourcie pour des études détaillées. Ensemble, ces bactéries modifiées constituent une plateforme pour explorer un large éventail de composés apparentés à la moénomycine. Avec le temps, cette approche pourrait aider chimistes et microbiologistes à trouver un équilibre entre puissance et propriétés pharmacologiques plus sûres et maniables, rapprochant les antibiotiques inspirés de la moénomycine d’une utilisation clinique.
Citation: Ostash, B., Makitrynskyy, R., Fedchyshyn, M. et al. Genetically engineered Streptomyces viridosporus ATCC 14672 strains for the discovery of novel moenomycins. Sci Rep 16, 12851 (2026). https://doi.org/10.1038/s41598-026-43988-6
Mots-clés: résistance aux antibiotiques, moénomycine, Streptomyces, génie génétique, produits naturels