Clear Sky Science · sv
En preklinisk CT- och MRI-datamängd för leveravbildning med anatomiska, funktionella och segmenteringsdata
Varför detta spelar roll för leversjukdom och medicinsk avbildning
Kroniska leversjukdomar som fettlever, fibros och levercancer ökar globalt, men mycket av den detaljerade forskningsdata som skulle kunna påskynda nya diagnostiska verktyg och behandlingar är låst i enskilda laboratorier. Denna artikel presenterar en sällsynt resurs: en stor, öppet delad samling CT- och MRI-skanningar från möss med olika leversjukdomar, tillsammans med precisa organavgränsningar och rik metadata. Genom att göra dessa data fritt tillgängliga vill författarna snabba på avbildningsforskning, förbättra datorverktyg för att tolka skanningar och i slutändan stödja mindre invasiva sätt att övervaka leverhälsa.
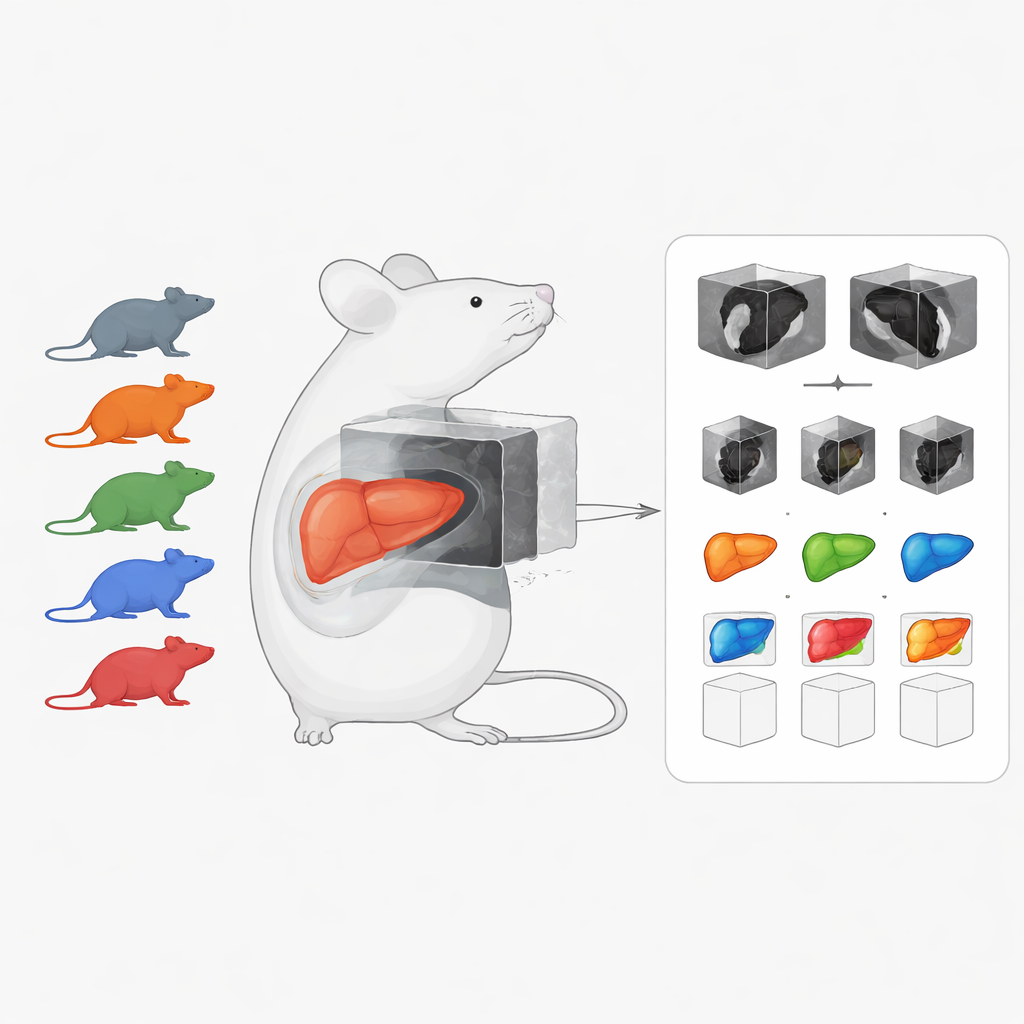
Ett delat bildbibliotek med sjuka och friska lever
Kärnan i arbetet är en kurerad preklinisk avbildningsdatamängd med fokus på kronisk leversjukdom hos möss. Den kombinerar 222 tredimensionella CT- och MRI-skanningar som täcker flera vanliga tillstånd: levercancer (hepatocellulärt karcinom), fett- och inflammerad lever (metabol funktionsrelaterad steatohepatit, eller MASH) och leverfibros, plus skanningar från friska djur. Till skillnad från många befintliga resurser för museavbildning som riktar sig mot friska organ eller enskilda avbildningsmetoder, betonar denna samling sjuka lever och förenar olika skanningstyper på ett ställe. Många skanningar åtföljs av handritade organkonturer, så kallade segmenteringar, vilka är avgörande för att träna och testa datoralgoritmer.
Flera skanningstyper för att fånga struktur och funktion
Datamängden bygger på fem separata djurstudier som poolats för att täcka ett brett spektrum av leverskador och avbildningsansatser. I en studie utvecklade mössen levercancer i en kroniskt skadad lever, och högfälts-MRI användes upprepade gånger över veckor för att följa hur tumörer uppstod och växte. En annan studie använde ”multiparametrisk” MRI, där varje mus genomgick flera typer av skanningar: vissa som framhäver anatomin, andra som mäter hur vatten diffunderar genom vävnad, och ytterligare som spårar hur injicerade kontrastmedel rör sig genom levern. Dessa olika mätningar ger information om viktiga egenskaper som ärrbildning, fettinnehåll, levercellsfunktion, vävnadsskada och immuncellsaktivitet.
CT-skanningar för att kartlägga kroppsfett, leverstorlek och genetik
För att komplettera MRI lade författarna till flera CT-baserade studier. I en studie fick möss en västerländsk högfettkost, med eller utan havre-beta-glukan, en kostfiber som antas skydda levern. Helkropps-CT användes för att mäta levervolym och fettfördelning, och leverna ritades manuellt ut för noggranna volymuppskattningar. En andra CT-studie undersökte möss som saknade ett funktionellt ICAM-1-gen, som är involverad i inflammation, för att se hur denna genetiska förändring påverkade fettfördelning och leverstorlek när djuren fodrades med högfettkost. I båda CT-studierna segmenterades kroppsfett, lever och andra strukturer så att forskare direkt kan analysera hur diet och gener formar organsstorlek och kroppssammansättning.
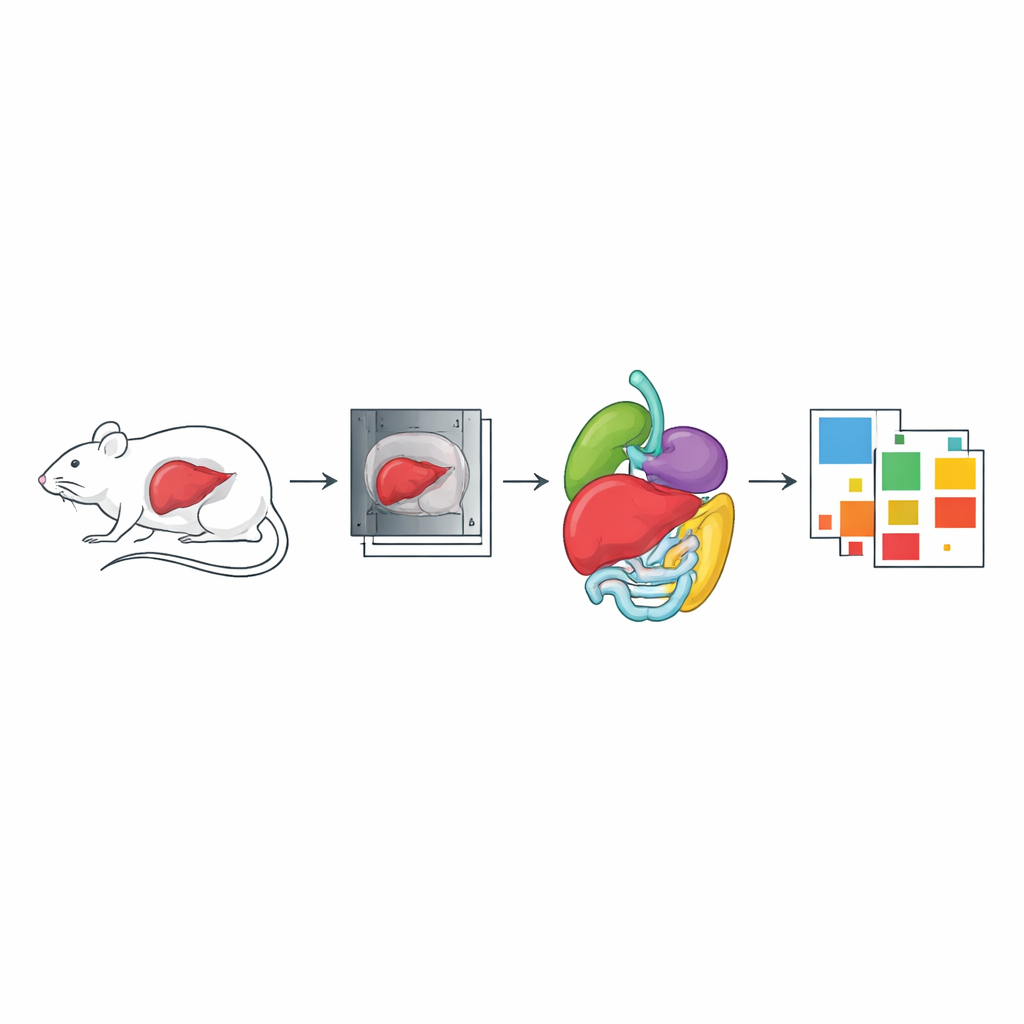
Att koppla ihop CT och MRI i samma djur
En annan del av datamängden fokuserar på friska nakna möss som skannades med både CT och MRI i samma avbildningshållare. Målet här var att skapa överlappande vyer av samma anatomi så att bilder från de två teknikerna kan aligneras exakt. Djuren skannades med helkropps-CT och därefter med en special-MRI-sekvens som separerar vatten- och fettsignaler. Många organ — inklusive lever, lungor, hjärta, njurar, mjälte, magsäck, tarmar, hjärna och ryggmärg — segmenterades i antingen CT, MRI eller båda. Sådana parade skanningar är värdefulla för uppgifter som att bygga dämpningskartor för PET-MR-skannrar och för att testa bildregistreringsmetoder som justerar olika avbildningsmodaliteter.
Rik metadata för att stödja återanvändning och reproducerbarhet
Utöver bilderna själva investerade författarna stort i standardiserad metadata så att andra kan förstå och återanvända datan. För varje djur och skanning registrerar de information såsom musstam, ålder, sjukdomsmodell, avbildningsmodalitet, apparatmärke, kontrastmedel och exakta skanningsinställningar som fält av vy, voxelformat och tidpunkter. Organsegmenteringar kopplas till tydliga definitioner av vad varje etikett representerar (till exempel lever, visceralt fett, blåsa eller ryggrad). All denna information lagras i ISA-Tab-filer enligt en skräddarsydd metadataprofil, och hela paketet ligger värd på Zenodo som öppna data. Skanningarna tillhandahålls i standardiserade medicinska format (DICOM eller NIfTI) med segmenteringar i allmänt använda filtyper för segmentering.
Hur denna resurs kan påskynda framtida upptäckter
För en allmän läsare är huvudpoängen att detta arbete inte presenterar ett nytt läkemedel eller diagnostiskt test, utan bygger grunden för många sådana framsteg. Genom att släppa ett stort, välannoterat bibliotek av lever-CT och MRI-skanningar hos möss gör författarna det lättare för forskare att träna datormodeller som automatiskt ritar organkonturer, upptäcker tumörer eller förutser hur leversjukdom kommer att utvecklas — utan att behöva utsätta nya djur för varje experiment. Datamängden kan fungera som referens för avbildningsstudier, minska redundant djuranvändning och stödja öppen, reproducerbar vetenskap. Kort sagt förvandlar den år av specialiserat avbildningsarbete till en delad gemenskapsresurs för att tackla kronisk leversjukdom.
Citering: Schraven, S., Gonzalez, C., Baskaya, F. et al. A preclinical CT and MRI Liver Imaging Dataset with Anatomical, Functional and Segmentation Data. Sci Data 13, 446 (2026). https://doi.org/10.1038/s41597-026-07003-x
Nyckelord: kronisk leversjukdom, preklinisk avbildning, MRI, CT, musmodeller