Clear Sky Science · fr
Un jeu de données préclinique d’imagerie hépatique CT et IRM avec données anatomiques, fonctionnelles et de segmentation
Pourquoi cela compte pour les maladies du foie et l’imagerie médicale
Les maladies chroniques du foie, comme la stéatose, la fibrose et le cancer du foie, augmentent partout dans le monde, mais une grande partie des données détaillées susceptibles d’accélérer le développement de nouveaux diagnostics et traitements reste confinée dans des laboratoires isolés. Cet article présente une ressource rare : une grande collection partagée de scans CT et IRM de souris atteintes de différentes maladies hépatiques, accompagnée de contours d’organes précis et de métadonnées riches. En rendant ces données librement accessibles, les auteurs visent à accélérer la recherche en imagerie, améliorer les outils informatiques d’analyse des images et, à terme, favoriser des méthodes moins invasives pour surveiller la santé du foie.
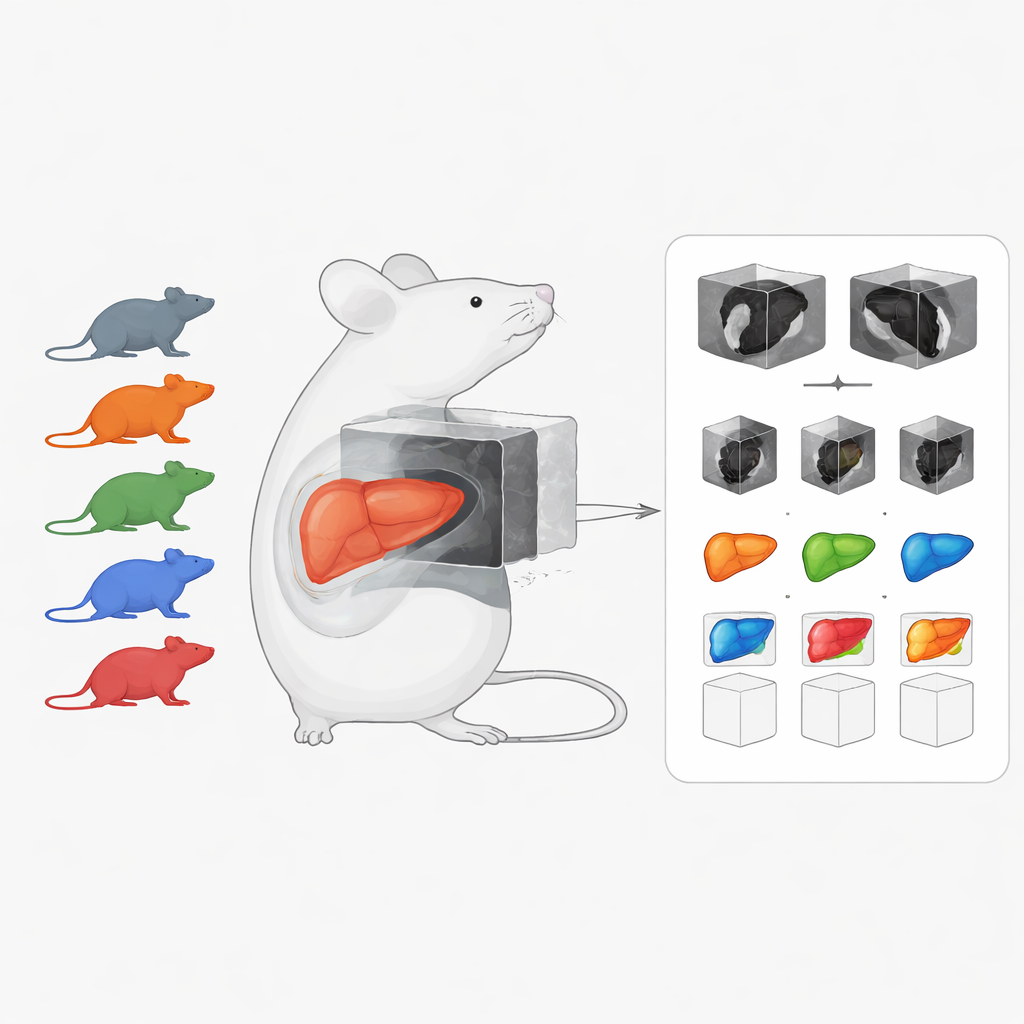
Une bibliothèque partagée de foies malades et sains
Le cœur du travail est un jeu de données d’imagerie préclinique soigneusement sélectionné, axé sur les maladies hépatiques chroniques chez la souris. Il regroupe 222 scans tridimensionnels CT et IRM couvrant plusieurs affections courantes : cancer du foie (carcinome hépatocellulaire), foie gras et inflammatoire (stéatohépatite associée à un dysfonctionnement métabolique, ou MASH), et fibrose hépatique, ainsi que des scans d’animaux sains. Contrairement à de nombreuses ressources murines existantes qui ciblent des organes sains ou une seule modalité d’imagerie, cette collection met l’accent sur les foies malades et réunit différents types de scans au même endroit. De nombreux scans sont accompagnés de contours d’organes dessinés à la main, appelés segmentations, essentiels pour l’entraînement et l’évaluation des algorithmes informatiques.
Plusieurs types de scans pour capter structure et fonction
Le jeu de données est construit à partir de cinq études animales distinctes regroupées pour couvrir une large gamme de lésions hépatiques et d’approches d’imagerie. Dans une étude, les souris ont développé un cancer du foie dans un foie chroniquement lésé, et une IRM haute intensité a été utilisée de manière répétée sur plusieurs semaines pour suivre l’apparition et la croissance des tumeurs. Une autre étude a employé une IRM « multiparamétrique », dans laquelle chaque souris a subi plusieurs types de scans : certains mettant en évidence l’anatomie, d’autres mesurant la diffusion de l’eau dans les tissus, et d’autres encore suivant le mouvement d’agents de contraste injectés dans le foie. Ces différentes mesures rendent compte de caractéristiques clés comme la cicatrisation, la teneur en graisses, la fonction hépatocytaire, les lésions tissulaires et l’activité des cellules immunitaires.
Scans CT pour cartographier la graisse corporelle, le volume hépatique et la génétique
Pour compléter l’IRM, les auteurs ont ajouté plusieurs études basées sur la tomodensitométrie (CT). Dans l’une d’elles, des souris ont été nourries avec un régime occidental riche en graisses, avec ou sans bêta-glucane d’avoine, une fibre alimentaire supposée protéger le foie. Des scans CT du corps entier ont été utilisés pour mesurer le volume du foie et la répartition des graisses, et les foies ont été délimités manuellement pour estimer précisément les volumes. Une seconde étude CT a examiné des souris dépourvues d’un gène ICAM-1 fonctionnel, impliqué dans l’inflammation, pour évaluer comment cette modification génétique influençait la répartition des graisses et la taille du foie lorsque les animaux étaient alimentés avec un régime riche en graisses. Dans les deux études CT, la graisse corporelle, le foie et d’autres structures ont été segmentés afin que les chercheurs puissent analyser directement comment l’alimentation et la génétique façonnent la taille des organes et la composition corporelle.
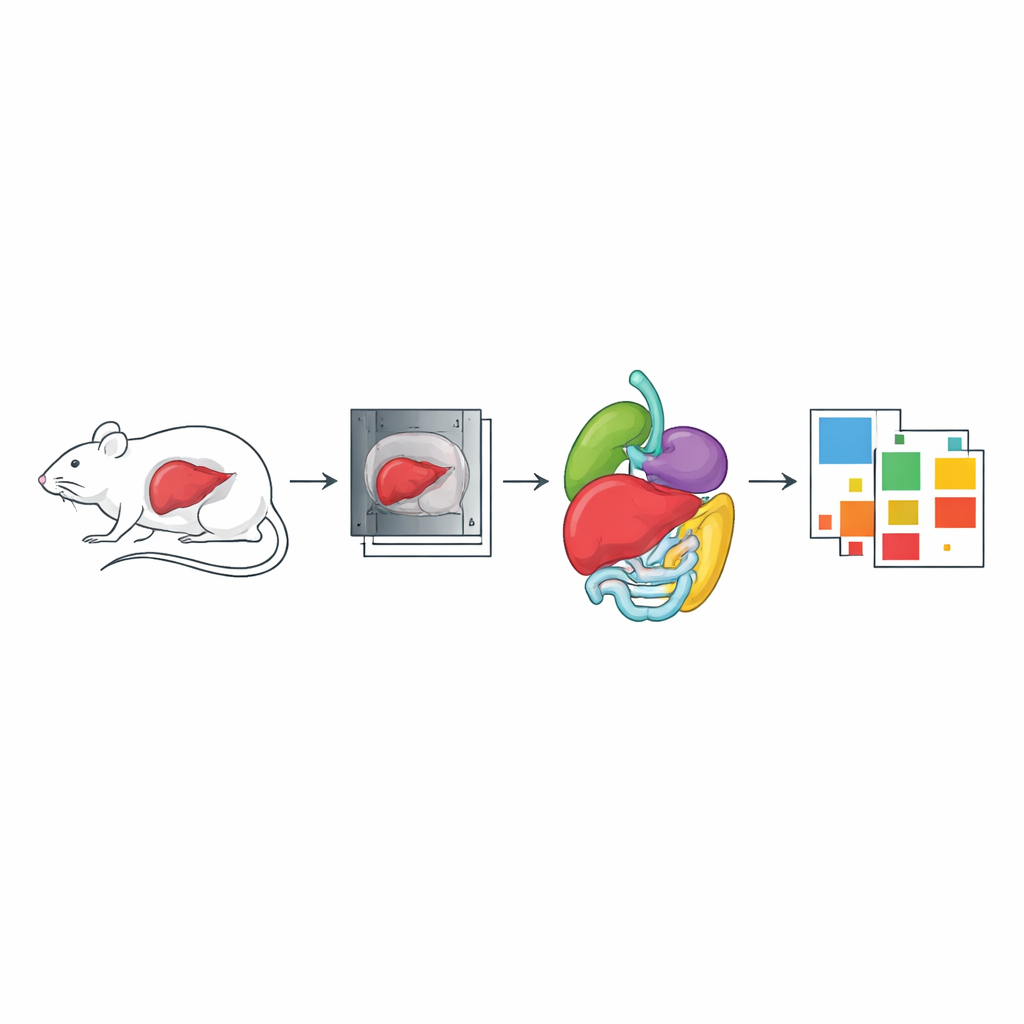
Relier CT et IRM chez les mêmes animaux
Un autre volet du jeu de données se concentre sur des souris nues saines scannées à la fois en CT et en IRM dans le même dispositif d’imagerie. L’objectif était de créer des vues superposables de la même anatomie afin que les images des deux technologies puissent être alignées de façon précise. Les animaux ont d’abord été scannés en CT corps entier, puis avec une séquence IRM spéciale qui sépare les signaux d’eau et de graisse. De nombreux organes — notamment le foie, les poumons, le cœur, les reins, la rate, l’estomac, les intestins, le cerveau et la moelle épinière — ont été segmentés en CT, IRM ou les deux. Ces scans appariés sont précieux pour des tâches telles que la construction de cartes d’atténuation pour les scanners PET-MR et pour tester des méthodes d’enregistrement d’images qui alignent différentes modalités d’imagerie.
Métadonnées riches pour soutenir la réutilisation et la reproductibilité
Au-delà des images elles-mêmes, les auteurs ont investi massivement dans des métadonnées standardisées afin que d’autres puissent comprendre et réutiliser les données. Pour chaque animal et chaque scan, ils enregistrent des informations telles que la souche de souris, l’âge, le modèle de maladie, la modalité d’imagerie, la marque de l’appareil, les agents de contraste et les paramètres de scan exacts comme le champ de vue, la taille des voxels et le calendrier temporel. Les segmentations d’organes sont reliées à des définitions claires de ce que représente chaque étiquette (par exemple, foie, graisse viscérale, vessie ou colonne vertébrale). Toutes ces informations sont stockées dans des fichiers ISA-Tab suivant un profil de métadonnées adapté, et l’ensemble est hébergé sur Zenodo en données ouvertes. Les scans sont fournis dans des formats médicaux standard (DICOM ou NIfTI) avec des segmentations dans des types de fichiers de segmentation largement utilisés.
Comment cette ressource peut accélérer les découvertes futures
Pour un lecteur non spécialiste, l’essentiel est que ce travail ne présente pas un nouveau médicament ni un nouveau test diagnostique, mais pose les bases de nombreuses avancées possibles. En publiant une grande bibliothèque bien annotée de scans CT et IRM du foie chez la souris, les auteurs facilitent l’entraînement de modèles informatiques capables de délimiter automatiquement les organes, détecter les tumeurs ou prédire l’évolution des maladies du foie — sans soumettre de nouveaux animaux à chaque expérience. Le jeu de données peut servir de référence pour les études d’imagerie, réduire l’usage redondant d’animaux et soutenir une science ouverte et reproductible. En bref, il convertit des années de travaux d’imagerie spécialisés en un actif communautaire partagé pour lutter contre les maladies hépatiques chroniques.
Citation: Schraven, S., Gonzalez, C., Baskaya, F. et al. A preclinical CT and MRI Liver Imaging Dataset with Anatomical, Functional and Segmentation Data. Sci Data 13, 446 (2026). https://doi.org/10.1038/s41597-026-07003-x
Mots-clés: maladie hépatique chronique, imagerie préclinique, IRM, CT, modèles murins