Clear Sky Science · sv
Återskapa enkelcellsupplösning från spatial transkriptomik med CellRefiner
Se celler i deras omgivningar
Modern biologi kan nu läsa den genetiska aktiviteten i hundratusentals enskilda celler samtidigt, men förlorar ofta spåret av var dessa celler faktiskt befinner sig i en vävnad. Samtidigt kan nya ”spatiala” metoder kartlägga genaktivitet över en vävnadsskiva, men de suddar vanligen ihop flera celler i varje mätpunkt. Den här artikeln presenterar CellRefiner, en beräkningsmetod som kombinerar styrkorna från båda världarna för att rekonstruera var enskilda celler är lokaliserade och hur de vidrör varandra i verkliga vävnader. Resultatet är en mycket skarpare bild av hur celler är arrangerade och hur de kommunicerar, särskilt i hjärnan, lymfkörtlar och tumörer.
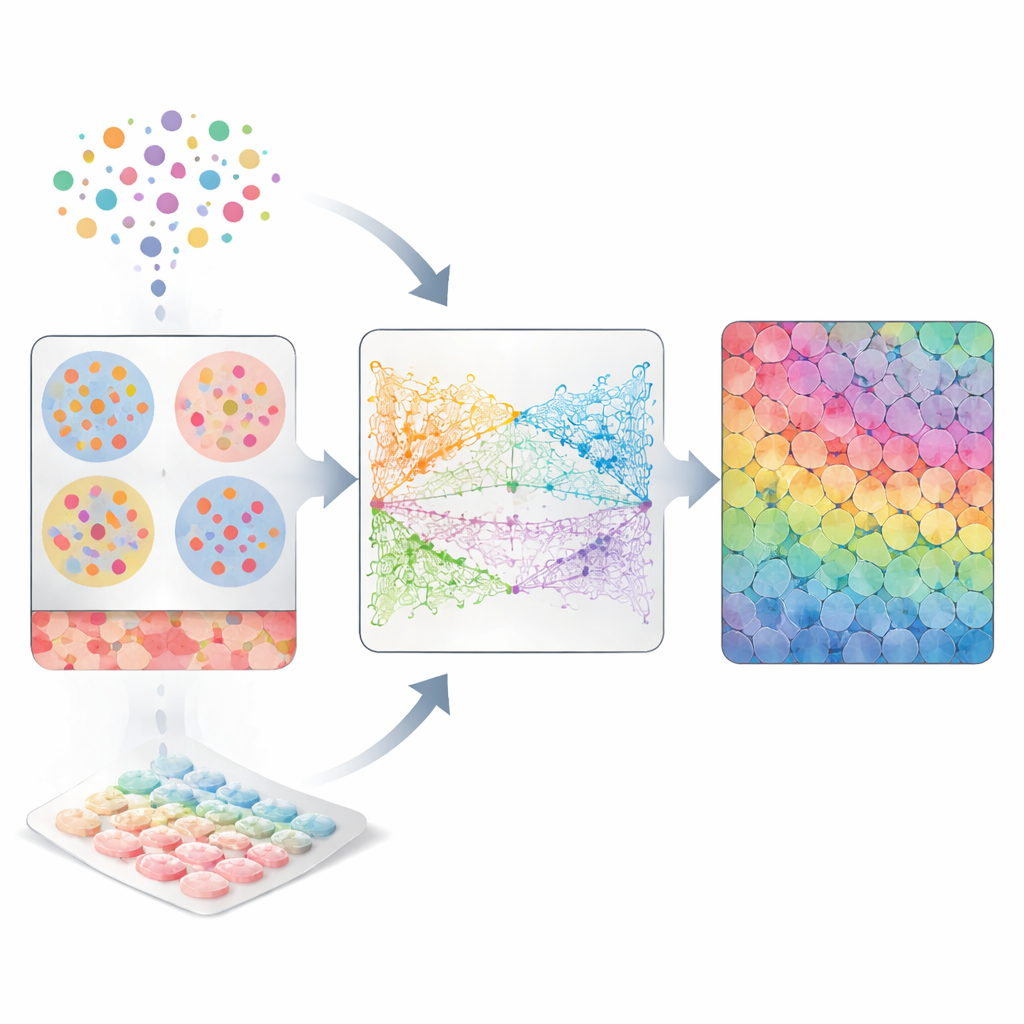
Två ofullständiga vyer av levande vävnader
Biologer använder ofta single-cell RNA-sekvensering för att fånga vilka gener som är aktiva i enskilda celler. För att göra detta måste vävnaden lösas upp, så att varje cell blir en fritt flytande enhet med rik molekylär information men utan adress. Spatial transkriptomik tar motsatt ansats: den håller cellerna på plats på ett preparat och läser av genaktivitet i små punkter över vävnaden. Dock innehåller varje punkt ofta flera blandade celler, och många bildbaserade plattformar mäter bara en delmängd av generna. Som en följd kan ingen av teknikerna ensamma fullt ut besvara frågor som kräver att man vet både vad varje cell gör och exakt var den sitter, till exempel vilka celler som är grannar eller vilka par som är i fysisk kontakt.
En fysikinspirerad kartmakare för celler
CellRefiner tar itu med detta glapp genom att behandla celler som små interagerande partiklar som kan röra sig inom vävnaden tills de hamnar i realistiska positioner. Först använder metoden befintliga verktyg för att ungefärligen tilldela grupper av enskilda celler till varje spatial punkt baserat på hur lika deras genaktivitet är det som mäts i den punkten. Dessa tilldelade celler är initialt utspridda slumpmässigt inom varje punkt. Därefter applicerar CellRefiner tre typer av virtuella ”krafter” för att gradvis omorganisera dem: en kraft hindrar celler från att överlappa eller lämna tomma luckor, en annan drar försiktigt ihop celler med liknande genaktivitet, och en valfri tredje kraft drar ihop celler som visar matchande ”sändar”‑ och ”mottagar”‑molekyler som används i cell‑till‑cell‑signalering. Över flera iterationer förfinar denna simulering en grov punkt‑nivåbild till en trovärdig karta på enkelcellsnivå.
Testning av metoden över många vävnader
För att kontrollera om CellRefiner återskapar realistiska strukturer skapade författarna först testdatamängder där cellernas verkliga positioner var kända. De utgick från högupplösta bildbaserade data där varje cell är individuellt kartlagd och suddade sedan konstlat ner dessa data till lägre upplösningspunkter som efterliknar populära spatiala plattformar. Genom att mata in endast den nedsuddade versionen plus originalprofilernas single-cell-data till CellRefiner undersökte de hur väl metoden kunde rekonstruera den ursprungliga finskaliga kartan. Med flera mått på spatial felmarginal förbättrade CellRefiner konsekvent cellplaceringen jämfört med de initiala grova tilldelningarna och övertrumfade andra ledande metoder över flera dataset från musens hjärnregioner och andra vävnader. Den fångade skarpa strukturer såsom smala band av ependymala celler, lager i hippocampus och kortikala lager mer troget än konkurrerande tillvägagångssätt.
Från punkter till former och samtal
Utöver att bara placera cellcentra kan CellRefiner även rekonstruera ungefärliga cellformer. Den representerar varje cell som en samling av många små element förbundna med virtuella fjädrar, vilka svarar på tryck- och dragkrafter mellan närliggande celler. Detta gör det möjligt för metoden att härleda vilka celler som är i direkt fysikaliskt kontakt, ett centralt krav för att studera kontaktbaserad signalering där molekyler på en cells yta binder till partner på en intilliggande cell. När metoden tillämpades på högupplösta bilddataset matchade de rekonstruerade formerna väl de observerade cellegrenserna och återvann realistiska kontaktnätverk. Tillämpad på lägre upplösta plattformar som Visium producerade CellRefiner detaljerade kontaktkartor som den ursprungliga punktdata inte kan tillhandahålla.
Avslöja dold signalering i hjärnan och cancer
Med sina förfinade kartor och kontaktnät kunde CellRefiner återupptäcka kända signaleringsmönster i human skivepitelcancer och i muscortex. I tumörer framhävde metoden signaleringssystem involverade i celladhesion, blodkärlsbildning och interaktioner vid tumörgränsen, inklusive vägar som hjälper cancerceller att hålla ihop eller att interagera med sin omgivning. I musens hjärna visade CellRefiner strukturerad signalering mellan kortikala lager och specifika klasser av interneuroner, vilket stöder roller i neuronmigration, kretskoppling och synapsbildning. Viktigt är att metoden visade att vad som ser ut som stark signalering i en enskild blandad punkt faktiskt kan uppstå från endast en delmängd av cellerna inom den punkten, vilket blottlägger dold mångfald i hur närliggande celler svarar.
Skarpare vävnadskartor för framtidens biologi
I grunden förvandlar CellRefiner suddiga spatiala mätningar till detaljerade kartor där varje cell både har en molekylär identitet och en realistisk position och form. Denna skarpare vy möjliggör mer tillförlitliga studier av hur celler är organiserade, hur de klustrar sig i lager och regioner och hur de kommunicerar genom direkt kontakt. Även om metoden är beroende av insignalernas kvalitet och gör förenklande antaganden om celldensitet och storlek, erbjuder den ett flexibelt, fysikinspirerat ramverk som kan utvidgas till andra molekylära lager såsom proteiner eller kromatin. För icke‑specialister representerar CellRefiner ett steg mot virtuella mikroskop som visar inte bara var celler är, utan hur de interagerar som dynamiska gemenskaper i levande vävnader.
Citering: Bourgain-Chang, E., Kuang, X., Cang, Z. et al. Reconstructing single-cell resolution from spatial transcriptomics with CellRefiner. Nat Commun 17, 3304 (2026). https://doi.org/10.1038/s41467-026-70090-2
Nyckelord: spatial transkriptomik, single-cell RNA-sekvensering, cell-till-cell-kommunikation, beräkningsbiologi, tumörmikromiljö