Clear Sky Science · de
Rekonstruktion einzelzellulärer Auflösung aus räumlicher Transkriptomik mit CellRefiner
Zellen in ihrem Umfeld sehen
Die moderne Biologie kann inzwischen die genetische Aktivität von Hunderttausenden einzelner Zellen gleichzeitig lesen, verliert dabei aber oft die Information, wo sich diese Zellen im Gewebe befinden. Gleichzeitig können neue "räumliche" Methoden die Genaktivität über einen Gewebeschnitt kartieren, verwischen dabei jedoch typischerweise mehrere Zellen in jeder Messung. Dieser Artikel stellt CellRefiner vor, einen rechnerischen Ansatz, der die Stärken beider Welten kombiniert, um zu rekonstruieren, wo einzelne Zellen liegen und wie sie sich innerhalb realer Gewebe berühren. Das Ergebnis ist ein deutlich schärferes Bild der Anordnung von Zellen und ihrer Kommunikation, insbesondere im Gehirn, in Lymphknoten und in Tumoren.
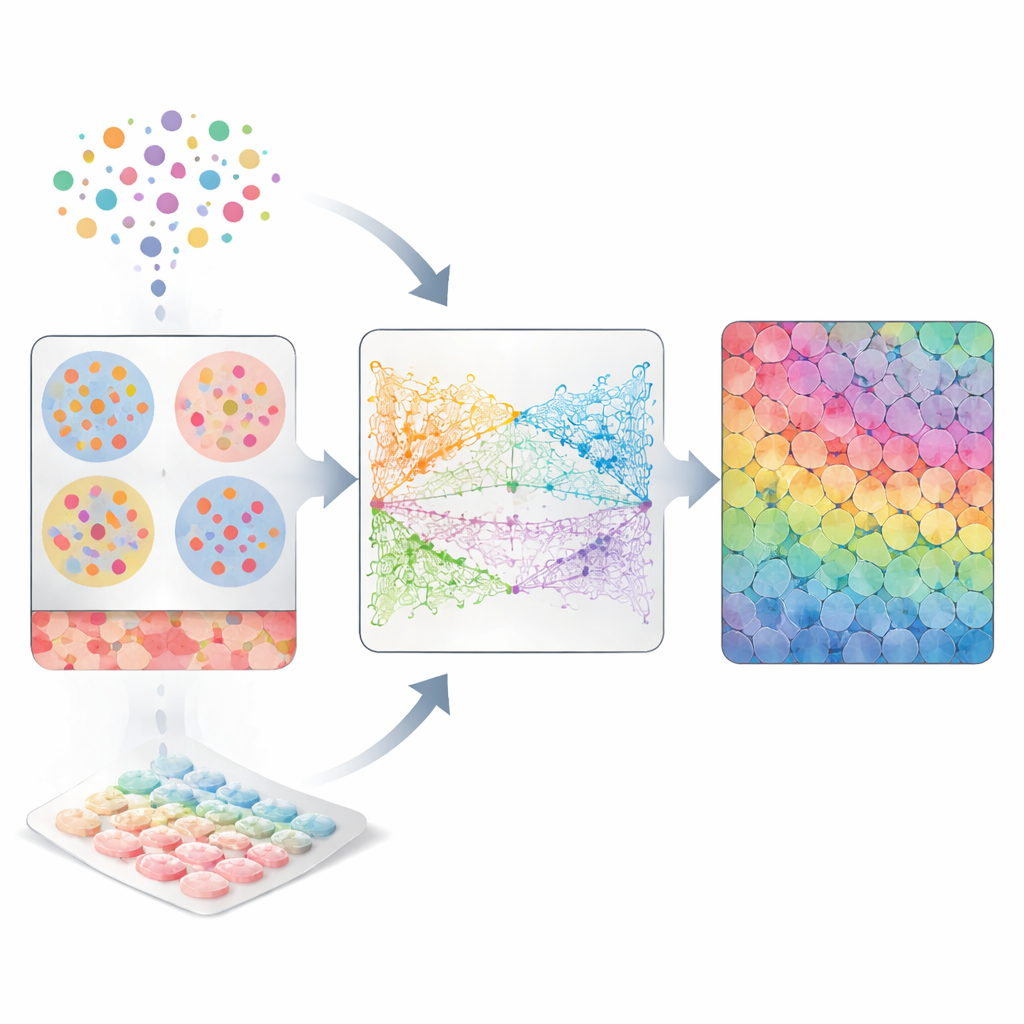
Zwei unvollkommene Blickwinkel auf lebendes Gewebe
Biologinnen und Biologen nutzen häufig die Einzelzell-RNA-Sequenzierung, um festzustellen, welche Gene in einzelnen Zellen aktiviert sind. Dazu muss Gewebe zerkleinert werden, sodass jede Zelle eine frei schwimmende Einheit mit reichhaltiger molekularer Information, aber ohne Ortsangabe wird. Die räumliche Transkriptomik verfolgt den umgekehrten Ansatz: Sie belässt Zellen an ihrem Platz auf einem Objektträger und liest die Genaktivität in kleinen Punkten über das Gewebe hinweg aus. Allerdings enthält jeder Punkt oft mehrere gemischte Zellen, und viele bildgebende Plattformen messen nur eine Teilmenge der Gene. Daher kann keine der beiden Technologien allein vollständig Fragen beantworten, die sowohl wissen müssen, was jede Zelle tut, als auch genau wo sie sitzt — etwa welche Zellen Nachbarn sind oder welche Paare physischen Kontakt haben.
Ein physik-inspirierter Kartograph für Zellen
CellRefiner schließt diese Lücke, indem es Zellen wie winzige interagierende Teilchen behandelt, die sich innerhalb des Gewebes bewegen können, bis sie realistische Positionen einnehmen. Zunächst verwendet es bestehende Methoden, um Gruppen von Einzelzellen grob den räumlichen Punkten zuzuordnen, basierend auf der Ähnlichkeit ihrer Genaktivität mit dem, was in diesem Punkt gemessen wurde. Diese zugeordneten Zellen werden anfänglich zufällig innerhalb jedes Punkts verteilt. Dann wendet CellRefiner drei Arten virtueller "Kräfte" an, um sie schrittweise umzuordnen: eine Kraft verhindert Überlappung oder das Entstehen leerer Lücken, eine andere zieht Zellen mit ähnlicher Genaktivität sanft zusammen, und eine optionale dritte Kraft verbindet Zellen, die passende "Sender"- und "Empfänger"-Moleküle für Zell-zu-Zell-Signale zeigen. Über mehrere Iterationen verwandelt diese Simulation ein grobes punktbasiertes Bild in eine plausible Einzelzellkarte.
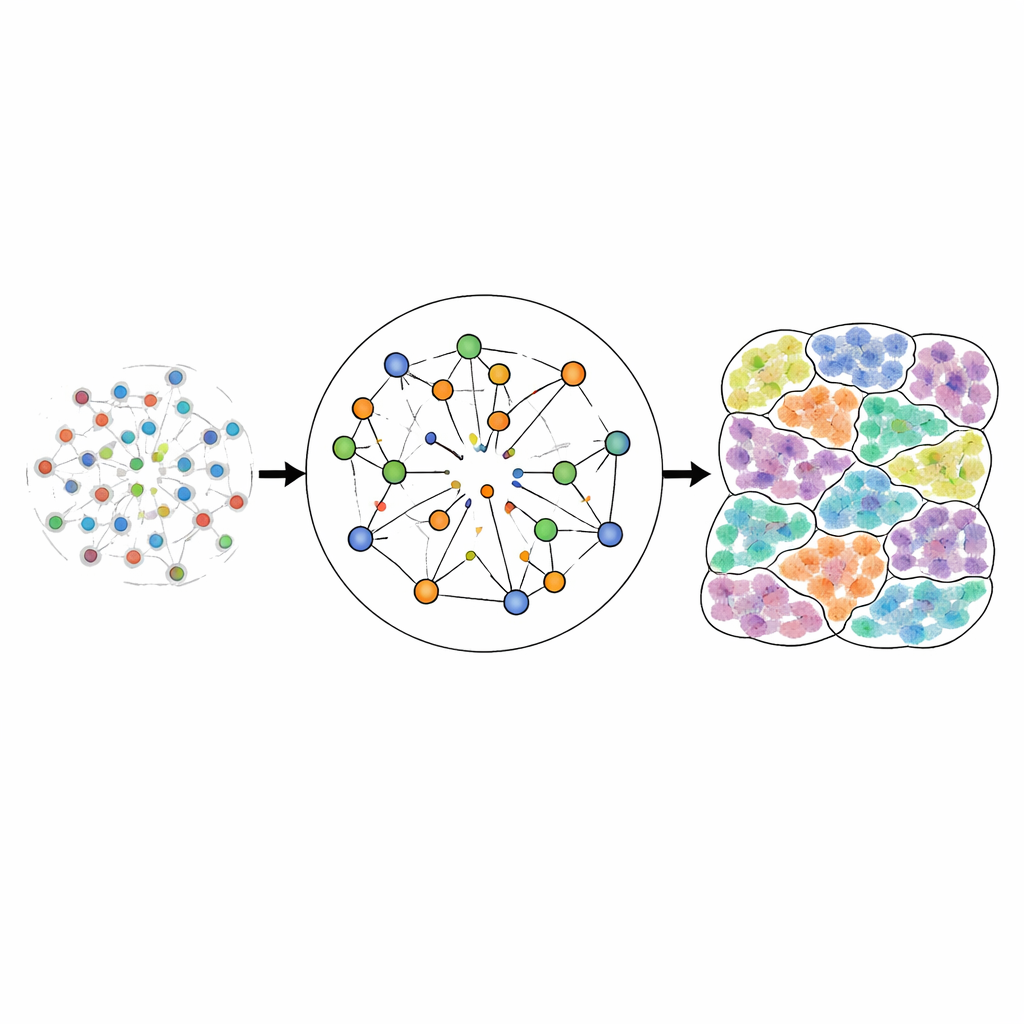
Test des Verfahrens in vielen Geweben
Um zu prüfen, ob CellRefiner realistische Strukturen rekonstruiert, erzeugten die Autorinnen und Autoren zunächst Testdatensätze, in denen die wahren Zellpositionen bekannt sind. Sie begannen mit hochauflösenden bildgebenden Daten, in denen jede Zelle einzeln kartiert ist, und verwischten diese Daten künstlich in niedrigauflösigere Punkte, die gängige räumliche Plattformen nachahmen. Indem sie nur die verwischte Version zusammen mit den ursprünglichen Einzelzellprofilen in CellRefiner einspeisten, fragten sie, wie gut die Methode die ursprüngliche Feinstruktur rekonstruieren kann. Anhand mehrerer Maße räumlicher Fehler verbesserte CellRefiner durchweg die Zellplatzierung gegenüber den anfänglichen groben Zuordnungen und übertraf andere führende Methoden in mehreren Datensätzen aus Regionen des Mausgehirns und anderen Geweben. Es erfasste scharfe Strukturen wie schmale Bänder von Ependymzellen, geschichtete Hippocampusbereiche und kortikale Schichten treuer als konkurrierende Ansätze.
Von Punkten zu Formen und Gesprächen
Über die bloße Platzierung von Zellzentren hinaus kann CellRefiner auch annähernde Zellformen rekonstruieren. Jede Zelle wird als Cluster vieler kleiner Elemente dargestellt, die durch virtuelle Federn verbunden sind und auf Druck- und Zugkräfte zwischen benachbarten Zellen reagieren. Dadurch kann die Methode ableiten, welche Zellen in direktem physischem Kontakt stehen — eine Schlüsselvoraussetzung, um kontaktbasierte Signalübertragung zu untersuchen, bei der Moleküle auf der Oberfläche einer Zelle an Partner auf einer Nachbarzelle binden. Bei Anwendung auf hochauflösende Bilddatensätze stimmten die rekonstruierten Formen eng mit den beobachteten Zellumrissen überein und stellten realistische Kontaktnetzwerke wieder her. Auf niedriger auflösenden Plattformen wie Visium erzeugte CellRefiner detaillierte Kontaktkarten, die die ursprünglichen Punktdaten nicht liefern können.
Verborgene Signale in Gehirn und Krebs aufdecken
Mit seinen verfeinerten Karten und Kontaktnetzwerken konnte CellRefiner bekannte Signalsysteme im menschlichen Plattenepithelkarzinom und in der Maus-Rinde wiederentdecken. In Tumoren hob es Signalwege hervor, die an Zelladhäsion, Gefäßbildung und Interaktionen an der Tumorrandzone beteiligt sind, einschließlich Pfade, die Krebszellen helfen, zusammenzuhalten oder mit ihrer Umgebung zu interagieren. Im Mausgehirn offenbarte CellRefiner strukturierte Signalisierung zwischen kortikalen Schichten und speziellen Klassen von Interneuronen, die Rollen bei Neuronmigration, Verschaltung und Synapsenbildung nahelegen. Wichtig ist, dass die Methode zeigte, dass stark erscheinende Signale in einem einzelnen gemischten Punkt tatsächlich nur von einer Untergruppe der Zellen in diesem Punkt ausgehen können und so verborgene Diversität in der Reaktion benachbarter Zellen offenlegt.
Scharfere Gewebekarten für die zukünftige Biologie
Im Kern verwandelt CellRefiner verschwommene räumliche Messungen in detaillierte Karten, in denen jede Zelle sowohl eine molekulare Identität als auch eine realistische Position und Form hat. Dieser schärfere Blick ermöglicht verlässlichere Studien darüber, wie Zellen organisiert sind, wie sie sich zu Schichten und Regionen zusammenlagern und wie sie durch direkten Kontakt kommunizieren. Obwohl die Methode von der Qualität der Eingangsdaten abhängt und vereinfachende Annahmen über Zelldichte und -größe trifft, bietet sie ein flexibles, physik-inspiriertes Rahmenwerk, das auf andere molekulare Ebenen wie Proteine oder Chromatin erweitert werden kann. Für Nicht-Spezialisten stellt CellRefiner einen Schritt in Richtung virtueller Mikroskope dar, die nicht nur zeigen, wo Zellen sind, sondern wie sie als dynamische Gemeinschaften in lebenden Geweben miteinander interagieren.
Zitation: Bourgain-Chang, E., Kuang, X., Cang, Z. et al. Reconstructing single-cell resolution from spatial transcriptomics with CellRefiner. Nat Commun 17, 3304 (2026). https://doi.org/10.1038/s41467-026-70090-2
Schlüsselwörter: räumliche Transkriptomik, Einzelzell-RNA-Sequenzierung, Zell-Zell-Kommunikation, computationale Biologie, Tumormikroumgebung