Clear Sky Science · pt
Predizendo candidatos a genes FOX para fixação de nitrogênio em condições óxicas usando aprendizado de máquina multi-ômico e bioinformática comparativa
Por que transformar o ar em alimento vegetal importa
A agricultura moderna depende fortemente do fertilizante industrial, produzido ao forçar o nitrogênio do ar para uma forma utilizável usando enormes quantidades de combustíveis fósseis. Esse processo alimenta bilhões de pessoas, mas também impulsiona emissões climáticas e poluição da água. Na natureza, porém, certos microrganismos realizam silenciosamente o mesmo truque químico usando luz solar e muito menos energia. Este artigo explora como decodificar e catalogar os genes que permitem a um desses microrganismos, uma cianobactéria, fixar nitrogênio mesmo enquanto produz oxigênio — algo que normalmente interrompe essa química. Compreender esses genes pode apontar caminhos para plantas e micróbios industriais que se autofertilizam.
O ato de equilíbrio dentro de uma célula minúscula
O gás nitrogênio compõe a maior parte do ar, mas plantas e animais não podem usá‑lo diretamente. Microrganismos especializados dependem de uma enzima chamada nitrogenase para converter o nitrogênio gasoso em amônia, uma forma que a vida pode utilizar. A nitrogenase é extremamente sensível ao oxigênio, que a destrói. Ainda assim, algumas cianobactérias, incluindo a espécie Anabaena 7120, realizam fotossíntese produtora de oxigênio e fixação de nitrogênio no mesmo filamento. Elas conseguem isso formando células especiais chamadas heterócistos, que mantêm um ambiente de baixo oxigênio para a nitrogenase. Além dos genes centrais da nitrogenase, muitos genes acessórios são necessários para construir as paredes celulares protetoras, controlar a química interna e transportar elétrons e nutrientes. Genes cuja perda interrompe o crescimento usando nitrogênio gasoso na presença de oxigênio são conhecidos como genes FOX, e apenas uma fração deles é atualmente conhecida.
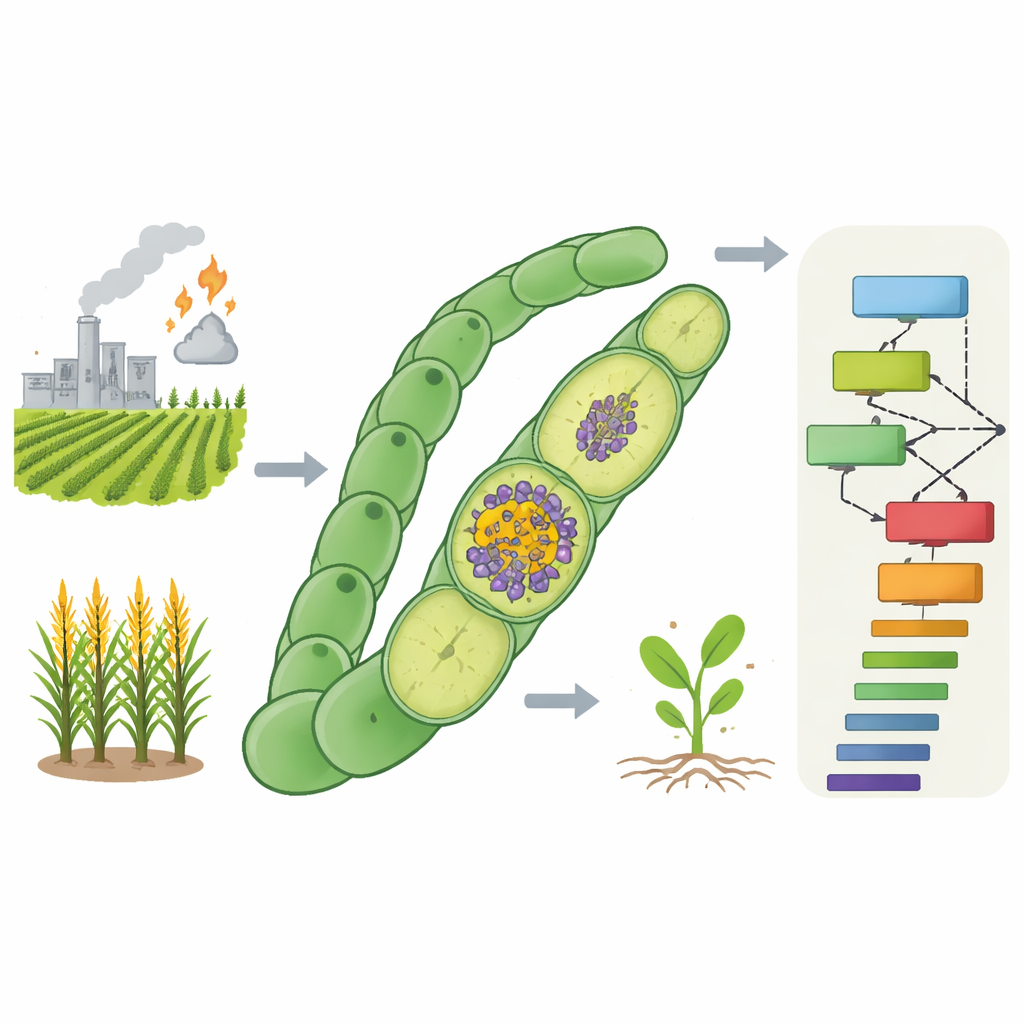
Ensinando computadores a identificar genes ausentes de nitrogênio
Os autores propuseram prever novos candidatos a genes FOX em todo o genoma de Anabaena 7120 usando uma mistura de medições biológicas e aprendizado de máquina. Eles montaram um conjunto de dados “multi-ômico” que acompanhou como cada gene respondia quando o nitrogênio combinado era removido do meio de crescimento, um gatilho que causa a formação de heterócistos. Isso incluiu medições ao longo do tempo dos níveis de RNA, mudanças na abundância de proteínas, características das regiões de controle do DNA que dirigem a transcrição, o vizinhança física de cada gene no cromossomo e o quanto cada gene é conservado em outras cianobactérias fixadoras de nitrogênio versus não fixadoras. Em seguida, rotularam 68 genes já comprovados como FOX e escolheram 835 genes amplamente conservados e não essenciais como substitutos para o grupo não‑FOX.
Quão bem os modelos funcionaram e o que eles aprenderam
Usando esses exemplos rotulados, a equipe treinou três tipos de modelos — regressão logística, Random Forest e XGBoost — e os testou repetidamente em genes mantidos fora do treinamento. Todos os três conseguiram classificar de forma confiável os genes FOX conhecidos acima dos genes proxy não‑FOX, com os melhores modelos alcançando desempenho comparável a outros preditores de essencialidade gênica. Importante, os modelos não foram caixas‑pretas: os pesquisadores usaram uma técnica chamada SHAP para ver quais características empurravam um gene para uma previsão semelhante à de FOX ou para longe dela. Genes FOX tendiam a ser fortemente ativados tardiamente após a remoção de nitrogênio, mostravam baixa atividade antes da mudança, apareciam em aglomerados com outros genes da diazotrofia e eram mais conservados em fixadores de nitrogênio conhecidos do que em espécies relacionadas que não fixam nitrogênio. Em contraste, genes comumente compartilhados com cianobactérias não‑fixadoras, ou dispostos em certos layouts de promotor associados a funções de manutenção celular, eram menos propensos a ser FOX.
Novos candidatos a genes e uma ferramenta de projeto para engenheiros
Munidos dessas percepções, os autores geraram pontuações de probabilidade para cada gene do genoma, usando‑as como um ranking em vez de como probabilidades literais. Entre os candidatos mais bem classificados estavam genes inseridos na região do envelope do heterócisto, genes ligados ao balanceamento redox e ao transporte de elétrons, e vários fatores conhecidos em outros organismos por ajudar a montar ou suportar a nitrogenase, mas ainda não classificados como FOX em Anabaena. Alguns genes no topo da lista já têm indícios experimentais independentes de importância, conferindo credibilidade à abordagem. Para tornar os resultados práticos para a biologia sintética, a equipe também construiu uma ferramenta web que ajuda usuários a escolher conjuntos compactos de genes candidatos que caibam dentro de um limite de tamanho de DNA — aproximadamente a escala que já foi transferida para outras cianobactérias — usando ou uma ordenação simples por ranking ou uma estratégia gulosa sensível ao tamanho.
De previsões mais inteligentes a culturas mais inteligentes
Para o leitor geral, a mensagem principal é que este trabalho transforma uma busca genômica ampla e confusa em uma lista curta e focada de prováveis atores que permitem que microrganismos produtores de oxigênio ainda fixem nitrogênio. O estudo mostra que padrões em quando os genes são ativados, como estão conectados aos vizinhos e quais espécies os mantêm ou descartam em conjunto formam uma assinatura reconhecível da fixação de nitrogênio em condições óxicas. Embora cada candidato ainda precise de teste experimental, as listas classificadas e o aplicativo interativo dão aos pesquisadores um roteiro para preencher sistematicamente as lacunas. A longo prazo, esse roteiro pode orientar esforços para equipar culturas ou microrganismos industriais com sistemas de fixação de nitrogênio robustos e autocontidos, reduzindo a dependência de fábricas de fertilizantes consumidoras de energia e ajudando a agricultura a impactar o planeta de forma mais leve.
Citação: Young, J., Gu, L. & Zhou, R. Predicting FOX gene candidates for oxic nitrogen fixation using multi-omic machine learning and comparative bioinformatics. Sci Rep 16, 11412 (2026). https://doi.org/10.1038/s41598-026-41873-w
Palavras-chave: fixação de nitrogênio, cianobactérias, aprendizado de máquina, biologia sintética, heterócisto