Clear Sky Science · de
Vorhersage von FOX‑Genkandidaten für oxische Stickstofffixierung mittels multi-omischer Maschineller Intelligenz und vergleichender Bioinformatik
Warum die Umwandlung von Luft in Pflanzenfutter wichtig ist
Die moderne Landwirtschaft ist stark auf industriellen Dünger angewiesen, der hergestellt wird, indem Stickstoff aus der Luft in eine nutzbare Form gezwungen wird — ein Prozess, der enorme Mengen fossiler Brennstoffe verbraucht. Dieses Verfahren ernährt Milliarden von Menschen, trägt jedoch auch zu Treibhausgasemissionen und Wasserverschmutzung bei. In der Natur vollbringen bestimmte Mikroben dieselbe chemische Umwandlung auf leise Weise unter Nutzung von Sonnenlicht und deutlich geringerem Energieaufwand. Diese Studie untersucht, wie man die Gene entschlüsseln und katalogisieren kann, die einem solchen Mikroorganismus — einem Cyanobakterium — erlauben, Stickstoff zu fixieren, obwohl gleichzeitig Sauerstoff erzeugt wird, was diese Chemie normalerweise unterbricht. Das Verständnis dieser Gene könnte den Weg zu Pflanzen und industriellen Mikroben weisen, die sich selbst düngen.
Das Balanceakt in einer winzigen Zelle
Stickstoffgas macht den Großteil der Luft aus, doch Pflanzen und Tiere können es nicht direkt nutzen. Spezialisierte Mikroben verwenden ein Enzym, das Nitrogenase genannt wird, um Stickstoffgas in Ammoniak umzuwandeln, eine für Leben nutzbare Form. Nitrogenase ist extrem empfindlich gegenüber Sauerstoff, der es zerstört. Dennoch führen einige Cyanobakterien, darunter die Art Anabaena 7120, in demselben Filament Photosynthese mit Sauerstoffproduktion und Stickstofffixierung durch. Sie erreichen dies durch die Bildung spezieller Zellen, der Heterocysten, die eine geringe Sauerstoffumgebung für die Nitrogenase aufrechterhalten. Neben den Kern-Nitrogenasegenen werden viele zusätzliche Gene benötigt, um schützende Zellwände aufzubauen, die interne Chemie zu kontrollieren und Elektronen sowie Nährstoffe zu transportieren. Gene, deren Verlust das Wachstum auf Stickstoffgas in Gegenwart von Sauerstoff verhindert, werden als FOX‑Gene bezeichnet, und nur ein Bruchteil von ihnen ist derzeit bekannt.
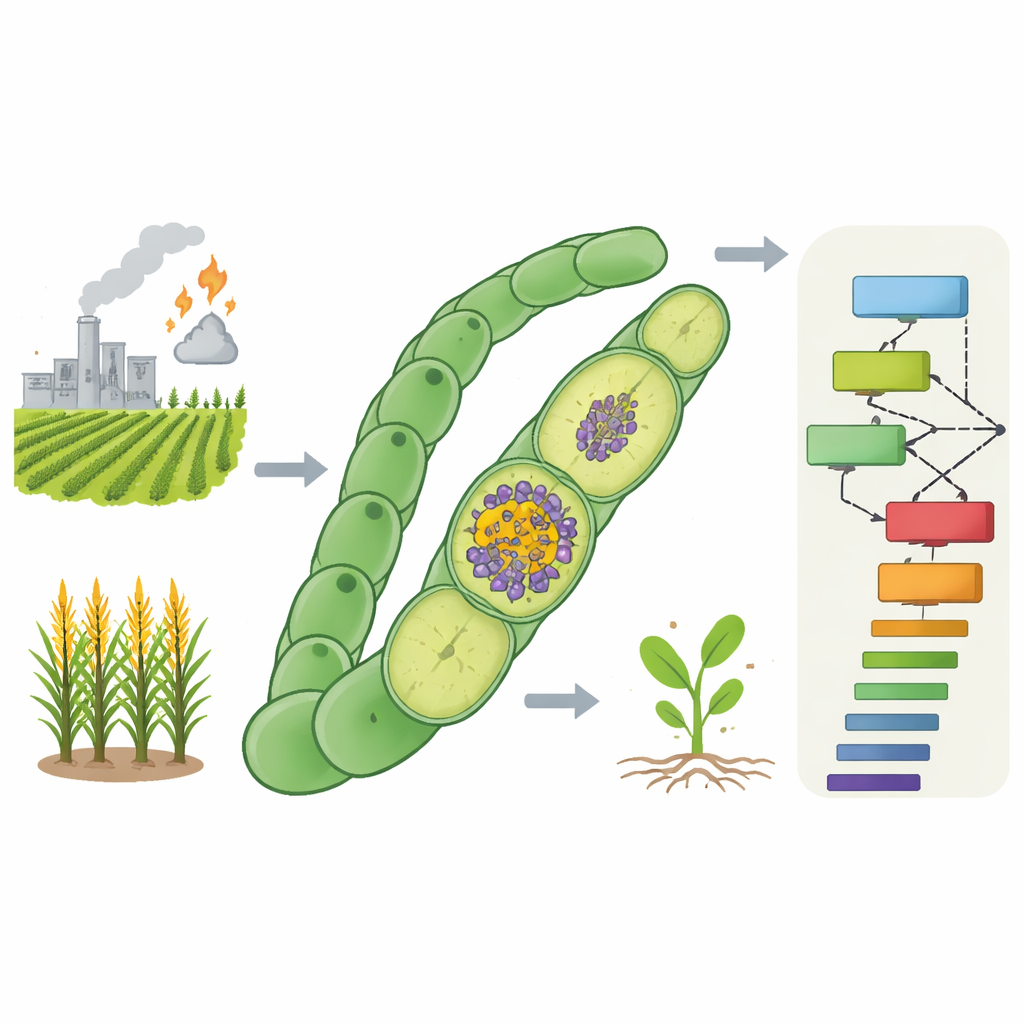
Computern beibringen, fehlende Stickstoffgene zu erkennen
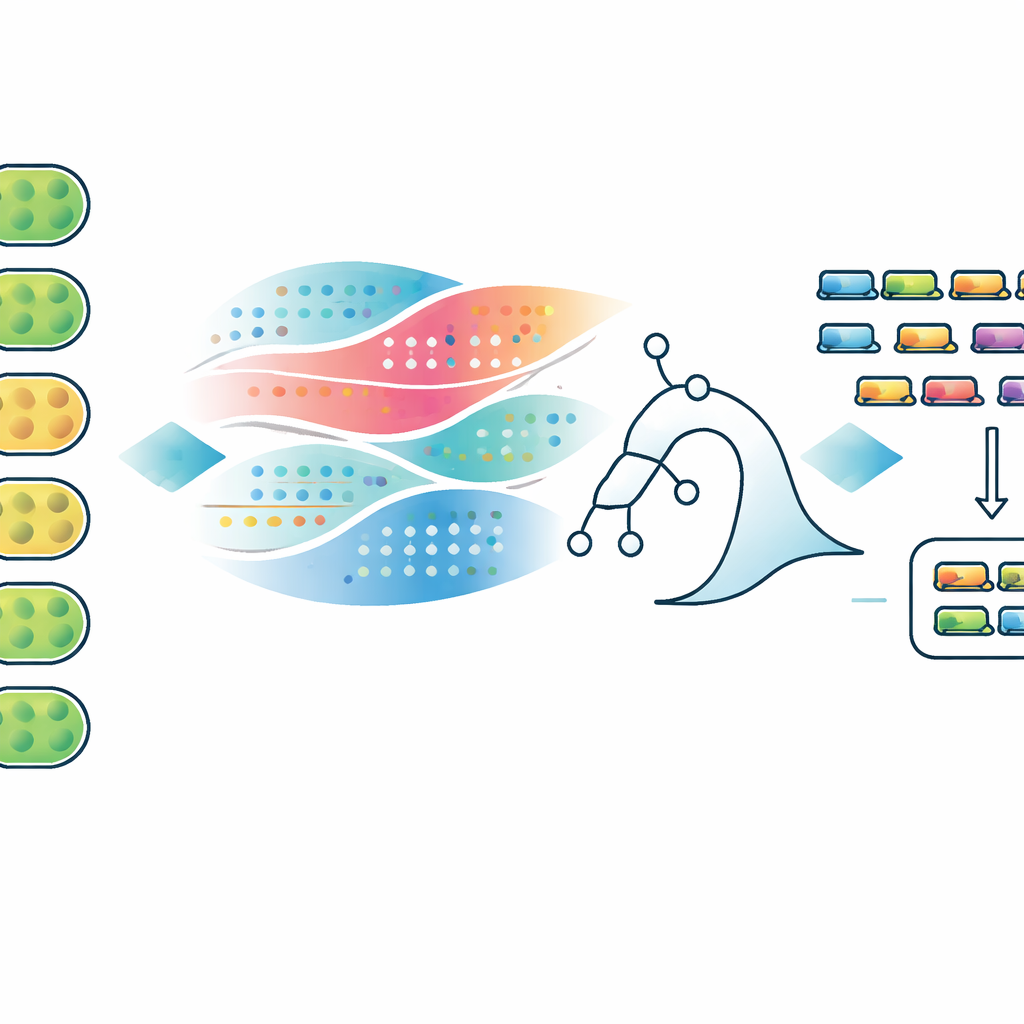
Die Autoren machten sich daran, neue FOX‑Genkandidaten im gesamten Genom von Anabaena 7120 vorherzusagen, indem sie biologische Messungen mit maschinellem Lernen kombinierten. Sie stellten einen „multi‑omischen" Datensatz zusammen, der verfolgte, wie jedes Gen reagierte, wenn kombinierter Stickstoff aus dem Wachstumsmedium entfernt wurde — ein Auslöser für die Bildung von Heterocysten. Dieser Datensatz umfasste Zeitverläufe der RNA‑Spiegel, Veränderungen der Proteinmenge, Merkmale der DNA‑Kontrollregionen, die die Transkription steuern, die physische Nachbarschaft jedes Gens auf dem Chromosom und wie stark jedes Gen in anderen stickstofffixierenden versus nicht‑fixierenden Cyanobakterien konserviert ist. Anschließend markierten sie 68 bereits als FOX nachgewiesene Gene und wählten 835 weit konservierte, nicht‑essentielle Gene als Stellvertreter für die Nicht‑FOX‑Gruppe aus.
Wie gut die Modelle funktionierten und was sie lernten
Anhand dieser beschrifteten Beispiele trainierte das Team drei Modelltypen — logistische Regression, Random Forest und XGBoost — und testete sie wiederholt an zurückgehaltenen Genen. Alle drei konnten bekannte FOX‑Gene zuverlässig über den Stellvertreter‑Nicht‑FOX‑Genen einordnen, wobei die besten Modelle Leistungen erreichten, die mit anderen Vorhersagern für Genessenzialität vergleichbar sind. Wichtig ist, dass die Modelle keine Black‑Boxen blieben: Die Forscher verwendeten eine Technik namens SHAP, um zu sehen, welche Merkmale ein Gen in Richtung einer FOX‑ähnlichen Vorhersage trieben oder davon abhielten. FOX‑Gene neigten dazu, spät nach der Stickstoffentfernung stark hochreguliert zu sein, zeigten vor dem Umschalten niedrige Aktivität, traten in Clustern mit anderen Diazotrophie‑Genen auf und waren in bekannten Stickstofffixierern stärker konserviert als in eng verwandten Arten, die keinen Stickstoff fixieren. Im Gegensatz dazu waren Gene, die häufig mit nicht‑fixierenden Cyanobakterien geteilt werden, oder die in bestimmten Promotor‑Layouts vorkommen, die mit Haushaltfunktionen assoziiert sind, weniger wahrscheinlich FOX.
Neue Genkandidaten und ein Design‑Werkzeug für Ingenieure
Mithilfe dieser Erkenntnisse erzeugten die Autoren Wahrscheinlichkeitswerte für jedes Gen im Genom und nutzten diese eher zur Rangordnung als als wörtliche Wahrscheinlichkeiten. Zu den am höchsten eingestuften Kandidaten gehörten Gene, die in der Heterocysten‑Hüllregion eingebettet sind, Gene, die mit Redox‑Ausgleich und Elektronentransport verbunden sind, sowie mehrere Faktoren, die in anderen Organismen bekannt sind, um Nitrogenase zusammenzubauen oder zu unterstützen, die aber in Anabaena noch nicht als FOX klassifiziert sind. Einige Spitzenkandidaten weisen bereits unabhängige experimentelle Hinweise auf Bedeutung auf, was der Methode Glaubwürdigkeit verleiht. Um die Ergebnisse für die synthetische Biologie praktisch nutzbar zu machen, entwickelten die Autoren außerdem ein Web‑Tool, das Nutzern hilft, kompakte Mengen von Genkandidaten auszuwählen, die innerhalb eines gewählten DNA‑Größenlimits liegen — in etwa dem Maßstab, der bereits in andere Cyanobakterien übertragen wurde — und das entweder eine einfache Reihenfolge nach Rang oder eine größenbewusste Greedy‑Strategie verwendet.
Von besseren Vorhersagen zu besseren Nutzpflanzen
Für eine allgemeine Leserschaft ist die zentrale Botschaft, dass diese Arbeit eine unübersichtliche genomweite Suche in eine fokussierte Shortlist wahrscheinlicher Akteure verwandelt, die es sauerstoffproduzierenden Mikroben dennoch ermöglichen, Stickstoff zu fixieren. Die Studie zeigt, dass Muster darin, wann Gene an- und ausgeschaltet werden, wie sie mit ihren Nachbarn verschaltet sind und welche Arten sie gemeinsam behalten oder verlieren, eine erkennbare Signatur der oxischen Stickstofffixierung bilden. Während jeder Kandidat noch experimentell geprüft werden muss, liefern die gereihten Listen und die interaktive App Forschern eine Roadmap, um systematisch die fehlenden Puzzleteile zu ergänzen. Langfristig könnte diese Roadmap Bemühungen leiten, Nutzpflanzen oder industrielle Mikroben mit robusten, in sich geschlossenen Stickstoff‑Fixierungssystemen auszustatten, wodurch die Abhängigkeit von energieintensiven Düngemittelfabriken verringert und die Landwirtschaft nachhaltiger gestaltet werden könnte.
Zitation: Young, J., Gu, L. & Zhou, R. Predicting FOX gene candidates for oxic nitrogen fixation using multi-omic machine learning and comparative bioinformatics. Sci Rep 16, 11412 (2026). https://doi.org/10.1038/s41598-026-41873-w
Schlüsselwörter: Stickstofffixierung, Cyanobakterien, Maschinelles Lernen, Synthetische Biologie, Heterocyste