Clear Sky Science · pl
Predykcja kandydatów genów FOX dla oksycznego wiązania azotu przy użyciu wieloomicznych metod uczenia maszynowego i porównawczej bioinformatyki
Dlaczego przekształcanie powietrza w pokarm dla roślin ma znaczenie
Współczesne rolnictwo opiera się w dużej mierze na nawozach przemysłowych, które powstają przez przekształcenie azotu z powietrza w formę dostępną dla roślin przy użyciu ogromnych ilości paliw kopalnych. Ten proces karmi miliardy ludzi, ale także napędza emisje klimatyczne i zanieczyszczanie wód. W przyrodzie pewne mikroby wykonują podobny chemiczny trik za pomocą światła słonecznego i znacznie mniejszej ilości energii. W artykule badano, jak rozszyfrować i skatalogować geny pozwalające jednemu z takich mikroorganizmów, sinicy, wiązać azot nawet podczas produkcji tlenu — procesu, który zwykle hamuje tę chemię. Poznanie tych genów może wskazać drogę do upraw i mikroorganizmów przemysłowych, które same się nawożą.
Równowaga wewnątrz maleńkiej komórki
Azot gazowy stanowi większość powietrza, ale rośliny i zwierzęta nie mogą go używać wprost. Specjalistyczne mikroby polegają na enzymie zwanym nitrogenazą, aby przekształcić azot gazowy w amoniak — formę, którą żywe organizmy mogą wykorzystać. Nitrogenaza jest niezwykle wrażliwa na tlen, który ją niszczy. Jednak niektóre sinice, w tym gatunek Anabaena 7120, prowadzą fotosyntezę produkującą tlen i jednocześnie wiążą azot w obrębie tego samego filamentum. Osiągają to, tworząc specjalne komórki zwane heterocystami, które utrzymują niskotlenowe środowisko dla nitrogenazy. Poza podstawowymi genami nitrogenazy potrzebnych jest wiele genów pomocniczych do budowy ochronnych ścian komórkowych, kontrolowania wewnętrznej chemii oraz przekazywania elektronów i składników odżywczych. Geny, których utrata zatrzymuje wzrost na azocie gazowym w obecności tlenu, nazywane są genami FOX, a znanych jest tylko ich ułamek.
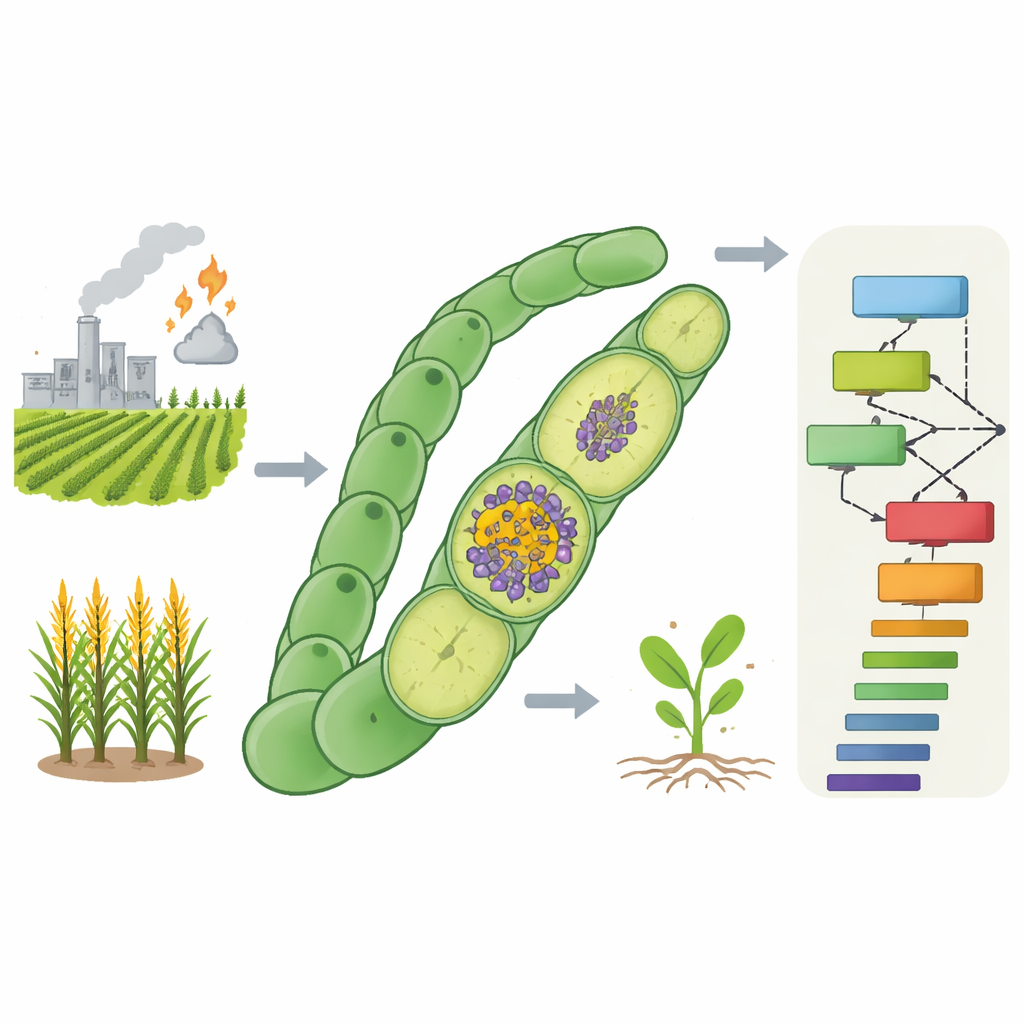
Nauczanie komputerów rozpoznawania brakujących genów azotowych
Autorzy postawili sobie za cel przewidzenie nowych kandydatów genów FOX w całym genomie Anabaena 7120, używając mieszanki pomiarów biologicznych i uczenia maszynowego. Zgromadzili „wieloomiczny” zestaw danych śledzący odpowiedź każdego genu po usunięciu azotu z pożywki — sygnału wywołującego tworzenie heterocyst. Zestaw obejmował pomiary czasowe poziomów RNA, zmiany w obfitości białek, cechy regionów kontrolnych DNA odpowiedzialnych za transkrypcję, fizyczne sąsiedztwo każdego genu na chromosomie oraz stopień konserwacji genu w innych azotowiążących w porównaniu z niewiązącymi sinicami. Oznaczyli następnie 68 genów już potwierdzonych jako FOX i wybrali 835 szeroko konserwowanych, nieistotnych genów jako reprezentację grupy nie‑FOX.
Jak dobrze działały modele i czego się nauczyły
Używając tych oznaczonych przykładów, zespół wytrenował trzy typy modeli — regresję logistyczną, Random Forest i XGBoost — i wielokrotnie testował je na wydzielonych genach. Wszystkie trzy potrafiły niezawodnie klasyfikować znane geny FOX wyżej niż geny proxy nie‑FOX, przy czym najlepsze modele osiągały wydajność porównywalną z innymi predyktorami istotności genów. Co ważne, modele nie były czarnymi skrzynkami: badacze zastosowali technikę SHAP, aby zobaczyć, które cechy przesuwały predykcję genu w kierunku lub z dala od profilu FOX. Geny FOX miały tendencję do silnego włączenia późno po usunięciu azotu, wykazywały niską aktywność przed przełączeniem, pojawiały się w skupiskach z innymi genami diazotroficznymi i były bardziej konserwowane w znanych azotowiążących gatunkach niż w blisko spokrewnionych gatunkach, które nie wiążą azotu. W przeciwieństwie do tego, geny powszechnie współdzielone z niewiązającymi sinicami lub ułożone w pewne układy promotorowe związane z rolami podstawowymi były mniej prawdopodobne, by być FOX.
Nowi kandydaci na geny i narzędzie projektowe dla inżynierów
Wyposażeni w te wnioski, autorzy wygenerowali skorowy wyniki prawdopodobieństwa dla każdego genu w genomie, traktując je jako ranking, a nie dosłowne odds. Wśród najwyżej ocenionych kandydatów znalazły się geny osadzone w regionie otoczki heterocyst, geny związane z równowagą redoks i transportem elektronów oraz kilka czynników znanych u innych organizmów z udziału w składaniu lub wsparciu nitrogenazy, ale jeszcze nie sklasyfikowanych jako FOX w Anabaena. Niektóre z najsilniej punktowanych genów mają już niezależne eksperymentalne wskazówki o znaczeniu, co zwiększa wiarygodność podejścia. Aby uczynić wyniki praktycznymi dla biologii syntetycznej, zespół zbudował też narzędzie internetowe, które pomaga użytkownikom wybierać kompaktowe zestawy kandydatów mieszczące się w wybranym limicie rozmiaru DNA — mniej więcej na skali, którą już przenoszono do innych sinic — używając prostego porządku rankingu lub strategii zachłannej uwzględniającej rozmiar.
Od inteligentniejszych predykcji do inteligentniejszych upraw
Dla ogólnego czytelnika kluczowe przesłanie jest takie, że ta praca przekształca chaotyczne, genomowe poszukiwania w ukierunkowaną krótką listę prawdopodobnych graczy, które pozwalają mikrobom produkującym tlen nadal wiązać azot. Badanie pokazuje, że wzorce dotyczące tego, kiedy geny się włączają, jak są powiązane z sąsiadami oraz które gatunki zachowują lub odrzucają je razem, tworzą rozpoznawalny podpis oksycznego wiązania azotu. Chociaż każdy kandydat nadal wymaga testów eksperymentalnych, uporządkowane listy i interaktywna aplikacja dają badaczom mapę drogową do systematycznego wypełniania brakujących elementów. W dłuższej perspektywie ta mapa może poprowadzić wysiłki, by wyposażyć uprawy lub mikroby przemysłowe w solidne, samodzielne systemy wiążące azot, zmniejszając zależność od energochłonnych fabryk nawozów i pomagając rolnictwu stawiać lżejsze kroki na planecie.
Cytowanie: Young, J., Gu, L. & Zhou, R. Predicting FOX gene candidates for oxic nitrogen fixation using multi-omic machine learning and comparative bioinformatics. Sci Rep 16, 11412 (2026). https://doi.org/10.1038/s41598-026-41873-w
Słowa kluczowe: wiązanie azotu, sinice, uczenie maszynowe, biologia syntetyczna, heterocyst