Clear Sky Science · pt
PCR multiplex em tempo real com análise de high-resolution melting para identificação rápida de genes de resistência a carbapenêmicos e colistina em isolados clínicos de Enterobacterales
Por que testes de infecção mais rápidos importam
Quando pacientes chegam ao hospital com infecções graves, os médicos frequentemente enfrentam uma corrida contra o tempo. Algumas bactérias comuns do intestino evoluíram formas de resistir até aos nossos antibióticos mais potentes, transformando infecções rotineiras em emergências com risco de vida. Testes de laboratório padrão podem levar dias para indicar quais medicamentos serão eficazes, atrasando o tratamento adequado e permitindo a disseminação de linhagens perigosas e altamente resistentes. Este estudo descreve um teste genético rápido e acessível que pode identificar sinais-chave de resistência nessas bactérias em poucas horas, usando equipamentos que muitos hospitais já possuem.
Antibióticos antigos, novas ameaças
O trabalho concentra-se em um grupo de bactérias chamado Enterobacterales, que inclui nomes familiares como Escherichia coli, Klebsiella pneumoniae e Salmonella. Esses microrganismos podem causar infecções na corrente sanguínea, pulmões, trato urinário e intestino, tanto em hospitais quanto na comunidade. Durante anos, os médicos dependeram de antibióticos potentes chamados carbapenêmicos para tratar infecções que resistiam a muitos outros fármacos. À medida que esses medicamentos perderam eficácia, um antibiótico mais antigo, a colistina, tornou-se opção de último recurso. Relatos alarmantes mostram agora que algumas bactérias estão se tornando resistentes até à colistina, levantando a possibilidade de infecções quase impossíveis de tratar.
Genes que desarmam nossos melhores medicamentos
O cerne dessa ameaça crescente está em um punhado de genes de resistência. Certos genes, conhecidos em termos gerais como genes codificadores de carbapenemase, permitem que as bactérias destruam carbapenêmicos. Outros, agrupados sob o nome mcr, podem proteger as bactérias da colistina. Muitos desses genes estão em fragmentos móveis de DNA que podem saltar entre bactérias, acelerando sua disseminação. Na Tailândia e em toda a Ásia, linhagens de Klebsiella e E. coli que carregam múltiplos genes de carbapenemase ao mesmo tempo tornaram-se cada vez mais comuns, e genes móveis de resistência à colistina, mcr‑1 e mcr‑3, estão sendo encontrados em Salmonella e outros Enterobacterales. Saber se a cepa que infecta um paciente carrega esses genes específicos pode orientar os médicos para combinações de drogas mais recentes que têm maior probabilidade de funcionar, mas os testes tradicionais são lentos ou limitados demais para acompanhar essa necessidade.
Um único teste rápido para muitos agentes perigosos
Os pesquisadores desenvolveram um teste capaz de detectar sete genes de resistência importantes em um único tubo pequeno, em menos de quatro horas a partir de DNA bacteriano purificado. O método se baseia em PCR em tempo real, uma tecnologia padrão que se tornou ubíqua durante a pandemia de COVID‑19. Em vez de usar sondas fluorescentes caras, a equipe combinou o PCR com uma técnica chamada high‑resolution melting, que observa como fragmentos de DNA se desassociam à medida que são aquecidos de forma controlada. Cada gene alvo produz um fragmento de DNA com comportamento de fusão ligeiramente diferente, como um código de barras térmico. Ao projetar primers cuidadosamente ajustados, a equipe garantiu que os sete genes de interesse — cinco genes de resistência a carbapenêmicos e dois genes de resistência à colistina — gerassem sinais de melting claros e distintos.
Aplicando o teste em hospitais reais
Para avaliar o desempenho na prática, a equipe examinou 576 isolados de Enterobacterales multirresistentes coletados em hospitais tailandeses, além de uma cepa de referência bem caracterizada. Compararam seu novo teste com PCR convencional, um método genético amplamente aceito. O novo ensaio identificou corretamente os genes de resistência com sensibilidade global de cerca de 97% e especificidade de cerca de 99,5%, o que significa que quase nunca deixou de detectar um gene ou gerou um alarme falso. Teve desempenho particularmente bom na detecção de genes comuns de carbapenemase em Klebsiella e E. coli e de mcr‑1 e mcr‑3 em Salmonella e Klebsiella resistentes à colistina. Em cerca de um quarto dos isolados resistentes à colistina, o teste detectou genes mcr, e revelou muitas cepas que carregavam mais de um gene de resistência simultaneamente.
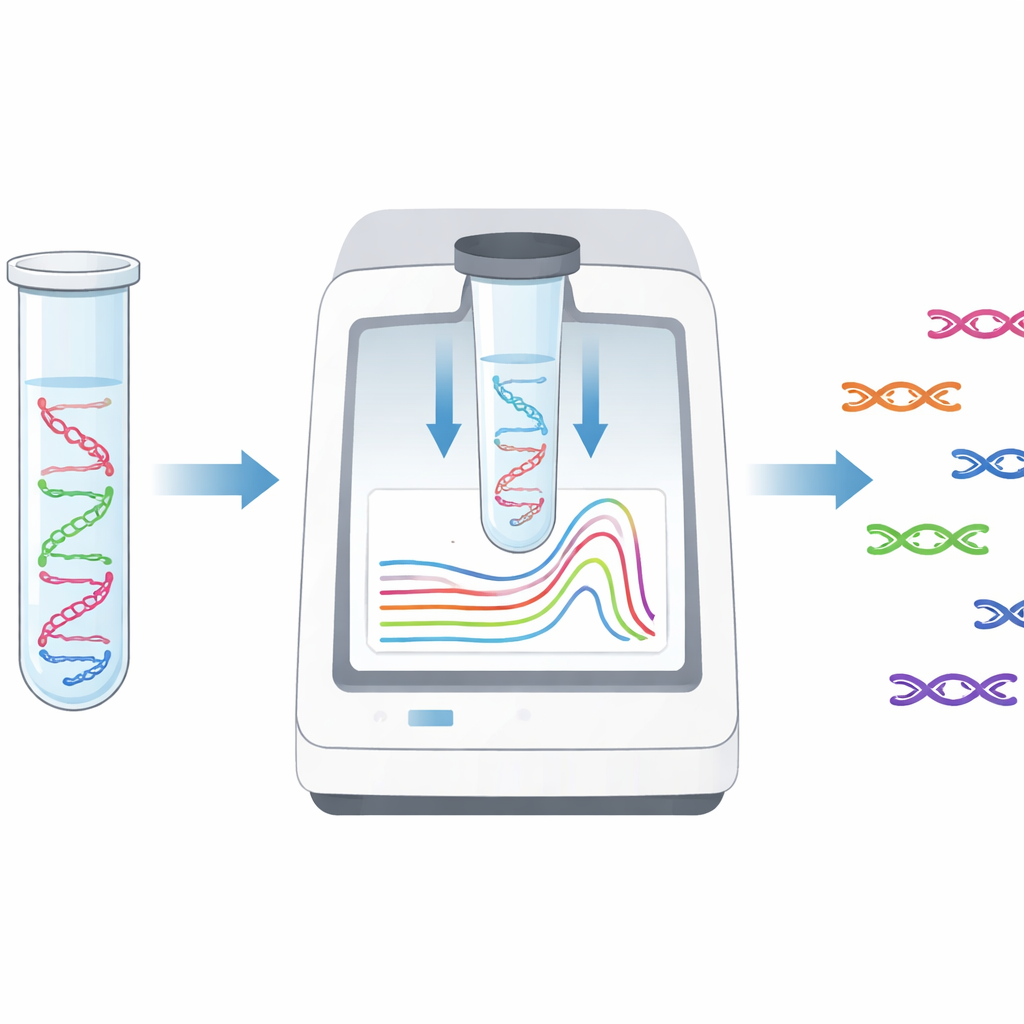
Vendo sinais sobrepostos com mais clareza
Algumas das bactérias mais preocupantes carregam dois genes de carbapenemase juntos, notadamente NDM e OXA‑48‑like, que são comuns na Tailândia e em países vizinhos. Como os sinais de melting desses genes se sobrepõem parcialmente, eles podem ser difíceis de distinguir quando estão ambos presentes. Para resolver isso, os pesquisadores usaram um software de análise avançado que alinha e compara curvas de melting com padrões de referência. Essa etapa extra melhorou a capacidade do teste de detectar linhagens com genes duplos, elevando a sensibilidade para NDM combinado com OXA‑48‑like de cerca de 83% para quase 93%. O ensaio também mostrou forte desempenho em testes quantitativos usando padrões de DNA clonados, detectando de forma confiável quantidades tão pequenas quanto aproximadamente cem cópias de um gene.
O que isso significa para pacientes e hospitais
Para os pacientes, esse tipo de teste não substitui a cultura padrão e os testes de sensibilidade a antibióticos, mas pode dar aos médicos um aviso precoce sobre se estão enfrentando uma infecção rotineira ou uma altamente resistente. Para hospitais e agências de saúde pública, oferece uma forma prática de acompanhar a disseminação de genes críticos de resistência e detectar combinações perigosas antes que se tornem endêmicas. Como o ensaio não usa sondas, emprega reagentes disponíveis comercialmente e roda em máquinas de PCR em tempo real amplamente disponíveis, ele pode ser implementado em muitos laboratórios a um custo relativamente baixo. Em resumo, este estudo demonstra que um único ensaio genético rápido pode oferecer uma visão ampla de algumas das ameaças de resistência mais importantes em Enterobacterales, ajudando a orientar melhores escolhas de antibióticos e um controle de infecção mais eficaz.
Citação: Luk-In, S., Phopin, K., Bangmuangngam, S. et al. Multiplex real-time PCR with high-resolution melting analysis for rapid identification of carbapenem and colistin resistance genes in clinical Enterobacterales isolates. Sci Rep 16, 11901 (2026). https://doi.org/10.1038/s41598-026-41530-2
Palavras-chave: resistência antimicrobiana, bactérias resistentes a carbapenêmicos, resistência à colistina, diagnóstico rápido por PCR, infecções hospitalares