Clear Sky Science · de
Multiplex‑Realtime‑PCR mit Hochauflösender Schmelzanalyse zur schnellen Identifikation von Carbapenem‑ und Colistin‑Resistenzgenen in klinischen Enterobacterales‑Isolaten
Warum schnellere Infektionstests wichtig sind
Wenn Patientinnen und Patienten mit schweren Infektionen ins Krankenhaus kommen, stehen Ärztinnen und Ärzte oft im Wettlauf gegen die Zeit. Einige verbreitete Darmbakterien haben Mechanismen entwickelt, die selbst unsere stärksten Antibiotika unwirksam machen und so routinemäßige Infektionen in lebensbedrohliche Notfälle verwandeln können. Standardlaboruntersuchungen können Tage dauern, bis klar ist, welche Wirkstoffe noch wirken — das verzögert die richtige Behandlung und ermöglicht die Ausbreitung hochresistenter Stämme. Diese Studie beschreibt einen schnellen, erschwinglichen Gentest, der entscheidende Resistenzmerkmale in diesen Bakterien binnen Stunden nachweisen kann und dabei Geräte nutzt, die in vielen Kliniken bereits vorhanden sind.
Alte Antibiotika, neue Bedrohungen
Die Arbeit konzentriert sich auf eine Gruppe von Bakterien, die als Enterobacterales bezeichnet werden und bekannte Vertreter wie Escherichia coli, Klebsiella pneumoniae und Salmonella einschließen. Diese Mikroben können Blutstrominfektionen, Lungenentzündungen, Harnwegsinfektionen und Darminfektionen sowohl im Krankenhaus als auch in der Gemeinschaft verursachen. Jahrelang verließen sich Ärztinnen und Ärzte auf potente Wirkstoffe, die Carbapeneme, um Infektionen zu behandeln, die gegen viele andere Antibiotika resistent waren. Da diese Wirkstoffe an Wirksamkeit verloren haben, ist ein älteres Antibiotikum, Colistin, zur Option der letzten Instanz geworden. Beunruhigende Berichte zeigen nun, dass einige Bakterien sogar gegenüber Colistin resistent werden — mit der Folge, dass Infektionen nahezu unbehandelbar erscheinen.
Gene, die unsere besten Wirkstoffe außer Kraft setzen
Der Schlüssel zu dieser wachsenden Bedrohung liegt in einer Handvoll Resistenzgene. Bestimmte Gene, allgemein als Carbapenemase‑Gene bezeichnet, ermöglichen es Bakterien, Carbapenem‑Antibiotika zu zerstören. Andere, unter dem Namen mcr zusammengefasst, schützen Bakterien vor Colistin. Viele dieser Gene sitzen auf mobilen DNA‑Elementen, die zwischen Bakterien springen können und so ihre Verbreitung beschleunigen. In Thailand und weiten Teilen Asiens sind Stämme von Klebsiella und E. coli, die mehrere Carbapenemase‑Gene gleichzeitig tragen, zunehmend verbreitet, und die mobilen Colistin‑Resistenzgene mcr‑1 und mcr‑3 werden in Salmonella und anderen Enterobacterales nachgewiesen. Zu wissen, ob der Infektionserreger eines Patienten diese spezifischen Gene trägt, kann Ärztinnen und Ärzten helfen, zu neueren Wirkstoffkombinationen zu greifen, die vermutlich wirksamer sind — aber herkömmliche Tests sind zu langsam oder zu eingeschränkt, um Schritt zu halten.
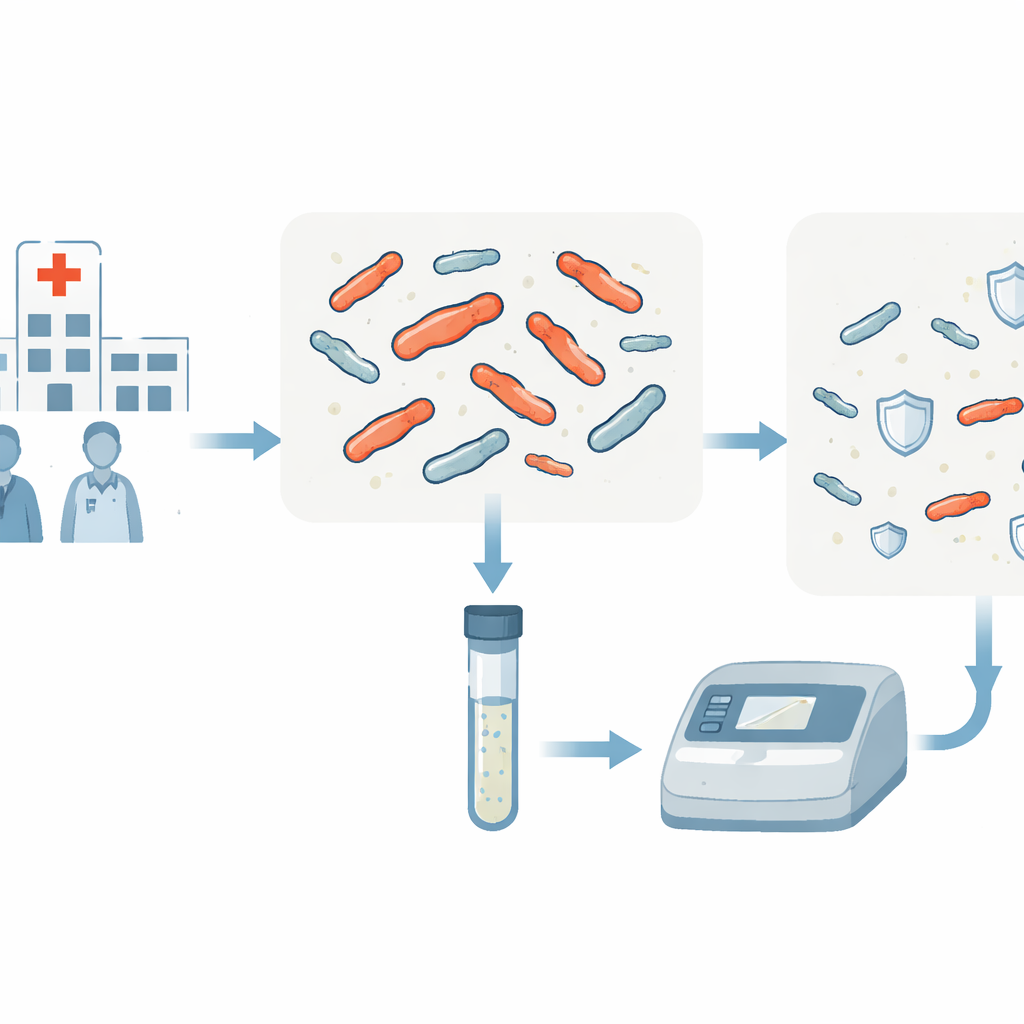
Ein einzelner schneller Test für viele Problemkeime
Die Forschenden entwickelten einen Test, der sieben wichtige Resistenzgene in einem einzigen kleinen Reaktionsgefäß nachweisen kann — in weniger als vier Stunden ab gereinigter bakterieller DNA. Das Verfahren beruht auf Real‑Time‑PCR, einer Standardtechnik, die während der COVID‑19‑Pandemie weit verbreitet wurde. Statt teure fluoreszierende Sonden zu verwenden, kombinierten die Autorinnen und Autoren PCR mit einer Methode namens Hochauflösende Schmelzanalyse, die beobachtet, wie DNA‑Fragmente beim schonenden Erwärmen auseinandergehen. Jedes Zielgen liefert einen DNA‑Abschnitt mit leicht unterschiedlichem Schmelzverhalten — wie ein Temperatur‑Barcode. Durch sorgfältig abgestimmte Primer sorgte das Team dafür, dass die sieben interessierenden Gene — fünf Carbapenemresistenzgene und zwei Colistinresistenzgene — jeweils ein klares, unterscheidbares Schmelzsignal erzeugen.
Anwendung des Tests in echten Krankenhäusern
Um die Praktikabilität zu prüfen, untersuchte das Team 576 multiresistente Enterobacterales‑Isolate aus thailändischen Krankenhäusern sowie einen gut charakterisierten Referenzstamm. Sie verglichen ihren neuen Test mit konventioneller PCR, einer weithin anerkannten molekularen Methode. Der neue Assay identifizierte Resistenzgene mit einer Gesamt‑Sensitivität von etwa 97 % und einer Spezifität von ungefähr 99,5 %, das heißt, er übersah kaum ein Gen und produzierte kaum falsch positive Ergebnisse. Besonders gut funktionierte der Test beim Nachweis häufiger Carbapenemase‑Gene in Klebsiella und E. coli sowie von mcr‑1 und mcr‑3 in Colistin‑resistenten Salmonella und Klebsiella. Bei etwa einem Viertel der colistinresistenten Isolate fand der Test mcr‑Gene, und er zeigte viele Stämme, die mehr als ein Resistenzgen gleichzeitig trugen.
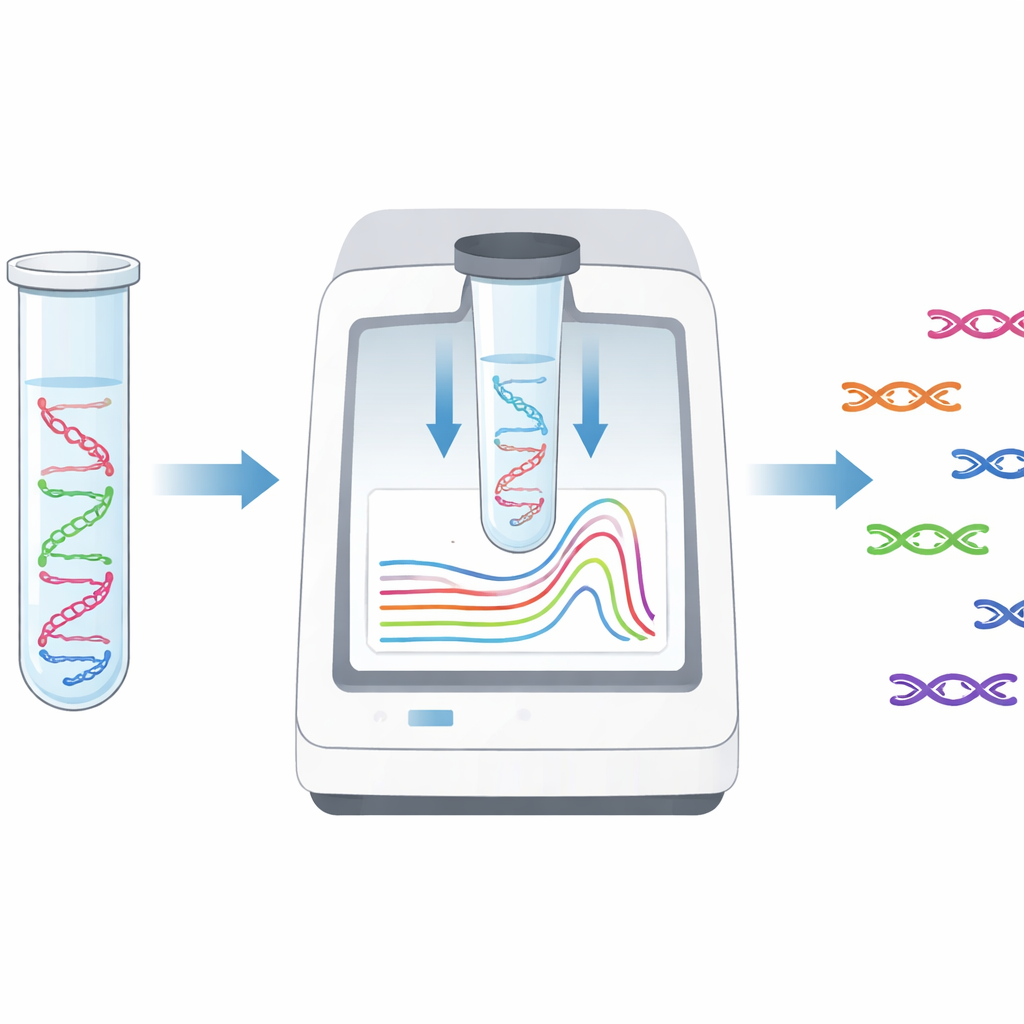
Überlappende Signale klarer erkennen
Einige der besorgniserregendsten Bakterien tragen zwei Carbapenemase‑Gene zusammen, namentlich NDM und OXA‑48‑ähnliche Gene, die in Thailand und den Nachbarländern häufig vorkommen. Weil die Schmelzsignale dieser Gene teilweise überlappen, sind sie schwer zu unterscheiden, wenn beide vorhanden sind. Um das zu lösen, nutzten die Forschenden fortgeschrittene Analyse‑Software, die Schmelzkurven gegen Referenzmuster ausrichtet und vergleicht. Dieser zusätzliche Schritt verbesserte die Fähigkeit des Tests, Doppel‑Gen‑Stämme zu erkennen, und erhöhte die Sensitivität für kombinierte NDM‑ und OXA‑48‑ähnliche Gene von etwa 83 % auf nahezu 93 %. Der Assay zeigte außerdem starke Leistung in quantitativen Tests mit klonierten DNA‑Standards und detektierte zuverlässig bereits etwa hundert Kopien eines Gens.
Was das für Patientinnen, Patienten und Kliniken bedeutet
Für Patientinnen und Patienten ersetzt ein solcher Test nicht die Standardkultur und das klassische Antibiotika‑Empfindlichkeitsscreening, aber er kann Ärztinnen und Ärzten frühzeitig anzeigen, ob sie es mit einer routinemäßigen oder einer hochresistenten Infektion zu tun haben. Für Krankenhäuser und Gesundheitsbehörden bietet er eine praktikable Möglichkeit, die Verbreitung kritischer Resistenzgene zu überwachen und gefährliche Genkombinationen zu erkennen, bevor sie sich fest etablieren. Weil der Assay ohne Sonden auskommt, handelsübliche Reagenzien verwendet und auf weitverbreiteten Real‑Time‑PCR‑Geräten lauffähig ist, könnte er in vielen Laboren relativ kostengünstig eingeführt werden. Kurz: Die Studie zeigt, dass ein einzelner, schneller Gentest einen breiten Überblick über einige der wichtigsten Resistenzbedrohungen bei Enterobacterales liefern kann und so bessere Antibiotika‑Entscheidungen und wirksamere Infektionskontrolle unterstützen kann.
Zitation: Luk-In, S., Phopin, K., Bangmuangngam, S. et al. Multiplex real-time PCR with high-resolution melting analysis for rapid identification of carbapenem and colistin resistance genes in clinical Enterobacterales isolates. Sci Rep 16, 11901 (2026). https://doi.org/10.1038/s41598-026-41530-2
Schlüsselwörter: antimikrobielle Resistenz, carbapenemresistente Bakterien, Colistinresistenz, schnelle PCR‑Diagnostik, nosokomiale Infektionen