Clear Sky Science · pt
Perfilagem metagenômica da resistência antimicrobiana em águas residuais de cidades metropolitanas da Índia
Por que a água suja importa para todos
Nas grandes cidades, o que descartamos pelo vaso ou pela pia não desaparece simplesmente. Acumula-se em valas e esgotos, formando uma mistura turva de resíduos humanos, efluentes industriais e inúmeros microrganismos. Esse mundo oculto pode funcionar como um sistema de alerta precoce para a saúde pública — especialmente para rastrear bactérias que já não respondem aos antibióticos. Este estudo investigou as águas residuais de quatro das maiores áreas metropolitanas da Índia para identificar quais micróbios estão presentes, quais genes de resistência eles carregam e como esses genes podem estar se espalhando. As descobertas ajudam a explicar como nosso ambiente compartilhado pode, silenciosamente, alimentar a crise global das infecções resistentes a medicamentos.
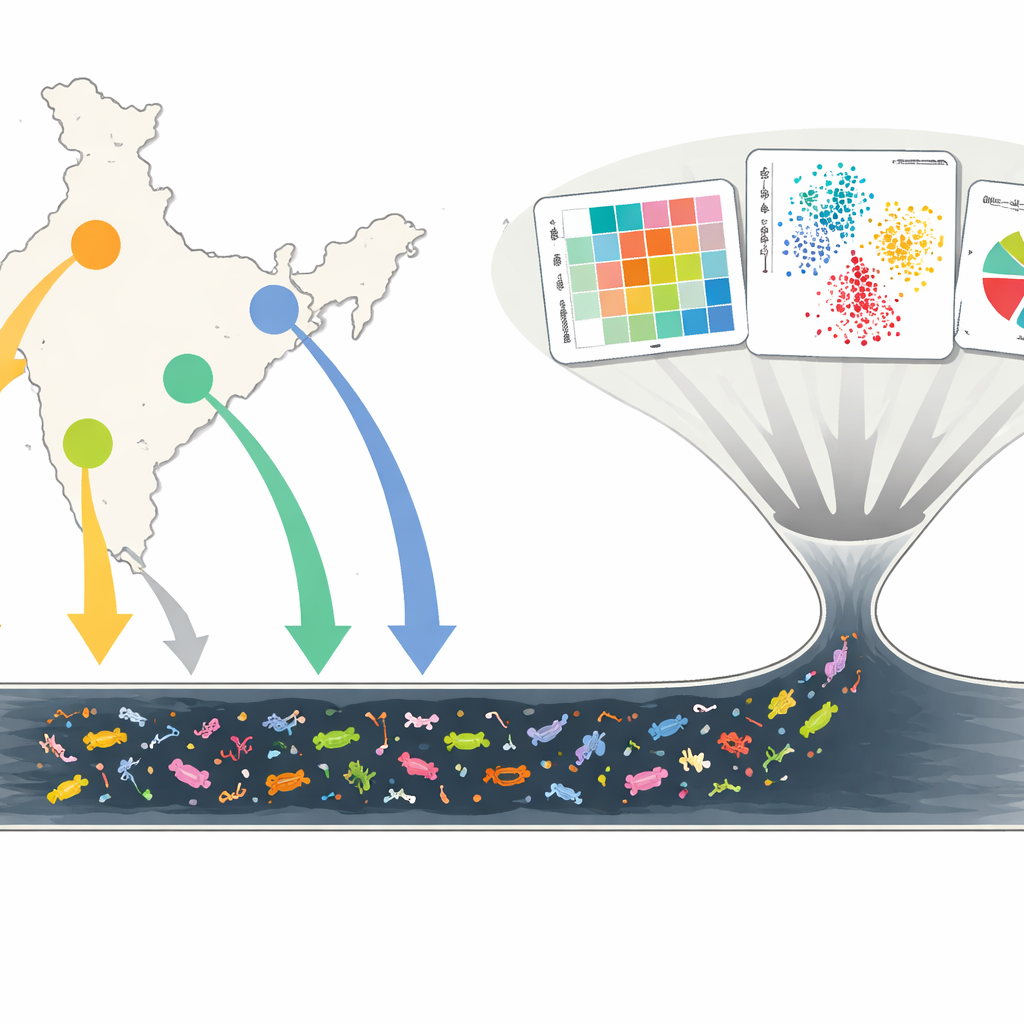
Espiando a sopa subterrânea da cidade
Os pesquisadores coletaram quase 450 amostras de águas residuais de 19 grandes valas abertas em Delhi, Mumbai, Chennai e Kolkata, mês após mês, ao longo de dois anos. Em vez de cultivar microrganismos em laboratório, usaram sequenciamento metagenômico por shotgun, um método que lê todo o DNA de uma amostra de uma só vez. Isso permitiu catalogar quais bactérias estavam presentes (o microbioma), quais genes de resistência apareciam (o resistoma) e com que frequência esses genes estavam ligados a elementos genéticos móveis — pequenos trechos de DNA que podem saltar entre micróbios. Ao comparar amostras ao longo do tempo e entre cidades, eles construíram um quadro detalhado de como as águas residuais urbanas refletem os riscos à saúde e as pressões por antibióticos de milhões de pessoas.
Micróbios da cidade com assinaturas locais
As comunidades bacterianas nas águas residuais de cada cidade eram distintas. Embora alguns grupos amplos de bactérias fossem comuns em todos os lugares, como Proteobacteria e Bacteroidetes, a combinação exata de espécies variou de cidade para cidade e às vezes de mês para mês. Mumbai apresentou a maior diversidade de espécies, enquanto Kolkata teve a menor. Certas bactérias associadas a doenças humanas, incluindo linhagens de Escherichia coli, Klebsiella pneumoniae e Pseudomonas aeruginosa, foram abundantes em pelo menos uma cidade, ressaltando a presença de patógenos clinicamente importantes nas águas residuais cotidianas. A equipe também reconstruíu milhares de genomas bacterianos quase completos a partir dos dados e descobriu que mais da metade não pôde ser associada a espécies conhecidas, sugerindo que os esgotos da Índia abrigam um vasto e em grande parte inexplorado mundo microbiano.
Genes de resistência que ignoram fronteiras urbanas
Quando os pesquisadores mudaram do foco dos micróbios inteiros para os próprios genes de resistência, emergiu um padrão diferente. Ao contrário dos micróbios, os genes de resistência a antibióticos não se agruparam nitidamente por cidade. Muitos dos mesmos genes apareceram nas quatro localidades, sugerindo um reservatório compartilhado de resistência moldado por uso semelhante de antibióticos e pressões ambientais. Genes que protegem bactérias contra múltiplas classes de fármacos eram especialmente comuns, assim como aqueles que conferem resistência a macrolídeos, tetraciclinas, rifamicinas e aminoglicosídeos. No entanto, genes que conferem proteção contra alguns dos nossos antibióticos críticos de última linha, como certas betalactamasas e colistina, foram relativamente raros nessas amostras, oferecendo uma pequena medida de tranquilidade.
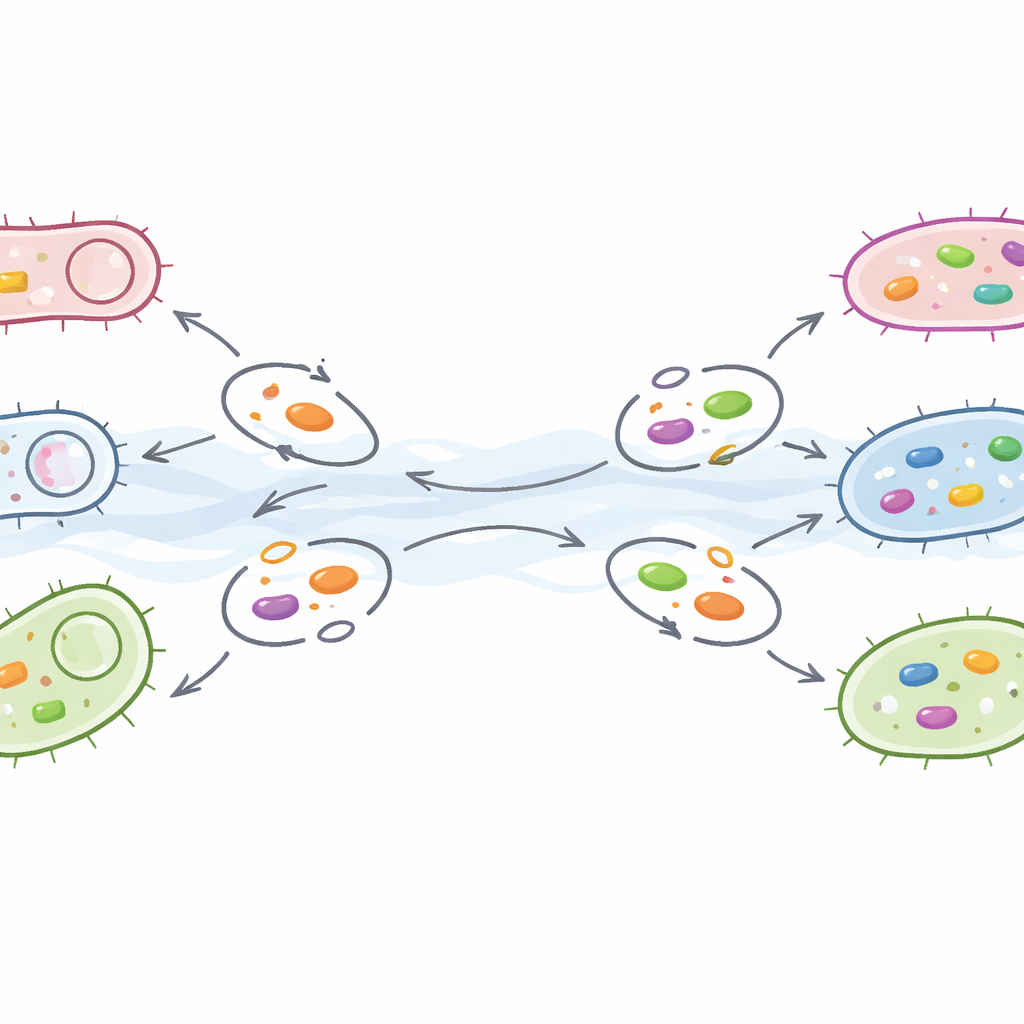
Como os genes pegam carona e formam alianças ocultas
A equipe investigou em seguida quão facilmente esses genes de resistência poderiam se espalhar. Procuraram nos genomas bacterianos por elementos genéticos móveis — plasmídeos e transposons — que atuam como transportadores, movendo DNA de um microrganismo para outro. Apenas cerca de um em cada dez fragmentos de DNA portadores de resistência também continha tais elementos móveis, mas esse subconjunto é crucial: representa genes prontos para pular. A resistência a famílias de fármacos comuns como tetraciclinas e betalactâmicos foi frequentemente encontrada nesses segmentos móveis, enquanto muitos genes de resistência a macrolídeos eram mais estáticos. Ao construir “redes de coocorrência”, os pesquisadores também mostraram que os micróbios de cada cidade formavam seus próprios padrões de interação, e que certos grupos bacterianos contribuíam de forma desproporcional para a carga local de genes de resistência.
O que isso significa para a saúde pública
No conjunto, o estudo mostra que as águas residuais da cidade não são apenas água suja — são um espelho sensível tanto da vida microbiana local quanto de um reservatório amplamente compartilhado de genes de resistência a antibióticos. Cada cidade tinha sua própria impressão microbiana, mas os genes de resistência em si eram surpreendentemente semelhantes, destacando com que facilidade a pressão por antibióticos pode gerar uma ameaça comum. A descoberta de muitas espécies bacterianas potencialmente novas e de combinações móveis de resistência ressalta o quanto ainda não sabemos sobre o ecossistema invisível sob nossos pés. Ao padronizar métodos simples de amostragem e armazenamento, os pesquisadores demonstram que a vigilância em larga escala de águas residuais é viável mesmo em contextos com recursos limitados. Esse monitoramento rotineiro poderia ajudar países como a Índia a detectar patógenos perigosos e resistências emergentes mais cedo, orientando políticas e infraestrutura mais inteligentes para desacelerar a disseminação da resistência antimicrobiana antes que ela chegue a clínicas e residências.
Citação: Singh, N.K., Garg, P., Kumari, S. et al. Metagenomic profiling of antimicrobial resistance in wastewater from metropolitan cities of India. Nat Commun 17, 4097 (2026). https://doi.org/10.1038/s41467-026-70702-x
Palavras-chave: vigilância de águas residuais, resistência antimicrobiana, metagenômica, microbioma urbano, Índia