Clear Sky Science · es
Perfil metagenómico de la resistencia antimicrobiana en aguas residuales de ciudades metropolitanas de la India
Por qué importa a todos el agua sucia
En las grandes ciudades, lo que arrojamos o desechamos no desaparece simplemente. Se acumula en desagües y alcantarillas, formando una mezcla turbulenta de residuos humanos, vertidos industriales y una multitud de microbios. Este mundo oculto puede actuar como un sistema de alerta temprana para la salud pública, especialmente para rastrear bacterias que ya no responden a los antibióticos. Este estudio exploró las aguas residuales de cuatro de las mayores áreas metropolitanas de la India para identificar qué microbios están presentes, qué genes de resistencia a antibióticos portan y cómo podrían estar propagándose esos genes. Los hallazgos ayudan a explicar cómo nuestro entorno compartido puede alimentar silenciosamente la crisis global de infecciones resistentes a los fármacos.
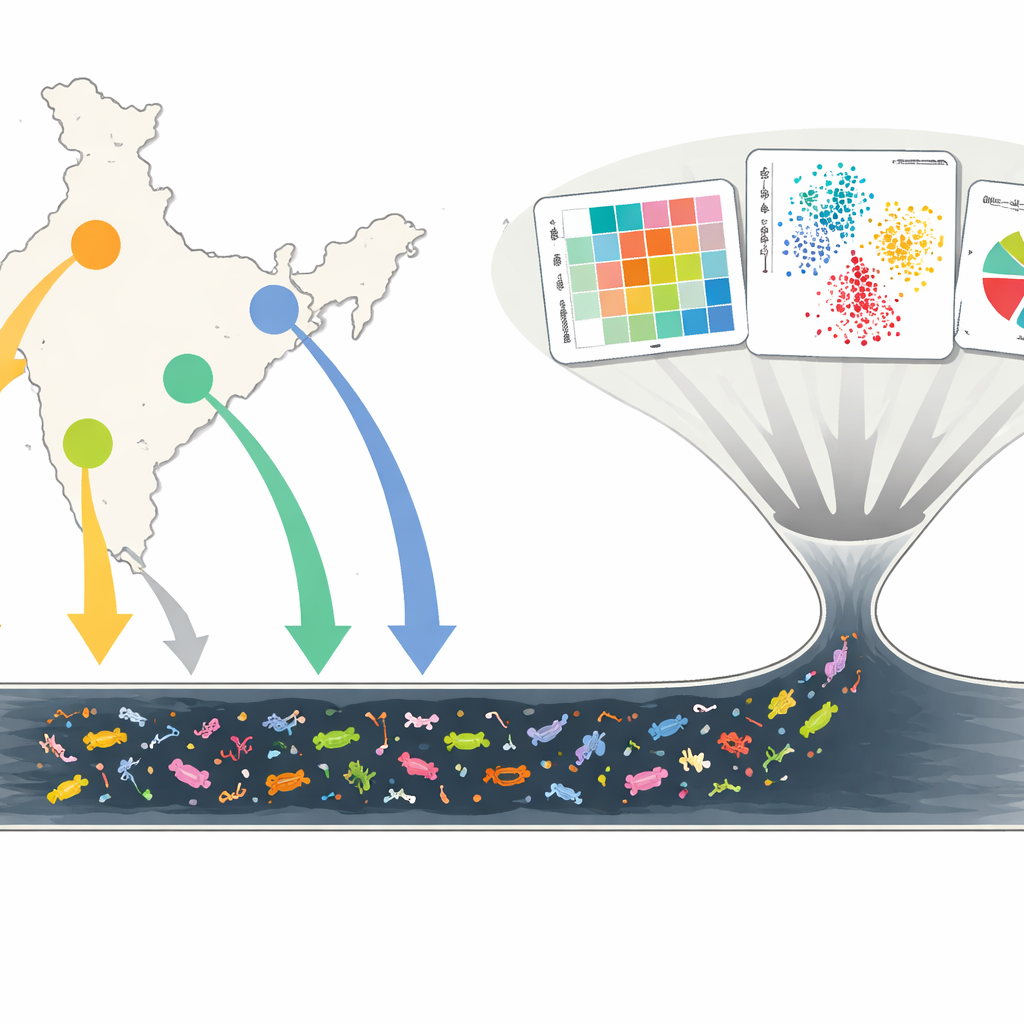
Un vistazo a la sopa subterránea de la ciudad
Los investigadores recogieron casi 450 muestras de aguas residuales de 19 grandes drenajes abiertos en Delhi, Mumbai, Chennai y Kolkata, mes tras mes durante dos años. En lugar de cultivar microbios en el laboratorio, emplearon secuenciación metagenómica tipo shotgun, un método que lee todo el ADN de una muestra de una sola vez. Esto les permitió catalogar qué bacterias estaban presentes (el microbioma), qué genes de resistencia aparecían (el resistoma) y con qué frecuencia esos genes se asociaban a elementos genéticos móviles—pequeños fragmentos de ADN que pueden saltar entre microbios. Al comparar muestras a lo largo del tiempo y entre ciudades, construyeron una imagen detallada de cómo las aguas residuales urbanas reflejan los riesgos para la salud y las presiones antimicrobianas de millones de personas.
Microbios urbanos con señas de identidad locales
Las comunidades bacterianas en las aguas residuales de cada ciudad eran distintas. Aunque algunos grupos amplios de bacterias eran comunes en todas partes, como Proteobacteria y Bacteroidetes, la mezcla exacta de especies variaba de una ciudad a otra y a veces de un mes a otro. Mumbai presentó la mayor riqueza de especies, mientras que Kolkata mostró la menor. Ciertas bacterias asociadas a enfermedades humanas, incluidas cepas de Escherichia coli, Klebsiella pneumoniae y Pseudomonas aeruginosa, fueron abundantes en al menos una ciudad, lo que subraya la presencia de patógenos clínicamente relevantes en las aguas residuales cotidianas. El equipo también reconstruyó miles de genomas bacterianos casi completos a partir de los datos y halló que más de la mitad no podían emparejarse con especies conocidas, lo que sugiere que las alcantarillas de la India albergan un vasto mundo microbiano, en gran parte inexplorado.
Genes de resistencia que no respetan fronteras ciudadanas
Cuando los investigadores se centraron en los propios genes de resistencia, emergió un patrón distinto. A diferencia de los microbios, los genes de resistencia a antibióticos no se agruparon claramente por ciudad. Muchos de los mismos genes aparecieron en las cuatro ubicaciones, lo que sugiere un reservorio compartido de resistencia moldeado por un uso de antibióticos y presiones ambientales similares. Los genes que protegen a las bacterias frente a múltiples clases de fármacos fueron especialmente comunes, al igual que los que confieren resistencia a macrólidos, tetraciclinas, rifamicinas y aminoglucósidos. Sin embargo, los genes que protegen frente a algunos de nuestros antibióticos de última línea más críticos, como ciertos betalactámicos y la colistina, fueron relativamente raros en estas muestras, ofreciendo una pequeña medida de tranquilidad.
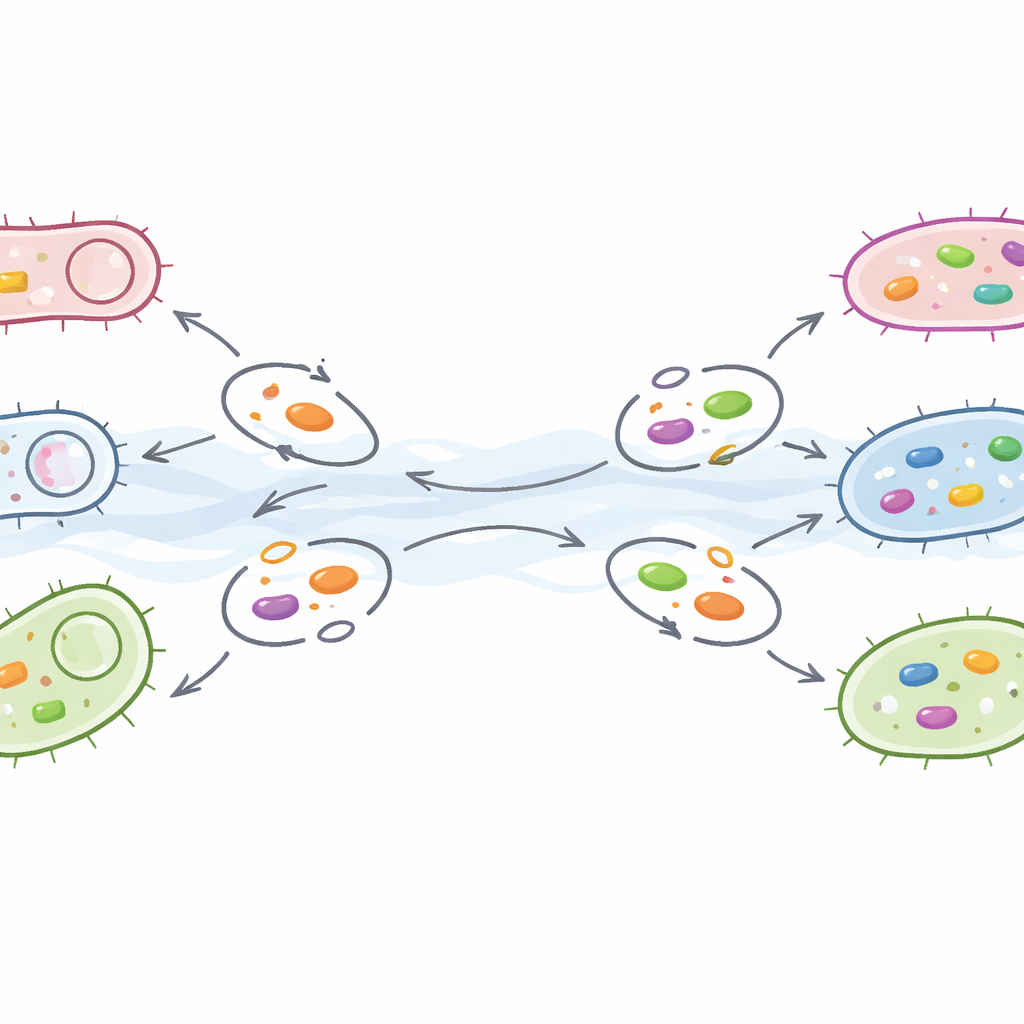
Cómo los genes hacen autostop y forman alianzas ocultas
El equipo preguntó a continuación cuán fácilmente podrían propagarse estos genes de resistencia. Buscaron en los genomas bacterianos elementos genéticos móviles—plásmidos y transposones—que actúan como lanzaderas, moviendo ADN de un microbio a otro. Solo alrededor de una de cada diez secuencias portadoras de resistencia también albergaba tales elementos móviles, pero este subconjunto es crucial: representa genes preparados para saltar. La resistencia a familias de fármacos comunes como tetraciclinas y betalactámicos se encontró con frecuencia en estos segmentos móviles, mientras que muchos genes de resistencia a macrólidos eran más estáticos. Mediante la construcción de “redes de coocurrencia”, los investigadores también mostraron que los microbios de cada ciudad formaban sus propios patrones de interacción, y que ciertos grupos de bacterias contribuían de manera desproporcionada a la carga local de genes de resistencia.
Qué significa esto para la salud pública
En conjunto, el estudio demuestra que las aguas residuales urbanas no son solo agua sucia: son un espejo sensible tanto de la vida microbiana local como de un reservorio ampliamente compartido de genes de resistencia a antibióticos. Cada ciudad tenía su propia huella microbiana, sin embargo los genes de resistencia eran sorprendentemente similares, lo que pone de manifiesto lo fácil que la presión antimicrobiana puede generar una amenaza común. El descubrimiento de muchas especies bacterianas potencialmente nuevas y combinaciones móviles de resistencia subraya cuánto desconocemos todavía sobre el ecosistema invisible bajo nuestros pies. Al estandarizar métodos sencillos de muestreo y conservación, los investigadores demuestran que la vigilancia a gran escala de aguas residuales es práctica incluso en entornos con recursos limitados. Un control rutinario así podría ayudar a países como la India a detectar patógenos peligrosos y resistencias emergentes antes, orientando políticas e infraestructuras más inteligentes para frenar la propagación de la resistencia antimicrobiana antes de que llegue a hospitales y hogares.
Cita: Singh, N.K., Garg, P., Kumari, S. et al. Metagenomic profiling of antimicrobial resistance in wastewater from metropolitan cities of India. Nat Commun 17, 4097 (2026). https://doi.org/10.1038/s41467-026-70702-x
Palabras clave: vigilancia de aguas residuales, resistencia antimicrobiana, metagenómica, microbioma urbano, India