Clear Sky Science · pl
Wzór ekspresji podjednostek EXO70 w pojedynczych komórkach liści Arabidopsis thaliana za pomocą analizy sieci współwystępowania
Jak liście roślin po cichu kierują ruchem
W każdym liściu roślin tysiące maleńkich pakunków przemieszczają lipidy, białka i cząsteczki sygnałowe na powierzchnię komórki. Ten mikroskopijny ruch utrzymuje wzrost liści, ich zdolność do wyczuwania światła i radzenia sobie ze stresem. Opisane tutaj badanie analizuje jedną grupę koordynatorów tego ruchu — rodzinę białek EXO70 u Arabidopsis thaliana — i pokazuje, jak różne warianty tych białek są aktywowane w różnych typach komórek liścia. Praca wprowadza też nowy sposób wykrywania wzorców w bardzo słabej aktywności genów, co otwiera możliwości badania wielu innych trudnych do wykrycia cząsteczek.
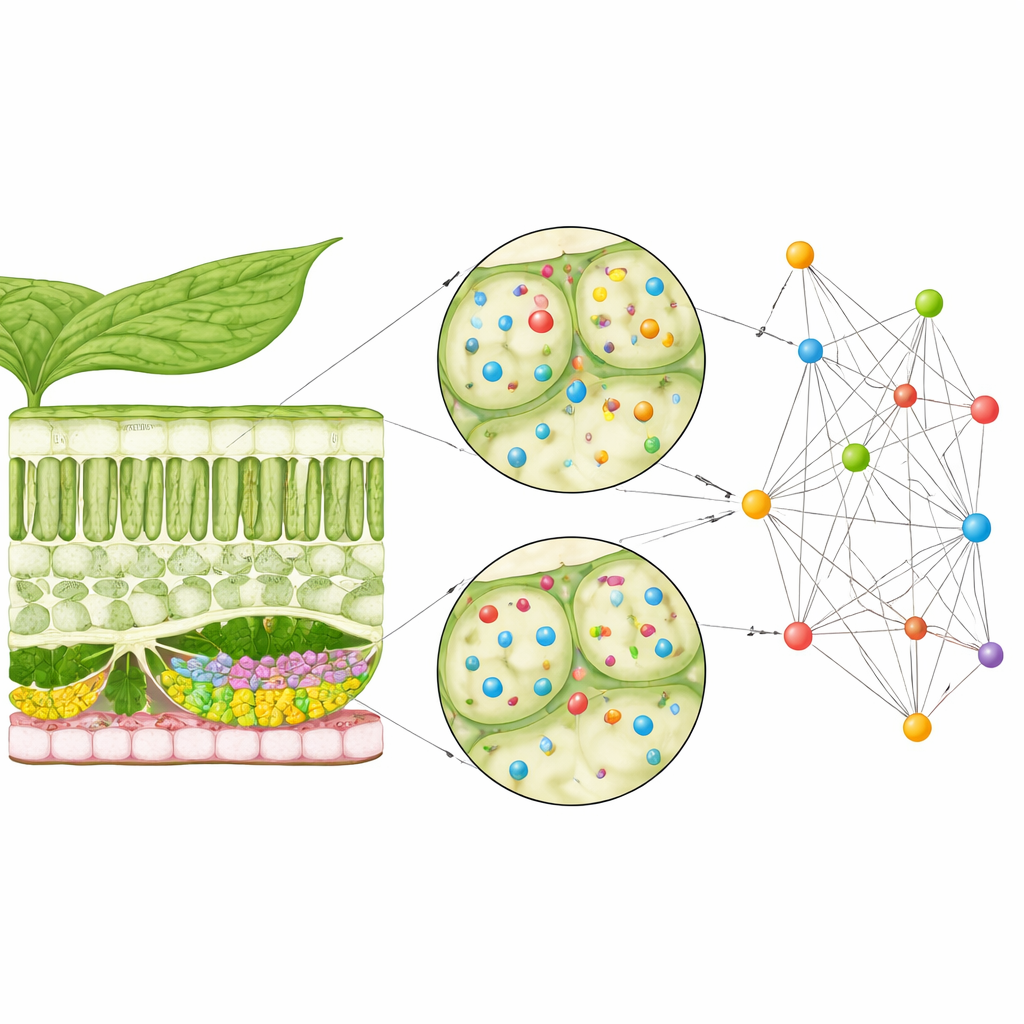
Dlaczego mali kierowcy ruchu mają znaczenie
Komórki roślin polegają na systemie dostarczania, który wysyła pęcherzyki otoczone błoną do określonych miejsc na powierzchni komórki. Duży kompleks białkowy zwany egzosomem pomaga dokować te pęcherzyki. Jedna grupa składników egzosomu, znana jako białka EXO70, występuje w wielu nieco różnych wersjach, tzw. izoformach, w liściach Arabidopsis. Wcześniejsze prace sugerowały, że różne izoformy EXO70 działają w różnych typach komórek i w różnych sytuacjach, ale nie było jasne, jak ich aktywność rozkłada się w wielowarstwowej strukturze liścia. Ponieważ geny kodujące te białka są często słabo aktywne, trudno je badać za pomocą standardowych narzędzi szukających silnych sygnałów genowych.
Analiza pojedynczych komórek in situ
Naukowcy zwrócili się ku potężnemu podejściu zwanemu przestrzenną transkryptomiką pojedynczych komórek, które odczytuje, które geny są aktywne w setkach pojedynczych komórek, zachowując ich pozycje w przekroju liścia. Wykorzystali publiczne dane „stereo‑seq” z liści Arabidopsis, które obejmowały warstwę górnej i dolnej epidermy, dwa rodzaje komórek fotosyntetycznych oraz komórki naczyniowe transportujące wodę i substancje odżywcze. Nawet przy tej wysokiej rozdzielczości każda komórka wykazywała aktywność tylko niewielkiej części wszystkich genów, a geny związane z EXO70 były szczególnie słabe. Tradycyjne analizy „współekspresji”, opierające się na porównywaniu, jak mocno geny włączają się razem, z trudem wykrywały sensowne wzorce w tych rozrzedzonych sygnałach.
Od współekspresji do współwystępowania
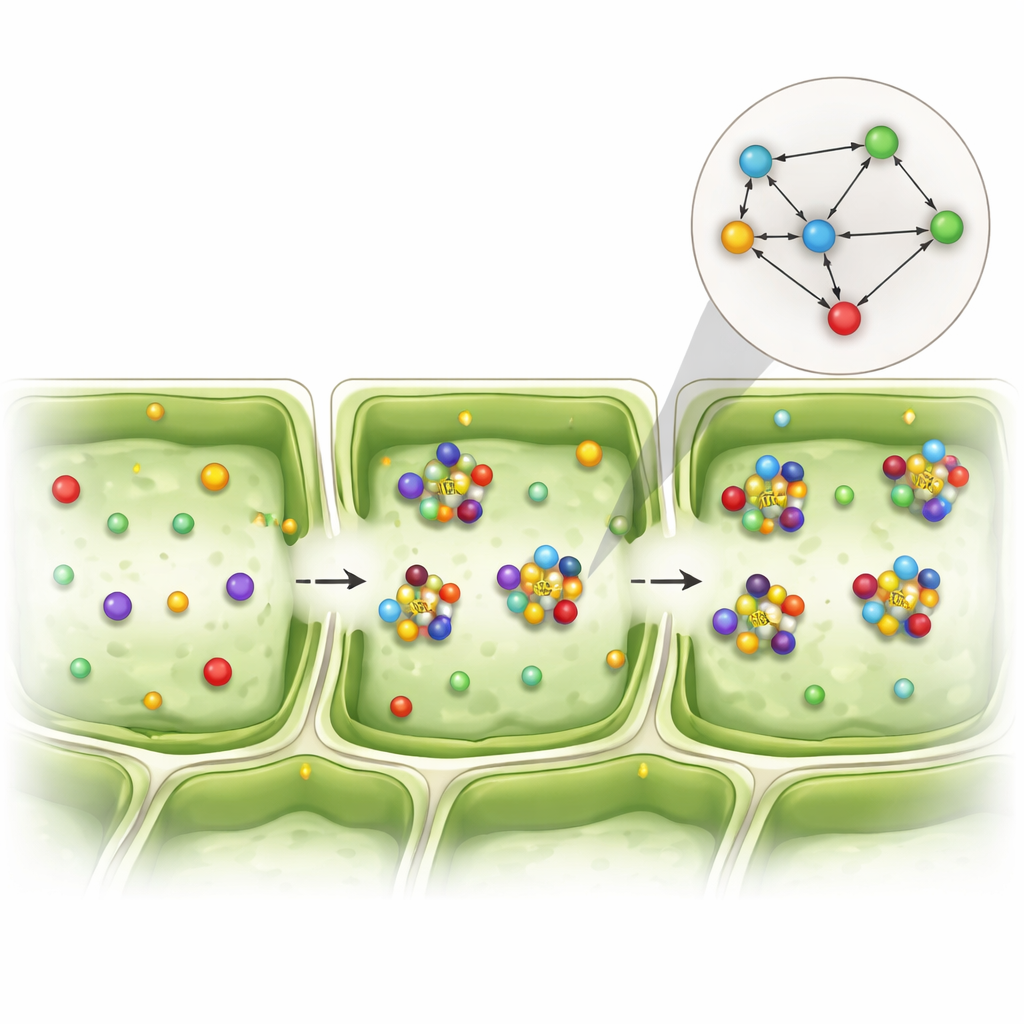
Aby pokonać ten problem, zespół przeformułował pytanie. Zamiast pytać, czy dwa geny są silnie aktywne razem, zadał prostsze pytanie typu tak‑nie: czy te dwa geny w ogóle pojawiają się w tej samej komórce? Dane przekształcono w siatkę zer i jedynek oznaczających jedynie obecność lub brak, a następnie mnożono i porównywano te wzorce w tysiącach komórek. To wygenerowało to, co autorzy nazywają „siecią współwystępowania”, mapę tego, jak często pary genów występują w tych samych komórkach częściej niż oczekiwano przypadkowo. Za pomocą statystycznych testów permutacyjnych wyodrębnili pary genów, których wspólne pojawienie się jest mało prawdopodobne do wyjaśnienia przypadkiem, nawet gdy każdy gen jest jedynie słabo aktywny.
Ukryte partnerstwa w tkankach liścia
Widok oparty na współwystępowaniu odsłonił wyraźne wzorce interakcji między izoformami EXO70, innymi składnikami egzosomu i białkami związanymi z pęcherzykami w różnych warstwach komórkowych. W szczególności pewne wersje EXO70 oraz inna podjednostka egzosomu, SEC3A, wielokrotnie pojawiały się razem w gąbczastych komórkach fotosyntetycznych, co sugeruje, że te białka współpracują przy kierowaniu dostarczaniem pęcherzyków w tym konkretnym typie tkanki. Inne kombinacje EXO70 wyróżniały się w komórkach górnej powierzchni liścia, wskazując na role w reakcjach na stres i kształtowaniu ściany komórkowej. Choć badanie skupiało się na aktywności genów, a nie poziomach białek, i wiadomo, że wiele białek EXO70 jest regulowanych po transkrypcyjnie, powtarzające się wzorce współwystępowania sugerują funkcjonalnie wyspecjalizowane partnerstwa w obrębie tej samej rodziny molekularnej.
Nowe spojrzenie na ciche, lecz kluczowe geny
Dla osób spoza specjalności kluczowy wniosek jest taki, że ważni gracze biologiczni nie zawsze są najgłośniejsi. Przechodząc od mierzenia, jak „mocno” geny włączają się razem, do prostego pytania, czy mają tendencję do pojawiania się w tej samej komórce, autorzy odzyskują subtelne, lecz znaczące powiązania między genami o niskiej aktywności. Pokazują, że białka EXO70 w liściach nie są wymienialnymi częściami, lecz członkami wyspecjalizowanych zespołów montowanych w określonych typach komórek. Podejście oparte na sieci współwystępowania oferuje ogólną strategię odkrywania podobnie cichych, ale istotnych regulatorów — od czynników transkrypcyjnych po białka sygnałowe — w wielu rodzajach tkanek.
Cytowanie: Yu, X., Shang, J. The expression pattern of EXO70 subunits in single-cell stereo-seq of Arabidopsis thaliana leaves using coexistence network analysis. Sci Rep 16, 10694 (2026). https://doi.org/10.1038/s41598-026-44501-9
Słowa kluczowe: egzosom, transkryptomika przestrzenna, Arabidopsis, transport pęcherzykowy, biologia pojedynczych komórek