Clear Sky Science · de
Expressionsmuster der EXO70-Untereinheiten in Single-Cell Stereo-seq von Arabidopsis thaliana-Blättern mittels Koexistenz-Netzwerkanalyse
Wie Pflanzenblätter den Verkehr still steuern
Im Inneren jedes Pflanzenblatts transportieren zahllose winzige Frachtpakete Fette, Proteine und Signalstoffe zur Zelloberfläche. Dieser mikroskopische Verkehr hält die Blätter im Wachstum, ermöglicht Lichtwahrnehmung und hilft beim Umgang mit Stress. Die hier beschriebene Studie betrachtet eine Gruppe von Verkehrssteuerern, die EXO70-Proteinfamilie in Arabidopsis thaliana, und zeigt, wie verschiedene Varianten dieser Proteine in unterschiedlichen Blattzelltypen aktiviert werden. Zudem führt sie einen neuen Weg ein, Muster in sehr schwacher Genaktivität zu entdecken, was den Zugang zur Untersuchung vieler anderer schwer nachweisbarer Moleküle öffnet.
Warum winzige Verkehrsleiter wichtig sind
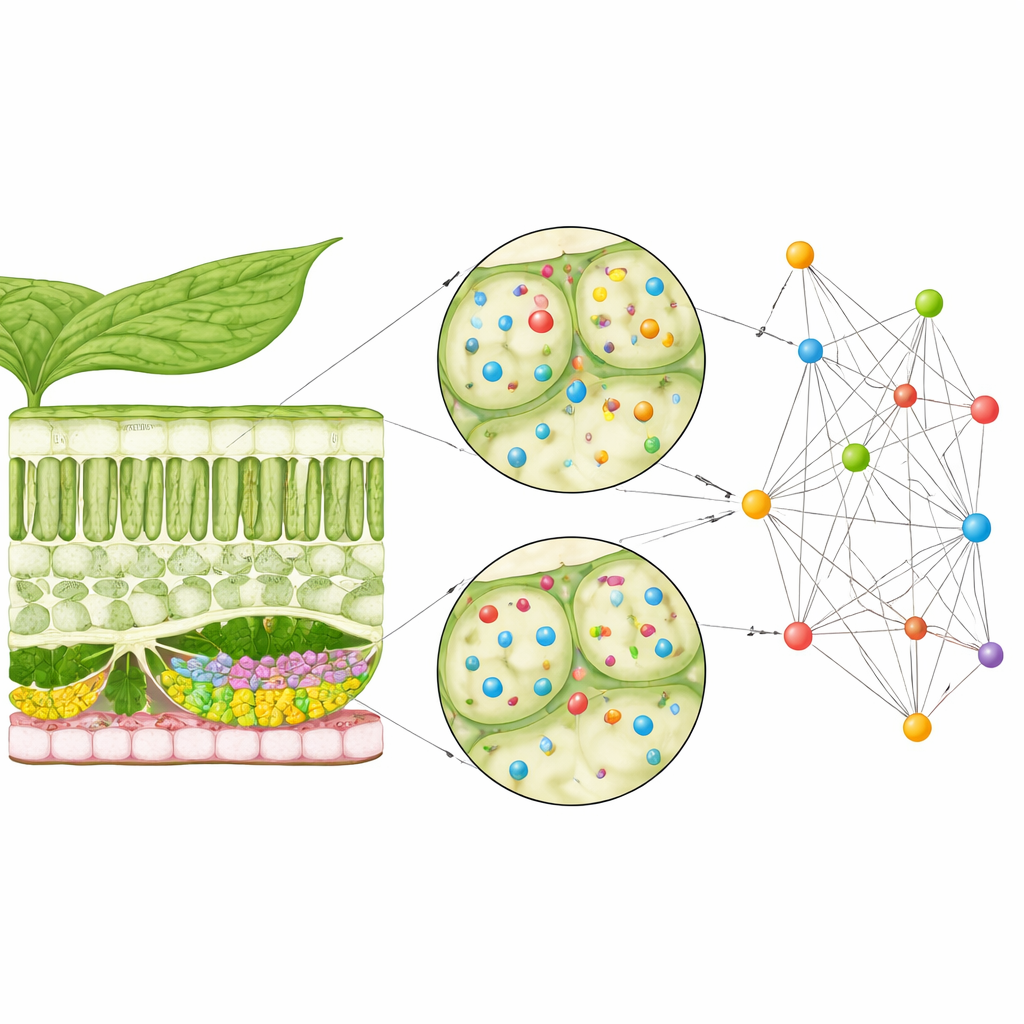
Pflanzenzellen sind auf ein Liefersystem angewiesen, das membranumhüllte Pakete, so genannte Vesikel, an bestimmte Stellen der Zelloberfläche bringt. Ein großer Proteinkomplex, das Exozyst, hilft beim Andocken dieser Vesikel. Eine Gruppe von Exozyst-Komponenten, bekannt als EXO70-Proteine, liegt in Arabidopsis-Blättern in vielen leicht unterschiedlichen Varianten oder Isoformen vor. Frühere Arbeiten deuteten bereits an, dass verschiedene EXO70-Isoformen in unterschiedlichen Zelltypen und Situationen wirken, doch war unklar, wie ihre Aktivität im geschichteten Aufbau des Blattes variiert. Da die Gene, die diese Proteine kodieren, oft nur schwach aktiv sind, sind sie mit Standardmethoden, die auf starke Gensignale ausgelegt sind, schwer zu untersuchen.
Einzelzellen im räumlichen Kontext betrachten
Die Forschenden griffen zu einem leistungsfähigen Ansatz namens Einzelzell-räumliche Transkriptomik, mit dem sich ermitteln lässt, welche Gene in hunderten einzelner Zellen aktiv sind, während ihre Positionen in einem Blattquerschnitt erhalten bleiben. Sie nutzten öffentlich verfügbare Stereo-seq-Daten von Arabidopsis-Blättern, die obere und untere Epidermis, zwei Arten photosynthetisch aktiver Zellen und Gefäßzellen, die Wasser und Nährstoffe transportieren, erfassten. Selbst mit dieser hochauflösenden Methode zeigte jede Zelle Aktivität nur für einen kleinen Bruchteil aller Gene, und EXO70-bezogene Gene waren besonders schwach ausgeprägt. Traditionelle Koexpressionsanalysen, die darauf basieren zu vergleichen, wie stark Gene gemeinsam anschalten, hatten daher Schwierigkeiten, in diesen dünnen Signalen sinnvolle Muster zu finden.
Von Koexpression zu Koexistenz
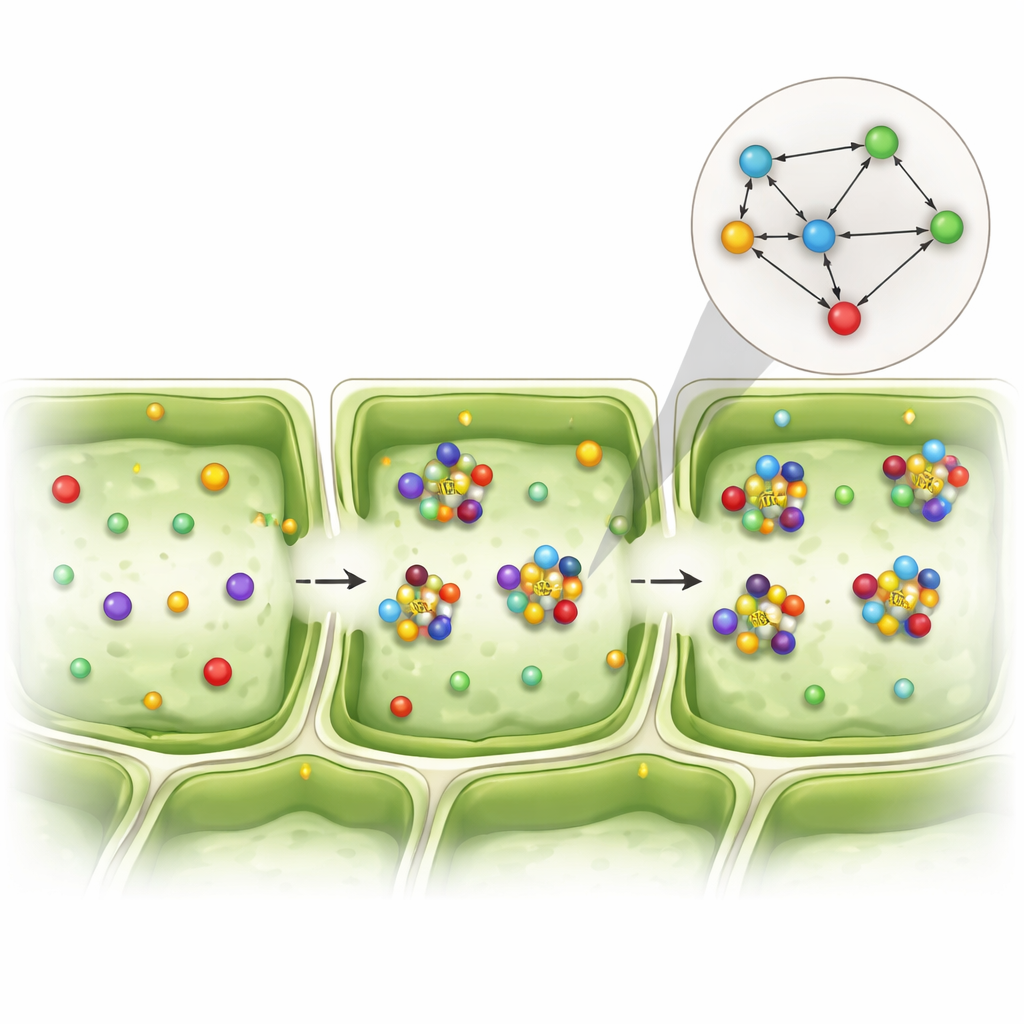
Um dieses Problem zu überwinden, stellte das Team die Fragestellung um. Anstatt zu fragen, ob zwei Gene stark gemeinsam aktiv sind, stellten sie eine einfachere Ja‑/Nein‑Frage: Tauchen diese beiden Gene überhaupt in derselben Zelle auf? Sie wandelten die Daten in ein Raster aus Nullen und Einsen um, das bloße Anwesenheit oder Abwesenheit markierte, und multiplizierten und verglichen diese Muster über Tausende von Zellen hinweg. Das erzeugte das, was sie ein „Koexistenz-Netzwerk“ nennen — eine Karte, wie häufig Genpaare öfter als zufällig in denselben Zellen vorkommen. Mit statistischen Zufallstests hoben sie Genpaare hervor, deren gemeinsames Auftreten unwahrscheinlich zufällig war, selbst wenn jedes einzelne Gen nur schwach aktiv war.
Verborgene Partnerschaften im Blattgewebe
Diese Koexistenz-Perspektive enthüllte unterschiedliche Interaktionsmuster zwischen EXO70-Isoformen, anderen Exozyst-Komponenten und vesikelbezogenen Proteinen in verschiedenen Zellschichten. Besonders auffällig war, dass bestimmte EXO70-Varianten und eine weitere Exozyst-Untereinheit, SEC3A, wiederholt gemeinsam in schwammigen photosynthetischen Zellen auftraten, was darauf hindeutet, dass diese Proteine in diesem Gewebe als Team die Vesikelzustellung steuern. Andere EXO70-Kombinationen hoben sich in den oberen Oberflächenzellen des Blattes hervor und deuten auf Rollen bei Stressreaktionen und der Formung der Zellwand hin. Zwar konzentrierte sich die Studie auf Genaktivität statt auf Proteinmengen und viele EXO70-Proteine werden nach der RNA-Bildung noch reguliert, doch diese wiederkehrenden Koexistenzmuster weisen auf funktionell spezialisierte Partnerschaften innerhalb derselben Proteinfamilie hin.
Eine neue Linse für leise, aber wichtige Gene
Für Nichtfachleute lautet die zentrale Botschaft: Wichtige biologische Akteure sind nicht immer die lautesten. Indem die Messung davon wegverlegt wurde, wie „stark“ Gene gemeinsam anschalten, hin zu der einfachen Frage, ob sie dazu neigen, in derselben Zelle aufzutauchen, stellt diese Arbeit subtile, aber bedeutungsvolle Verbindungen zwischen schwach aktiven Genen wieder her. Die Autorinnen und Autoren zeigen, dass EXO70-Proteine in Blättern keine austauschbaren Bauteile sind, sondern Mitglieder maßgeschneiderter Teams, die in bestimmten Zelltypen zusammengesetzt werden. Ihr Koexistenz-Netzwerk-Ansatz bietet eine allgemeine Strategie, ähnlich leise, aber essenzielle Regulatoren — von Transkriptionsfaktoren bis zu Signalmolekülen — in vielen Gewebetypen aufzuspüren.
Zitation: Yu, X., Shang, J. The expression pattern of EXO70 subunits in single-cell stereo-seq of Arabidopsis thaliana leaves using coexistence network analysis. Sci Rep 16, 10694 (2026). https://doi.org/10.1038/s41598-026-44501-9
Schlüsselwörter: Exozyst, räumliche Transkriptomik, Arabidopsis, Vesikeltransport, Einzelzellbiologie