Clear Sky Science · pl
Predykcja mikrobiomu gleby przy użyciu tradycyjnych metod uczenia maszynowego i modeli głębokiego uczenia
Dlaczego drobne życie w glebie ma znaczenie
Każda łyżeczka gleby kryje tętniący życiem świat bakterii i grzybów, które po cichu napędzają produkcję żywności, magazynują węgiel i recyklingują składniki odżywcze. Mimo to wciąż trudno nam przewidzieć, które mikroby wystąpią w danym miejscu i jak zareagują na zmiany klimatu i użytkowania terenu. W tym badaniu postawiono praktyczne pytanie: czy nowoczesne modele komputerowe, wytrenowane na podstawowych pomiarach środowiskowych, takich jak temperatura, opady i chemia gleby, potrafią wiarygodnie przewidzieć skład tych ukrytych wspólnot?
Wielkie zbiory danych spotykają podziemny świat
Naukowcy skupili się na mikrobiomie gleby — ogromnej wspólnocie mikroorganizmów żyjących w glebie — traktując ją jako system, który może być przewidywalny na podstawie otoczenia. Korzystając z dwóch dużych publicznych zestawów danych: globalnych badań gleb oraz zasobów National Ecological Observatory Network (NEON) w USA, zebrali informacje o wspólnotach bakterii i grzybów wraz z pomiarami takimi jak pH gleby, zawartość węgla i azotu, klimat i pokrycie roślinne. Zamiast śledzić każdy gatunek osobno, pogrupowali mikroby na szersze kategorie: poziomy taksonomiczne jak typ, klasa, rząd, rodzina i rodzaj oraz grupy funkcjonalne opisujące, co mikroby robią, np. biorą udział w cyklu węgla lub azotu.
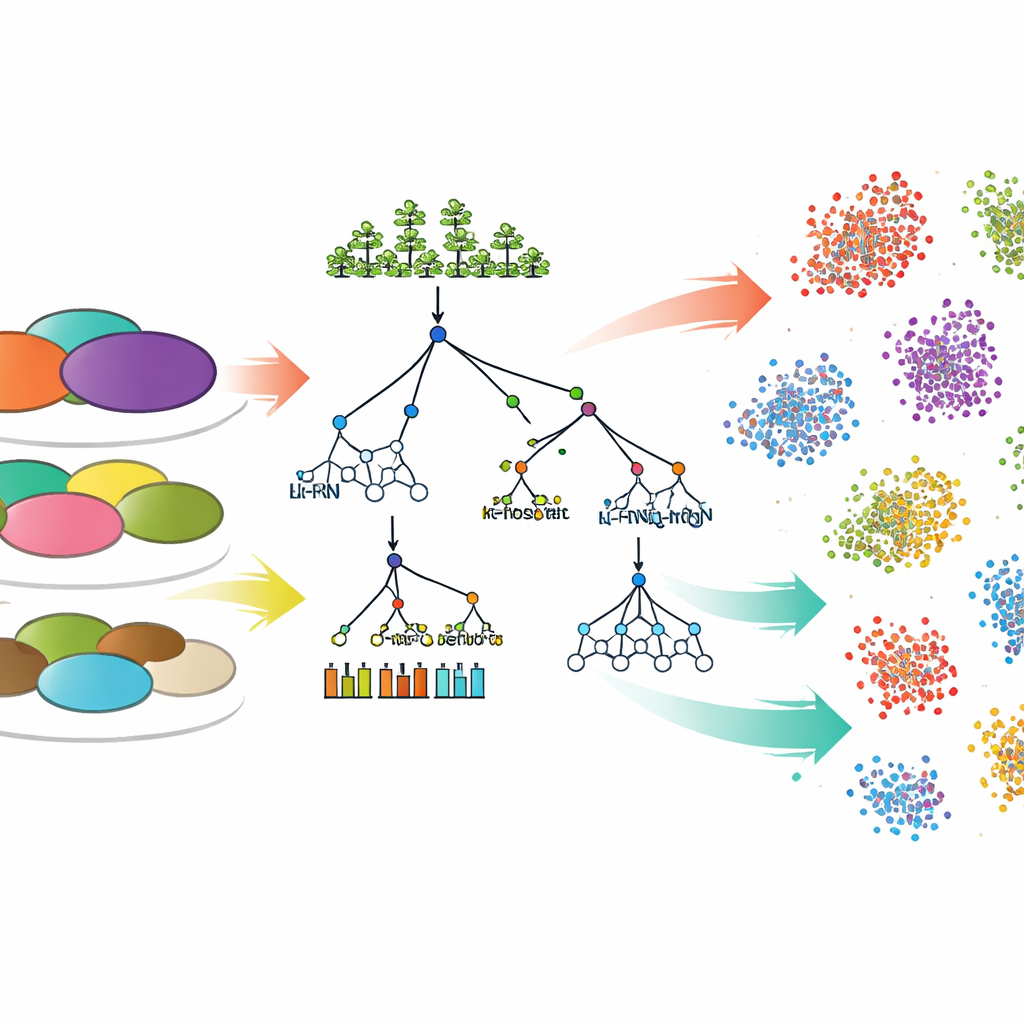
Testowanie różnych sposobów uczenia się z danych
Aby przekształcić pomiary środowiskowe w prognozy składu wspólnot, zespół porównał siedem podejść modelowania komputerowego. Sześć z nich to powszechnie stosowane „tradycyjne” metody uczenia maszynowego, w tym regresja liniowa, drzewa decyzyjne, lasy losowe, gradient boosting i k-najbliższych sąsiadów. Siódmym był model głębokiego uczenia zwany wielowarstwowym perceptronem, rodzaj sieci neuronowej. Dla każdego zestawu danych i każdego poziomu taksonomicznego lub funkcjonalnego modele były trenowane na większości próbek, a następnie proszone o przewidzenie względnych obfitości grup mikroorganizmów w nowych, nieznanych próbkach gleby. Dokładność tych prognoz mierzono standardową statystyką (R²), która odzwierciedla, jak dużą część rzeczywistej zmienności model potrafi wyjaśnić.
Wzory występujące w skali wspólnoty glebowej
Pojawił się wyraźny wzorzec: łatwiej przewidzieć szerokie grupy mikroorganizmów niż drobne szczegóły. Zarówno dla bakterii, jak i dla grzybów, modele zwykle osiągały najlepsze wyniki na wyższych poziomach taksonomicznych, takich jak typ i klasa, a dokładność malała przy próbach rozróżnienia mniejszych kategorii, np. rodziny i rodzaju. To sugeruje, że choć dokładny skład blisko spokrewnionych mikroorganizmów może być trudny do przewidzenia, ogólna struktura wspólnoty jest silniej związana ze środowiskiem. Wyjątek zaobserwowano dla bakteryjnych grup funkcjonalnych w jednym zestawie danych, gdzie żaden z modeli nie uchwycił wzorców dobrze — prawdopodobnie dlatego, że wybrane kategorie funkcjonalne nie odzwierciedlały w pełni rzeczywistej złożoności ról mikroorganizmów.
Które modele sprawdziły się najlepiej i dlaczego
Wśród wszystkich testowanych podejść dwie tradycyjne metody — lasy losowe i k-najbliższych sąsiadów — konsekwentnie dawały najsilniejsze predykcje. Lasy losowe wyróżniały się na szerszych poziomach taksonomicznych, podczas gdy k-najbliższych sąsiadów był szczególnie skuteczny na bardziej szczegółowych poziomach, takich jak rodzina i rodzaj. Gradient boosting czasami dorównywał lub przewyższał te modele, zwłaszcza dla funkcjonalnych grup grzybów, ale jego wydajność była bardziej zmienna w zależności od poziomu. Zaskakująco, sieć neuronowa głębokiego uczenia rzadko przewyższała te prostsze metody. Autorzy twierdzą, że w dużej mierze wynika to z faktu, iż głębokie uczenie zwykle wymaga znacznie więcej danych treningowych niż kilkaset do kilku tysięcy próbek gleby dostępnych tutaj. Ogólnie rzecz biorąc, wspólnoty bakteryjne były łatwiejsze do przewidzenia niż grzybowe, a zestawy danych z większą liczbą próbek dawały lepsze wyniki.
Co to oznacza dla gospodarowania glebą
Badanie pokazuje, że nawet przy dzisiejszych nieidealnych danych uczenie maszynowe może już dostarczać stosunkowo dobrych prognoz składu mikrobiologicznego gleby na szerokich poziomach. To zachęcające dla działań związanych z zarządzaniem glebami w rolnictwie, przywracaniu terenów i łagodzeniu zmian klimatu, ponieważ sugeruje, że można używać stosunkowo prostych pomiarów środowiskowych do przewidywania największych zmian w podziemnym świecie. Jednocześnie trudność w przewidywaniu szczegółów na małą skalę i niektórych grup funkcjonalnych podkreśla, jak wiele wciąż nie wiemy o organizmach glebowych i ich rolach. Potrzebne będą lepsze, większe zbiory danych i bogatsze opisy funkcji mikroorganizmów, zanim głębokie uczenie i inne zaawansowane narzędzia będą mogły w pełni wykorzystać swój potencjał w kierowaniu opieką nad żywą glebą pod naszymi stopami.
Cytowanie: Aouabed, Z., Therrien, V., Bouaoune, M.A. et al. Soil microbiome prediction using traditional machine learning and deep learning models. Sci Rep 16, 11069 (2026). https://doi.org/10.1038/s41598-026-39537-w
Słowa kluczowe: mikrobiom gleby, uczenie maszynowe, bakterie i grzyby, gradienty środowiskowe, predykcja składu wspólnot