Clear Sky Science · pl
Monoz chromosomowy oraz anotacja genomu Rhinogobio ventralis — zagrożonego, endemicznego gatunku ryby z Jangcy
Rzeczna ryba na krawędzi
Rhinogobio ventralis to niewielka, srebrzysta ryba występująca wyłącznie w szybkopłynących górnych odcinkach chińskiej rzeki Jangcy. Kiedyś ceniona jako ryba stołowa lokalnie, została wypchnięta na skraj wyginięcia przez zapory, zanieczyszczenia i nadmierne połowy. W tym badaniu zbudowano kompletny genetyczny schemat dla tego gatunku, dając ochroniarzom potężne nowe narzędzie do zrozumienia, jak ryba żyje, adaptuje się i jak można ją uratować.
Dlaczego ta mała ryba ma znaczenie
Rhinogobio ventralis należy do rodziny karpiowatych i ewoluowała tak, by dobrze funkcjonować w silnym nurcie, składając unoszące się jaja, które płyną z prądem rzeki. Ponieważ nie występuje nigdzie indziej na Ziemi, jej spadek stanowi utratę unikalnego dziedzictwa przyrodniczego oraz sygnał ostrzegawczy o stanie górnej Jangcy. Do tej pory większość badań skupiała się na podstawowej biologii gatunku i próbach hodowli w niewoli. Brakowało szczegółowej mapy DNA — zestawu instrukcji kształtujących budowę ciała, zachowanie i zdolność do radzenia sobie ze zmianami środowiska.
Tworzenie genetycznego planu
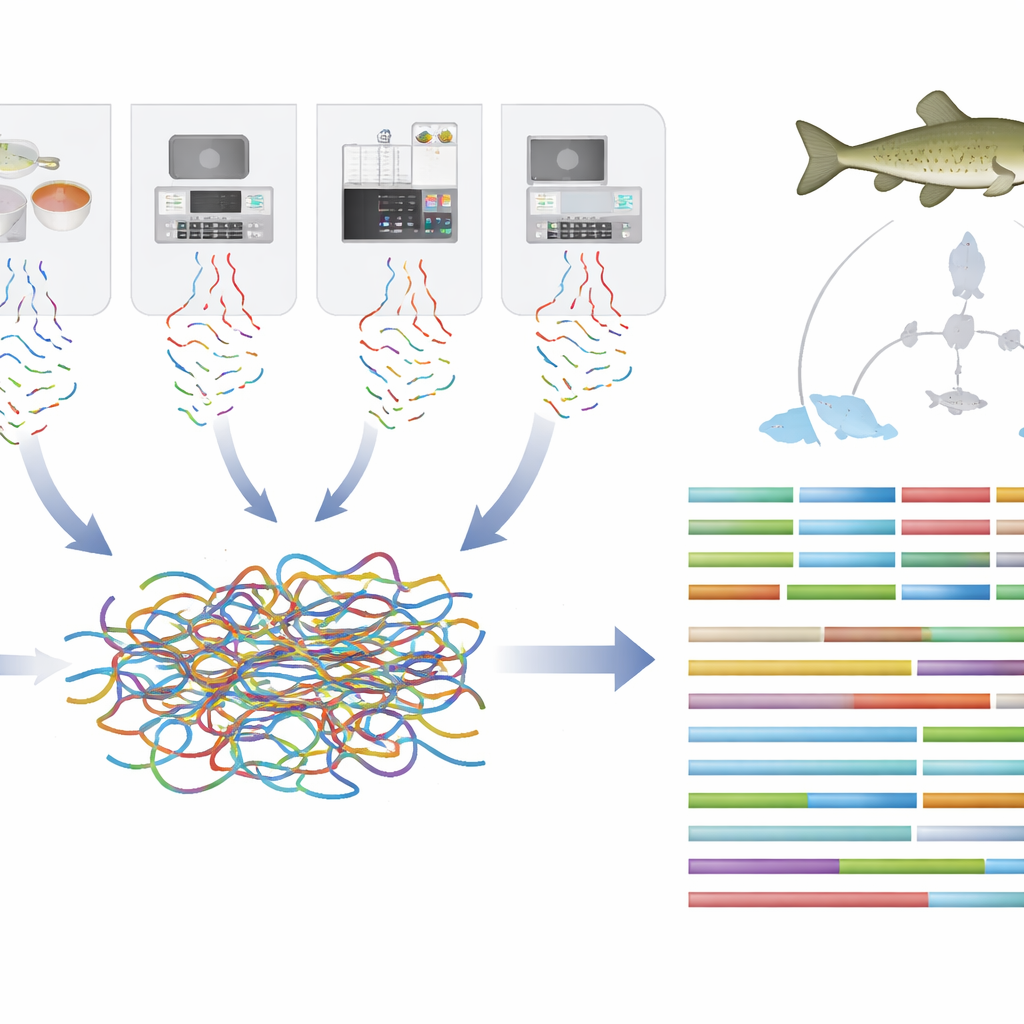
Aby stworzyć tę mapę, badacze pobrali tkanki od zdrowej dorosłej samicy hodowanej w niewoli. Wykorzystali kilka zaawansowanych technologii sekwencjonowania DNA, z których każda dostarcza innego kawałka układanki. Sekwencjonowanie długich odczytów ujawnia rozległe fragmenty DNA w jednym przebiegu, sekwencjonowanie krótkich odczytów sprawdza drobne szczegóły z bardzo wysoką dokładnością, a metoda zwana Hi‑C rejestruje, jak fragmenty DNA są fizycznie ułożone w jądrze komórkowym. Poprzez staranne połączenie tych danych zmontowano genom ryby w 25 długich jednostek DNA odpowiadających chromosomom, z bardzo niewielkimi lukami i błędami.
Co ujawnia genom
Gotowy genom ma nieco ponad miliard „liter” i przechodzi rygorystyczne kontrole jakości zwykle stosowane do genomów referencyjnych gatunków modelowych. Prawie dwie trzecie stanowią powtarzalne segmenty, z których wiele to ruchome elementy DNA zdolne do kopiowania się i przemieszczania w genomie. Powtórzenia te tłumaczą, dlaczego sekwencja jest tak złożona i mogą wpływać na zdolność ryby do adaptacji do zmieniającego się środowiska. W ramach tej struktury zespół zidentyfikował ponad 23 000 genów kodujących białka i był w stanie przypisać prawdopodobne funkcje niemal wszystkim z nich, porównując je z genami już zbadanymi u innych ryb.
Umieszczenie ryby na drzewie życia
Dysponując tym szczegółowym genomem, naukowcy porównali Rhinogobio ventralis z różnymi innymi promieniopłetwymi rybami. Pogrupowali jego geny w rodziny występujące u wielu gatunków, odkryli kilkaset rodzin genowych unikatowych dla tej ryby oraz prześledzili, które rodziny się rozszerzyły lub skurczyły w czasie. Analiza ewolucyjna pokazuje, że Rhinogobio ventralis jest blisko spokrewniona z inną rybą z Jangcy, Coreius guichenoti, a ich linie rozdzieliły się mniej więcej 23,5 miliona lat temu. Te porównania potwierdzają, że nowy genom jest zarówno biologicznie spójny, jak i technicznie solidny.
Podstawa do ratowania gatunku
Autorzy umieścili wszystkie surowe dane i zmontowany genom w publicznych bazach danych, aby inni badacze mogli z nich swobodnie korzystać. Ta genetyczna mapa będzie wspierać przyszłe prace nad strukturą populacji Rhinogobio ventralis w naturze, nad tym, które zmiany DNA warunkują istotne cechy, oraz nad tym, jak najlepiej zaprojektować programy hodowli i wypuszczania. Mówiąc prosto, badanie zamienia mało znaną zagrożoną rybę w gatunek dobrze poznany genetycznie, dając biologii ochrony mocniejsze naukowe podstawy, by zapobiec jej całkowitemu zniknięciu z Jangcy.
Cytowanie: Zhao, Y., Wu, X., Zheng, W. et al. Chromosome-level genome assembly and annotation of the Rhinogobio ventralis, an endangered endemic fish from the Yangtze River. Sci Data 13, 615 (2026). https://doi.org/10.1038/s41597-026-06949-2
Słowa kluczowe: zagrożona ryba, składanie genomu, Rzeka Jangcy, genetyka ochrony, bioróżnorodność słodkowodna