Clear Sky Science · de
Chromosomenebene Genomassemblierung und Annotation von Rhinogobio ventralis, einem bedrohten endemischen Fisch des Jangtse
Ein Flussfisch am Abgrund
Rhinogobio ventralis ist ein kleiner, silbrig schimmernder Fisch, der nur in den schnell fließenden Oberläufen des chinesischen Jangtse lebt. Einst als lokaler Speisefisch geschätzt, wurde er durch Staudämme, Verschmutzung und Überfischung an den Rand des Aussterbens gedrängt. Diese Studie erstellt einen vollständigen genetischen Bauplan der Art und liefert Naturschützern ein mächtiges neues Werkzeug, um zu verstehen, wie der Fisch lebt, sich anpasst und möglicherweise gerettet werden kann.
Warum dieser kleine Fisch wichtig ist
Rhinogobio ventralis gehört zur Familie der Karpfen und hat sich an das Leben in starken Strömungen angepasst, indem er treibende Eier legt, die mit der Flussströmung verwehen. Weil er nirgendwo sonst auf der Erde vorkommt, signalisiert sein Rückgang nicht nur den Verlust eines einzigartigen Naturerbes, sondern auch eine Warnung über den Zustand des oberen Jangtse. Bisher konzentrierte sich die Forschung vor allem auf seine Grundbiologie und Versuche zur Zucht in Gefangenschaft. Was fehlte, war eine detaillierte Karte seiner DNA – das Instruktionsset, das Körperbau, Verhalten und die Fähigkeit zur Bewältigung von Umweltveränderungen steuert.
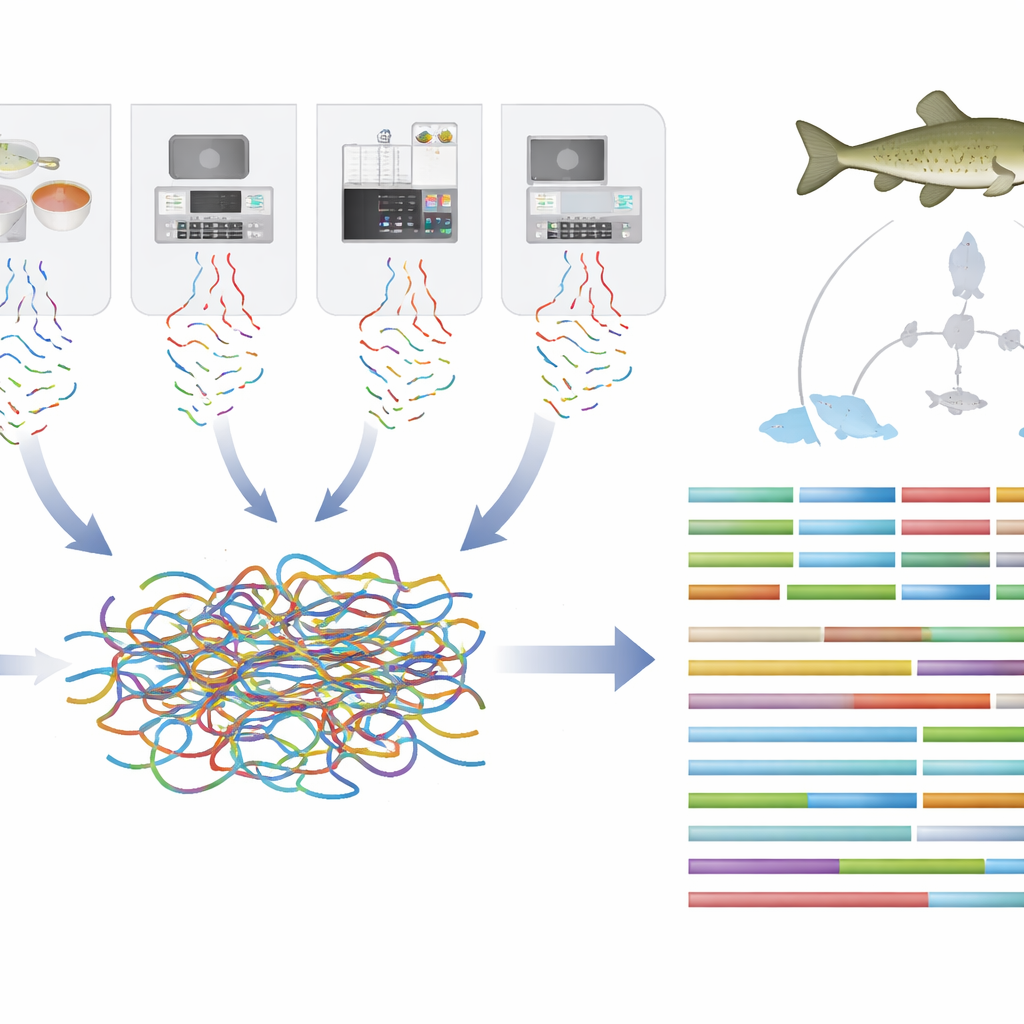
Aufbau eines genetischen Bauplans
Um diese Karte zu erstellen, sammelten die Forscher Gewebeproben von einem gesunden, in Gefangenschaft aufgezogenen erwachsenen Weibchen. Sie nutzten mehrere fortschrittliche DNA-Sequenziermethoden, die jeweils unterschiedliche Teile des Puzzles erfassen. Langlese-Sequenzierung zeigt große DNA-Abschnitte in einem Durchgang, Kurzlese-Sequenzierung prüft feine Details mit sehr hoher Genauigkeit, und eine Methode namens Hi‑C dokumentiert, wie DNA-Stücke physisch im Zellkern angeordnet sind. Durch die sorgfältige Kombination dieser Daten setzten sie das Genom des Fisches in 25 lange DNA-Einheiten zusammen, die seinen Chromosomen entsprechen, mit sehr wenigen Lücken oder Fehlern.
Was das Genom offenbart
Das fertige Genom ist etwas mehr als eine Milliarde „Buchstaben“ lang und besteht strenge Qualitätskontrollen, wie sie normalerweise an Referenzgenomen von Modellorganismen angelegt werden. Fast zwei Drittel bestehen aus sich wiederholenden Segmenten, viele davon mobile DNA-Elemente, die sich im Genom kopieren und bewegen können. Diese Wiederholungen erklären teilweise die Komplexität der DNA und können beeinflussen, wie der Fisch sich an seine sich verändernde Umwelt anpasst. Innerhalb dieses Rahmens identifizierte das Team mehr als 23.000 proteinkodierende Gene und konnte fast allen durch Vergleiche mit bereits bei anderen Fischen untersuchten Genen wahrscheinliche Funktionen zuweisen.
Einordnung des Fisches im Stammbaum des Lebens
Mit diesem detaillierten Genom verglichen die Wissenschaftler Rhinogobio ventralis mit einer Reihe anderer Strahlenflosser. Sie gruppierten seine Gene in Familien, die über Arten hinweg geteilt werden, entdeckten mehrere hundert Genfamilien, die für diesen Fisch einzigartig sind, und verfolgten, welche Familien sich im Laufe der Zeit vergrößert oder verkleinert haben. Ihre Evolutionsanalyse zeigt, dass Rhinogobio ventralis eng verwandt ist mit einem anderen Jangtse-Fisch, Coreius guichenoti, und dass sich ihre Linien vor etwa 23,5 Millionen Jahren getrennt haben. Diese Vergleiche bestätigen, dass das neue Genom sowohl biologisch plausibel als auch technisch robust ist.
Eine Grundlage zur Rettung einer Art
Die Autoren haben alle Rohdaten und das zusammengefügte Genom in öffentlichen Datenbanken hinterlegt, damit andere Forschende sie frei nutzen können. Diese genetische Landkarte wird künftige Arbeiten zur Populationsstruktur von Rhinogobio ventralis in freier Wildbahn, zu den DNA-Veränderungen, die wichtige Merkmale bestimmen, und zur Gestaltung von Zucht- und Auswilderungsprogrammen unterstützen. Kurz gesagt verwandelt die Studie einen wenig bekannten bedrohten Fisch in eine genetisch gut verstandene Art und gibt der Erhaltungsbiologie eine solidere wissenschaftliche Grundlage, um ihn dauerhaft vor dem Verschwinden aus dem Jangtse zu bewahren.
Zitation: Zhao, Y., Wu, X., Zheng, W. et al. Chromosome-level genome assembly and annotation of the Rhinogobio ventralis, an endangered endemic fish from the Yangtze River. Sci Data 13, 615 (2026). https://doi.org/10.1038/s41597-026-06949-2
Schlüsselwörter: bedrohter Fisch, Genomassemblierung, Jangtse, Erhaltungsgenetik, Süßwasser-Biodiversität