Clear Sky Science · pl
Profilowanie metylomu i transkryptomu na skalę genomową w jelicie Bombyx mori zakażonym BmCPV
Dlaczego jelita jedwabnika mają dla nas znaczenie
Jedwabniki mogą wydawać się skromnymi owadami hodowlanymi, ale znajdują się w centrum przemysłu tekstylnego, rolnego, a nawet biomedycznego. Gdy atakuje je wirus infekujący jelito, całe plony kokonów mogą zostać utracone. W tym badaniu zbadano, jak jeden z takich wirusów subtelnie przestawia system kontroli genetycznej jedwabnika — nie przez zmianę samego DNA, lecz przez modyfikację chemicznych znaczników na nim. Zrozumienie tej ukrytej warstwy regulacji może pomóc chronić ważny dla gospodarki owad i pogłębić nasze ogólne rozumienie sposobów, w jakie wirusy manipulują swoimi żywicielami.
Wirus jelitowy o dużym znaczeniu gospodarczym
Praca koncentruje się na Bombyx mori, udomowionym jedwabniku, oraz na powszechnym patogenie zwanym Bombyx mori cytoplasmic polyhedrosis virus (BmCPV). Ten dwuniciowy wirus RNA celuje specyficznie w komórki jelita środkowego jedwabnika, narządu odpowiedzialnego za trawienie. Wybuchy BmCPV mogą zahamować wzrost larw i je zabijać, powodując poważne straty gospodarcze. Wcześniejsze badania wykazały, że infekcja BmCPV zmienia, które geny jedwabnika są włączane lub wyłączane, a także modyfikuje znaczniki na białkach pakujących DNA, zwanych histonami. Jednak rola innego kluczowego rodzaju chemicznego znacznika bezpośrednio na DNA, czyli metylacji DNA, w tej historii była w dużej mierze nieznana.
Ukryty kod na DNA
Metylacja DNA to niewielka zmiana chemiczna: grupa metylowa jest dodawana do określonych zasad DNA, często tam, gdzie cytozyna sąsiaduje z guaniną. Pomimo niewielkiego rozmiaru, ten znacznik może silnie wpływać na to, czy pobliskie geny są aktywne. U wielu zwierząt metylacja DNA pomaga regulować rozwój, uciszać powtarzalne sekwencje DNA i precyzyjnie sterować czasem oraz miejscem ekspresji genów. Wiadomo, że wirusy zakażające ludzi i inne kręgowce zmieniają metylację DNA gospodarza na swoją korzyść, przesuwając aktywność genów gospodarza. U owadów ogólny poziom metylacji jest znacznie niższy, lecz wcześniejsze prace sugerowały, że wirusy jedwabników nadal mogą wykorzystywać ten mechanizm. Autorzy postanowili zbadać, w skali całego genomu, jak infekcja BmCPV przekształca wzory metylacji w jelicie jedwabnika i jak te zmiany korelują z aktywnością genów.
Odczytywanie chemicznych znaczników w całym genomie
Aby to zrobić, zespół zaraził dobrze zbadany szczep jedwabnika i pobrał tkankę jelita środkowego w dwóch punktach czasowych: 48 i 96 godzin po zakażeniu. Pobierano też dopasowane próbki jelit od niezainfekowanych larw w tym samym wieku. Z tych tkanek wykonano dwa pomiary na dużą skalę. Po pierwsze, użyto bisulfitowego sekwencjonowania całego genomu, metody ujawniającej, które cytozyny w genomie noszą grupy metylowe. Po drugie, zastosowano sekwencjonowanie RNA, aby zmierzyć, które geny były bardziej lub mniej aktywne w każdym warunku. Starannie przefiltrowano i wyrównano setki milionów odczytów DNA, sprawdzono jakość danych i obliczono poziomy metylacji na pojedynczych miejscach oraz w szerszych regionach genomowych, takich jak ciało genu, promotory i regiony niepodlegające translacji.
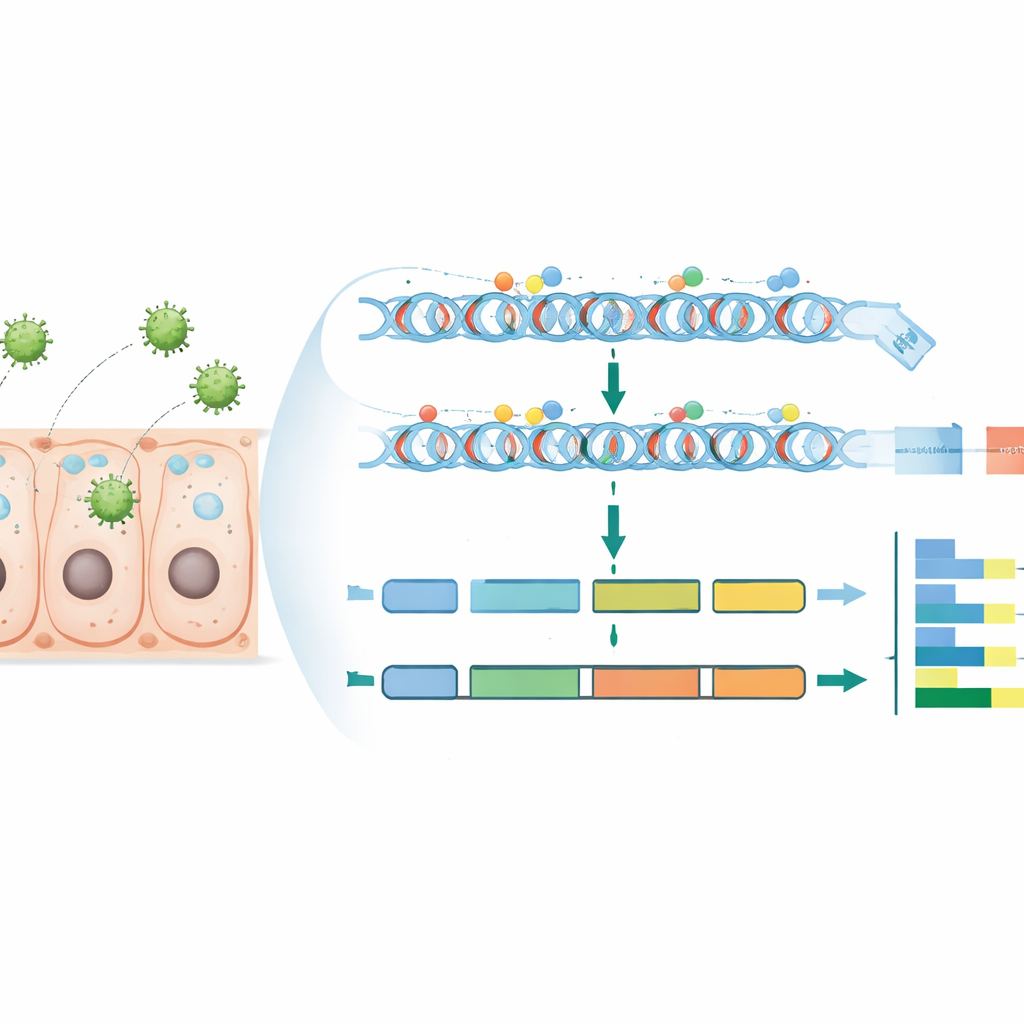
Gdzie wirus ingeruje w regulatory
Naukowcy stwierdzili, że, podobnie jak u wielu owadów, ogólna metylacja DNA u jedwabnika jest niska, a większość zmetylowanych miejsc występuje w znanym kontekście CG. W genomie metylacja nie była rozłożona równomiernie: miała tendencję do występowania w wyższych poziomach w regionach związanych z genami, takich jak eksony i regiony niepodlegające translacji, a niższych w klasycznych wyspach CpG i powtarzających się sekwencjach DNA. Porównując próbki zakażone i niezakażone w obu punktach czasowych, zidentyfikowali różnicowo metylowane regiony (DMR) — fragmenty DNA, w których metylacja wzrosła lub spadła podczas infekcji. Następnie powiązali te regiony z pobliskimi genami, szczególnie gdy DMR pokrywały regiony promotorowe tuż przed genami, które są kluczowe dla włączania i wyłączania genów. Wreszcie, integrując dane o metylacji z sekwencjonowaniem RNA, zidentyfikowali geny, których zmiany aktywności były ściśle powiązane ze zmianami metylacji w promotorach.
Weryfikacja sygnałów i udostępnienie danych
Aby upewnić się, że te wzory obejmujące cały genom są prawdziwe, zespół zwalidował wybrane regiony za pomocą metod celowanych. Wykorzystali metylację-specyficzny PCR, aby potwierdzić zmiany metylacji w wybranych miejscach, oraz ilościowy PCR, aby zweryfikować przesunięcia w poziomach ekspresji genów. W każdym przypadku testy ukierunkowane zgadzały się z wynikami sekwencjonowania na dużą skalę, co zwiększa zaufanie do zbioru danych. Wszystkie odczyty sekwencji, przetworzone ścieżki metylacji oraz listy zmetylowanych miejsc i różnicowo metylowanych regionów zostały złożone w publicznych bazach danych, dostarczając cennego zasobu dla innych badaczy zajmujących się odpornością owadów, interakcjami wirus–gospodarz czy regulacją epigenetyczną.
Co to oznacza dla zdrowia jedwabników
W prostych słowach, badanie pokazuje, że wirus jelitowy BmCPV nie tylko najeżdża komórki jedwabnika; wiąże się z subtelnym, ale rozległym dostrajaniem genetycznych przełączników jedwabnika poprzez metylację DNA. Konkretne geny zyskują lub tracą te chemiczne markery w pobliżu regionów startowych, a te same geny wykazują odpowiadające wzrosty lub spadki aktywności. Choć praca nie przekłada się jeszcze bezpośrednio na lek, mapuje panel sterowania, którego zdaje się dotykać wirus. Na dłuższą metę takie wnioski mogą pomóc hodowcom i biotechnologom w projektowaniu szczepów jedwabników bardziej odpornych na infekcje oraz mogą rzucić światło na wspólne zasady, którymi rządzą się wirusy manipulujące maszynerią epigenetyczną swoich gospodarzy.
Cytowanie: Qiu, Q., Liu, Z., Huang, Y. et al. Genome-scale DNA methylome and transcriptome profiling of midgut of Bombyx mori infected with BmCPV. Sci Data 13, 568 (2026). https://doi.org/10.1038/s41597-026-06922-z
Słowa kluczowe: wirus jedwabnika, metylacja DNA, epigenetyka, interakcja gospodarz–wirus, jelito Bombyx mori