Clear Sky Science · pl
Cyfrowe archiwum ukazuje, jak agencja finansująca współpracowała z naukowcami, by wesprzeć powstającą dziedzinę genomiki
Jak ukryte archiwum ukształtowało nowoczesną genetykę
Dziś na co dzień słyszymy o testach DNA, medycynie spersonalizowanej i odkryciach łączących geny z chorobami. Za tymi przełomami stoi ogrom planowania, finansowania i cichej koordynacji. Niniejszy artykuł otwiera okno na tę zaplecze, analizując wyjątkowe cyfrowe archiwum Narodowego Instytutu Badań Genomu Ludzkiego (NHGRI) w USA. Pokazuje, z bezprecedensową szczegółowością, jak jedna publiczna agencja finansująca pracowała ramię w ramię z naukowcami uniwersyteckimi, aby przekształcić genomikę z odważnej idei w kluczowy filar współczesnej biomedycyny. 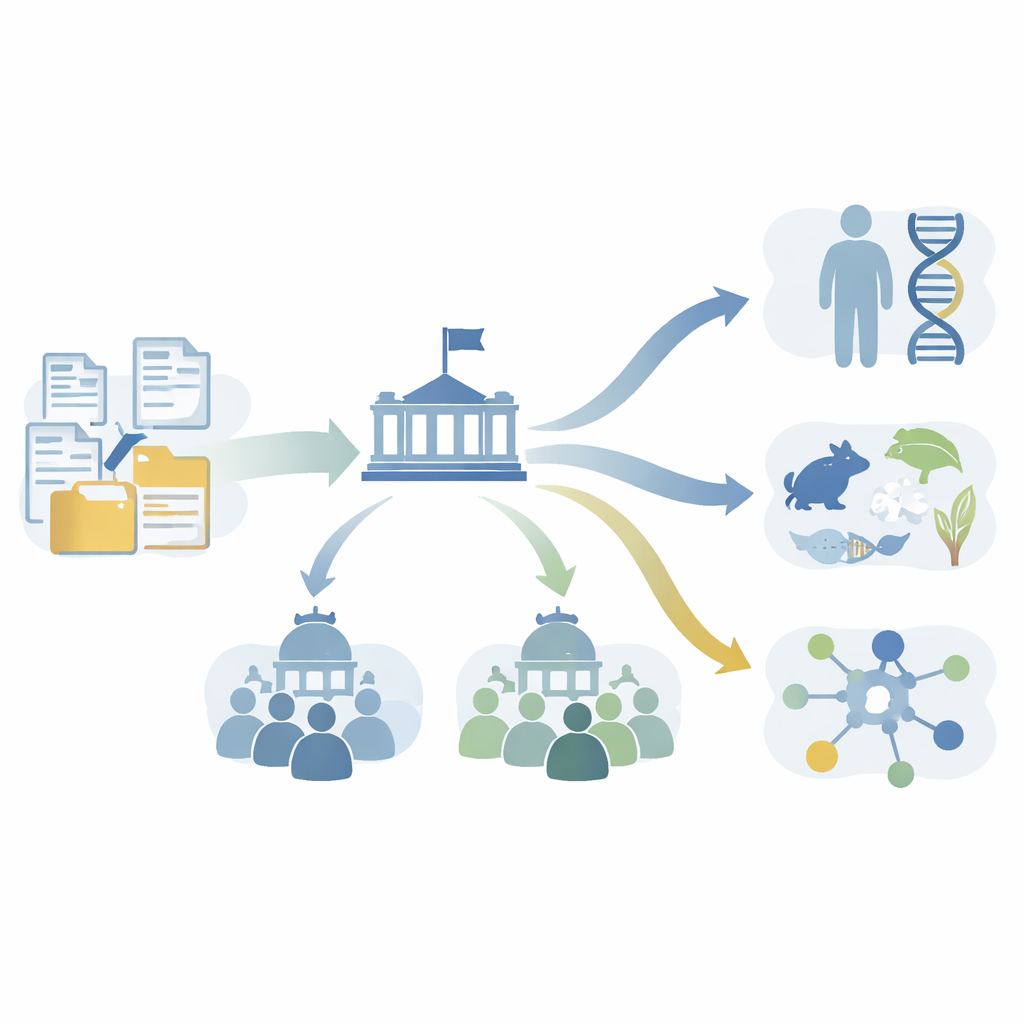
Przekształcanie pudeł z papierami w cyfrowy skarb
Historia zaczyna się od archiwum, które może brzmieć prozaicznie: ponad dwa miliony stron e-maili, raportów, notatek i protokołów spotkań przechowywanych w NHGRI. Materiały te dokumentują Projekt Genomu Człowieka i inicjatywy genomiki, które nastąpiły po nim. Autorzy przekształcili starannie wyselekcjonowany podzbiór, nazwany Kolekcją Podstawową, w w pełni cyfrowe źródło. Wykorzystali szybkie skanowanie, przetwarzanie obrazu do usuwania odręcznych notatek oraz optyczne rozpoznawanie znaków, aby wydobyć drukowany tekst. Następnie zastosowali metody sztucznej inteligencji do wykrywania nazwisk, organizacji, kluczowych terminów naukowych i dat, jednocześnie kodując lub maskując dane osobowe w celu ochrony prywatności. Ten proces przemienił zakurzone sterty papierów w przeszukiwalne, analizowalne dane o tym, jak faktycznie budowano genomikę.
Odnajdywanie narodzin nowego sposobu badania chorób
Dysponując tym cyfrowym skarbem, badacze zadali pytanie: czy uda się odtworzyć wczesne kroki dużych idei naukowych zanim stały się sławne? Skoncentrowali się na badaniach asocjacyjnych obejmujących cały genom (GWAS), obecnie standardowej metodzie wyszukiwania drobnych różnic powiązanych z powszechnymi chorobami. Dane bibliometryczne pokazują, że GWAS stały się jedną z najbardziej wpływowych technik we współczesnej biomedycynie, zarówno pod względem cytowań, jak i wprowadzania wcześniej nieznanych genów do literatury. Przeszukując archiwum, autorzy znaleźli wzmianki o GWAS w dokumentach NHGRI na wiele lat przed publikacją pierwszych przełomowych artykułów. Wewnętrzne programy warsztatów i dokumenty planistyczne pokazują, że liderzy NHGRI i zewnętrzni eksperci dostrzegali potencjał GWAS, debatowali o niezbędnych zasobach danych, a następnie uruchomili Międzynarodowy Projekt HapMap, by te zasoby zbudować. Innymi słowy, agencja i środowisko akademickie wspólnie przygotowały grunt pod GWAS, zanim pojedyncze laboratoria mogły je realistycznie przeprowadzić.
Za kulisami wielkich projektów międzynarodowych
Aby zrozumieć codzienną socjalną maszynerię dużych współprac, archiwum ujawnia również zrekonstruowane sieci z ponad 47 000 wymian e-mailowych. Autorzy odwzorowali, kto z kim rozmawiał podczas Projektu Genomu Człowieka i późniejszego projektu HapMap. Zamiast jednego centrum dowodzenia, odkryli wiele nakładających się grup pracowników rządowych i naukowców zewnętrznych. Małe, wcześniej niedoceniane kręgi kluczowych postaci—w niektórych wiadomościach nazywane „Szafką Kuchenną” (Kitchen Cabinet)—łączyły liderów wewnętrznych, rady doradcze i międzynarodowe komitety sterujące. Analiza sieci sugeruje, że ta grupa często pełniła role pośredników: tłumaczyła kwestie techniczne, przygotowywała złożone zagadnienia przed formalnymi spotkaniami i zachowywała ciągłość, gdy projekty ewoluowały, a dołączały nowe osoby. 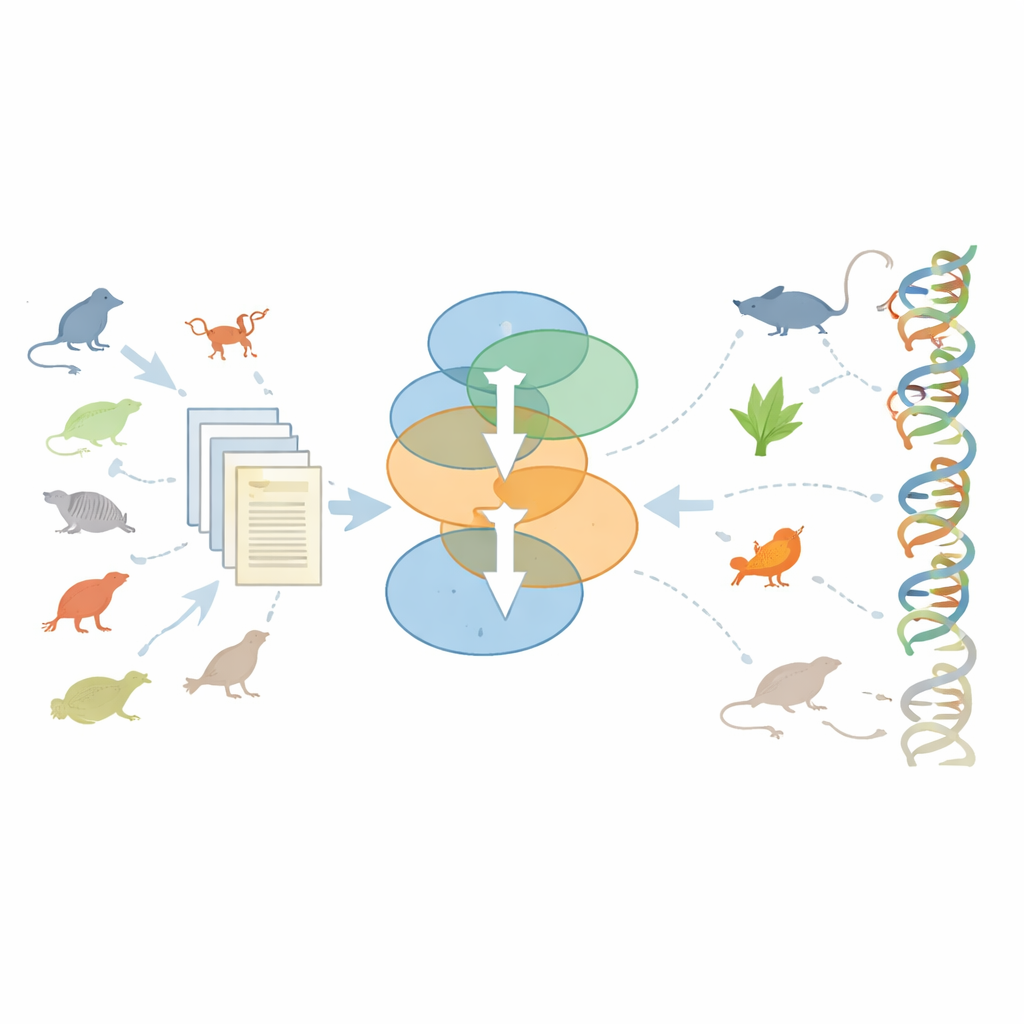
Wybór, które organizmy otrzymają zsekwencjonowane genomy
Innym istotnym pytaniem było, jak NHGRI i środowisko badawcze decydowały, które gatunki niebędące ludźmi powinny mieć sekwencjonowane genomy po Projekcie Genomu Człowieka. Propozycje napływały zarówno z wewnętrznych grup roboczych, jak i od zewnętrznych naukowców, którzy argumentowali za konkretnymi zwierzętami—od dobrze znanych kręgowców po mało znane bezkręgowce. Autorzy ręcznie odtworzyli ten proces selekcji, a następnie zbudowali modele uczenia maszynowego, aby sprawdzić, czy da się naśladować decyzje rady doradczej używając cech takich jak wielkość społeczności badawczej skupionej wokół organizmu, różnorodność i przekonujący charakter języka propozycji oraz proste fakty biologiczne, na przykład rozmiar genomu. Ich modele przewidywały decyzje zatwierdzające z wysoką dokładnością, co wskazuje, że te czynniki razem oddawały dużą część rzeczywistego rozumowania. Co ważne, organizmy zatwierdzone niekoniecznie przyciągały więcej publikacji ogółem w późniejszym czasie, ale badania nad nimi przesunęły się zdecydowanie w kierunku metod genomiki po udostępnieniu ich genomów.
Dlaczego ta ukryta historia ma dziś znaczenie
Łącząc wydobywanie tekstu, analizę sieci i staranne zabezpieczenia etyczne, badanie pokazuje, że innowacja w genomice nie była jedynie efektem samotnych geniuszy czy przypadkowych odkryć. Zamiast tego NHGRI działało jako centrum współpracy, które słuchało zewnętrznych ekspertów, gromadziło wspólne zasoby danych i strategicznie wspierało gatunki oraz technologie zdolne przesunąć całe dziedziny do przodu. Cyfrowe archiwum ujawnia, że niektóre z najważniejszych kroków—jak planowanie GWAS czy priorytetyzacja organizmów do sekwencjonowania—miały miejsce zanim numery grantów czy liczby cytowań pojawiły się w publicznych bazach danych. Dla czytelnika ogólnego kluczowy wniosek jest taki, że przemyślane finansowanie publiczne, prowadzone w dialogu z naukowcami i oparte na odpowiedzialnym zarządzaniu danymi, może cicho kształtować kierunek nauki przez dekady.
Cytowanie: Hong, S.S., Utz, Z., Hosseini, M. et al. A digital archive reveals how a funding agency cooperated with academics to support the nascent field of genomics. Nat Commun 17, 3621 (2026). https://doi.org/10.1038/s41467-026-71700-9
Słowa kluczowe: genomika, finansowanie badań, Projekt Genomu Człowieka, archiwa cyfrowe, sekwencjonowanie genomu