Clear Sky Science · pl
Równoważnościowe rozwiązanie dyfuzyjne do wyznaczania struktury kryształów nieorganicznych z danych proszkowej dyfrakcji rentgenowskiej
Nauczanie komputerów czytania „odcisków palców” kryształów
Wiele współczesnych technologii, od baterii po katalizatory i magnesy, opiera się na precyzyjnym rozmieszczeniu atomów w kryształach nieorganicznych. Ta niewidoczna architektura jest zwykle odczytywana za pomocą promieniowania rentgenowskiego, które pozostawia charakterystyczny „odcisk palca”. Jednak przekształcenie tych wzorców w dokładną mapę atomową od dawna wymaga lat treningu i żmudnych prób oraz błędów. W tym badaniu zaprezentowano system AI o nazwie XRDSol, który potrafi czytać te odciski i w mniej niż sekundę zaproponować pełne struktury krystaliczne, otwierając drogę do szybszego odkrywania materiałów i bardziej wiarygodnych baz danych materiałowych.
Dlaczego wzory proszkowe są tak trudne do rozszyfrowania
Gdy promienie rentgenowskie przechodzą przez idealnie ukształtowany pojedynczy kryształ, tworzą bogaty, trójwymiarowy wzór, który pozwala dokładnie zlokalizować każdy atom. W praktyce jednak próbki często występują jako proszki złożone z wielu drobnych ziaren. Ich obraz dyfrakcyjny zapada się do jednowymiarowego ciągu pików, w którym znaczna część pierwotnej informacji przestrzennej zostaje utracona. Eksperci zazwyczaj muszą połączyć ten skondensowany wzór z wiedzą chemiczną i krystalograficzną, zgadując parametry sieci, symetrię i pozycje atomów, a następnie wielokrotnie dopracowywać swoje przypuszczenia. Dla materiałów złożonych lub słabo poznanych rozwiązania mogą być niepełne, kontrowersyjne lub wręcz błędne, a duże bazy struktur zawierają tysiące wpisów z brakującymi lub nieprawdopodobnymi współrzędnymi atomów.
Sztuczna inteligencja rekonstruująca rozmieszczenie atomów
Autorzy rozwiązują ten problem za pomocą XRDSol — modelu sztucznej inteligencji opartego na równoważnościowym procesie dyfuzyjnym działającym na grafowym odwzorowaniu kryształu. Zamiast zaczynać od dobrego przypuszczenia, XRDSol rozpoczyna od atomów umieszczonych losowo wewnątrz znanej komórki elementarnej (ze znaną formułą chemiczną i parametrami sieci). Podczas treningu model uczy się odwracać stopniowy proces „zaszumiania”, w którym dobrze ustalone, termodynamicznie stabilne struktury są wielokrotnie zniekształcane. Kierowany skompresowaną reprezentacją docelowego wzoru proszkowej dyfrakcji rentgenowskiej, model iteracyjnie „odszumia” losowe rozmieszczenie, stopniowo popychając atomy na pozycje jednocześnie chemicznie sensowne i zgodne z obserwowanym wzorem. Ponieważ bazowa sieć neuronowa respektuje symetrie obrotowe i translacyjne kryształów, naturalnie preferuje fizycznie uzasadnione układy.
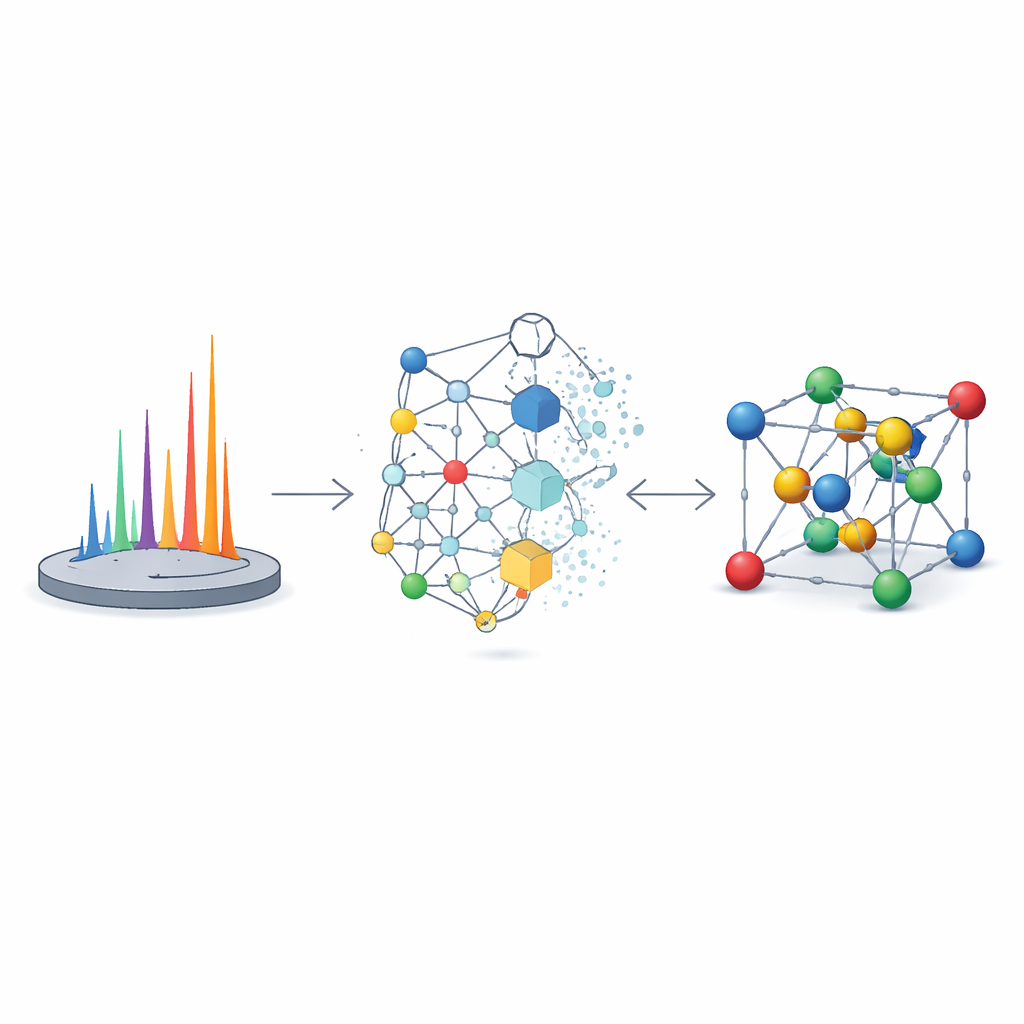
Szybkie i dokładne rozwiązania dla wielu materiałów
Aby przetestować XRDSol, zespół użył zbioru danych ponad 9 000 stabilnych struktur nieorganicznych z zasymulowanymi wzorami proszkowymi. Na pojedynczym procesorze graficznym model potrzebuje około 0,6 sekundy, by wygenerować rozwiązanie dla jednej struktury — czyli od około dziesięciu do stu tysięcy razy szybciej niż wcześniejsze metody polegające na kosztownych obliczeniach kwantowo-mechanicznych i poszukiwaniach ewolucyjnych. W ponad 80 procentach przypadków XRDSol odtwarza pozycje atomów bardzo zbliżone do znanych struktur, a w ponad 90 procentach zrekonstruowany wzór dyfrakcyjny jest wysoce podobny do celu. Metoda sprawdza się szczególnie dobrze dla kryształów o wysokiej symetrii, choć wydajność spada dla przypadków o niskiej symetrii i większym stopniu złożoności. Mimo to przykłady od prostych soli po złożone tlenki, siarczki i związki międzymetaliczne pokazują, że podejście jest szeroko stosowalne w różnych układach chemicznych.
Poprawianie starych rekordów i uzupełnianie brakujących struktur
Ponad odtwarzaniem znanych rozwiązań, XRDSol potrafi też poprawiać wątpliwe dane. Autorzy ponownie przeanalizowali tysiące wpisów w bazach danych, które miały wyjątkowo wysokie obliczone energie — wskaźnik sugerujący, że opublikowana struktura może być błędna. Używając jedynie wzoru proszkowego, parametrów sieci i składu jako danych wejściowych, XRDSol zaproponował alternatywne rozmieszczenia atomów. Dla co najmniej 39 związków nowe struktury lepiej pasowały do danych dyfrakcyjnych i miały znacznie niższe energie, zgadzając się w kilku dobrze zbadanych przypadkach z późniejszymi eksperymentalnymi ponownymi wyznaczeniami. System uzupełnił także brakujące współrzędne dla 912 wpisów, których wzory dyfrakcyjne były znane, ale pozycje atomów nie zostały podane — w tym trudne przykłady zawierające lekkie pierwiastki, takie jak wodór i lit, naturalne minerały z zanieczyszczeniami oraz materiały wykazujące nieuporządkowanie chemiczne. Te struktury wygenerowane przez AI zostały sprawdzone obliczeniami kwantowymi i inspekcją ręczną i uznano je za energetycznie prawdopodobne oraz chemicznie sensowne.
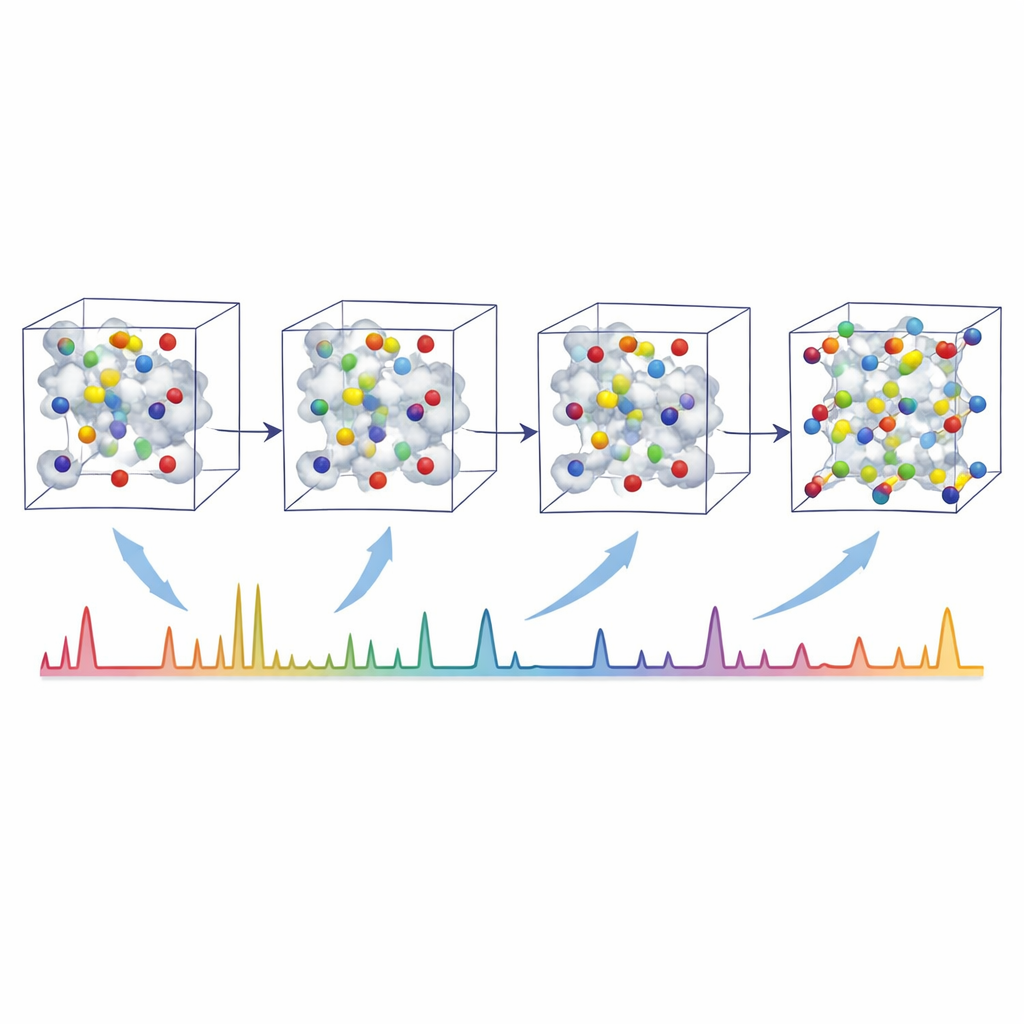
W kierunku zautomatyzowanego odkrywania materiałów
XRDSol pokazuje, że sieć neuronowa oparta na dyfuzji i uwzględniająca symetrię może przyswoić dużą część wiedzy ekspertów potrzebnej do rozwiązywania struktur kryształów nieorganicznych bezpośrednio z danych proszkowej dyfrakcji rentgenowskiej. Chociaż metoda wciąż ma problemy z bardzo dużymi komórkami elementarnymi, fazami o niskiej symetrii i w pełni zdezorganizowanymi miejscami, już teraz dostarcza szybkie, wysokiej jakości modele początkowe do dalszej optymalizacji. W praktyce oznacza to szybszą rutynową analizę dla osób niebędących specjalistami, potężne narzędzie do oczyszczania i uzupełniania dużych baz danych strukturalnych oraz istotny element laboratoriów zamkniętej pętli, w których komputery projektują, syntetyzują, charakteryzują i optymalizują nowe materiały przy minimalnym udziale człowieka.
Cytowanie: Yu, D., Zhu, Z., Leng, F. et al. Equivariant diffusion solution for inorganic crystal structure determination from powder X-ray diffraction data. Nat Commun 17, 3274 (2026). https://doi.org/10.1038/s41467-026-70035-9
Słowa kluczowe: proszkowa dyfrakcja rentgenowska, wyznaczanie struktury kryształów, równoważnościowy model dyfuzyjny, informatyka materiałowa, sieć neuronowa grafowa